peptides
spectra
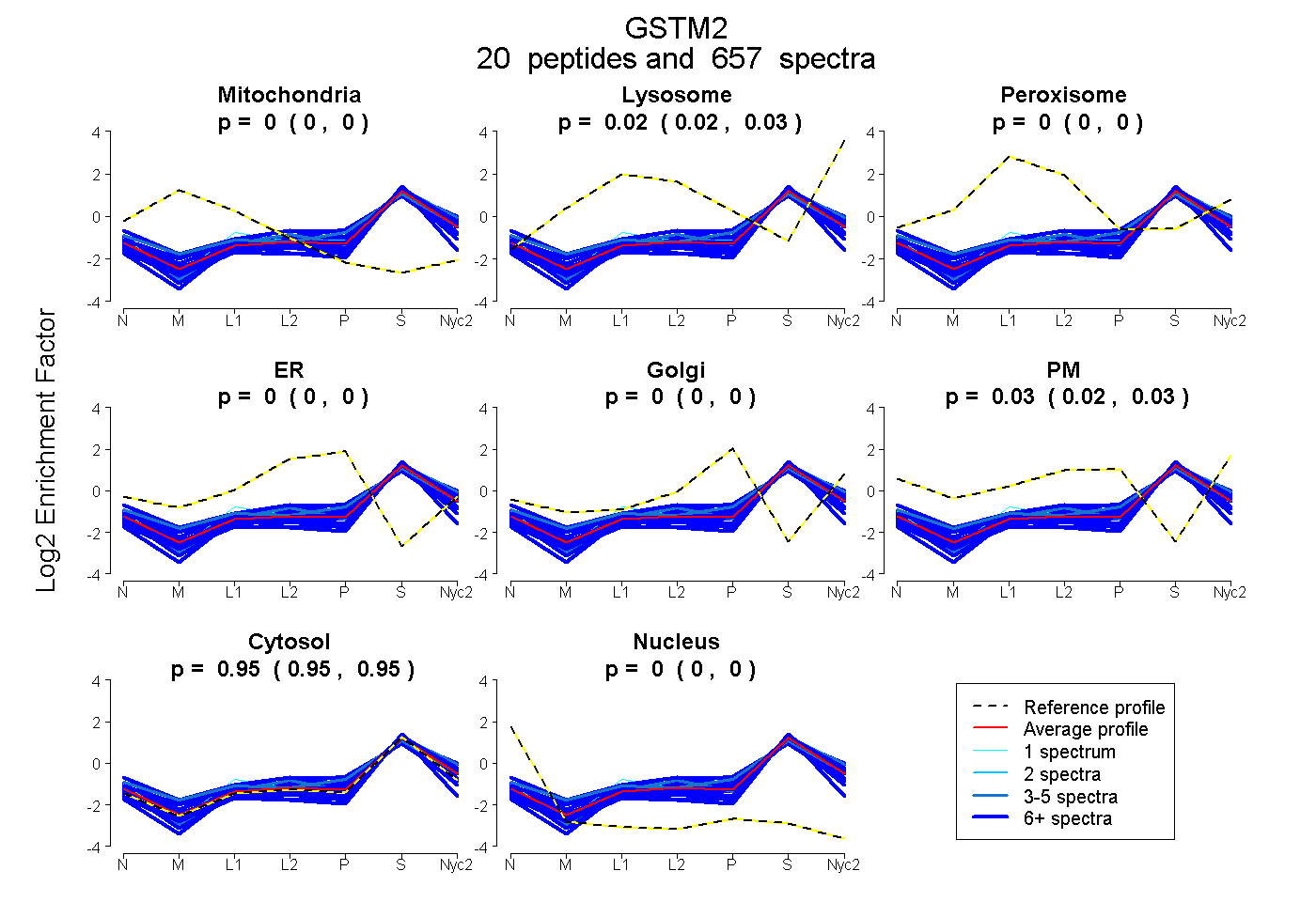
0.000 | 0.000
0.023 | 0.026
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.024 | 0.026
0.949 | 0.951
0.000 | 0.000
peptides
spectra
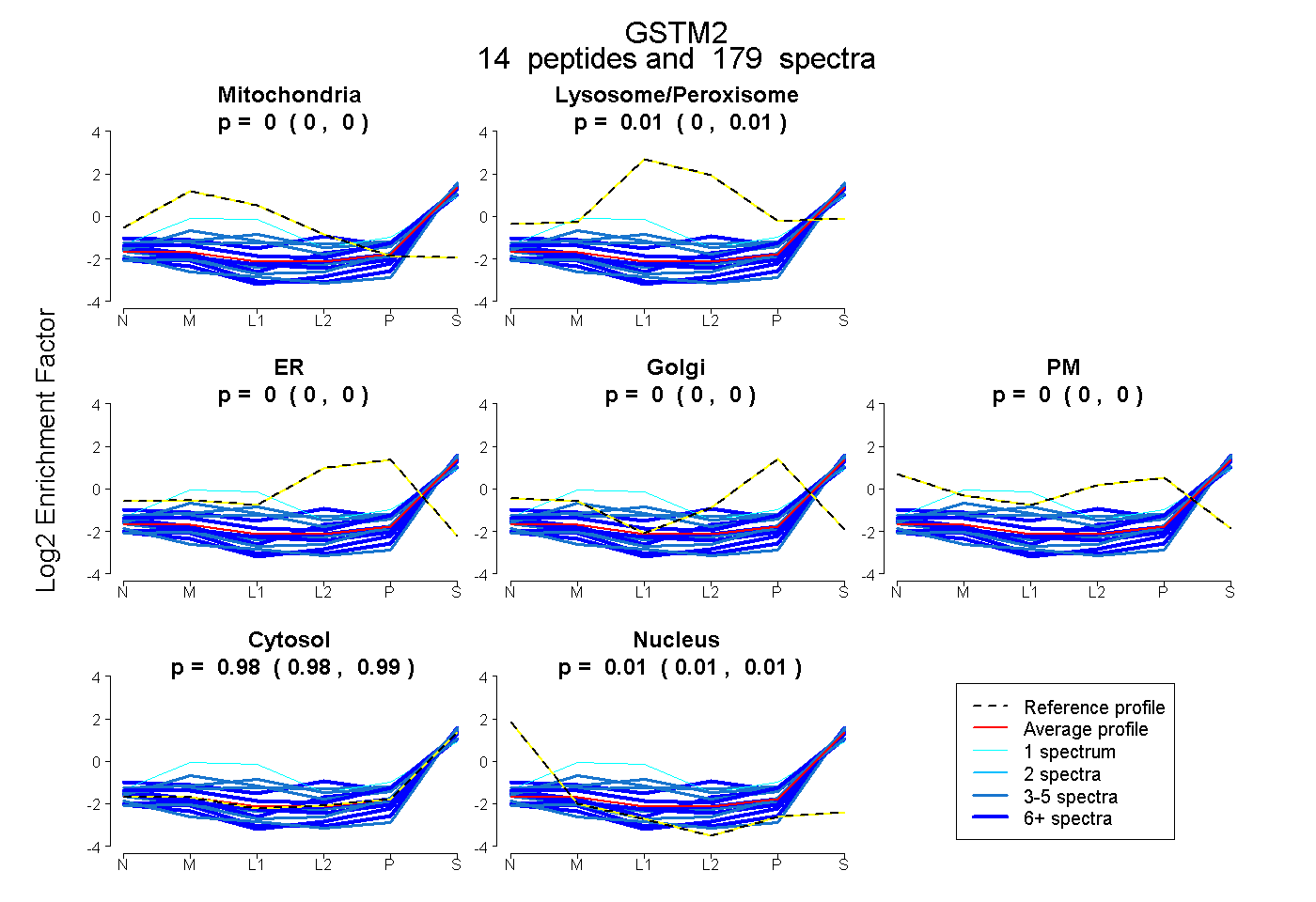
0.000 | 0.000
0.002 | 0.009
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.979 | 0.986
0.008 | 0.013
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
657 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.023 | 0.026 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.025 0.024 | 0.026 |
0.950 0.949 | 0.951 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
179 spectra |
 |
0.000 0.000 | 0.000 |
0.006 0.002 | 0.009 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.983 0.979 | 0.986 |
0.011 0.008 | 0.013 |
| 4 spectra, MAFWNPK | 0.000 | 0.200 | 0.000 | 0.000 | 0.000 | 0.800 | 0.000 | |||
| 5 spectra, LGLDFPNLPYLIDGSHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.944 | 0.056 | |||
| 9 spectra, VDVLENQAMDTR | 0.000 | 0.055 | 0.000 | 0.075 | 0.000 | 0.870 | 0.000 | |||
| 11 spectra, ITYVDFLVYDVLDQHR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.988 | 0.012 | |||
| 4 spectra, PMTLGYWDIR | 0.121 | 0.109 | 0.000 | 0.000 | 0.000 | 0.770 | 0.000 | |||
| 44 spectra, GLAHAIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 5 spectra, SQWLSEK | 0.044 | 0.216 | 0.000 | 0.000 | 0.000 | 0.739 | 0.001 | |||
| 6 spectra, LFLEYTDTSYEDK | 0.000 | 0.000 | 0.000 | 0.088 | 0.000 | 0.912 | 0.000 | |||
| 65 spectra, ITQSNAILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.978 | 0.022 | |||
| 7 spectra, LQLAMVCYSPDFER | 0.000 | 0.160 | 0.000 | 0.000 | 0.107 | 0.734 | 0.000 | |||
| 4 spectra, YSMGDAPDYDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, QPWFAGNK | 0.214 | 0.230 | 0.000 | 0.000 | 0.000 | 0.556 | 0.000 | |||
| 10 spectra, HNLCGETEEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.019 | |||
| 4 spectra, FLSKPIFAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.016 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
580 spectra |
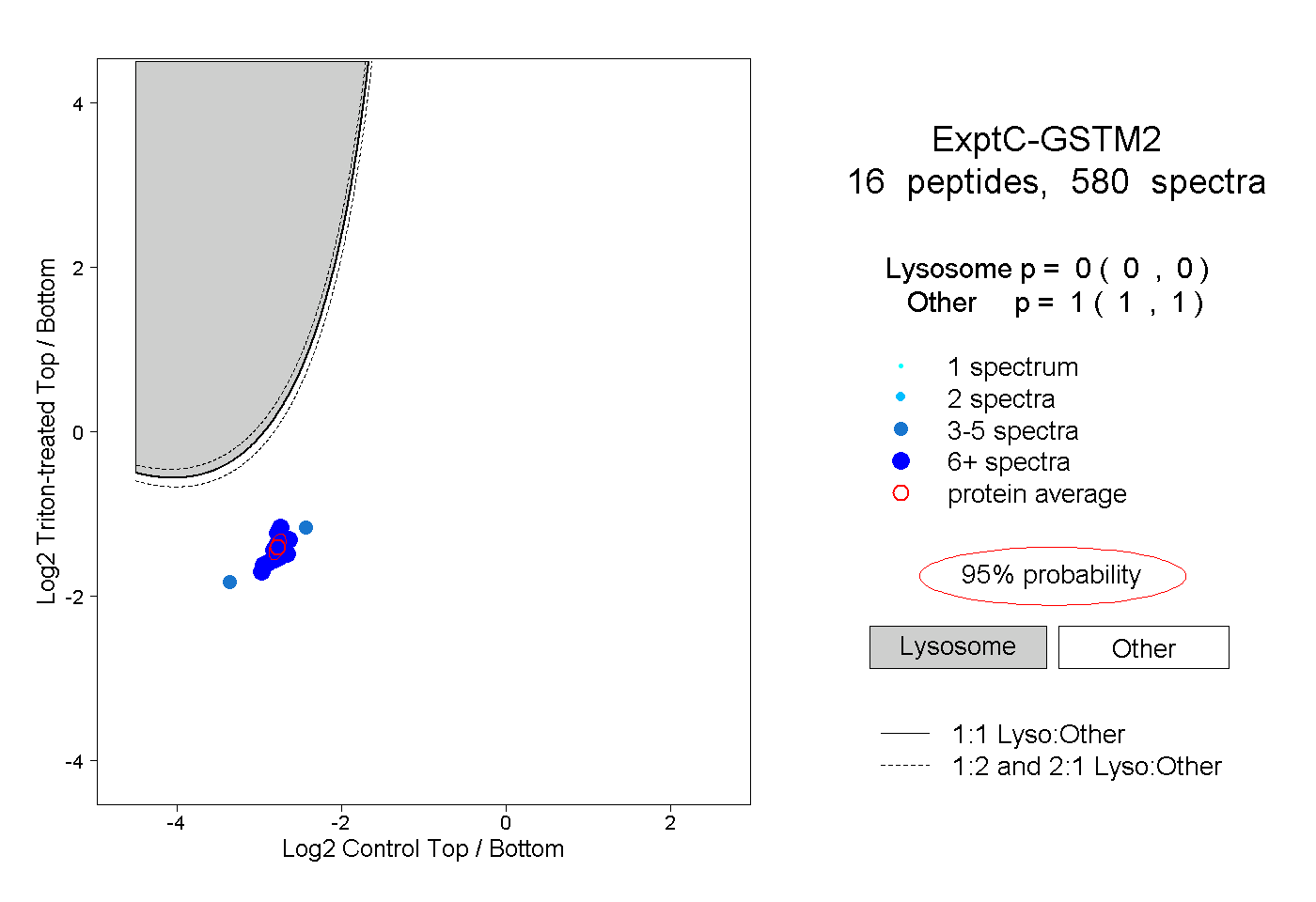 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
56 spectra |
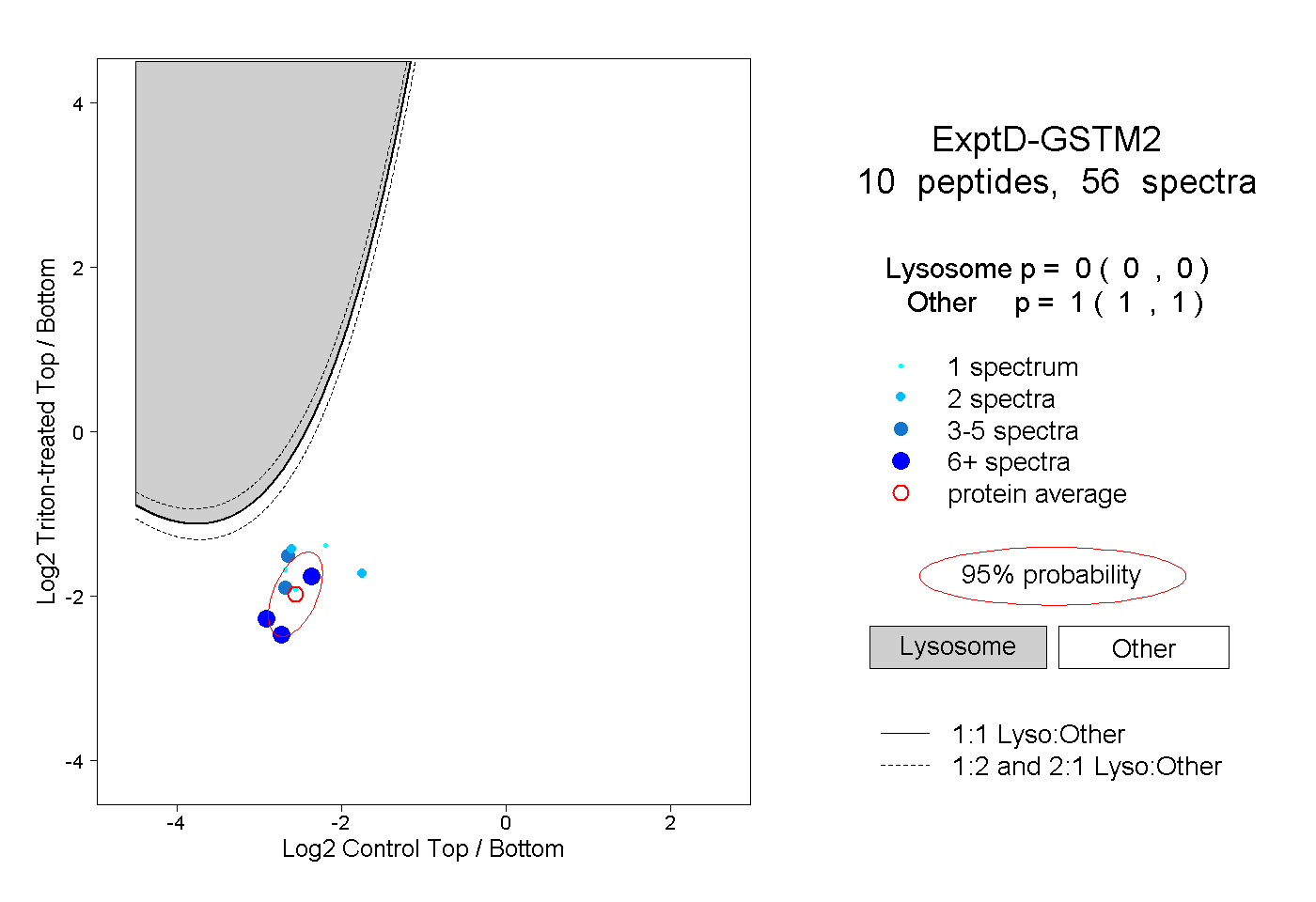 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |