peptides
spectra
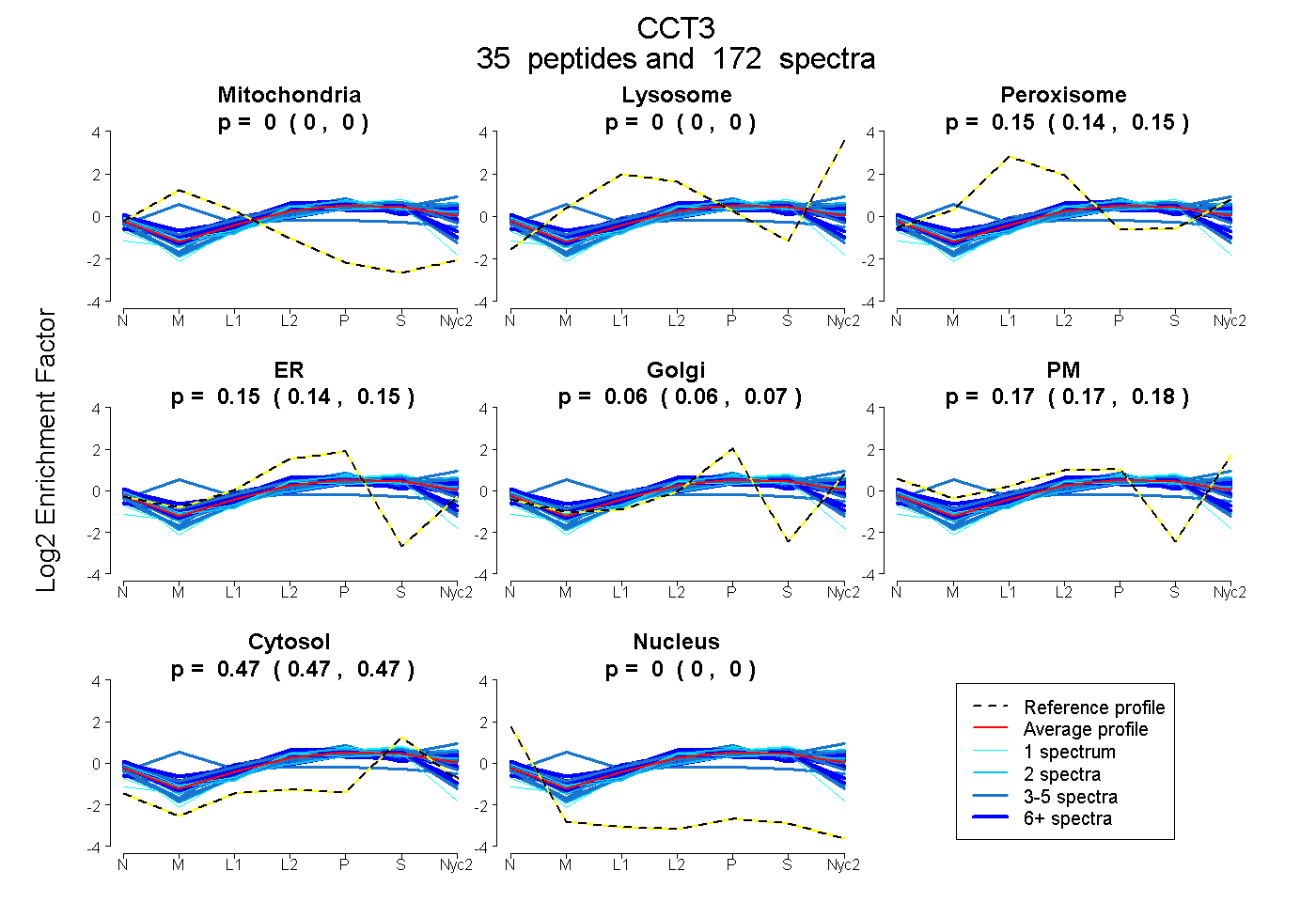
0.000 | 0.000
0.000 | 0.000
0.144 | 0.148
0.139 | 0.151
0.057 | 0.069
0.167 | 0.176
0.471 | 0.474
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
172 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.146 0.144 | 0.148 |
0.146 0.139 | 0.151 |
0.064 0.057 | 0.069 |
0.172 0.167 | 0.176 |
0.472 0.471 | 0.474 |
0.000 0.000 | 0.000 |
| 6 spectra, MALDDMVSTLK | 0.000 | 0.077 | 0.187 | 0.000 | 0.318 | 0.000 | 0.418 | 0.000 | ||
| 2 spectra, GESQTDIEITR | 0.000 | 0.024 | 0.000 | 0.000 | 0.036 | 0.379 | 0.561 | 0.000 | ||
| 12 spectra, LLTSLR | 0.000 | 0.000 | 0.128 | 0.077 | 0.000 | 0.427 | 0.367 | 0.000 | ||
| 3 spectra, DMMLNIINSSITTK | 0.000 | 0.007 | 0.224 | 0.141 | 0.152 | 0.000 | 0.476 | 0.000 | ||
| 10 spectra, TLIQNCGASTIR | 0.000 | 0.000 | 0.117 | 0.355 | 0.000 | 0.000 | 0.528 | 0.000 | ||
| 3 spectra, SMIEISR | 0.000 | 0.186 | 0.000 | 0.004 | 0.089 | 0.276 | 0.445 | 0.000 | ||
| 10 spectra, EEDFTR | 0.000 | 0.067 | 0.060 | 0.130 | 0.007 | 0.262 | 0.476 | 0.000 | ||
| 8 spectra, AMTGVEQWPYR | 0.000 | 0.003 | 0.220 | 0.000 | 0.132 | 0.219 | 0.426 | 0.000 | ||
| 6 spectra, DVTHPR | 0.000 | 0.000 | 0.180 | 0.055 | 0.000 | 0.341 | 0.423 | 0.000 | ||
| 3 spectra, IDDIVSGHK | 0.000 | 0.062 | 0.059 | 0.062 | 0.000 | 0.317 | 0.501 | 0.000 | ||
| 2 spectra, IGDEYFTFITDCK | 0.000 | 0.000 | 0.238 | 0.060 | 0.209 | 0.000 | 0.493 | 0.000 | ||
| 4 spectra, GVMINK | 0.000 | 0.000 | 0.081 | 0.053 | 0.000 | 0.367 | 0.499 | 0.000 | ||
| 3 spectra, ELEVQHPAAK | 0.275 | 0.000 | 0.233 | 0.000 | 0.228 | 0.000 | 0.264 | 0.000 | ||
| 5 spectra, IPGGIIEDSCVLR | 0.000 | 0.000 | 0.111 | 0.338 | 0.000 | 0.000 | 0.551 | 0.000 | ||
| 7 spectra, ACTILLR | 0.000 | 0.000 | 0.093 | 0.254 | 0.021 | 0.160 | 0.472 | 0.000 | ||
| 6 spectra, AVAQALEVIPR | 0.000 | 0.000 | 0.200 | 0.050 | 0.090 | 0.229 | 0.432 | 0.000 | ||
| 5 spectra, TCLGPK | 0.000 | 0.000 | 0.091 | 0.369 | 0.000 | 0.000 | 0.539 | 0.000 | ||
| 8 spectra, TAVETAVLLLR | 0.000 | 0.000 | 0.148 | 0.059 | 0.081 | 0.270 | 0.443 | 0.000 | ||
| 10 spectra, NLQDAMQVCR | 0.000 | 0.000 | 0.118 | 0.397 | 0.000 | 0.000 | 0.484 | 0.000 | ||
| 4 spectra, ISTPVDVNNR | 0.000 | 0.068 | 0.034 | 0.057 | 0.000 | 0.367 | 0.475 | 0.000 | ||
| 2 spectra, ELGIWEPLAVK | 0.000 | 0.040 | 0.147 | 0.000 | 0.280 | 0.126 | 0.407 | 0.000 | ||
| 2 spectra, VQSGNINAAK | 0.000 | 0.034 | 0.014 | 0.219 | 0.000 | 0.261 | 0.471 | 0.000 | ||
| 3 spectra, TVQFEENGR | 0.000 | 0.017 | 0.200 | 0.000 | 0.051 | 0.322 | 0.411 | 0.000 | ||
| 3 spectra, EIQVQHPAAK | 0.000 | 0.000 | 0.182 | 0.184 | 0.167 | 0.091 | 0.376 | 0.000 | ||
| 6 spectra, IVLLDSSLEYK | 0.000 | 0.000 | 0.159 | 0.219 | 0.000 | 0.131 | 0.491 | 0.000 | ||
| 1 spectrum, MLLDPMGGIVMTNDGNAILR | 0.000 | 0.194 | 0.000 | 0.251 | 0.000 | 0.000 | 0.555 | 0.000 | ||
| 1 spectrum, NVLLDPQLVPGGGASEMAVAHALTEK | 0.000 | 0.000 | 0.000 | 0.141 | 0.026 | 0.306 | 0.527 | 0.000 | ||
| 14 spectra, GISDLAQHYLMR | 0.000 | 0.000 | 0.228 | 0.000 | 0.176 | 0.133 | 0.463 | 0.000 | ||
| 3 spectra, QTGAPDAGQE | 0.000 | 0.000 | 0.071 | 0.320 | 0.000 | 0.054 | 0.556 | 0.000 | ||
| 7 spectra, ANVTAIR | 0.000 | 0.000 | 0.110 | 0.079 | 0.021 | 0.292 | 0.498 | 0.000 | ||
| 1 spectrum, WSSLACNIALDAVK | 0.033 | 0.000 | 0.067 | 0.372 | 0.000 | 0.000 | 0.502 | 0.026 | ||
| 2 spectra, IVSRPEELR | 0.000 | 0.081 | 0.000 | 0.109 | 0.000 | 0.375 | 0.435 | 0.000 | ||
| 1 spectrum, EDDVGTGAGLLEIK | 0.000 | 0.061 | 0.081 | 0.116 | 0.178 | 0.000 | 0.565 | 0.000 | ||
| 5 spectra, TLADLIR | 0.000 | 0.028 | 0.035 | 0.172 | 0.000 | 0.199 | 0.566 | 0.000 | ||
| 4 spectra, MMGHRPVLVLSQNTK | 0.000 | 0.000 | 0.156 | 0.134 | 0.138 | 0.115 | 0.457 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
75 spectra |
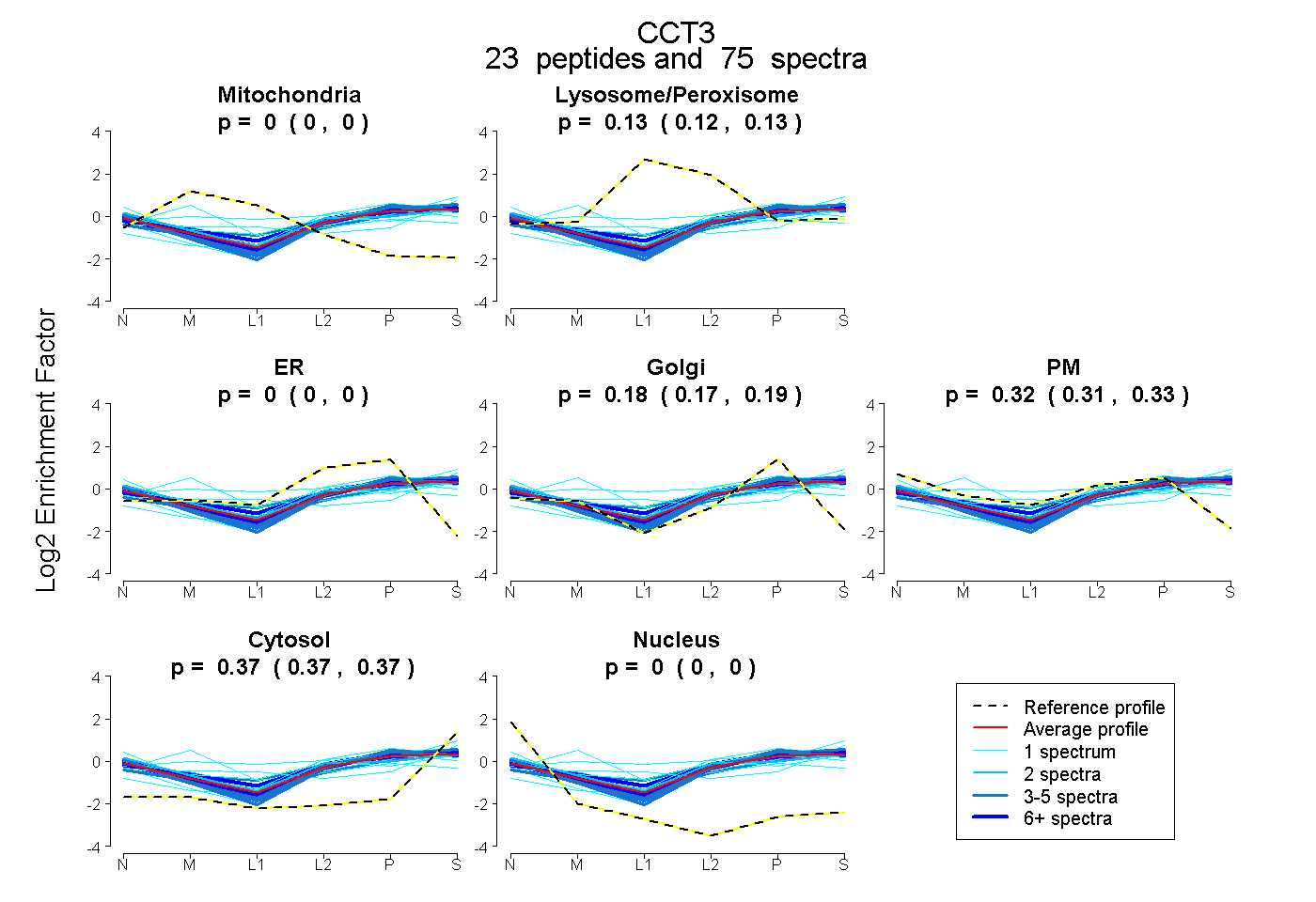 |
0.000 0.000 | 0.000 |
0.128 0.124 | 0.132 |
0.000 0.000 | 0.000 |
0.180 0.173 | 0.185 |
0.322 0.314 | 0.329 |
0.369 0.367 | 0.371 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
238 spectra |
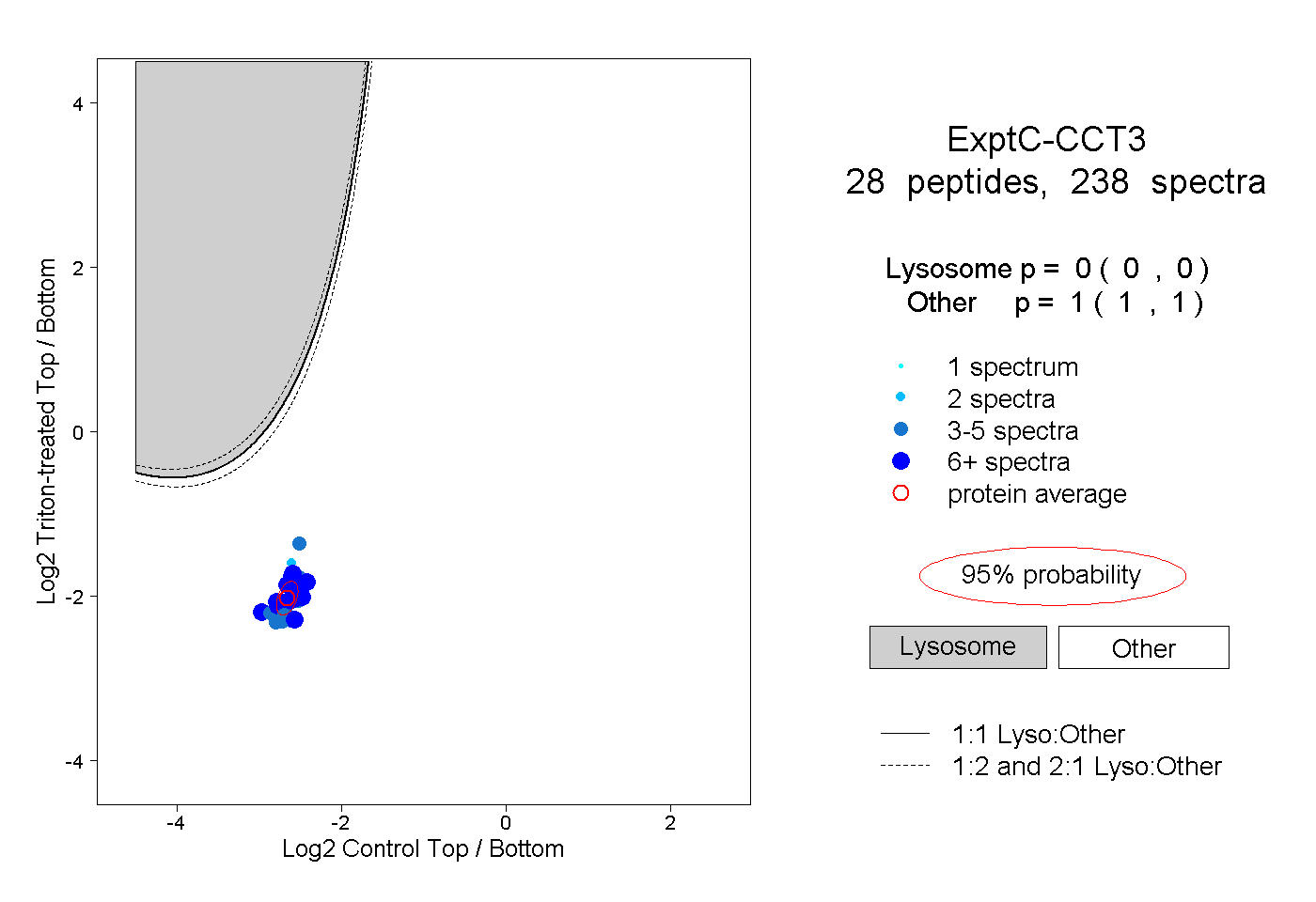 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
31 spectra |
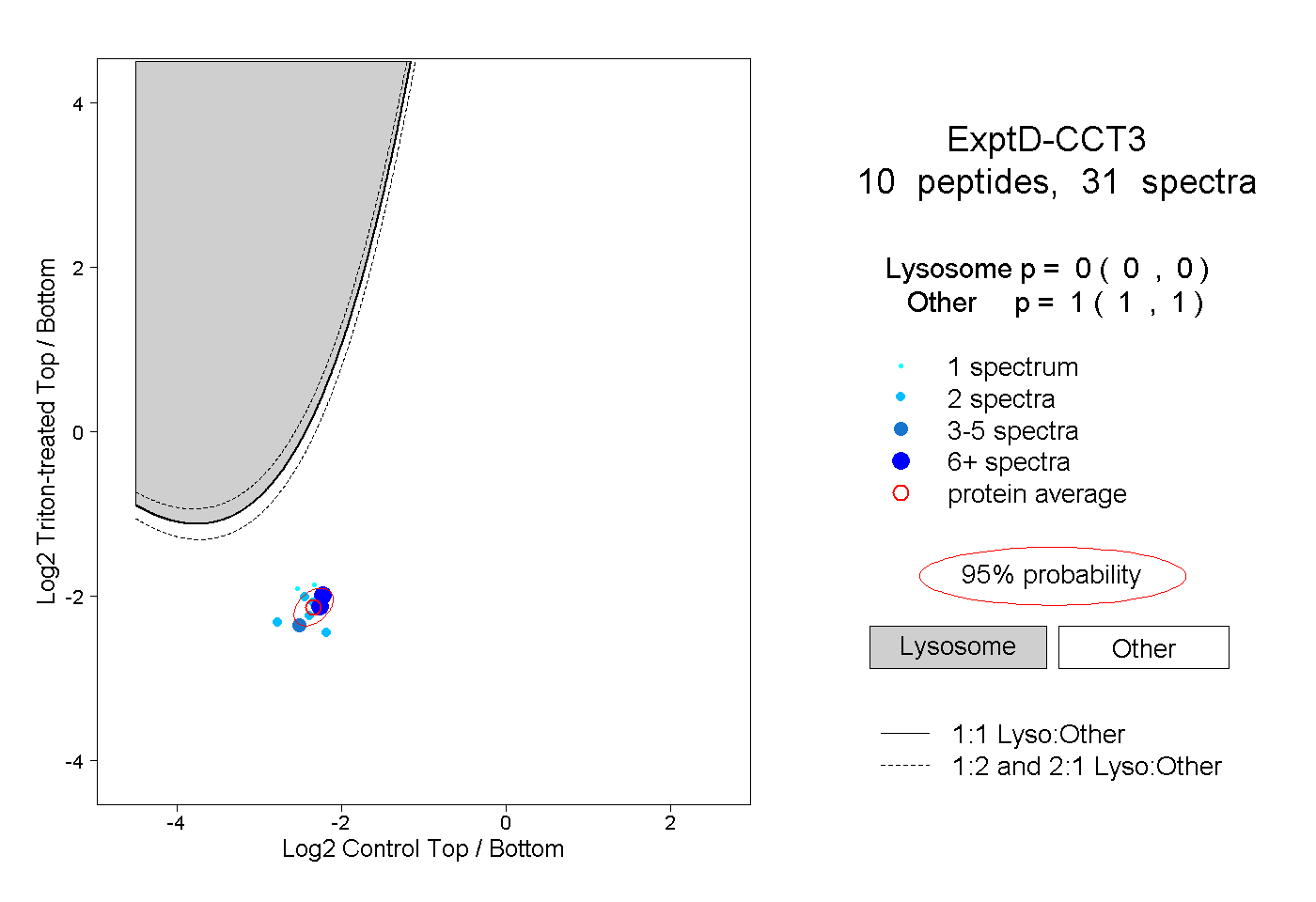 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |