peptides
spectra
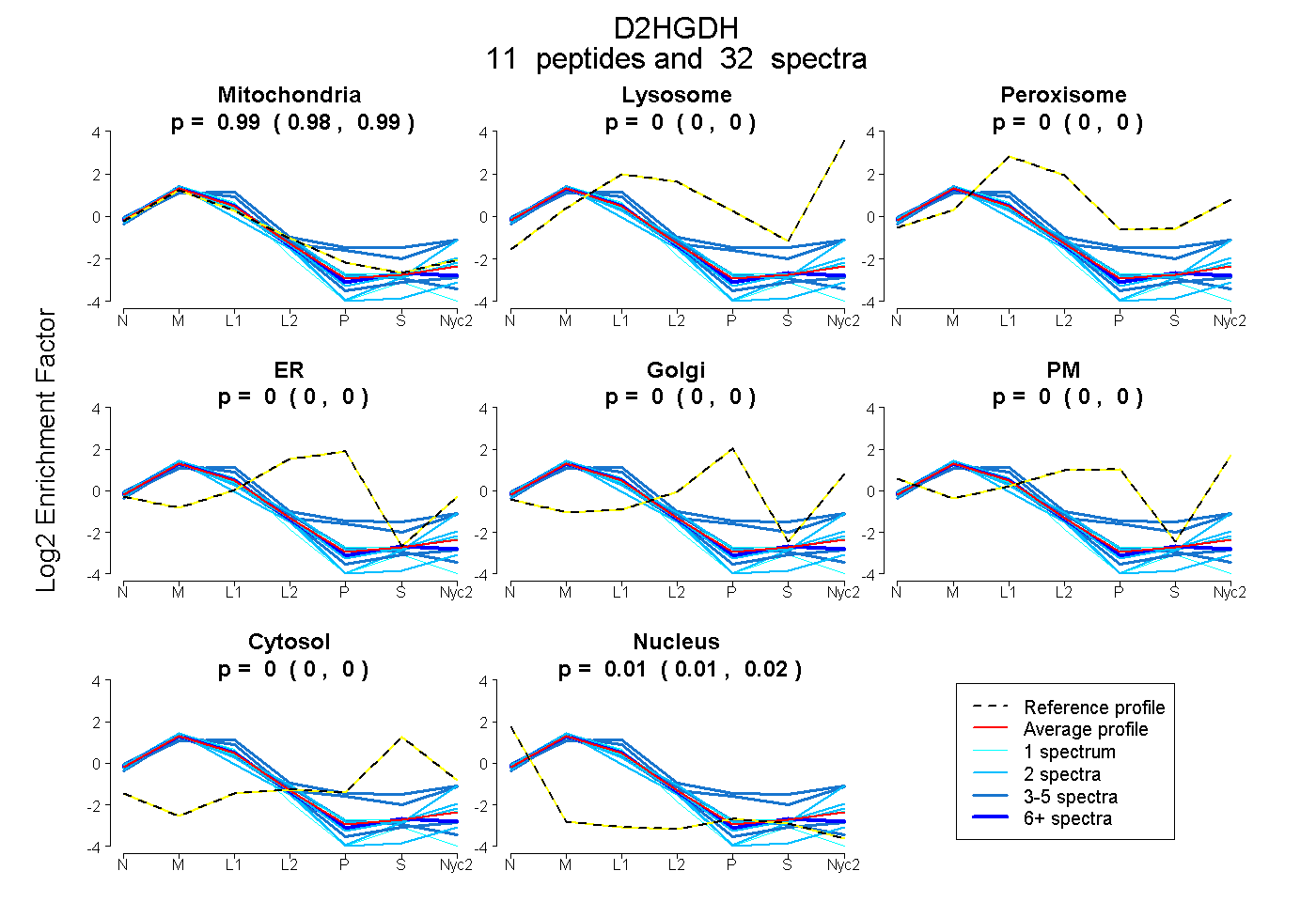
0.981 | 0.991
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.008 | 0.018
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
32 spectra |
 |
0.987 0.981 | 0.991 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.013 0.008 | 0.018 |
| 3 spectra, GSVSAEHGLGFK | 0.679 | 0.014 | 0.243 | 0.000 | 0.000 | 0.000 | 0.065 | 0.000 | ||
| 1 spectrum, VSGSPEVMLTPER | 0.988 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.012 | ||
| 1 spectrum, LPFSTVSEEDLAAFECIIPGR | 0.903 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.097 | ||
| 5 spectra, DFIMPLDLGAK | 0.929 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.071 | ||
| 2 spectra, VQMLWALR | 0.937 | 0.063 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, LYDLVIDLR | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.055 | ||
| 6 spectra, VLLRPQTSEEVSQILR | 0.958 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.042 | ||
| 2 spectra, VITDPEQLQTCNVDWLR | 0.947 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | ||
| 2 spectra, YDLSLPVER | 0.980 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | ||
| 3 spectra, GSCHIGGNVATNAGGLR | 0.821 | 0.134 | 0.021 | 0.000 | 0.000 | 0.000 | 0.025 | 0.000 | ||
| 2 spectra, ITEALSR | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
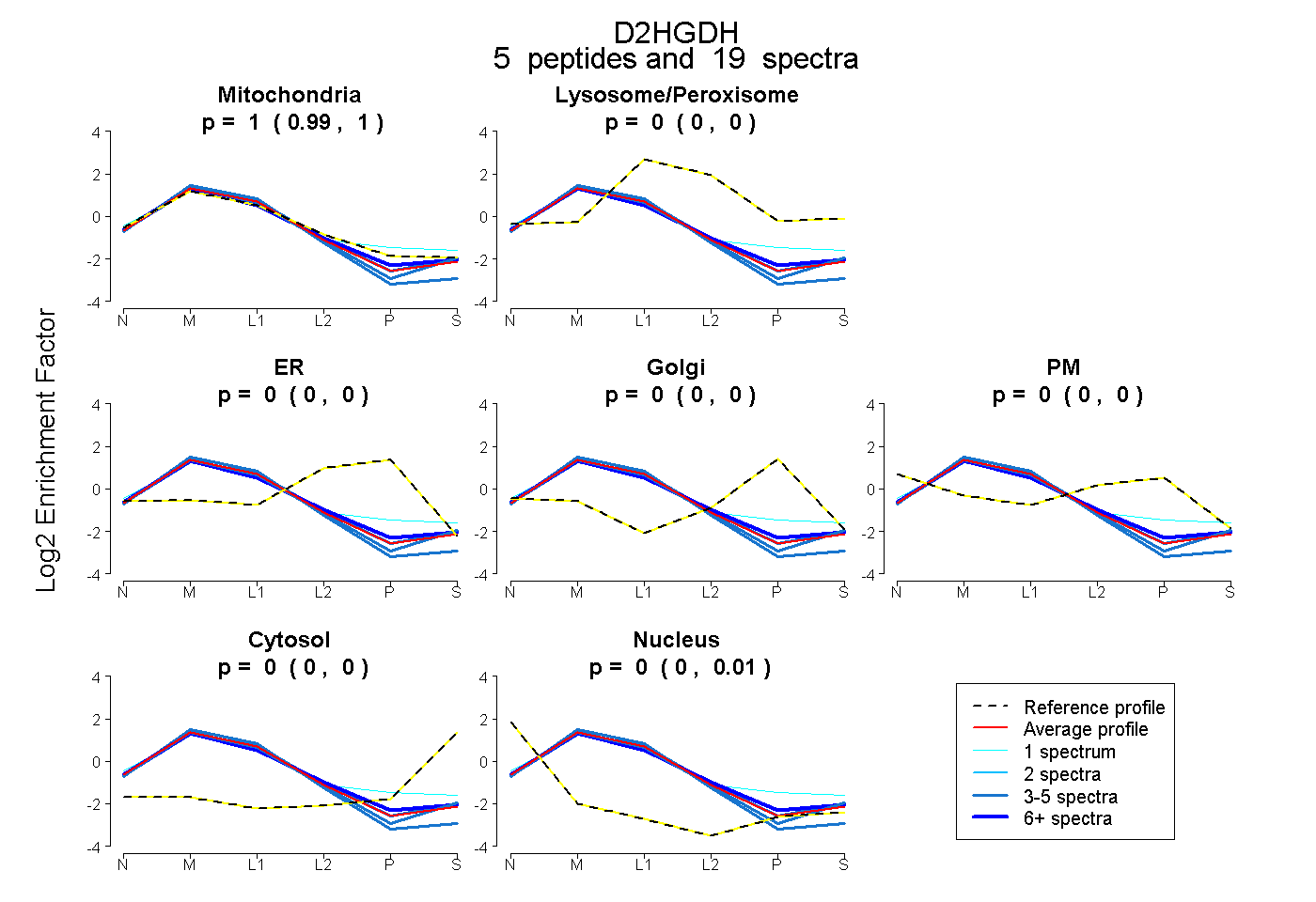 |
0.998 0.994 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.005 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
109 spectra |
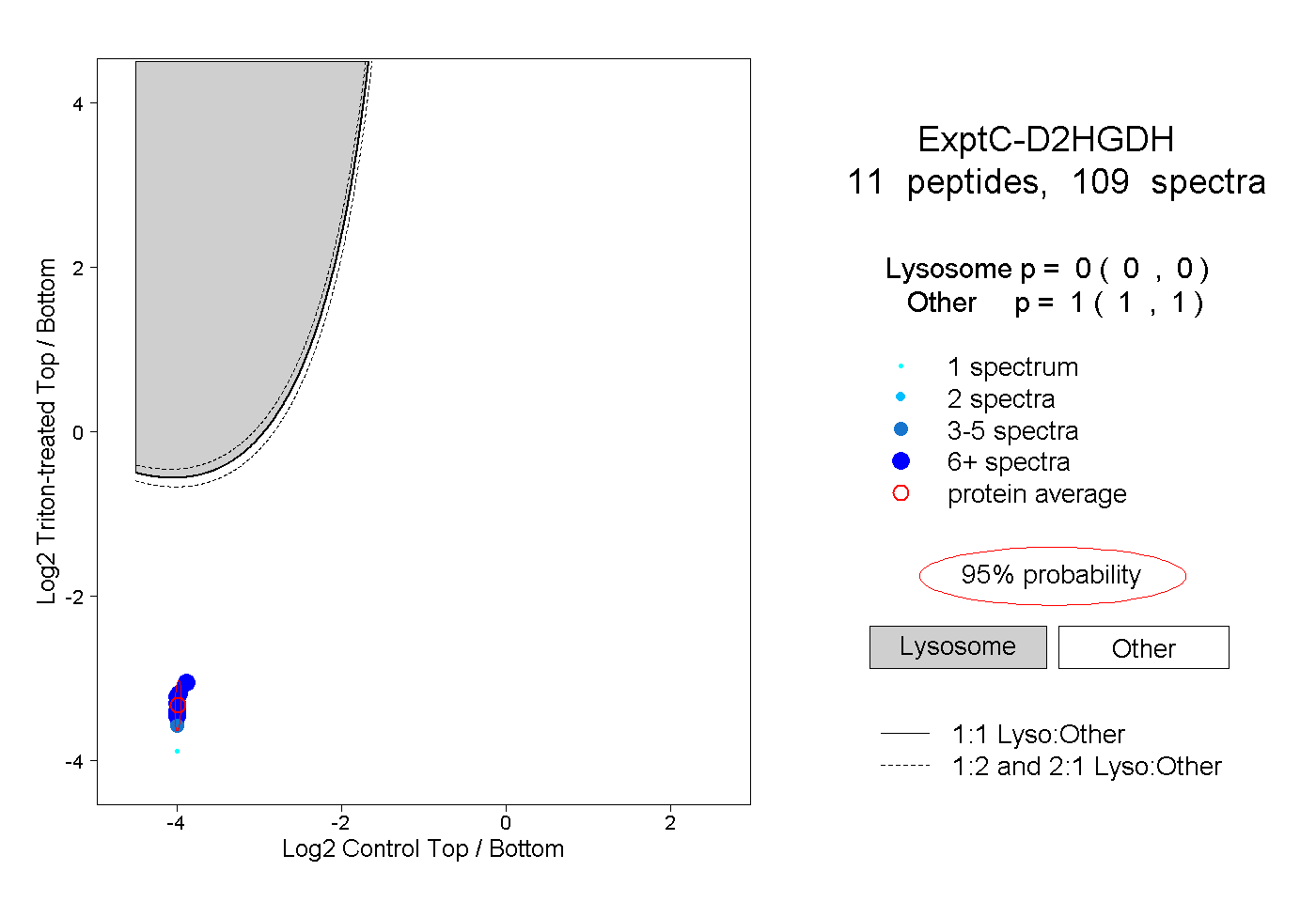 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
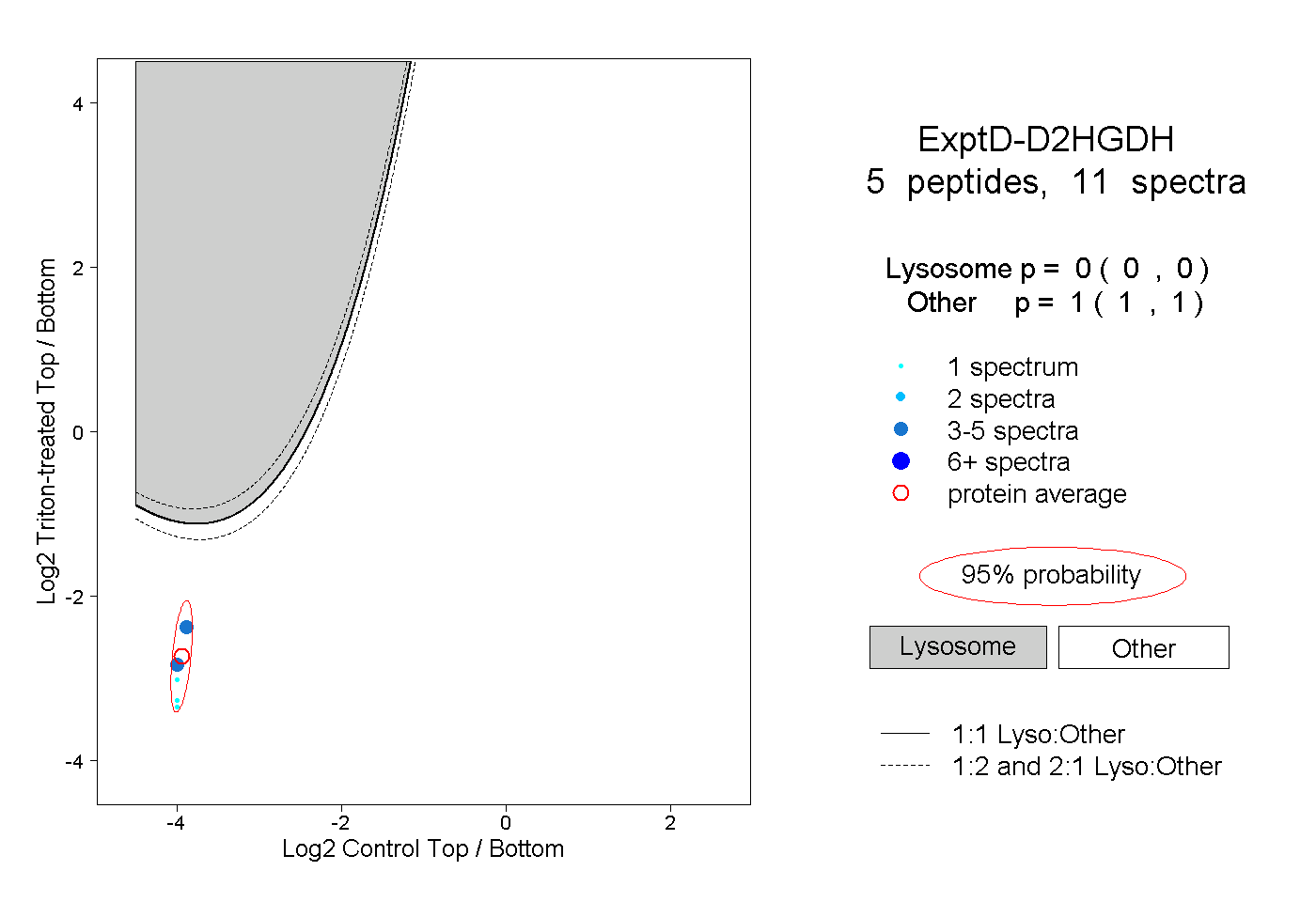 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |