peptides
spectra
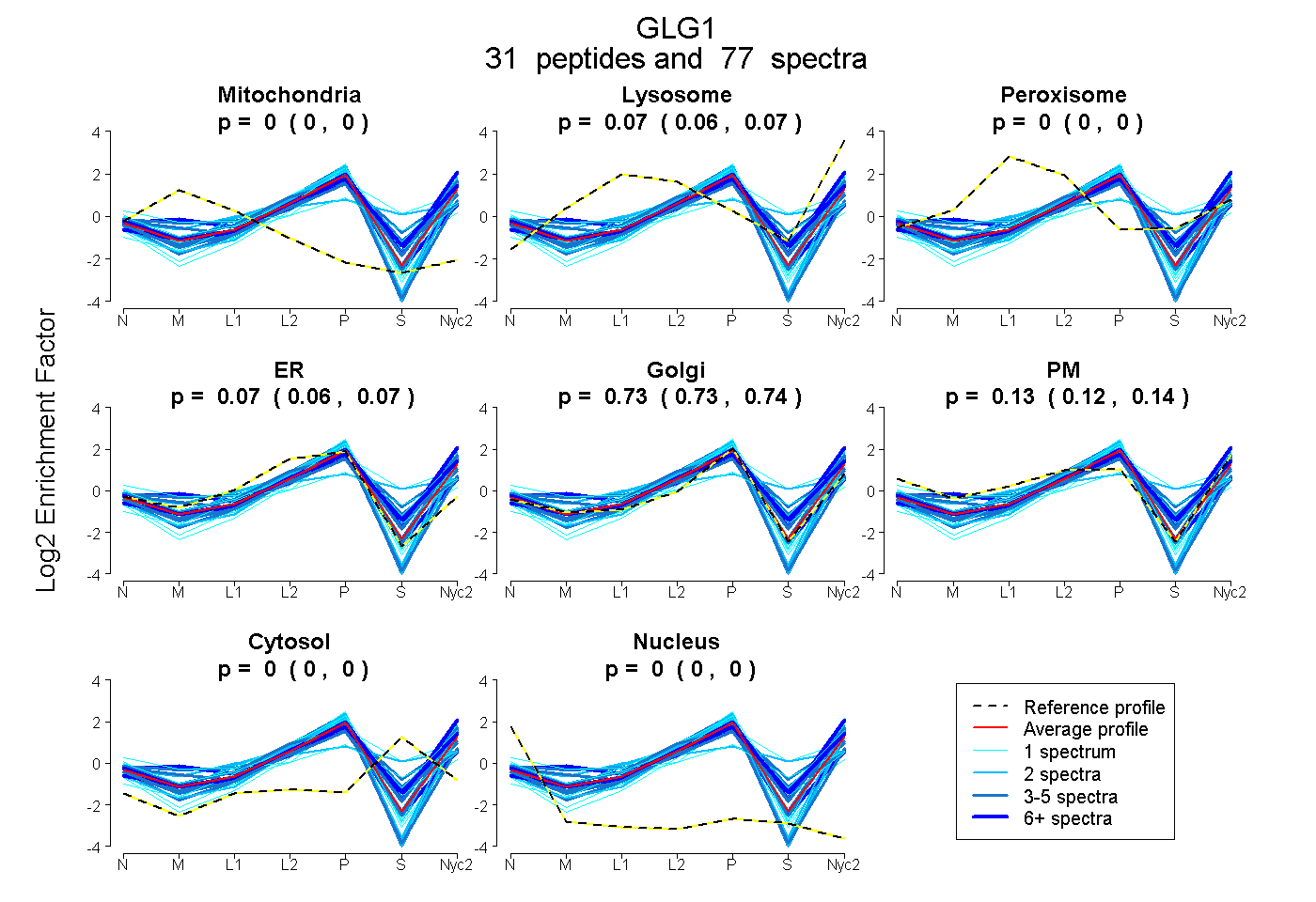
0.000 | 0.000
0.061 | 0.072
0.000 | 0.000
0.057 | 0.072
0.727 | 0.740
0.124 | 0.144
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.067 0.061 | 0.072 |
0.000 0.000 | 0.000 |
0.065 0.057 | 0.072 |
0.734 0.727 | 0.740 |
0.134 0.124 | 0.144 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, LEPDLYEACK | 0.000 | 0.000 | 0.000 | 0.194 | 0.736 | 0.070 | 0.000 | 0.000 | ||
| 6 spectra, NSELMDPK | 0.000 | 0.229 | 0.000 | 0.000 | 0.771 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, ADIFVDPVLHTACALDIK | 0.000 | 0.000 | 0.000 | 0.338 | 0.662 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, TMLQCLK | 0.000 | 0.127 | 0.000 | 0.000 | 0.455 | 0.322 | 0.097 | 0.000 | ||
| 6 spectra, HLYFACR | 0.088 | 0.040 | 0.000 | 0.191 | 0.561 | 0.120 | 0.000 | 0.000 | ||
| 3 spectra, LIAQDYK | 0.000 | 0.132 | 0.000 | 0.000 | 0.493 | 0.375 | 0.000 | 0.000 | ||
| 4 spectra, LDPALQDK | 0.000 | 0.070 | 0.000 | 0.000 | 0.723 | 0.207 | 0.000 | 0.000 | ||
| 2 spectra, HHCAAITPGR | 0.000 | 0.002 | 0.270 | 0.000 | 0.257 | 0.179 | 0.292 | 0.000 | ||
| 2 spectra, EVLNMLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.983 | 0.017 | 0.000 | 0.000 | ||
| 1 spectrum, GGAGPGGTGGGWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.899 | 0.101 | 0.000 | 0.000 | ||
| 3 spectra, ECAEEPVGK | 0.000 | 0.097 | 0.000 | 0.054 | 0.606 | 0.019 | 0.224 | 0.000 | ||
| 6 spectra, VAELSSDDFHLDR | 0.000 | 0.127 | 0.000 | 0.000 | 0.620 | 0.167 | 0.086 | 0.000 | ||
| 1 spectrum, SGDPMILSCLMEHLYTEK | 0.000 | 0.035 | 0.000 | 0.275 | 0.582 | 0.000 | 0.107 | 0.000 | ||
| 1 spectrum, FESVAR | 0.000 | 0.052 | 0.000 | 0.000 | 0.539 | 0.410 | 0.000 | 0.000 | ||
| 4 spectra, LSSDCEDQIR | 0.008 | 0.000 | 0.000 | 0.242 | 0.638 | 0.112 | 0.000 | 0.000 | ||
| 2 spectra, LLELQYFISR | 0.000 | 0.000 | 0.000 | 0.000 | 0.652 | 0.348 | 0.000 | 0.000 | ||
| 4 spectra, FCENTQAGEGR | 0.000 | 0.000 | 0.000 | 0.175 | 0.666 | 0.159 | 0.000 | 0.000 | ||
| 2 spectra, IIIQESALDYR | 0.000 | 0.217 | 0.000 | 0.000 | 0.692 | 0.091 | 0.000 | 0.000 | ||
| 3 spectra, QITQNTDYR | 0.000 | 0.138 | 0.000 | 0.000 | 0.844 | 0.000 | 0.019 | 0.000 | ||
| 1 spectrum, CLFNHK | 0.000 | 0.000 | 0.000 | 0.282 | 0.717 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, CLIDLGK | 0.000 | 0.000 | 0.000 | 0.235 | 0.605 | 0.160 | 0.000 | 0.000 | ||
| 1 spectrum, DDSELEGQVISCLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.787 | 0.213 | 0.000 | 0.000 | ||
| 2 spectra, LAEEESCR | 0.000 | 0.000 | 0.000 | 0.141 | 0.653 | 0.206 | 0.000 | 0.000 | ||
| 1 spectrum, QMSCLMEALEDK | 0.021 | 0.000 | 0.110 | 0.000 | 0.215 | 0.416 | 0.237 | 0.000 | ||
| 1 spectrum, CNVENLPR | 0.000 | 0.065 | 0.000 | 0.000 | 0.567 | 0.000 | 0.367 | 0.000 | ||
| 5 spectra, MVEDCEHR | 0.000 | 0.048 | 0.000 | 0.282 | 0.520 | 0.000 | 0.150 | 0.000 | ||
| 3 spectra, FCPEADSK | 0.000 | 0.038 | 0.000 | 0.030 | 0.607 | 0.175 | 0.150 | 0.000 | ||
| 1 spectrum, MTAIIFSDYR | 0.000 | 0.177 | 0.000 | 0.084 | 0.656 | 0.084 | 0.000 | 0.000 | ||
| 1 spectrum, ALNEACESVIQTACK | 0.000 | 0.000 | 0.000 | 0.205 | 0.658 | 0.000 | 0.131 | 0.007 | ||
| 2 spectra, CAIGVTHFQLVQMK | 0.000 | 0.068 | 0.000 | 0.269 | 0.436 | 0.226 | 0.000 | 0.000 | ||
| 3 spectra, QVSSECQGEMLDYR | 0.000 | 0.138 | 0.000 | 0.066 | 0.469 | 0.286 | 0.042 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
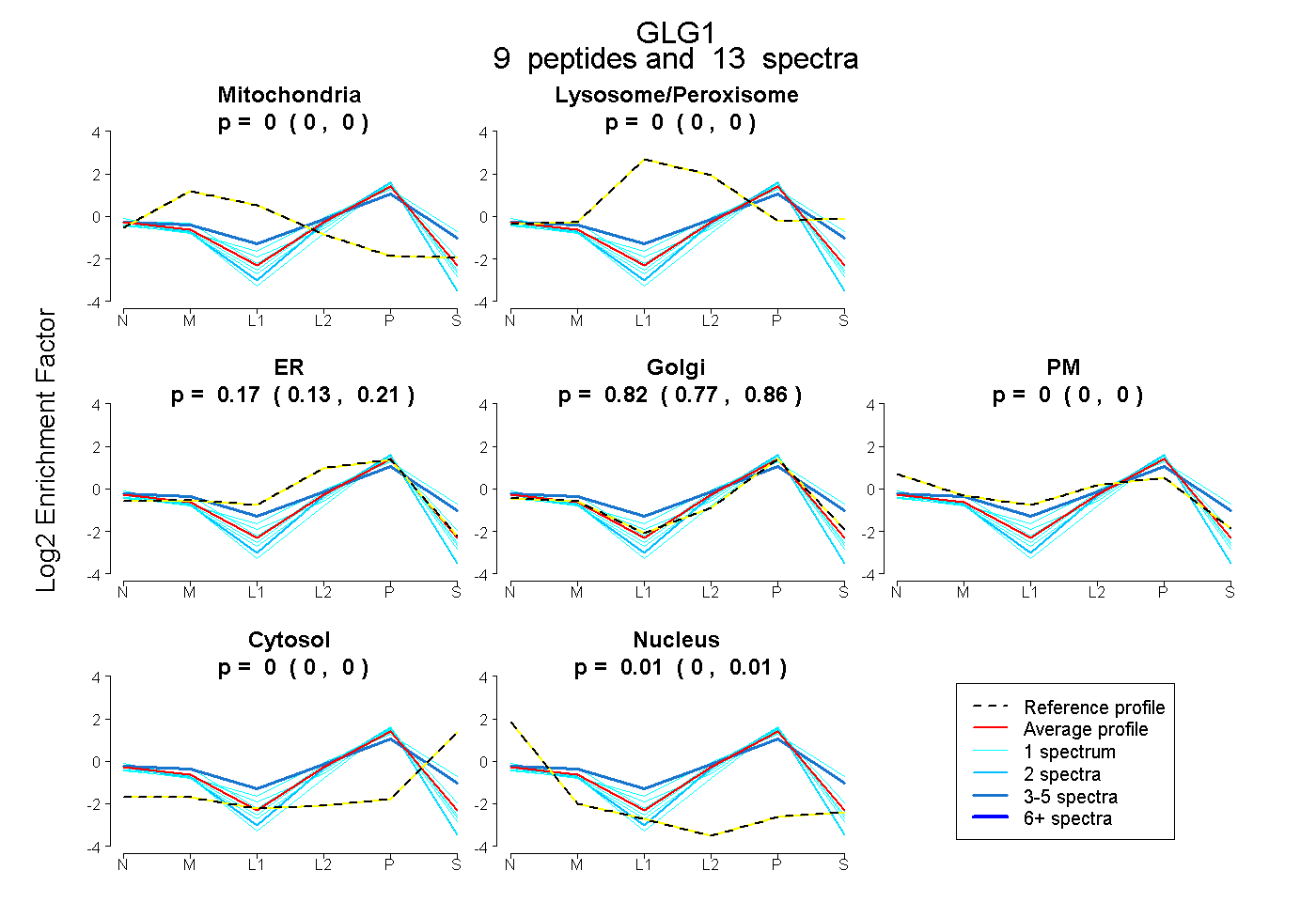 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.174 0.135 | 0.208 |
0.821 0.772 | 0.856 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.006 0.000 | 0.015 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
145 spectra |
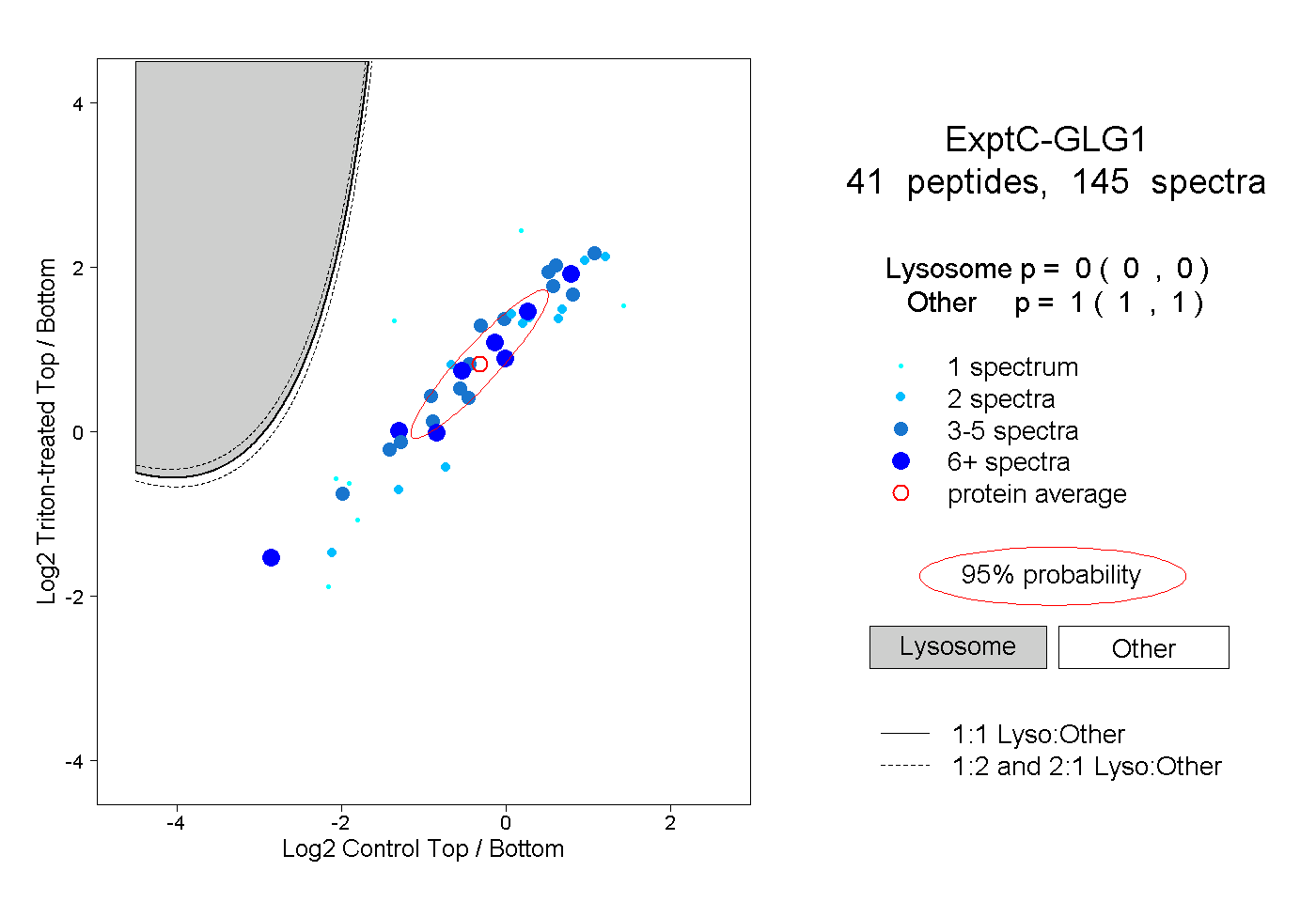 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
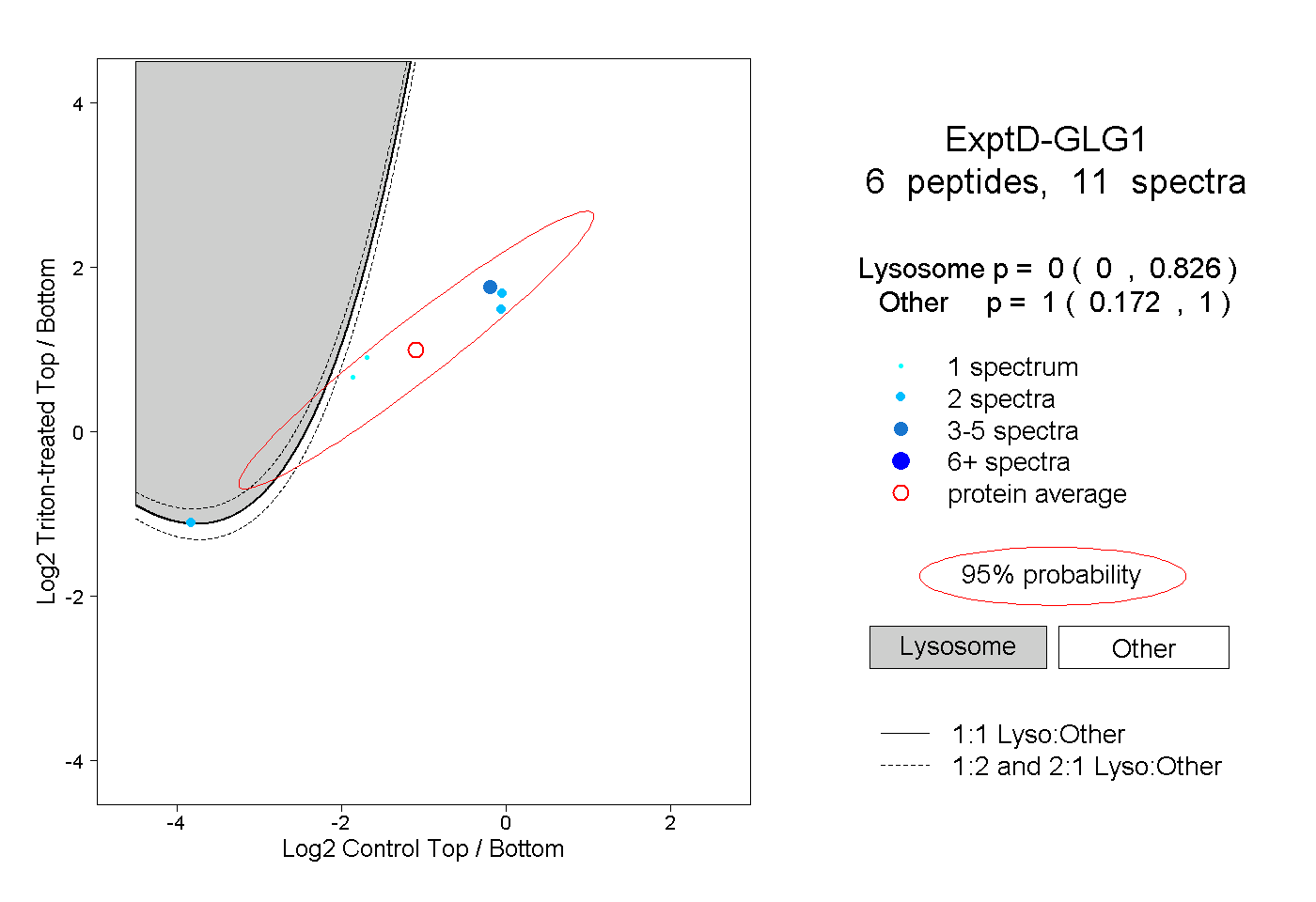 |
0.000 0.000 | 0.826 |
1.000 0.172 | 1.000 |