peptides
spectra
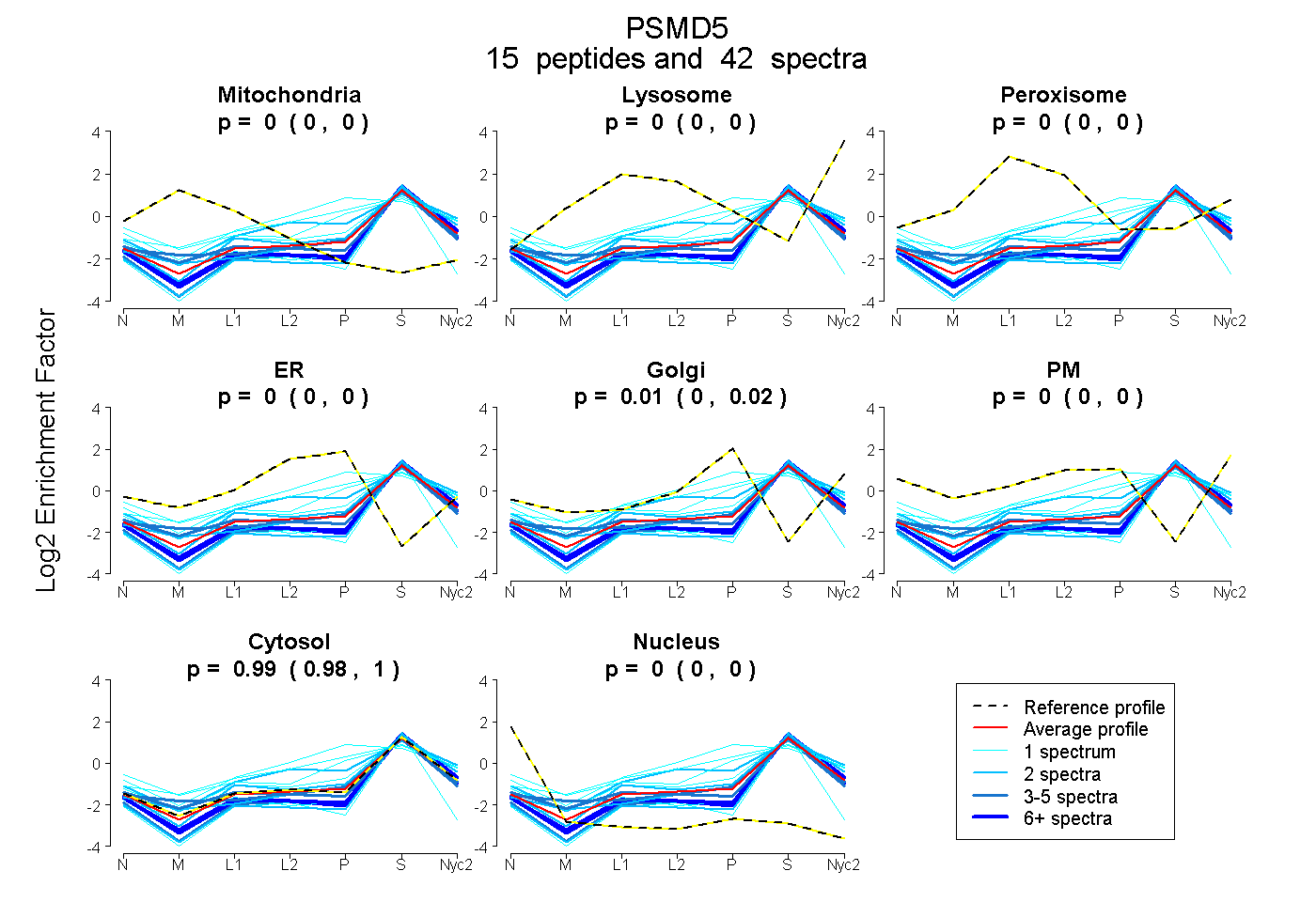
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.016
0.000 | 0.000
0.983 | 0.999
0.000 | 0.001
peptides
spectra
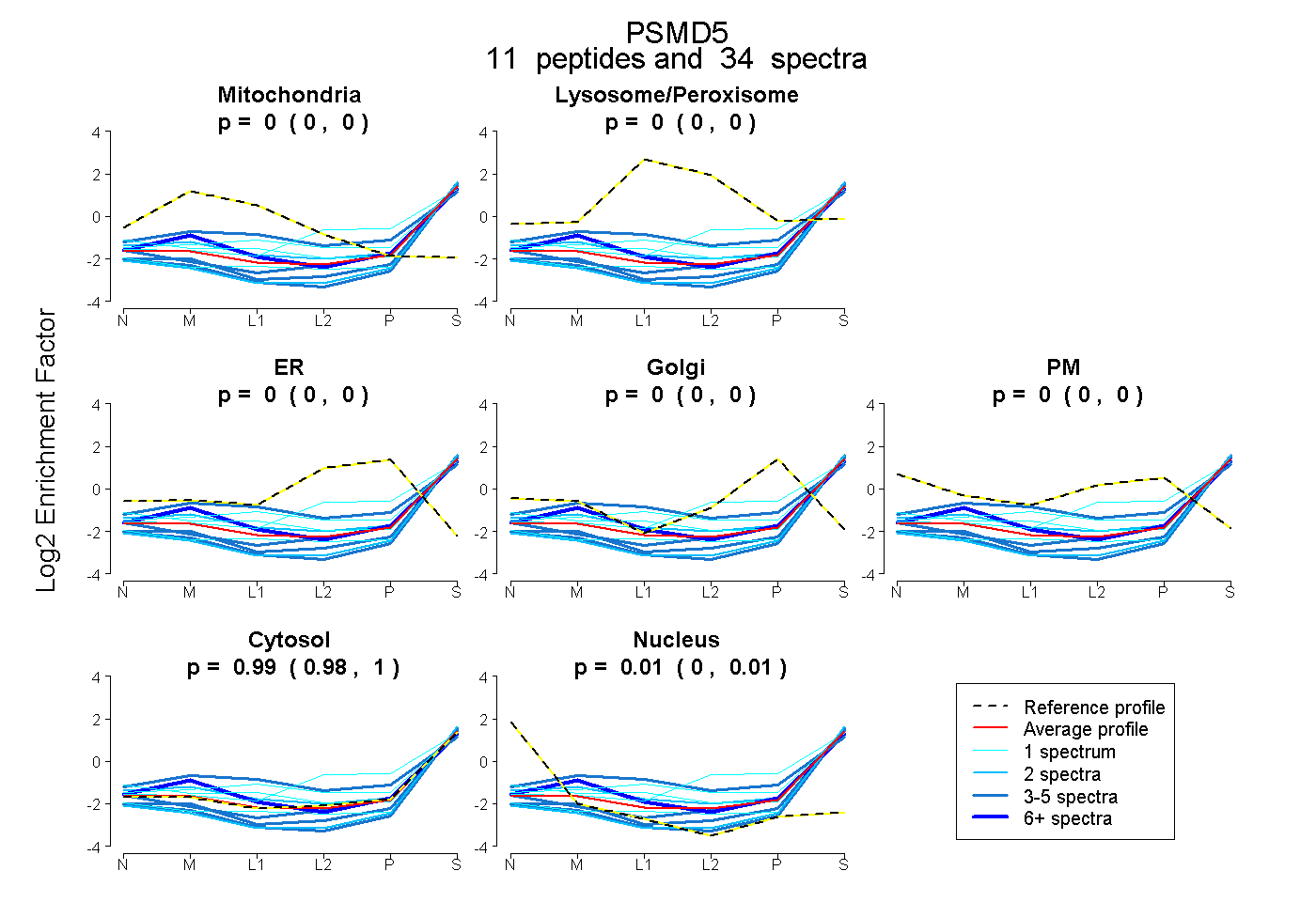
0.000 | 0.005
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.984 | 0.995
0.002 | 0.015
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.008 0.000 | 0.016 |
0.000 0.000 | 0.000 |
0.992 0.983 | 0.999 |
0.000 0.000 | 0.001 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.000 0.000 | 0.005 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.990 0.984 | 0.995 |
0.010 0.002 | 0.015 |
| 9 spectra, LLQAVEPIHLAR | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | 0.895 | 0.000 | |||
| 2 spectra, ALQSVVQAVPLHELR | 0.070 | 0.033 | 0.000 | 0.000 | 0.000 | 0.898 | 0.000 | |||
| 1 spectrum, TVAEIFGNSNYLR | 0.000 | 0.191 | 0.000 | 0.000 | 0.000 | 0.809 | 0.000 | |||
| 1 spectrum, QVVCCIGGENLSVAK | 0.000 | 0.098 | 0.000 | 0.000 | 0.000 | 0.853 | 0.049 | |||
| 4 spectra, LEAPLEELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.975 | 0.025 | |||
| 4 spectra, ELTGEDVLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.965 | 0.035 | |||
| 2 spectra, TLTLSQIGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.019 | |||
| 4 spectra, DSLELFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.995 | 0.005 | |||
| 1 spectrum, GISNQPFPELHCAALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 5 spectra, LRPLFSLLNQNNR | 0.080 | 0.216 | 0.000 | 0.010 | 0.000 | 0.693 | 0.000 | |||
| 1 spectrum, VFTAIANQPWAQK | 0.000 | 0.084 | 0.174 | 0.000 | 0.000 | 0.742 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
39 spectra |
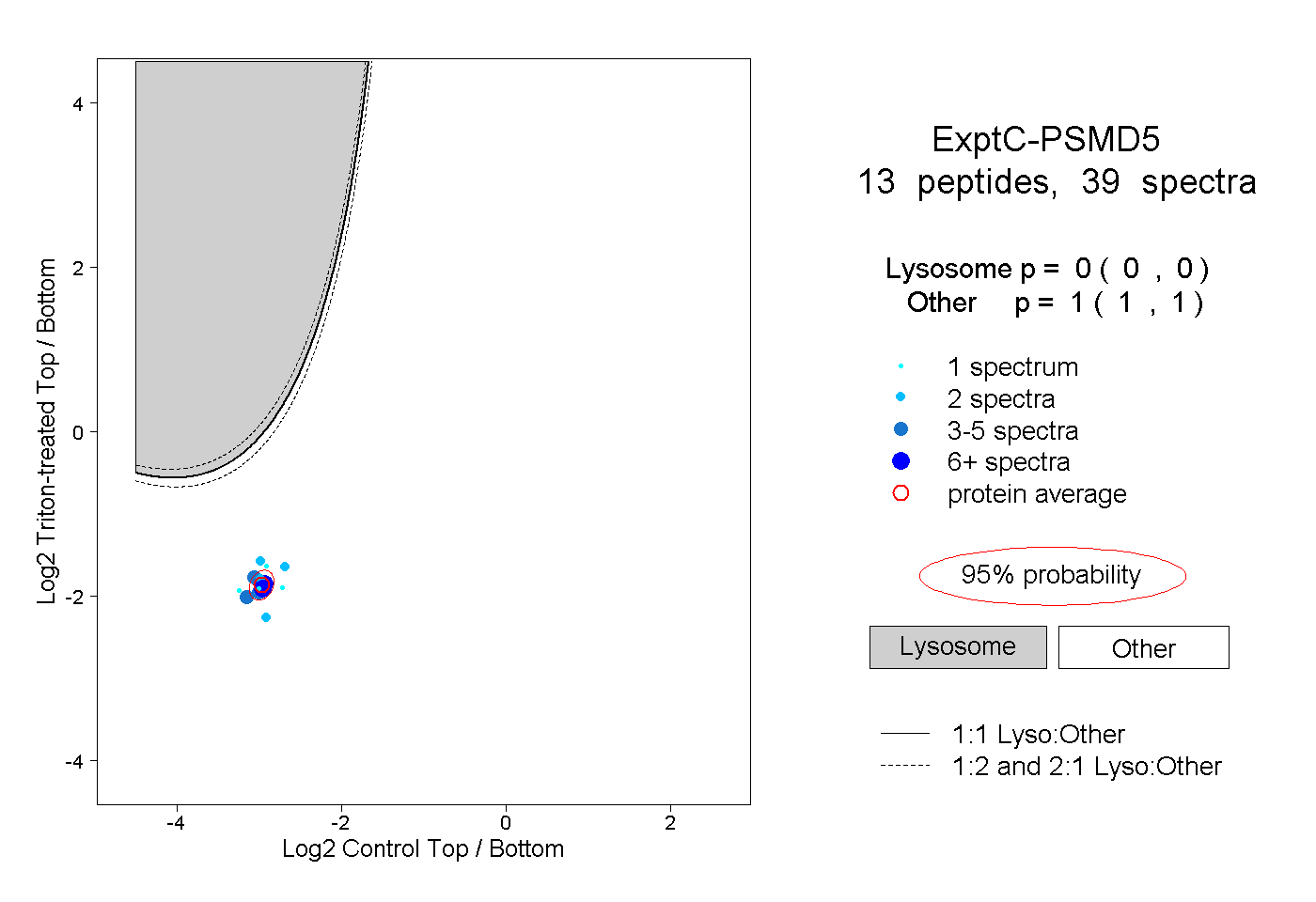 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
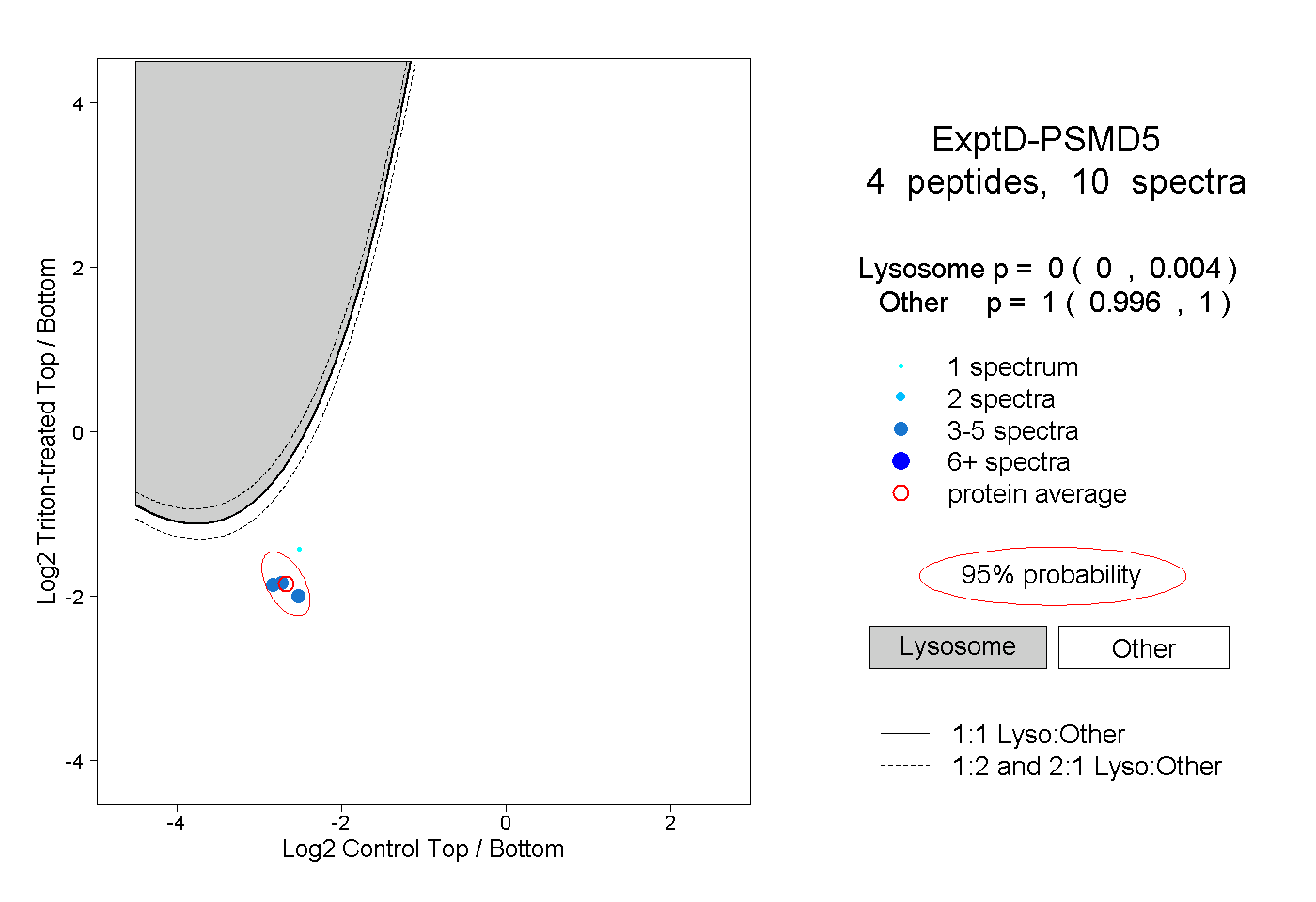 |
0.000 0.000 | 0.004 |
1.000 0.996 | 1.000 |