peptides
spectra
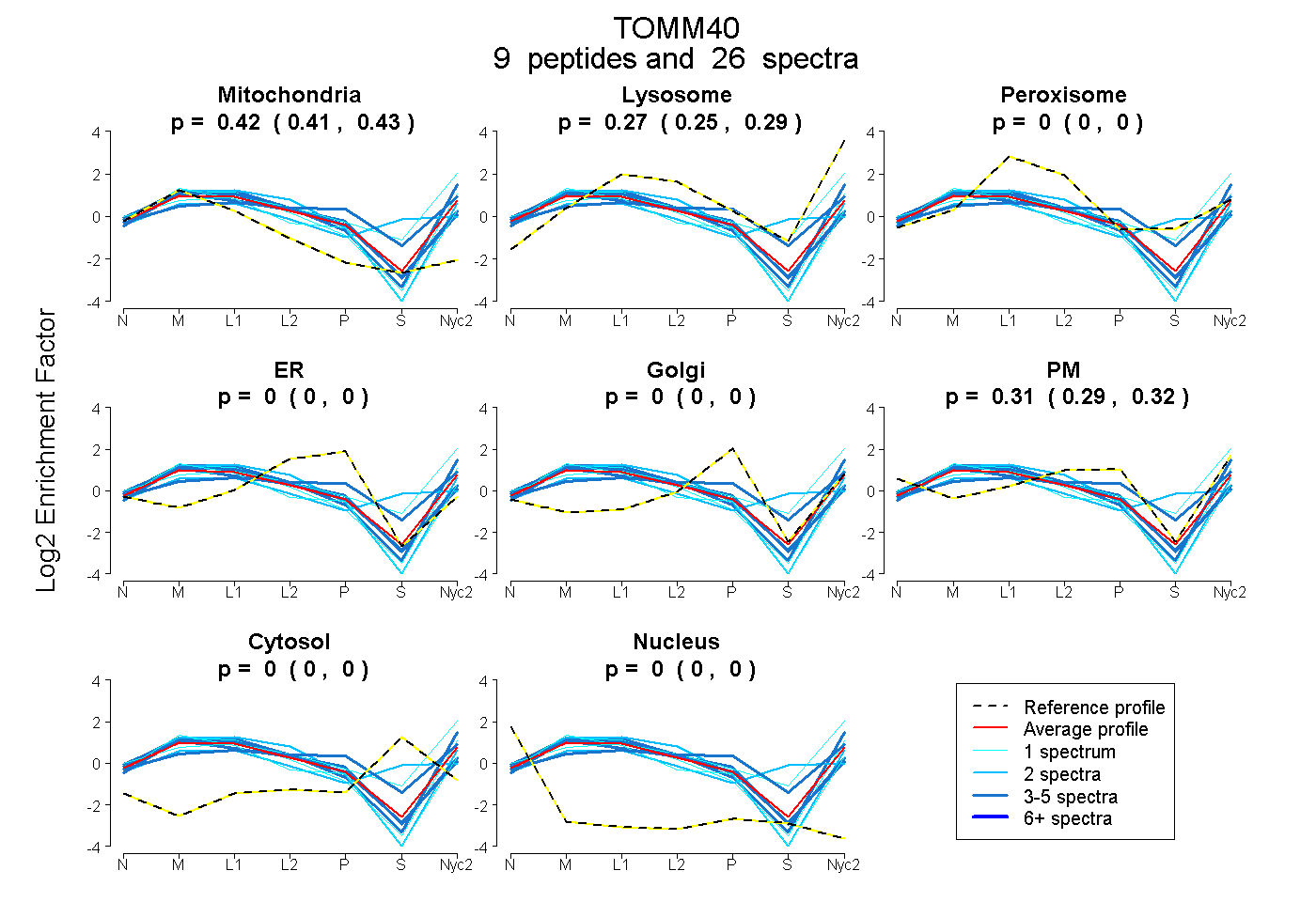
0.407 | 0.430
0.254 | 0.289
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.285 | 0.325
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
26 spectra |
 |
0.420 0.407 | 0.430 |
0.274 0.254 | 0.289 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.306 0.285 | 0.325 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, MQDTSASFGYQLDLPK | 0.213 | 0.484 | 0.003 | 0.000 | 0.000 | 0.253 | 0.047 | 0.000 | ||
| 5 spectra, MAIQTQQSK | 0.453 | 0.262 | 0.000 | 0.133 | 0.000 | 0.152 | 0.000 | 0.000 | ||
| 2 spectra, ELFPVQMEGVK | 0.427 | 0.192 | 0.000 | 0.000 | 0.000 | 0.381 | 0.000 | 0.000 | ||
| 2 spectra, GSVNSNWIVGATLEK | 0.305 | 0.140 | 0.287 | 0.000 | 0.000 | 0.000 | 0.268 | 0.000 | ||
| 5 spectra, ANFLFK | 0.373 | 0.346 | 0.000 | 0.000 | 0.000 | 0.281 | 0.000 | 0.000 | ||
| 4 spectra, FVNWQVDGEYR | 0.484 | 0.140 | 0.000 | 0.023 | 0.000 | 0.353 | 0.000 | 0.000 | ||
| 1 spectrum, QLSPTEAFPVLVGDMDNSGSLNAQVIHQLSPGLR | 0.537 | 0.116 | 0.000 | 0.000 | 0.000 | 0.347 | 0.000 | 0.000 | ||
| 5 spectra, RPGEEGTVMSLAGK | 0.198 | 0.197 | 0.174 | 0.000 | 0.220 | 0.182 | 0.029 | 0.000 | ||
| 1 spectrum, ASDQLQVGVEFEASTR | 0.453 | 0.273 | 0.000 | 0.000 | 0.000 | 0.274 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
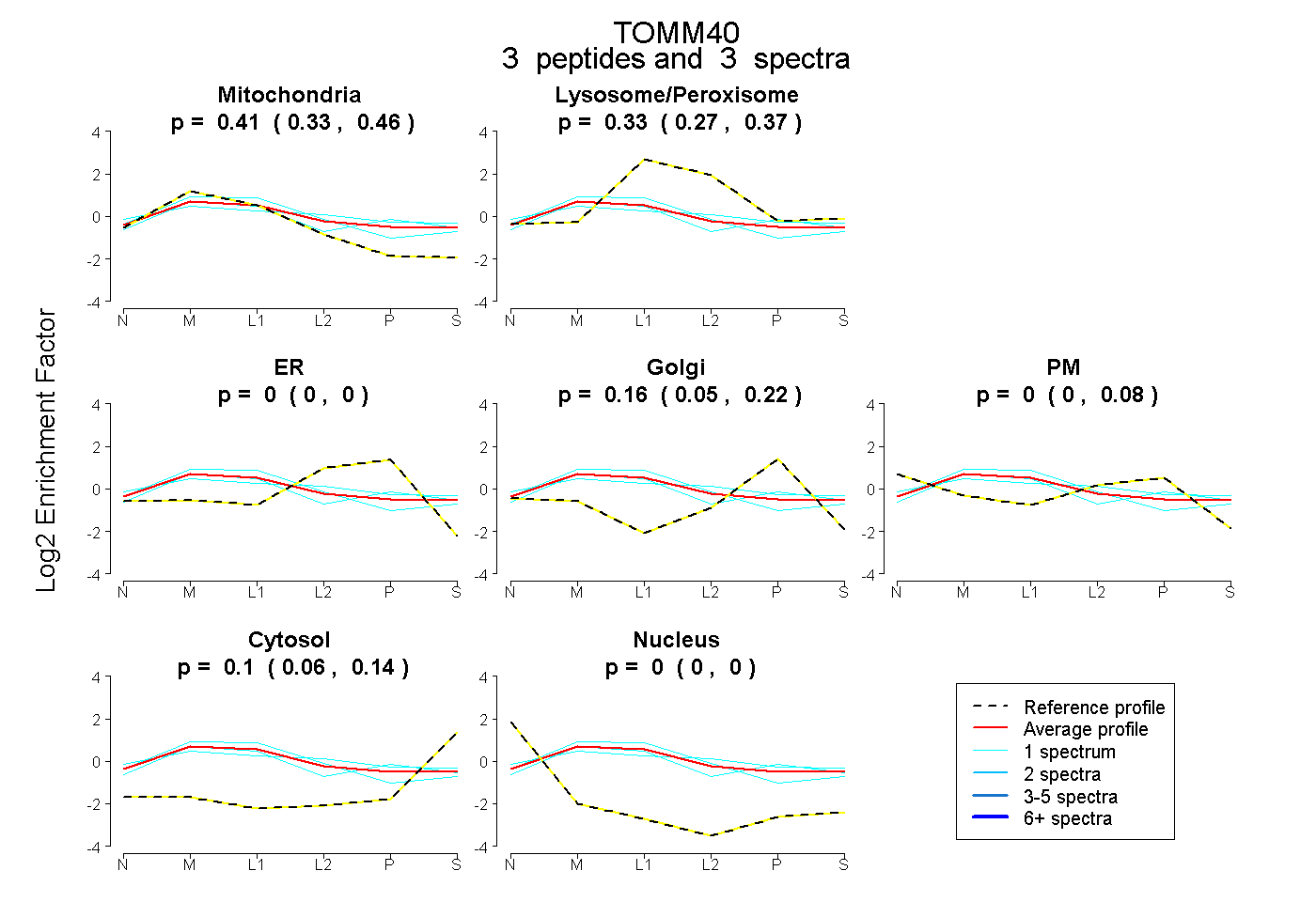 |
0.407 0.334 | 0.461 |
0.330 0.274 | 0.372 |
0.000 0.000 | 0.000 |
0.162 0.049 | 0.219 |
0.000 0.000 | 0.084 |
0.101 0.057 | 0.138 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
102 spectra |
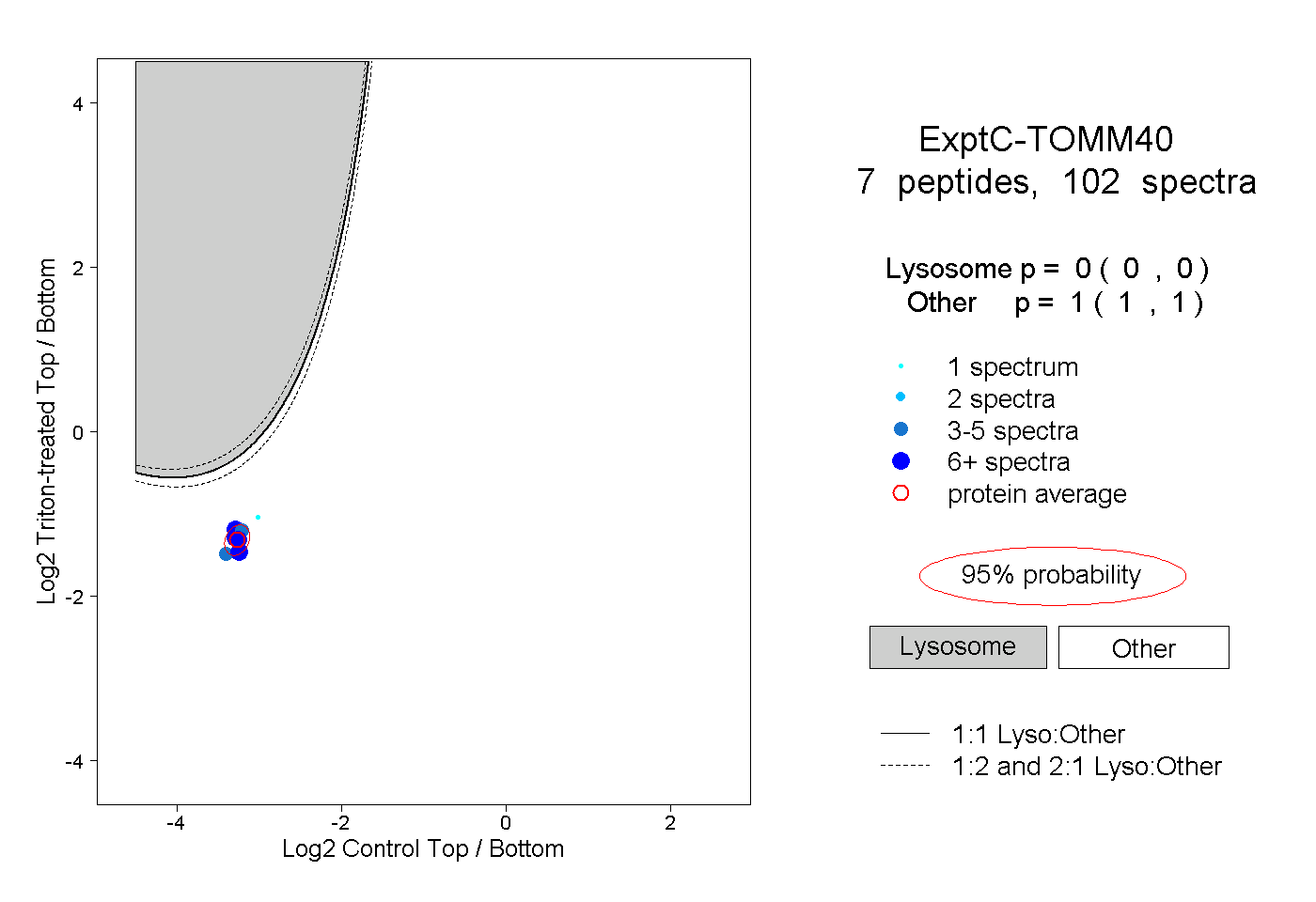 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
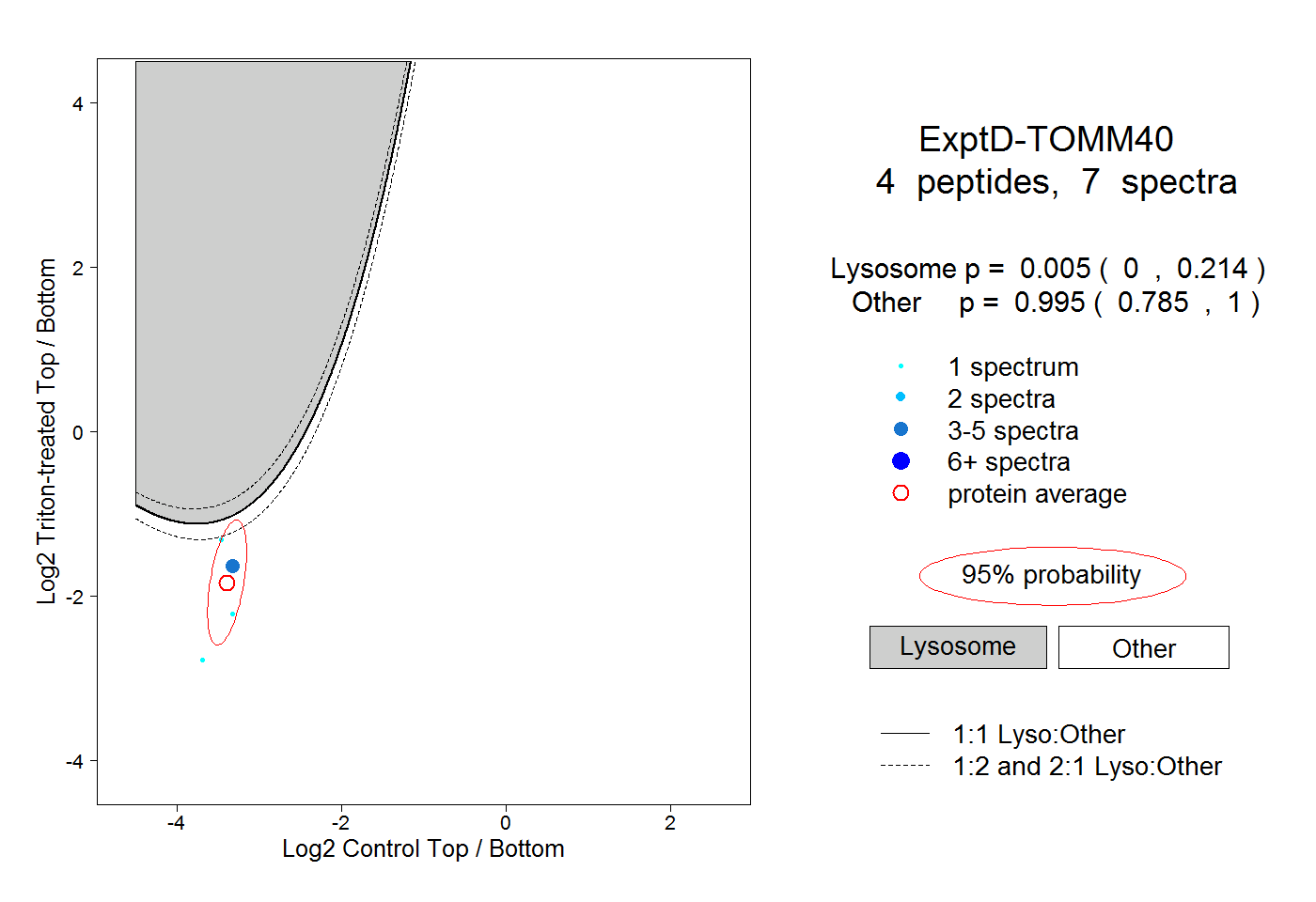 |
0.005 0.000 | 0.214 |
0.995 0.785 | 1.000 |