peptides
spectra
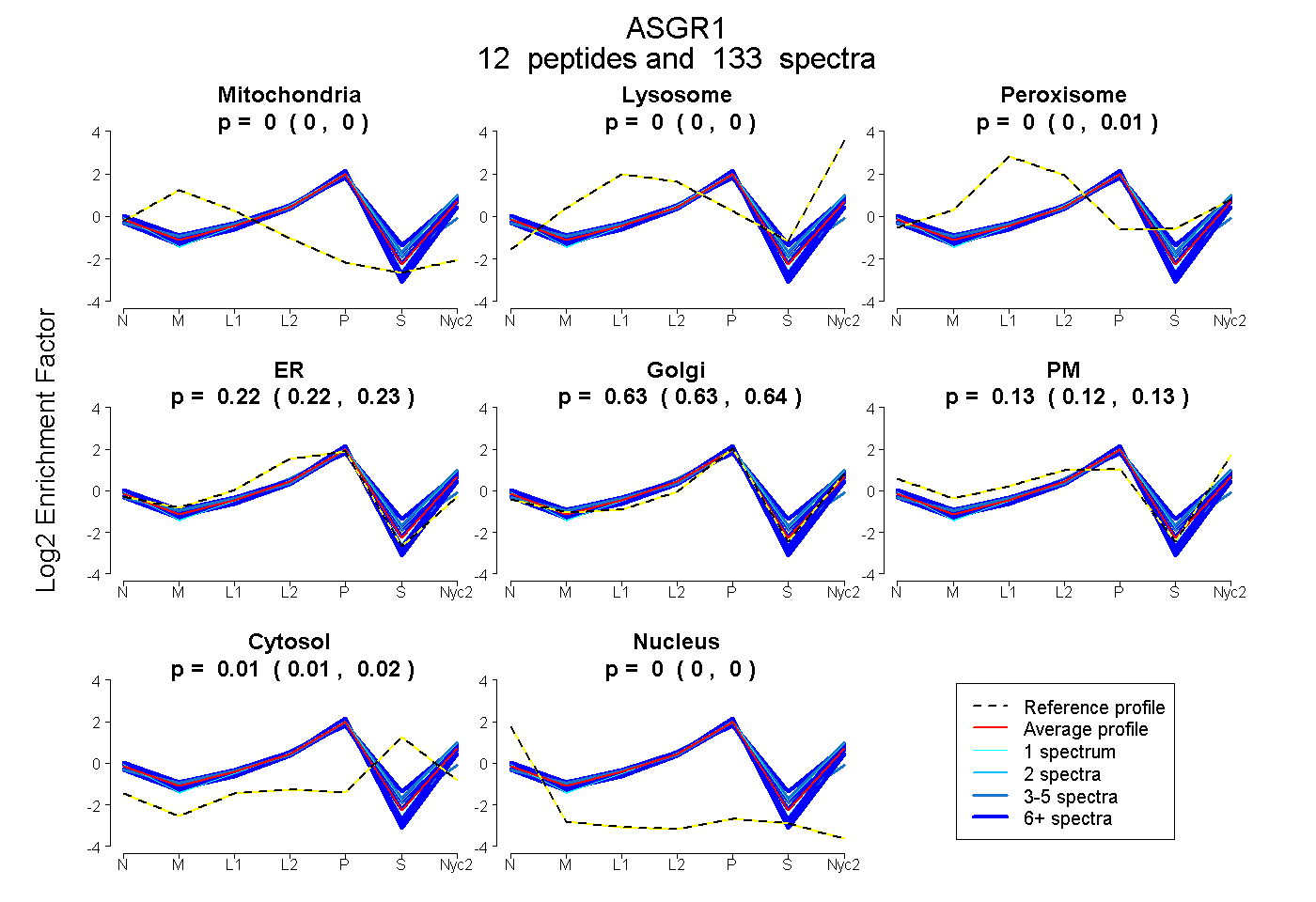
0.000 | 0.000
0.000 | 0.000
0.000 | 0.006
0.216 | 0.230
0.626 | 0.638
0.120 | 0.132
0.012 | 0.018
0.000 | 0.000
peptides
spectra
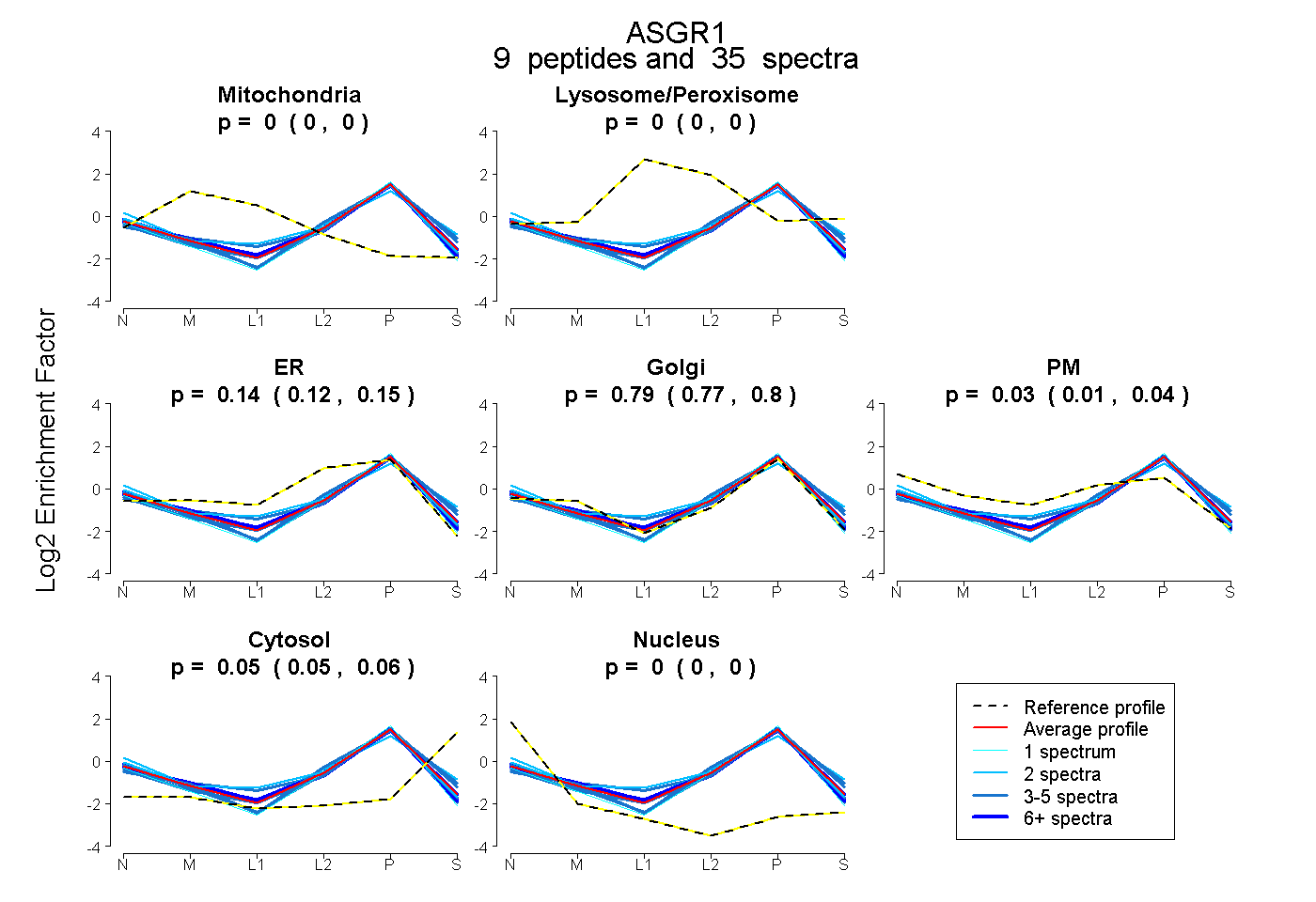
0.000 | 0.000
0.000 | 0.000
0.122 | 0.147
0.769 | 0.802
0.011 | 0.038
0.045 | 0.058
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
133 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.006 |
0.224 0.216 | 0.230 |
0.631 0.626 | 0.638 |
0.128 0.120 | 0.132 |
0.015 0.012 | 0.018 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.135 0.122 | 0.147 |
0.787 0.769 | 0.802 |
0.026 0.011 | 0.038 |
0.052 0.045 | 0.058 |
0.000 0.000 | 0.000 |
| 5 spectra, QLVSDVR | 0.000 | 0.000 | 0.022 | 0.955 | 0.000 | 0.010 | 0.014 | |||
| 1 spectrum, WVDGTDYETGFK | 0.000 | 0.000 | 0.003 | 0.997 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LLLHVK | 0.000 | 0.000 | 0.116 | 0.772 | 0.000 | 0.112 | 0.000 | |||
| 8 spectra, GPPPAPR | 0.000 | 0.001 | 0.141 | 0.841 | 0.000 | 0.000 | 0.018 | |||
| 2 spectra, LCSGFR | 0.000 | 0.001 | 0.037 | 0.499 | 0.319 | 0.145 | 0.000 | |||
| 6 spectra, LVESQLEK | 0.000 | 0.012 | 0.095 | 0.773 | 0.081 | 0.038 | 0.000 | |||
| 5 spectra, SLSCQMAALR | 0.000 | 0.000 | 0.142 | 0.731 | 0.000 | 0.127 | 0.000 | |||
| 3 spectra, ALTTQGER | 0.000 | 0.051 | 0.145 | 0.785 | 0.000 | 0.000 | 0.018 | |||
| 2 spectra, WVCETELGK | 0.000 | 0.101 | 0.086 | 0.740 | 0.055 | 0.000 | 0.019 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
160 spectra |
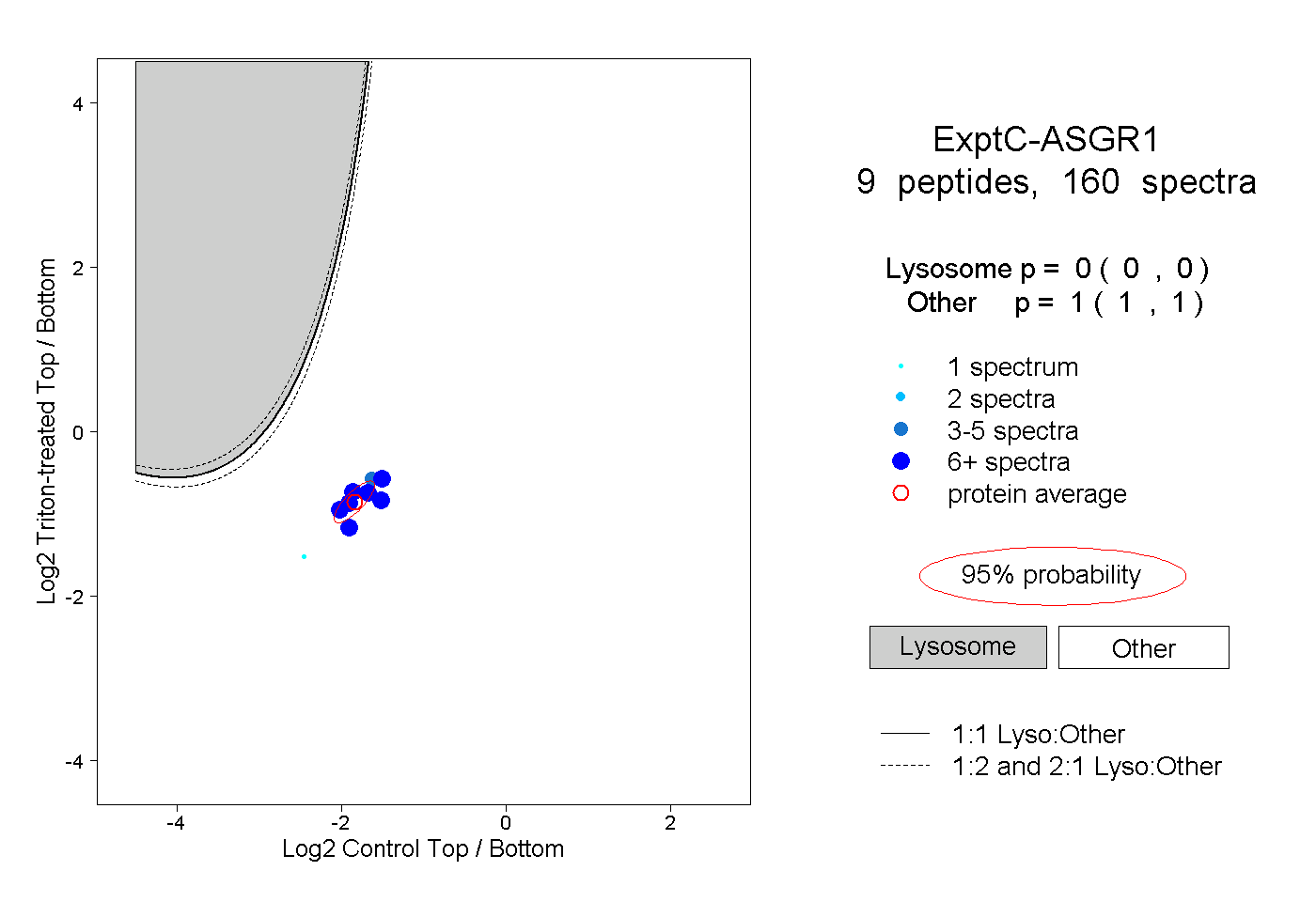 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
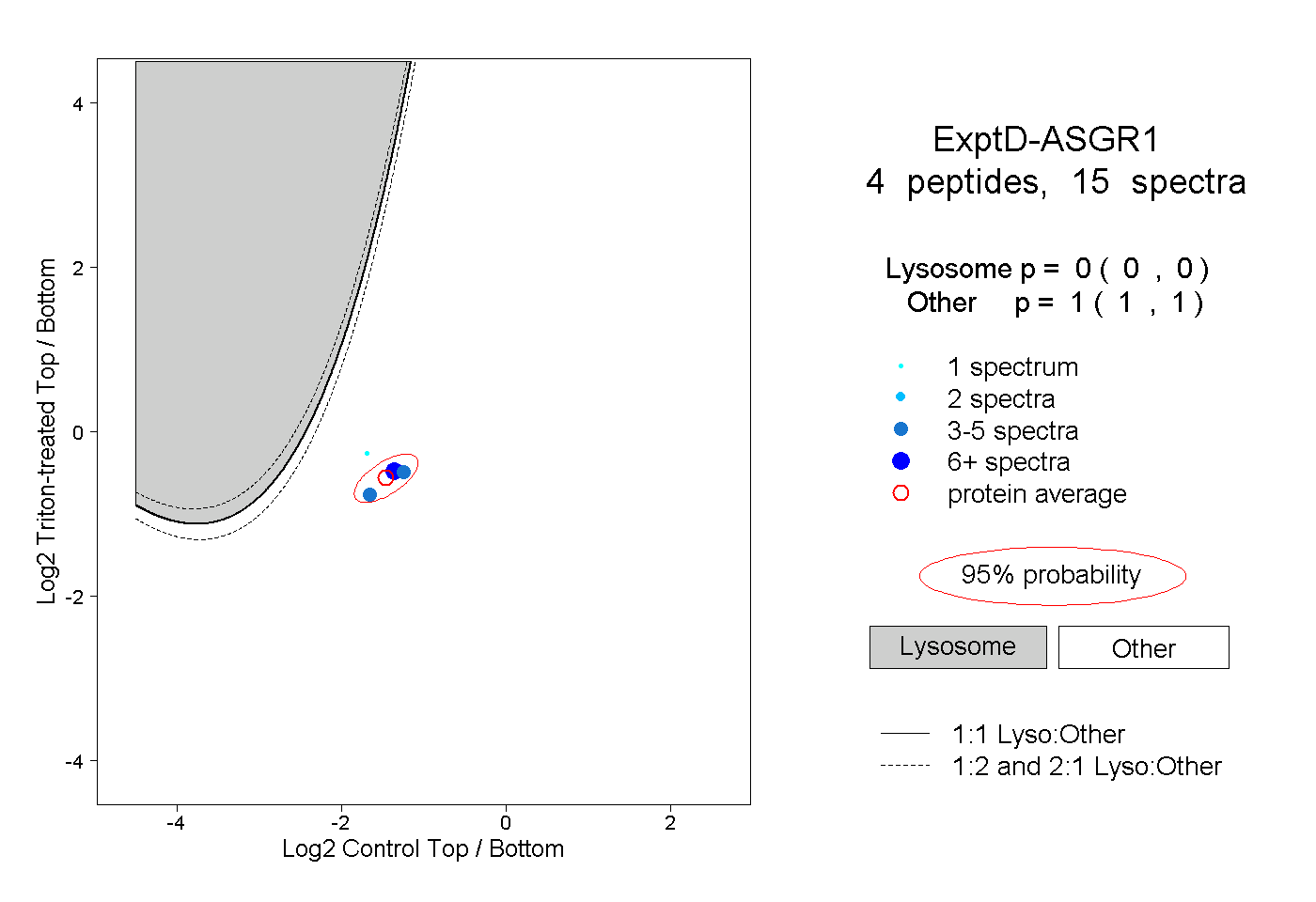 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |