peptides
spectra
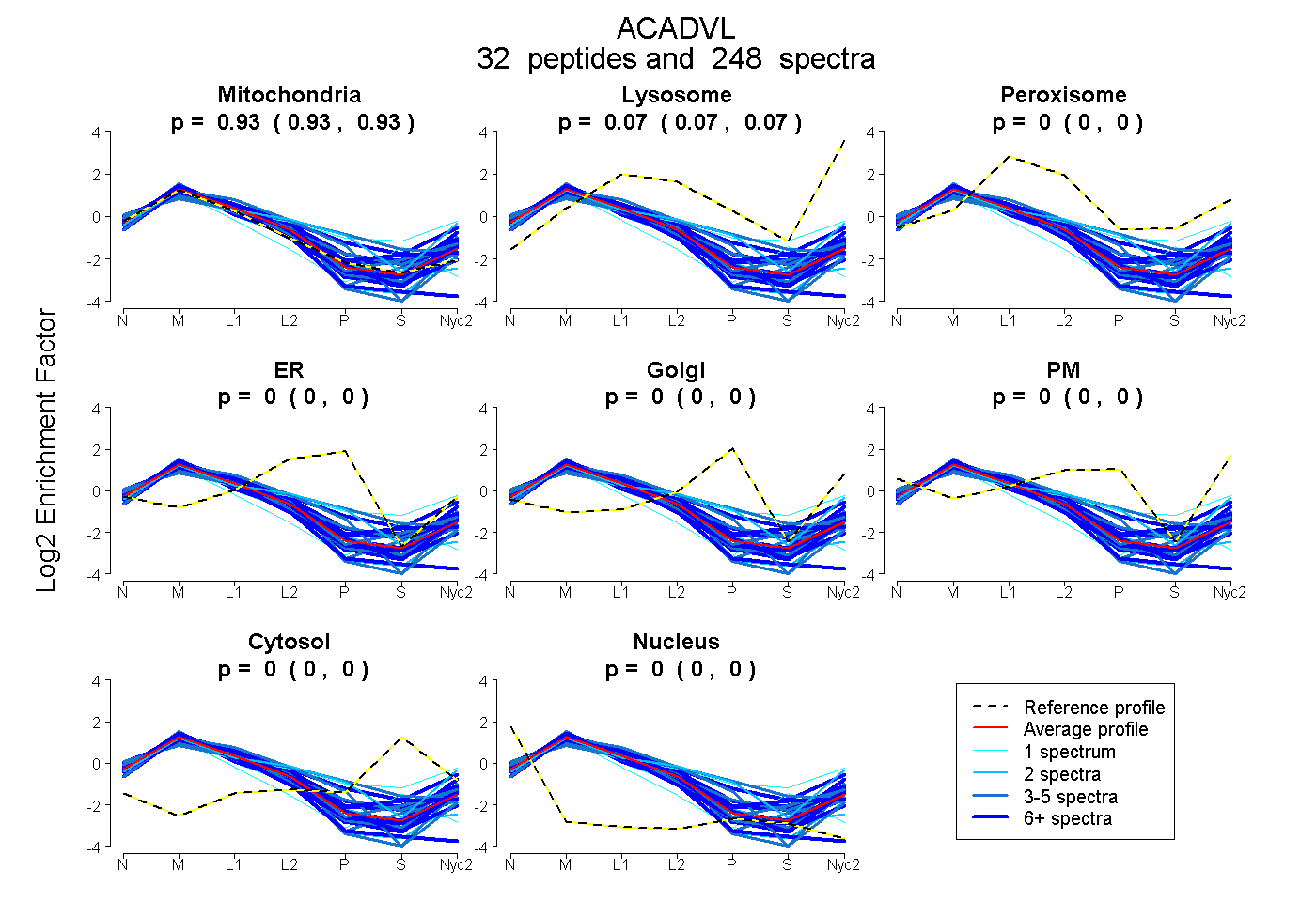
0.930 | 0.932
0.067 | 0.070
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
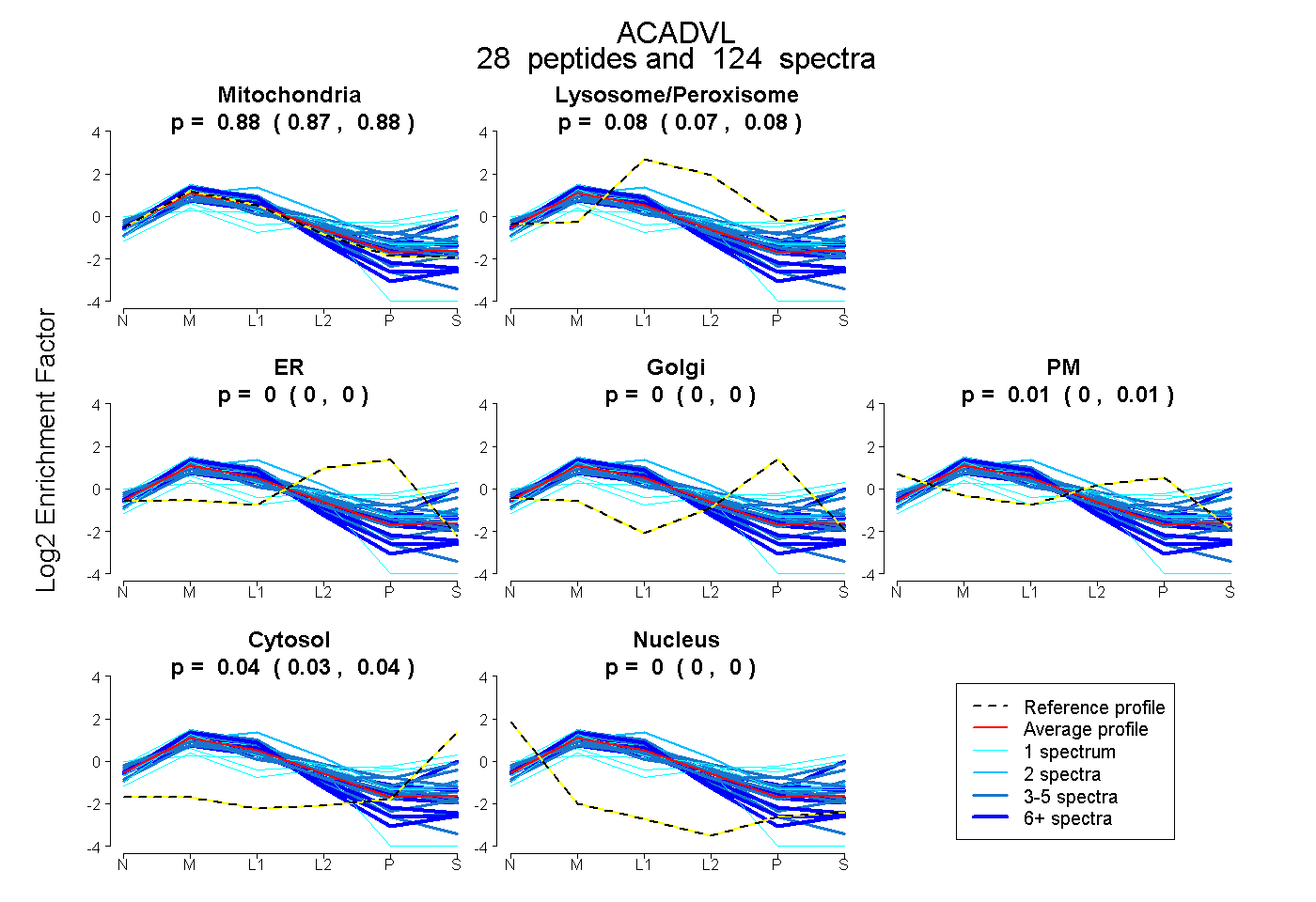
0.871 | 0.883
0.074 | 0.083
0.000 | 0.000
0.000 | 0.000
0.000 | 0.013
0.032 | 0.040
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
248 spectra |
 |
0.931 0.930 | 0.932 |
0.069 0.067 | 0.070 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
124 spectra |
 |
0.878 0.871 | 0.883 |
0.079 0.074 | 0.083 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.007 0.000 | 0.013 |
0.036 0.032 | 0.040 |
0.000 0.000 | 0.000 |
| 4 spectra, EPGVER | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VPAENVLGEVGDGFK | 0.517 | 0.235 | 0.000 | 0.000 | 0.070 | 0.178 | 0.000 | |||
| 15 spectra, ITAFVVER | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AMVENGGLVTSNPLR | 0.285 | 0.181 | 0.000 | 0.124 | 0.245 | 0.165 | 0.000 | |||
| 6 spectra, LFVALQGCMDK | 0.712 | 0.126 | 0.000 | 0.129 | 0.000 | 0.033 | 0.000 | |||
| 6 spectra, NPLGNVGLLIGEASK | 0.851 | 0.102 | 0.000 | 0.034 | 0.013 | 0.000 | 0.000 | |||
| 3 spectra, GILLYGTK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YYTLNGSK | 0.642 | 0.144 | 0.000 | 0.187 | 0.000 | 0.027 | 0.000 | |||
| 3 spectra, SFAVGMFK | 0.809 | 0.000 | 0.185 | 0.000 | 0.000 | 0.007 | 0.000 | |||
| 1 spectrum, ENMASLQSNPQQQELFR | 0.211 | 0.285 | 0.000 | 0.000 | 0.253 | 0.251 | 0.000 | |||
| 3 spectra, IHNFGVIQEK | 0.402 | 0.362 | 0.000 | 0.027 | 0.000 | 0.209 | 0.000 | |||
| 1 spectrum, SFGGVTHGLPEK | 0.670 | 0.210 | 0.000 | 0.021 | 0.044 | 0.055 | 0.000 | |||
| 2 spectra, IFGSEAAWK | 0.746 | 0.190 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | |||
| 1 spectrum, MLCDSWCIEAATR | 0.143 | 0.267 | 0.000 | 0.248 | 0.000 | 0.341 | 0.000 | |||
| 3 spectra, FFEEVNDPAK | 0.958 | 0.042 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ELTGLGNALK | 0.853 | 0.088 | 0.000 | 0.000 | 0.000 | 0.059 | 0.000 | |||
| 3 spectra, FGMAATLAGTMK | 0.843 | 0.084 | 0.016 | 0.000 | 0.000 | 0.057 | 0.000 | |||
| 16 spectra, ELVGPVAR | 0.955 | 0.045 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, IFEGTNDILR | 0.971 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.029 | |||
| 2 spectra, TGIGSGLSLSGIVHPELSR | 0.659 | 0.341 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ASNTSEVYFDGVK | 0.786 | 0.023 | 0.000 | 0.000 | 0.191 | 0.000 | 0.000 | |||
| 13 spectra, VAVNILNNGR | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | |||
| 1 spectrum, DAATGAVK | 0.999 | 0.001 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VTDECIQIMGGMGFMK | 0.744 | 0.107 | 0.095 | 0.000 | 0.000 | 0.053 | 0.000 | |||
| 3 spectra, TQFGDK | 0.872 | 0.075 | 0.000 | 0.000 | 0.053 | 0.000 | 0.000 | |||
| 5 spectra, SLSEGYPTAQHEK | 0.780 | 0.073 | 0.000 | 0.000 | 0.000 | 0.148 | 0.000 | |||
| 1 spectrum, SGELAVQALEQFATVVEAK | 0.980 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.020 | |||
| 6 spectra, GIVNEQFLLQR | 0.522 | 0.201 | 0.000 | 0.000 | 0.000 | 0.277 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
720 spectra |
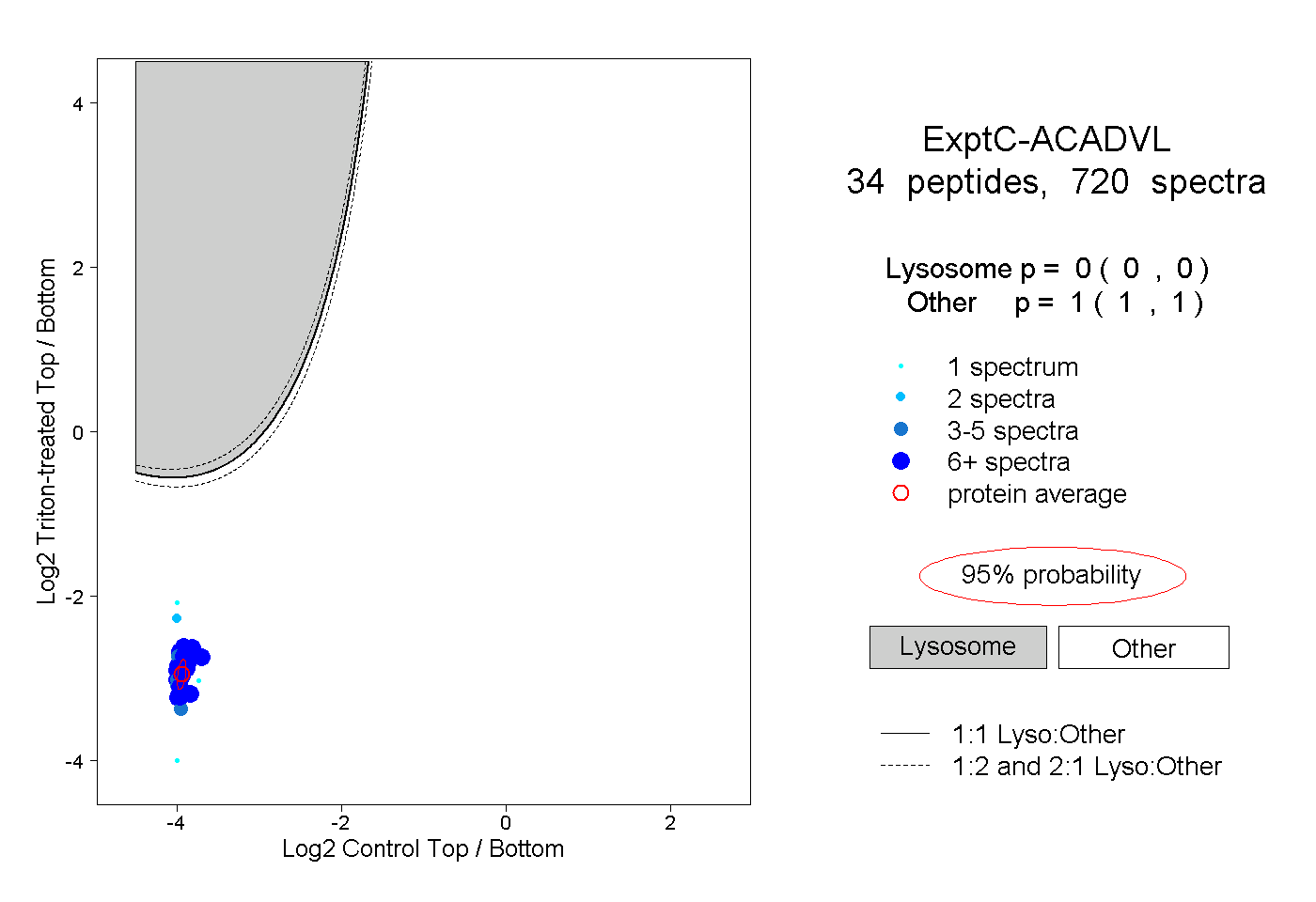 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
49 spectra |
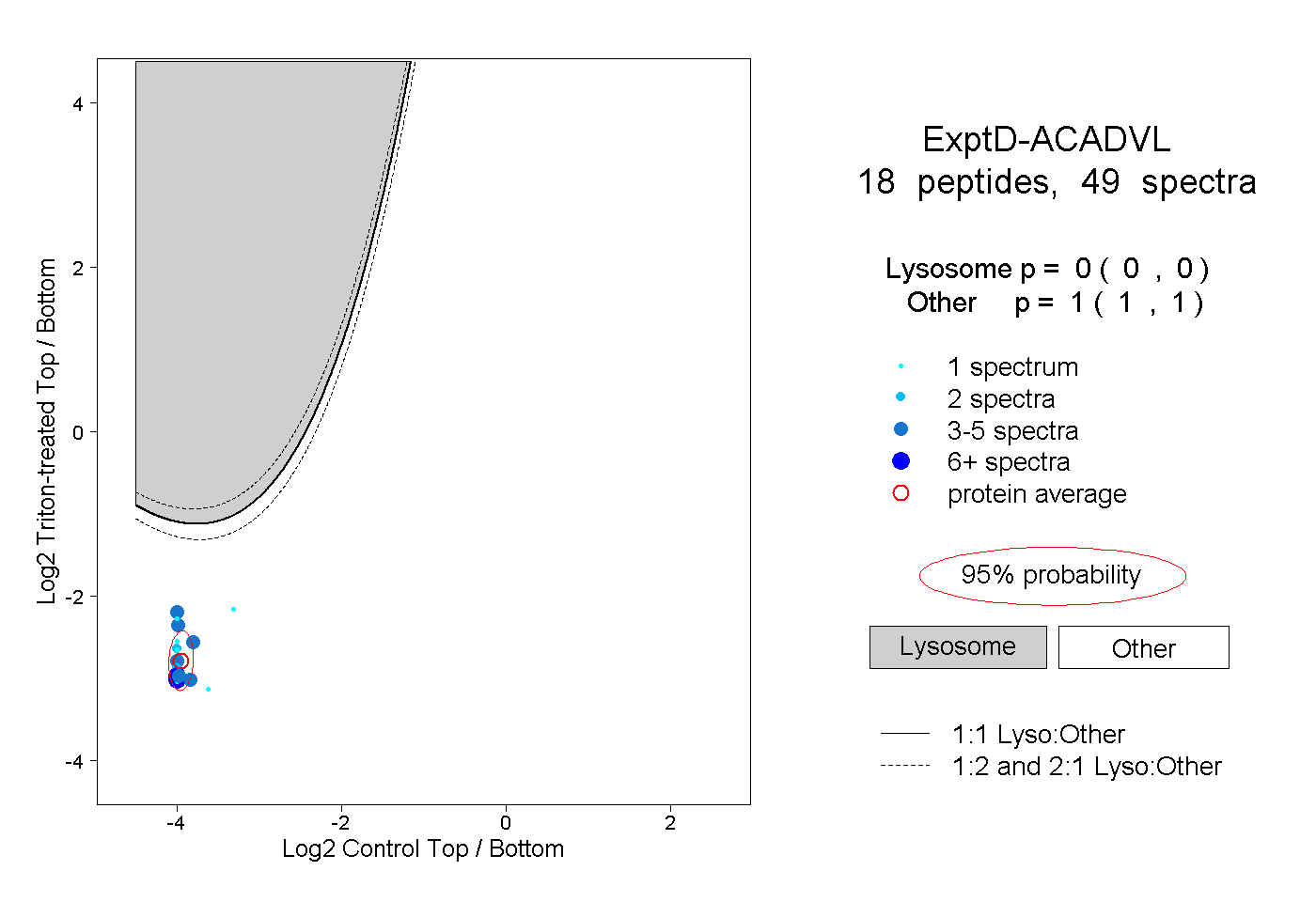 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |