peptides
spectra
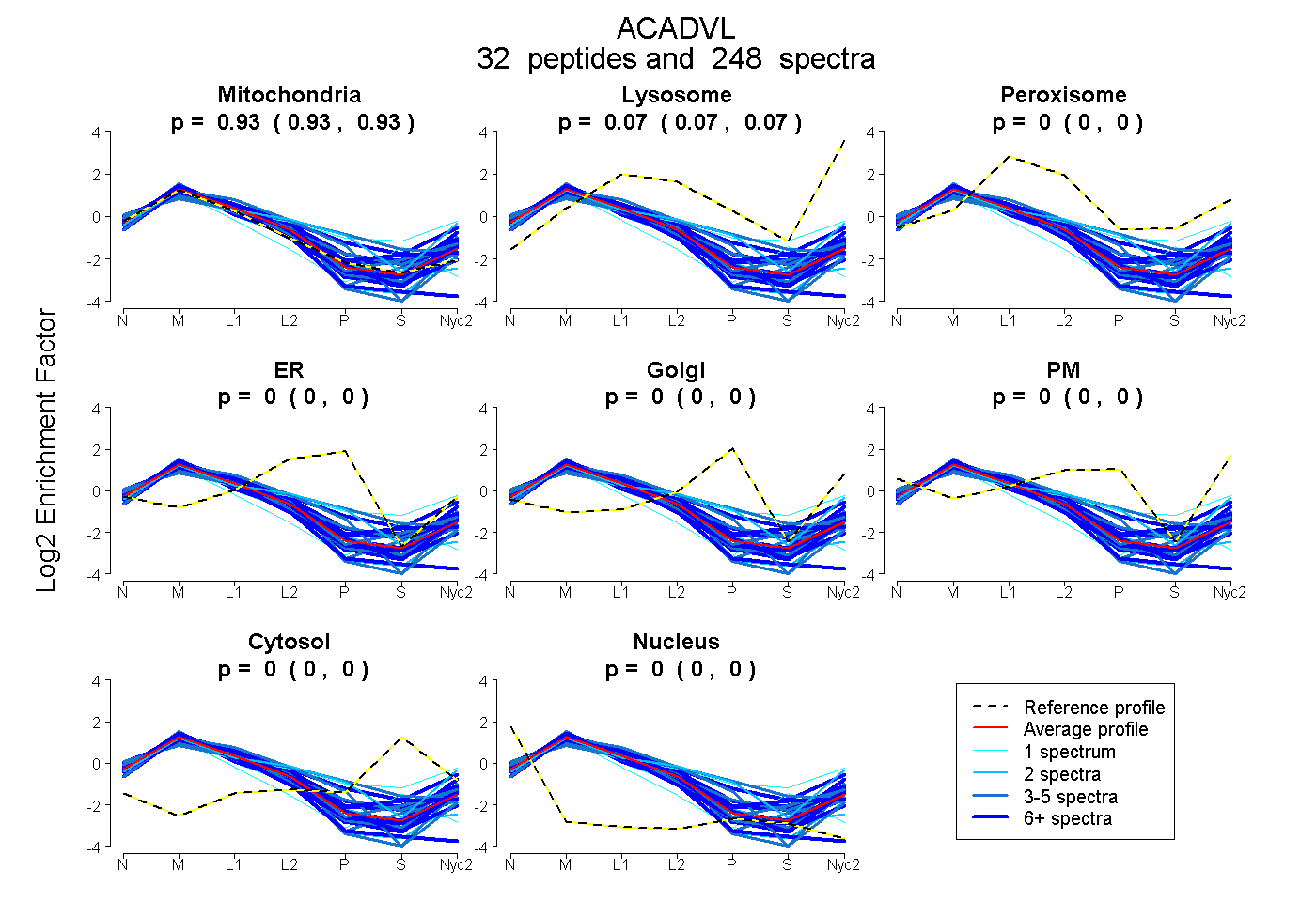
0.930 | 0.932
0.067 | 0.070
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
248 spectra |
 |
0.931 0.930 | 0.932 |
0.069 0.067 | 0.070 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, VPAENVLGEVGDGFK | 0.783 | 0.010 | 0.139 | 0.000 | 0.000 | 0.000 | 0.043 | 0.024 | ||
| 10 spectra, ITAFVVER | 0.952 | 0.048 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, AMVENGGLVTSNPLR | 0.919 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, LFVALQGCMDK | 0.809 | 0.031 | 0.103 | 0.032 | 0.000 | 0.010 | 0.014 | 0.000 | ||
| 11 spectra, NPLGNVGLLIGEASK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, GILLYGTK | 0.996 | 0.000 | 0.004 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, ENMASLQSNPQQQELFR | 0.892 | 0.108 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, SFGGVTHGLPEK | 0.487 | 0.086 | 0.095 | 0.000 | 0.000 | 0.194 | 0.137 | 0.000 | ||
| 6 spectra, MLCDSWCIEAATR | 0.949 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.051 | ||
| 5 spectra, FFEEVNDPAK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, ELTGLGNALK | 0.955 | 0.045 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, FGMAATLAGTMK | 0.817 | 0.160 | 0.006 | 0.000 | 0.000 | 0.000 | 0.017 | 0.000 | ||
| 18 spectra, ELVGPVAR | 0.835 | 0.075 | 0.056 | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | ||
| 3 spectra, TGIGSGLSLSGIVHPELSR | 0.817 | 0.000 | 0.000 | 0.183 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, ASNTSEVYFDGVK | 0.919 | 0.000 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DAATGAVK | 0.983 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.017 | ||
| 16 spectra, VTDECIQIMGGMGFMK | 0.806 | 0.000 | 0.136 | 0.000 | 0.000 | 0.000 | 0.057 | 0.000 | ||
| 10 spectra, VEEDTLQGLK | 0.954 | 0.046 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, SGELAVQALEQFATVVEAK | 0.622 | 0.000 | 0.117 | 0.183 | 0.000 | 0.000 | 0.079 | 0.000 | ||
| 11 spectra, GIVNEQFLLQR | 0.969 | 0.000 | 0.031 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, EPGVER | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YYTLNGSK | 0.629 | 0.155 | 0.000 | 0.003 | 0.041 | 0.172 | 0.000 | 0.000 | ||
| 22 spectra, SFAVGMFK | 0.928 | 0.072 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, AVDHATNR | 0.604 | 0.064 | 0.139 | 0.000 | 0.000 | 0.162 | 0.031 | 0.000 | ||
| 4 spectra, IHNFGVIQEK | 0.960 | 0.000 | 0.038 | 0.000 | 0.000 | 0.000 | 0.001 | 0.000 | ||
| 9 spectra, IFGSEAAWK | 0.864 | 0.136 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, IFEGTNDILR | 0.968 | 0.032 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, DFQIEAAISK | 0.836 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.071 | 0.094 | ||
| 17 spectra, VAVNILNNGR | 0.933 | 0.055 | 0.000 | 0.000 | 0.000 | 0.012 | 0.000 | 0.000 | ||
| 5 spectra, SSAVPSPCGK | 0.988 | 0.012 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, TQFGDK | 0.843 | 0.092 | 0.000 | 0.000 | 0.000 | 0.046 | 0.019 | 0.000 | ||
| 12 spectra, SLSEGYPTAQHEK | 0.825 | 0.085 | 0.069 | 0.000 | 0.000 | 0.000 | 0.020 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
124 spectra |
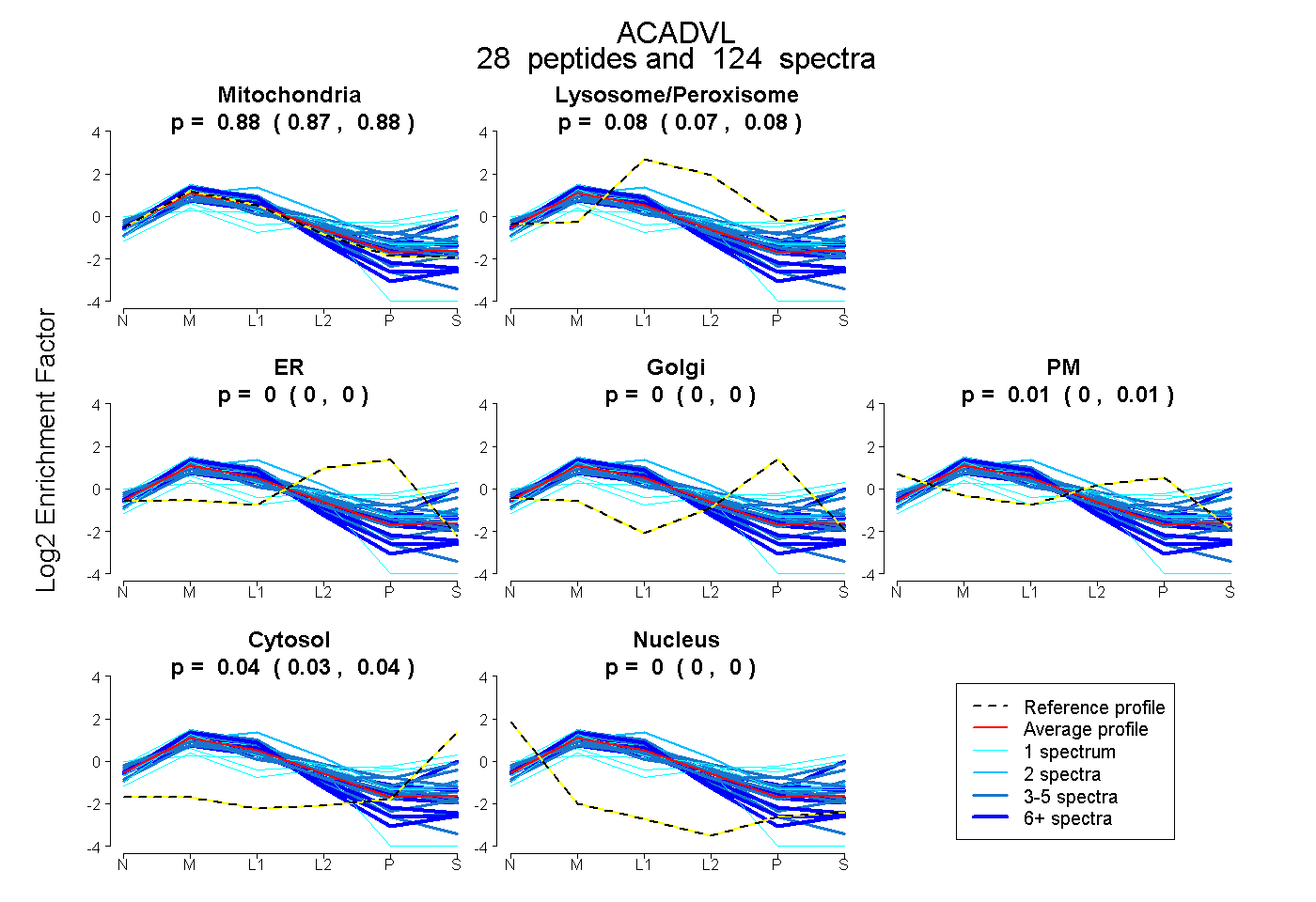 |
0.878 0.871 | 0.883 |
0.079 0.074 | 0.083 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.007 0.000 | 0.013 |
0.036 0.032 | 0.040 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
720 spectra |
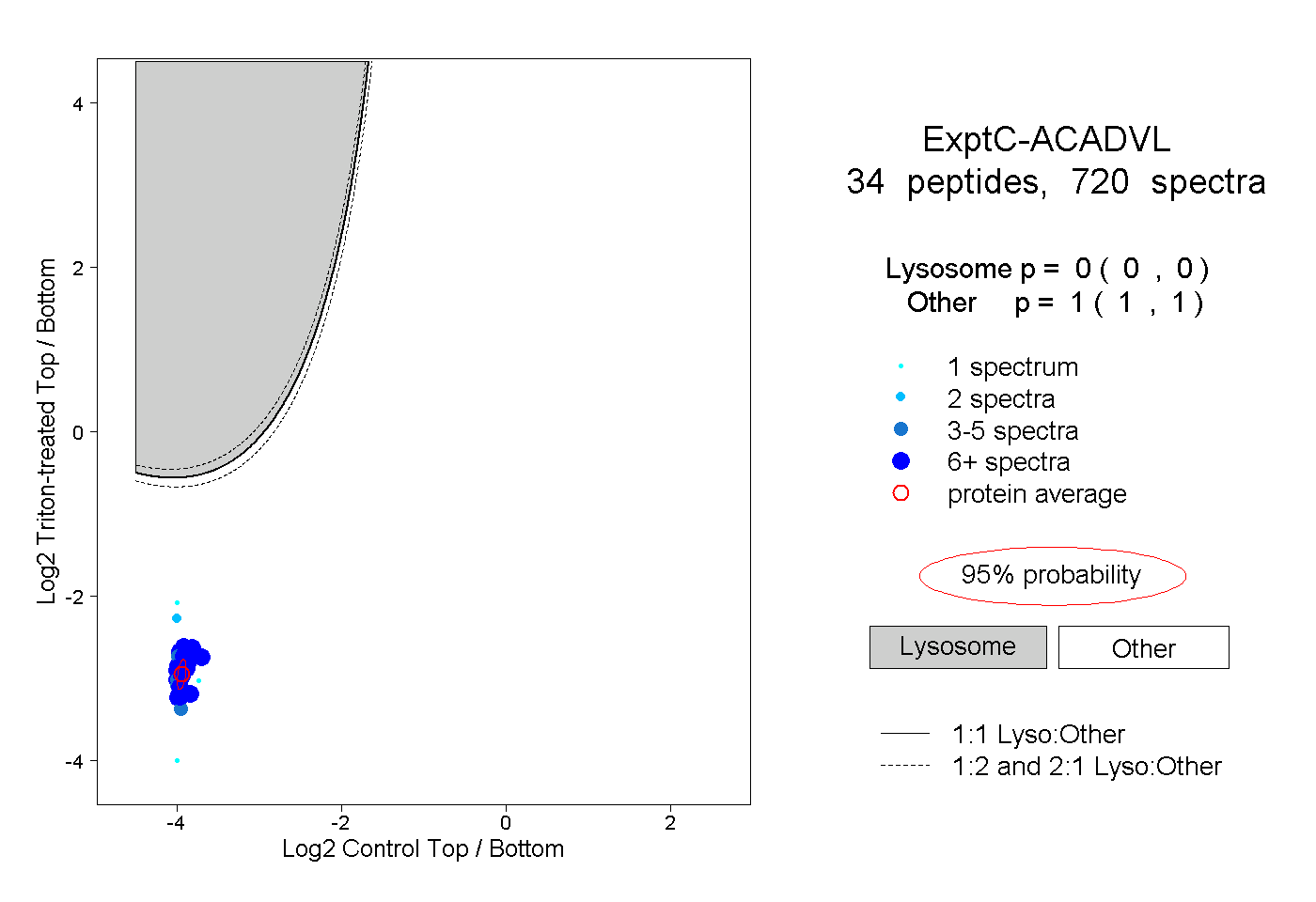 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
49 spectra |
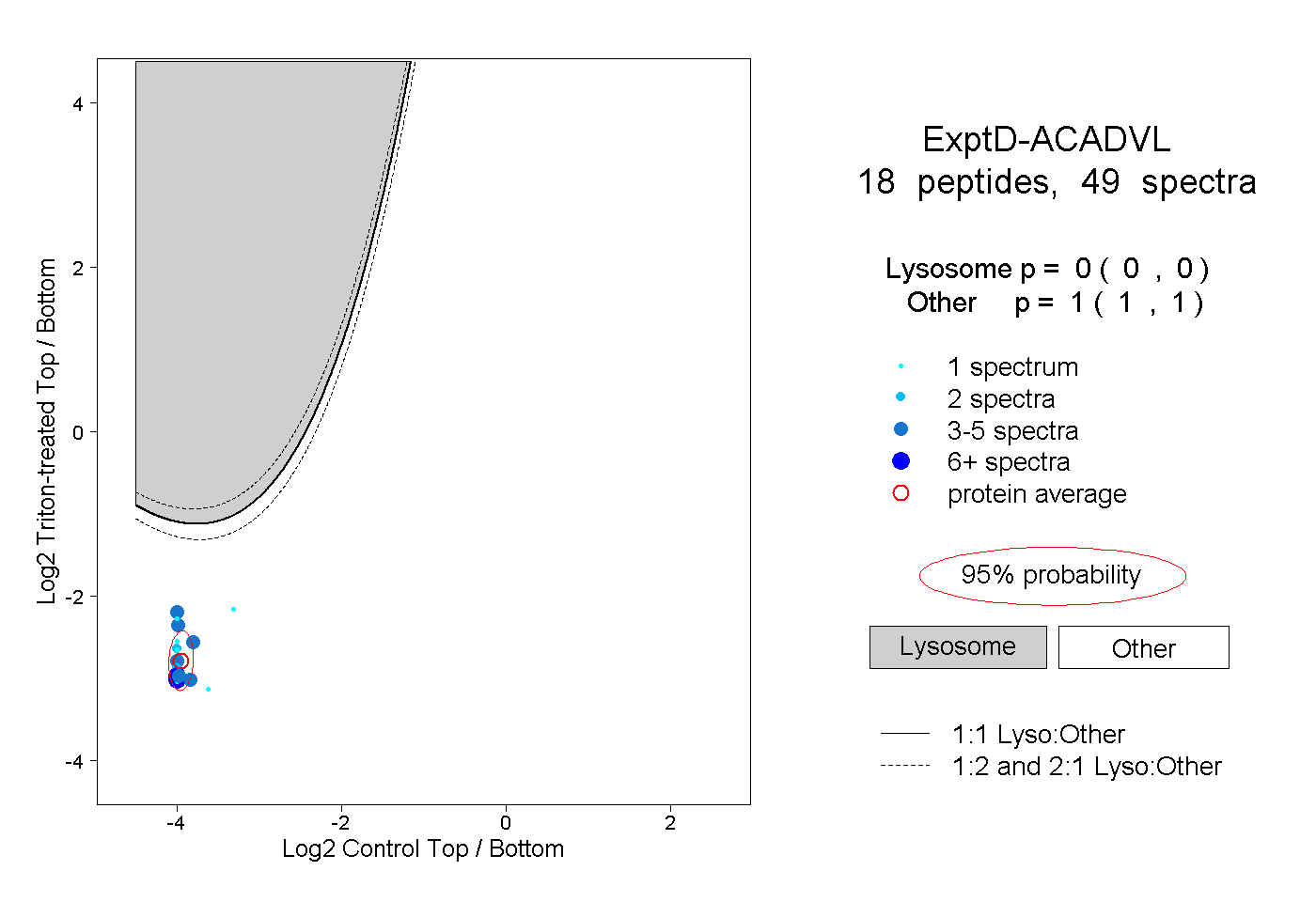 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |