peptides
spectra
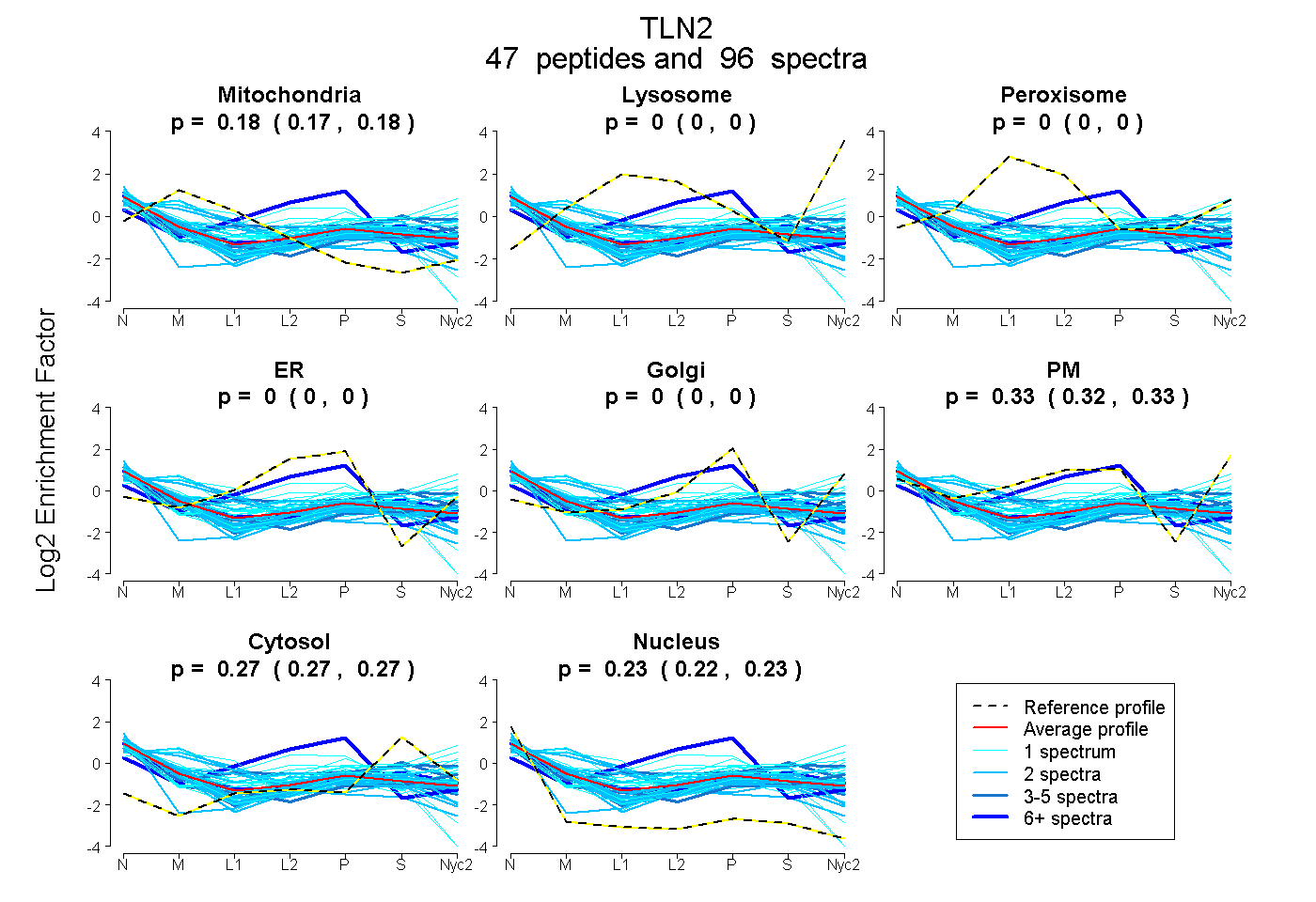
0.175 | 0.182
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.322 | 0.328
0.265 | 0.271
0.225 | 0.230
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
96 spectra |
 |
0.179 0.175 | 0.182 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.325 0.322 | 0.328 |
0.268 0.265 | 0.271 |
0.227 0.225 | 0.230 |
| 1 spectrum, AVANAAAMLVLK | 0.105 | 0.000 | 0.048 | 0.094 | 0.000 | 0.521 | 0.175 | 0.055 | ||
| 2 spectra, TVADHIPQLVQGVR | 0.198 | 0.000 | 0.000 | 0.000 | 0.000 | 0.417 | 0.311 | 0.074 | ||
| 1 spectrum, QELTVFQSK | 0.467 | 0.000 | 0.000 | 0.000 | 0.128 | 0.206 | 0.176 | 0.023 | ||
| 7 spectra, GQSGELAAASGK | 0.152 | 0.000 | 0.000 | 0.000 | 0.000 | 0.291 | 0.347 | 0.210 | ||
| 2 spectra, VATNAAAQNAIK | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | 0.346 | 0.277 | 0.271 | ||
| 2 spectra, TLAQAAR | 0.195 | 0.000 | 0.000 | 0.000 | 0.000 | 0.297 | 0.191 | 0.317 | ||
| 1 spectrum, GTFVDYQTTVVK | 0.566 | 0.000 | 0.000 | 0.000 | 0.077 | 0.126 | 0.218 | 0.012 | ||
| 1 spectrum, VWVQNK | 0.124 | 0.000 | 0.000 | 0.000 | 0.000 | 0.313 | 0.282 | 0.281 | ||
| 1 spectrum, SDAEAEIDMENSK | 0.096 | 0.000 | 0.000 | 0.000 | 0.000 | 0.350 | 0.370 | 0.183 | ||
| 1 spectrum, ACEFGGFQAQIQFGPHVEHK | 0.288 | 0.000 | 0.000 | 0.201 | 0.000 | 0.000 | 0.089 | 0.421 | ||
| 2 spectra, AVEDEATR | 0.083 | 0.000 | 0.000 | 0.000 | 0.000 | 0.367 | 0.188 | 0.362 | ||
| 1 spectrum, NGDILEYK | 0.006 | 0.000 | 0.000 | 0.000 | 0.000 | 0.472 | 0.240 | 0.282 | ||
| 1 spectrum, TLAESALQMLYAAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.527 | 0.452 | 0.021 | ||
| 1 spectrum, HTSALCNACR | 0.183 | 0.000 | 0.000 | 0.002 | 0.214 | 0.234 | 0.259 | 0.109 | ||
| 3 spectra, TLAGAVSDLLK | 0.198 | 0.000 | 0.000 | 0.000 | 0.000 | 0.303 | 0.233 | 0.265 | ||
| 2 spectra, QALIAPGDTESQQR | 0.143 | 0.000 | 0.000 | 0.000 | 0.000 | 0.342 | 0.286 | 0.229 | ||
| 14 spectra, ETAQAIK | 0.000 | 0.000 | 0.069 | 0.704 | 0.000 | 0.000 | 0.092 | 0.135 | ||
| 1 spectrum, SVENCVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.506 | 0.400 | 0.093 | ||
| 1 spectrum, EVLQEWPLTTVK | 0.142 | 0.000 | 0.000 | 0.000 | 0.000 | 0.429 | 0.175 | 0.253 | ||
| 3 spectra, NVAQVAEDTVLQNR | 0.000 | 0.000 | 0.183 | 0.000 | 0.000 | 0.315 | 0.357 | 0.145 | ||
| 1 spectrum, AAVPTVSDQAAAMQLSQCAK | 0.184 | 0.000 | 0.052 | 0.221 | 0.000 | 0.072 | 0.199 | 0.272 | ||
| 4 spectra, AVQPTSGEPR | 0.116 | 0.000 | 0.000 | 0.000 | 0.033 | 0.303 | 0.236 | 0.312 | ||
| 1 spectrum, LLAALMDDDVGSGEDLLR | 0.014 | 0.036 | 0.000 | 0.000 | 0.000 | 0.409 | 0.264 | 0.277 | ||
| 2 spectra, LLADSTAR | 0.149 | 0.000 | 0.000 | 0.000 | 0.000 | 0.340 | 0.213 | 0.297 | ||
| 2 spectra, DVMEGSAMLIQEAK | 0.733 | 0.000 | 0.000 | 0.036 | 0.000 | 0.000 | 0.104 | 0.127 | ||
| 1 spectrum, EGGGNPK | 0.133 | 0.000 | 0.000 | 0.000 | 0.017 | 0.318 | 0.246 | 0.285 | ||
| 4 spectra, GVAASTNDPEAAHAMLDSAR | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.250 | 0.489 | 0.195 | ||
| 2 spectra, DIEQASLAAVSQSLATR | 0.153 | 0.000 | 0.000 | 0.000 | 0.000 | 0.205 | 0.317 | 0.326 | ||
| 2 spectra, SLAINPK | 0.438 | 0.000 | 0.000 | 0.000 | 0.000 | 0.307 | 0.216 | 0.039 | ||
| 1 spectrum, HKPGFLDLK | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.385 | 0.220 | 0.383 | ||
| 2 spectra, VVSPTISSPVCQEQLIEAGK | 0.325 | 0.000 | 0.000 | 0.073 | 0.000 | 0.119 | 0.188 | 0.295 | ||
| 1 spectrum, TMQFEPSTAVYDACR | 0.082 | 0.000 | 0.000 | 0.252 | 0.000 | 0.000 | 0.206 | 0.459 | ||
| 2 spectra, AGALQVCPTDSYTK | 0.596 | 0.000 | 0.098 | 0.000 | 0.000 | 0.007 | 0.196 | 0.103 | ||
| 2 spectra, NLATSLAELR | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | 0.323 | 0.260 | 0.313 | ||
| 2 spectra, SLSVDPGAPNAK | 0.308 | 0.000 | 0.078 | 0.137 | 0.000 | 0.000 | 0.337 | 0.140 | ||
| 1 spectrum, NLLAAAAR | 0.069 | 0.000 | 0.156 | 0.132 | 0.000 | 0.222 | 0.246 | 0.175 | ||
| 1 spectrum, TVMVDDSK | 0.200 | 0.000 | 0.000 | 0.000 | 0.000 | 0.405 | 0.328 | 0.067 | ||
| 2 spectra, LIAAAK | 0.067 | 0.000 | 0.000 | 0.000 | 0.001 | 0.372 | 0.206 | 0.354 | ||
| 2 spectra, TMLESSSYLIR | 0.199 | 0.000 | 0.000 | 0.000 | 0.044 | 0.224 | 0.293 | 0.241 | ||
| 1 spectrum, SVENQMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.446 | 0.444 | 0.110 | ||
| 1 spectrum, LHTDDDLNWLDHSR | 0.155 | 0.000 | 0.000 | 0.278 | 0.000 | 0.000 | 0.155 | 0.412 | ||
| 1 spectrum, IFQEHK | 0.095 | 0.000 | 0.000 | 0.000 | 0.000 | 0.375 | 0.155 | 0.375 | ||
| 3 spectra, ALDGDFSEDNR | 0.155 | 0.000 | 0.000 | 0.000 | 0.056 | 0.210 | 0.234 | 0.345 | ||
| 2 spectra, STILQQQFNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | 0.258 | 0.245 | 0.383 | ||
| 2 spectra, QIGENETDER | 0.102 | 0.000 | 0.000 | 0.000 | 0.048 | 0.251 | 0.242 | 0.357 | ||
| 2 spectra, TSSPEESIR | 0.240 | 0.000 | 0.000 | 0.000 | 0.099 | 0.145 | 0.323 | 0.193 | ||
| 1 spectrum, FQDVLMSLAK | 0.287 | 0.000 | 0.000 | 0.000 | 0.000 | 0.288 | 0.271 | 0.155 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
9 spectra |
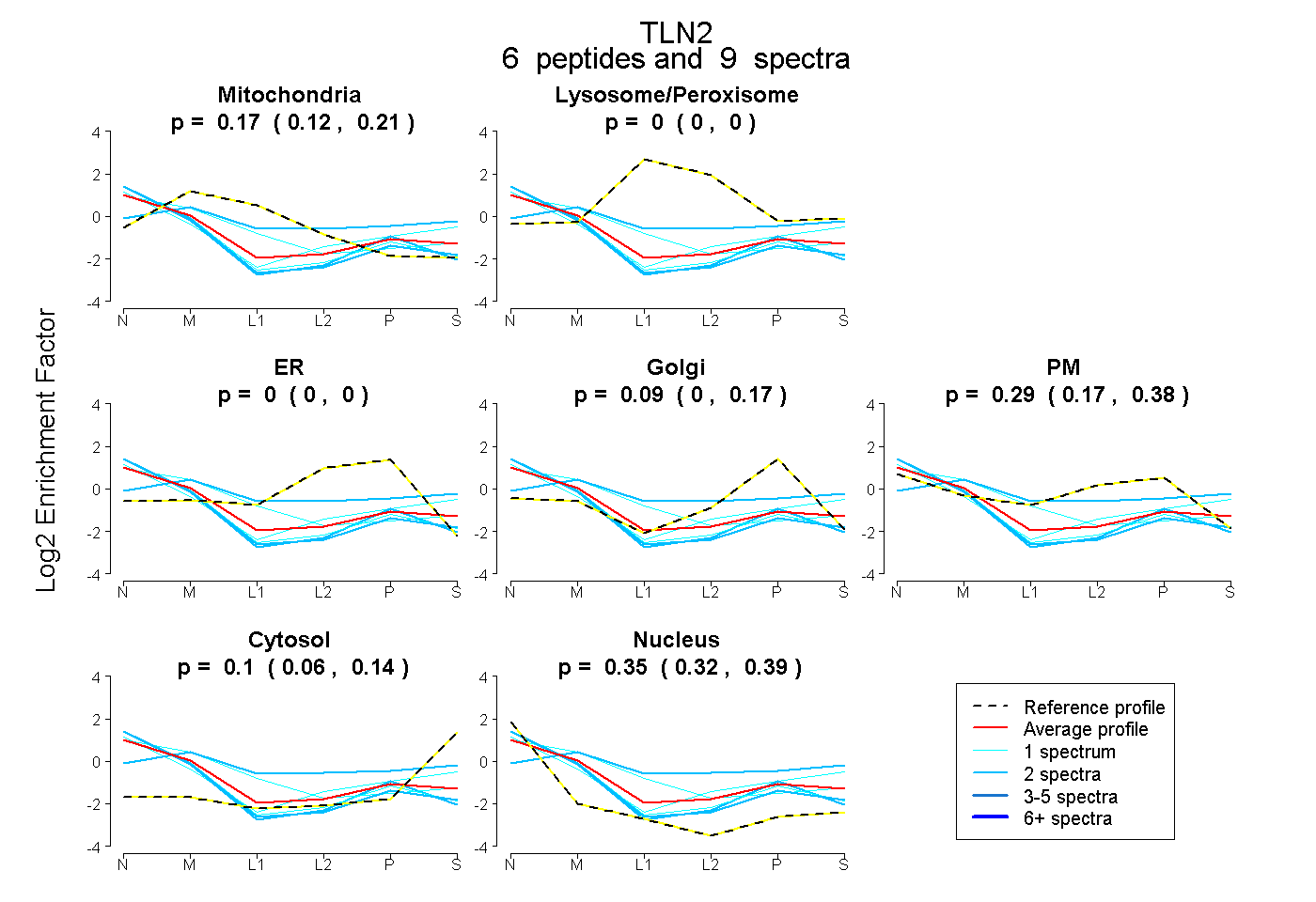 |
0.170 0.117 | 0.213 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.086 0.000 | 0.168 |
0.287 0.172 | 0.383 |
0.101 0.057 | 0.141 |
0.355 0.319 | 0.389 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
70 spectra |
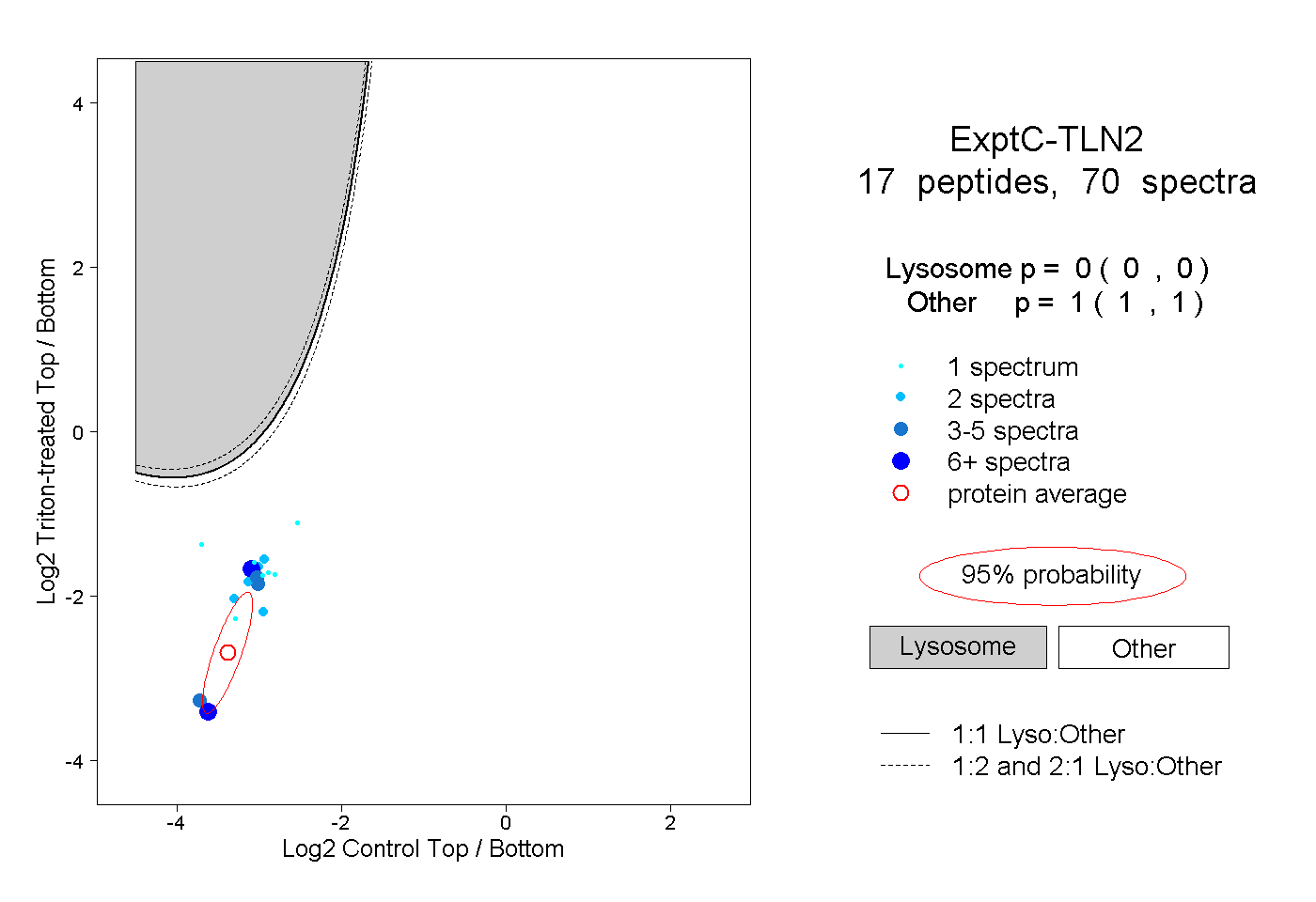 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
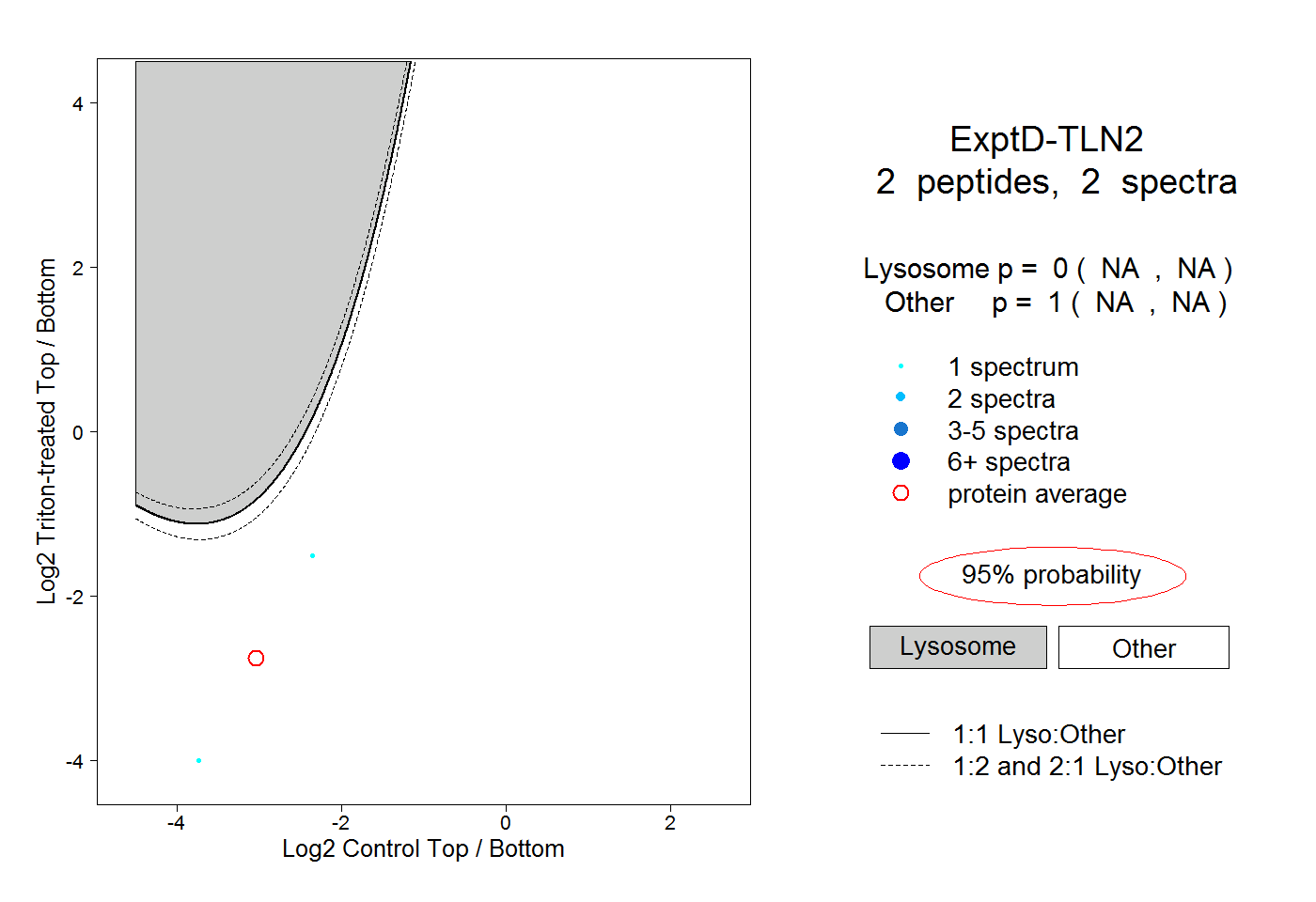 |
0.000 NA | NA |
1.000 NA | NA |