peptides
spectra
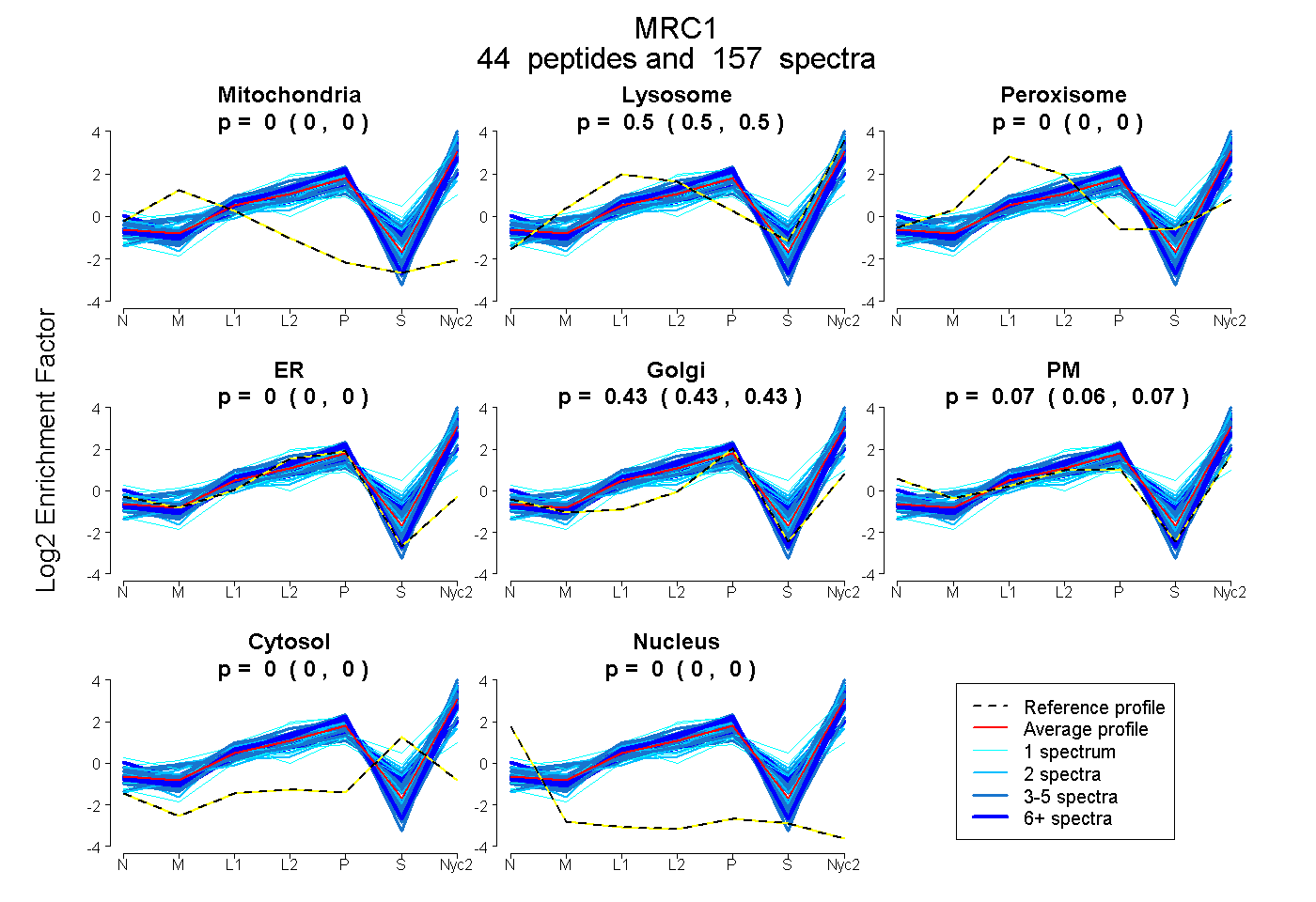
0.000 | 0.000
0.498 | 0.504
0.000 | 0.000
0.000 | 0.000
0.426 | 0.433
0.063 | 0.074
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
157 spectra |
 |
0.000 0.000 | 0.000 |
0.501 0.498 | 0.504 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.430 0.426 | 0.433 |
0.069 0.063 | 0.074 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, NFGDLATIK | 0.000 | 0.509 | 0.000 | 0.000 | 0.491 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, AGCVAMK | 0.000 | 0.509 | 0.000 | 0.000 | 0.465 | 0.000 | 0.026 | 0.000 | ||
| 1 spectrum, TGVAGGLWDVLSCEEK | 0.000 | 0.662 | 0.000 | 0.000 | 0.329 | 0.009 | 0.000 | 0.000 | ||
| 2 spectra, TWFESR | 0.000 | 0.655 | 0.000 | 0.000 | 0.314 | 0.031 | 0.000 | 0.000 | ||
| 3 spectra, QEDCVVMK | 0.000 | 0.535 | 0.000 | 0.000 | 0.418 | 0.047 | 0.000 | 0.000 | ||
| 2 spectra, ACEQPLGYICK | 0.000 | 0.312 | 0.000 | 0.337 | 0.352 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, TGDPSGER | 0.000 | 0.632 | 0.000 | 0.000 | 0.366 | 0.002 | 0.000 | 0.000 | ||
| 1 spectrum, QFLIYNEDHK | 0.000 | 0.555 | 0.000 | 0.000 | 0.291 | 0.000 | 0.154 | 0.000 | ||
| 2 spectra, DEQQVIWR | 0.000 | 0.397 | 0.000 | 0.000 | 0.285 | 0.318 | 0.000 | 0.000 | ||
| 4 spectra, TNFWIGMFR | 0.000 | 0.530 | 0.000 | 0.000 | 0.133 | 0.338 | 0.000 | 0.000 | ||
| 1 spectrum, YFWTGLSDVQNK | 0.000 | 0.555 | 0.000 | 0.000 | 0.182 | 0.000 | 0.263 | 0.000 | ||
| 8 spectra, DGYWADR | 0.000 | 0.524 | 0.000 | 0.000 | 0.329 | 0.148 | 0.000 | 0.000 | ||
| 2 spectra, WLPGEPSHENNR | 0.000 | 0.408 | 0.000 | 0.000 | 0.259 | 0.229 | 0.104 | 0.000 | ||
| 2 spectra, AIGGELASIK | 0.000 | 0.309 | 0.000 | 0.000 | 0.378 | 0.313 | 0.000 | 0.000 | ||
| 2 spectra, EQAFVTYHMR | 0.000 | 0.528 | 0.000 | 0.000 | 0.331 | 0.000 | 0.142 | 0.000 | ||
| 2 spectra, WVSESQIMSVAFK | 0.000 | 0.578 | 0.000 | 0.000 | 0.422 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, SWGQASLECLR | 0.000 | 0.261 | 0.000 | 0.147 | 0.247 | 0.345 | 0.000 | 0.000 | ||
| 3 spectra, FIWMDGSK | 0.000 | 0.513 | 0.000 | 0.000 | 0.377 | 0.110 | 0.000 | 0.000 | ||
| 4 spectra, EGWHLYNNK | 0.000 | 0.446 | 0.000 | 0.000 | 0.106 | 0.313 | 0.135 | 0.000 | ||
| 2 spectra, AYLTTVEDR | 0.000 | 0.572 | 0.000 | 0.000 | 0.301 | 0.000 | 0.127 | 0.000 | ||
| 6 spectra, WYADCTSAGR | 0.000 | 0.432 | 0.000 | 0.000 | 0.424 | 0.144 | 0.000 | 0.000 | ||
| 4 spectra, WTVDEQVQFTHWNADMPGR | 0.000 | 0.672 | 0.000 | 0.000 | 0.328 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, GSGLWSR | 0.000 | 0.552 | 0.000 | 0.000 | 0.305 | 0.143 | 0.000 | 0.000 | ||
| 5 spectra, EAGTWMDSTCDSK | 0.000 | 0.560 | 0.000 | 0.000 | 0.423 | 0.017 | 0.000 | 0.000 | ||
| 4 spectra, SCVSLNPGK | 0.000 | 0.460 | 0.000 | 0.000 | 0.366 | 0.174 | 0.000 | 0.000 | ||
| 2 spectra, GYPGGR | 0.000 | 0.523 | 0.000 | 0.000 | 0.440 | 0.037 | 0.000 | 0.000 | ||
| 3 spectra, VYGTTDDLCSR | 0.000 | 0.340 | 0.000 | 0.000 | 0.307 | 0.353 | 0.000 | 0.000 | ||
| 1 spectrum, LFGFCPLQFEGSK | 0.000 | 0.626 | 0.000 | 0.000 | 0.374 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, IQMYFEWSDGTPVTFTK | 0.000 | 0.484 | 0.000 | 0.000 | 0.244 | 0.247 | 0.024 | 0.000 | ||
| 5 spectra, YTNWGTDEPK | 0.000 | 0.515 | 0.000 | 0.000 | 0.364 | 0.099 | 0.022 | 0.000 | ||
| 1 spectrum, SSYALMK | 0.000 | 0.243 | 0.000 | 0.000 | 0.000 | 0.583 | 0.174 | 0.000 | ||
| 5 spectra, IFGFAEEEK | 0.000 | 0.619 | 0.000 | 0.000 | 0.327 | 0.054 | 0.000 | 0.000 | ||
| 1 spectrum, DLVGNIEQNEHAVI | 0.000 | 0.082 | 0.316 | 0.019 | 0.539 | 0.000 | 0.044 | 0.000 | ||
| 7 spectra, CPEDWGTTSK | 0.000 | 0.506 | 0.000 | 0.000 | 0.429 | 0.000 | 0.065 | 0.000 | ||
| 1 spectrum, GNLVSIENAK | 0.000 | 0.525 | 0.000 | 0.000 | 0.321 | 0.154 | 0.000 | 0.000 | ||
| 1 spectrum, TSMCFK | 0.000 | 0.521 | 0.000 | 0.000 | 0.479 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, ETMDNAR | 0.000 | 0.587 | 0.000 | 0.000 | 0.413 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LGYICK | 0.000 | 0.502 | 0.000 | 0.000 | 0.465 | 0.033 | 0.000 | 0.000 | ||
| 5 spectra, WENLECVQK | 0.000 | 0.321 | 0.000 | 0.000 | 0.277 | 0.401 | 0.000 | 0.000 | ||
| 11 spectra, YALQACR | 0.000 | 0.362 | 0.000 | 0.037 | 0.393 | 0.208 | 0.000 | 0.000 | ||
| 3 spectra, DYQYYFSK | 0.000 | 0.497 | 0.000 | 0.000 | 0.336 | 0.167 | 0.000 | 0.000 | ||
| 9 spectra, SALTWHQAR | 0.000 | 0.265 | 0.000 | 0.000 | 0.229 | 0.386 | 0.120 | 0.000 | ||
| 2 spectra, LCLGVPSK | 0.000 | 0.374 | 0.000 | 0.015 | 0.335 | 0.276 | 0.000 | 0.000 | ||
| 2 spectra, TDWASVTLYACDSK | 0.000 | 0.337 | 0.000 | 0.248 | 0.404 | 0.000 | 0.011 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
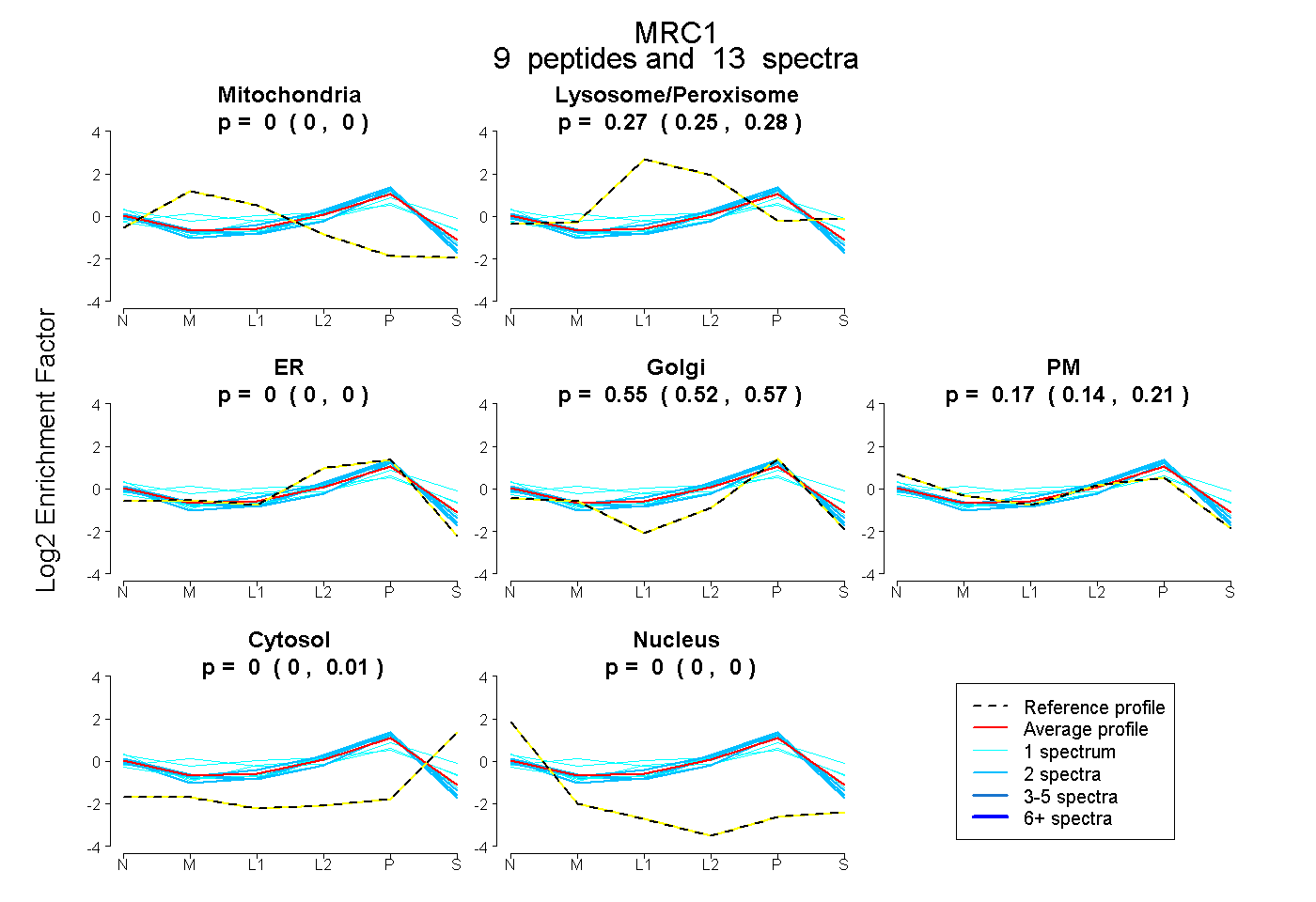 |
0.000 0.000 | 0.000 |
0.271 0.251 | 0.284 |
0.000 0.000 | 0.000 |
0.554 0.520 | 0.572 |
0.173 0.141 | 0.207 |
0.002 0.000 | 0.015 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
236 spectra |
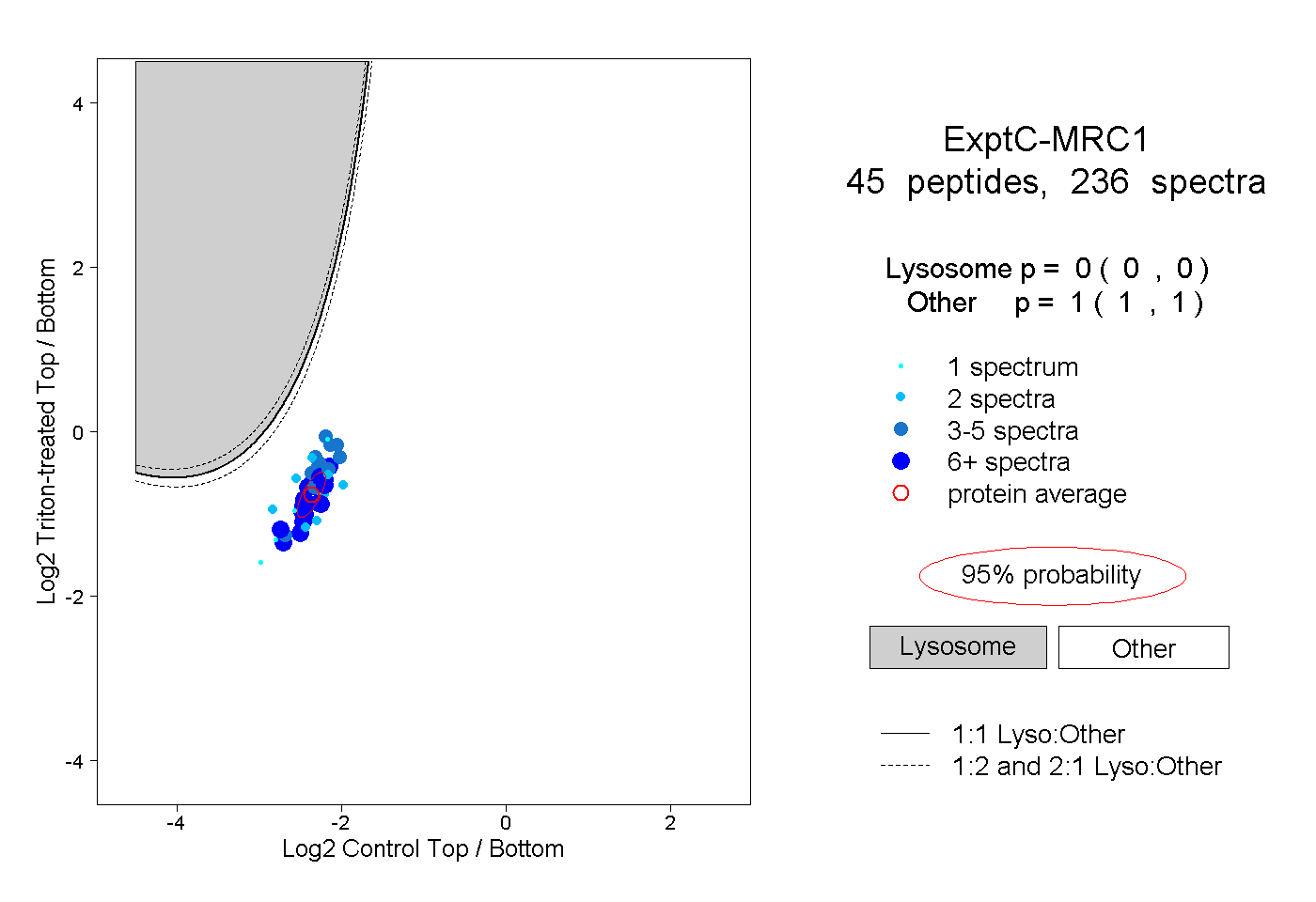 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
37 spectra |
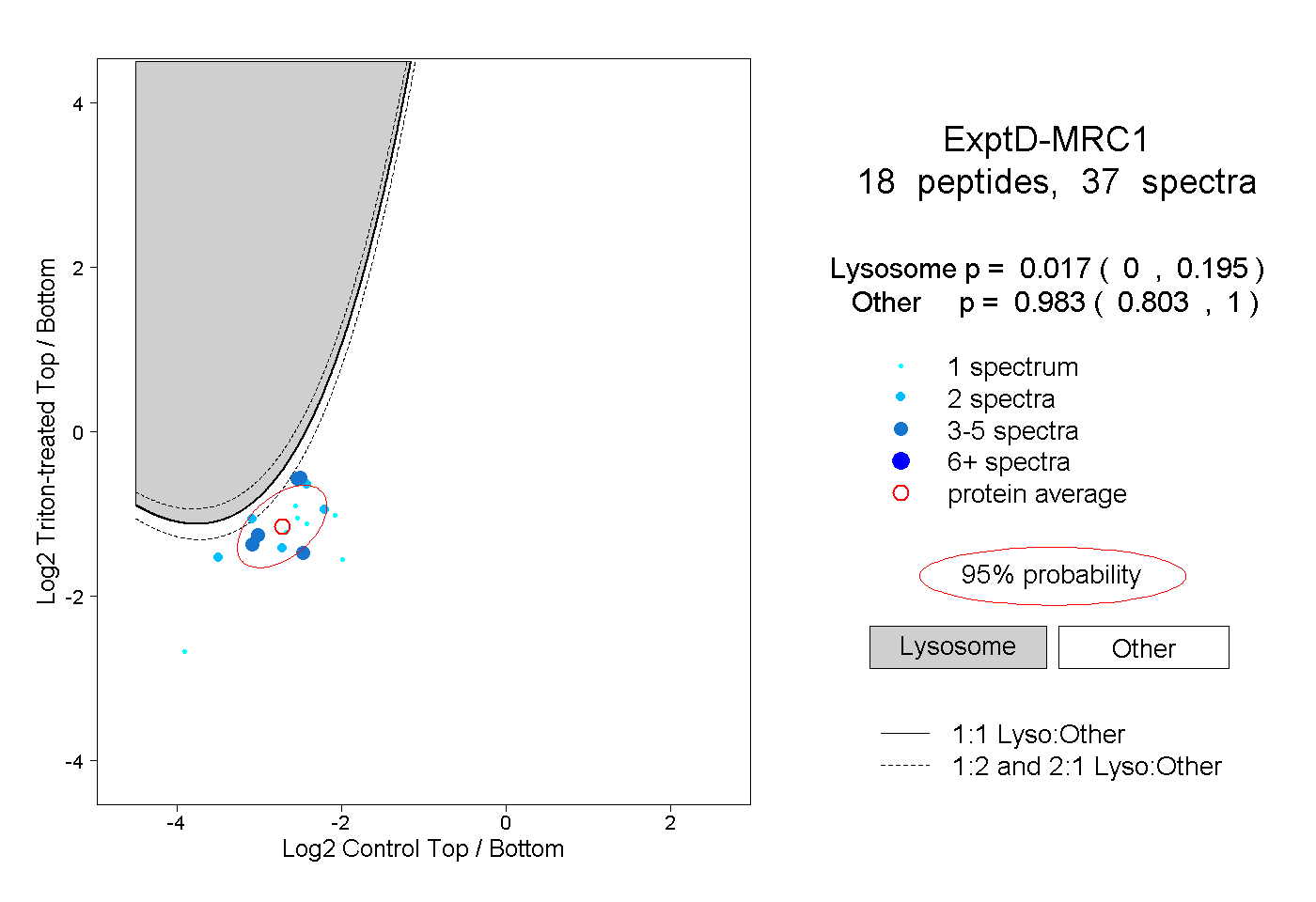 |
0.017 0.000 | 0.195 |
0.983 0.803 | 1.000 |