peptides
spectra
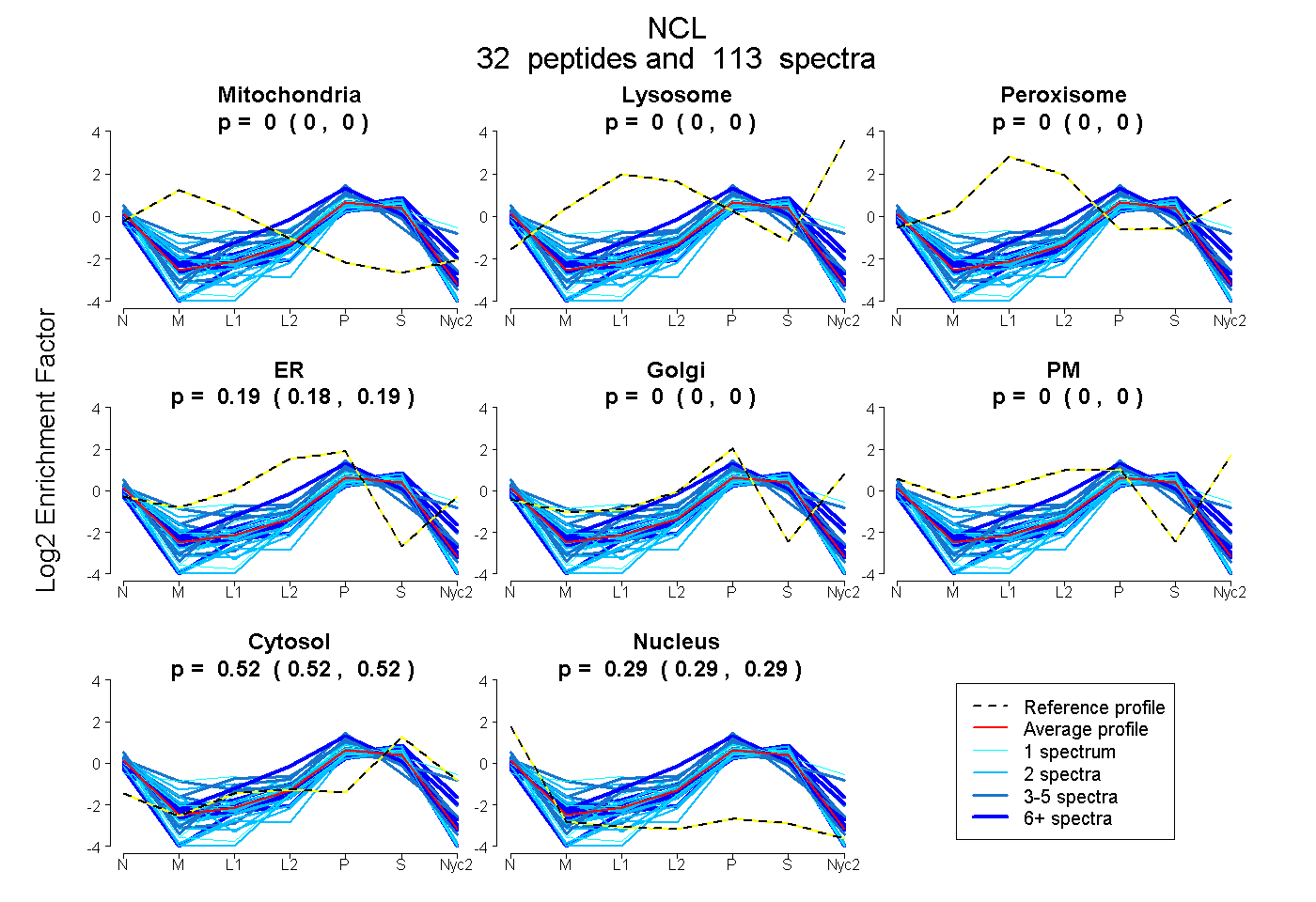
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.183 | 0.187
0.000 | 0.000
0.000 | 0.000
0.520 | 0.525
0.289 | 0.294
peptides
spectra
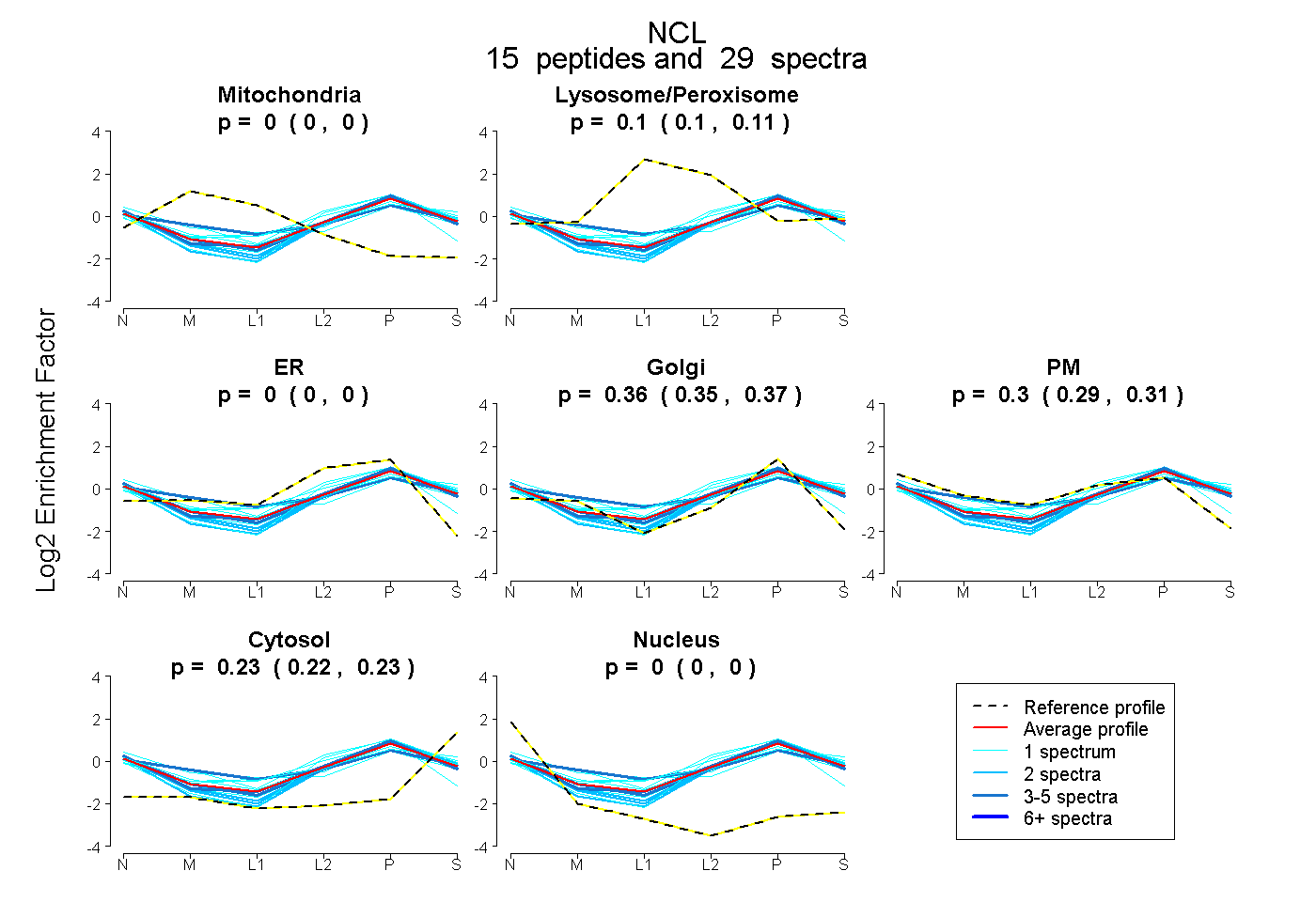
0.000 | 0.000
0.096 | 0.111
0.000 | 0.000
0.354 | 0.372
0.292 | 0.315
0.223 | 0.232
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
113 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.185 0.183 | 0.187 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.523 0.520 | 0.525 |
0.292 0.289 | 0.294 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.104 0.096 | 0.111 |
0.000 0.000 | 0.000 |
0.364 0.354 | 0.372 |
0.304 0.292 | 0.315 |
0.228 0.223 | 0.232 |
0.000 0.000 | 0.000 |
| 2 spectra, LELQGPR | 0.000 | 0.000 | 0.070 | 0.365 | 0.310 | 0.255 | 0.000 | |||
| 1 spectrum, NLSFNITEDELK | 0.000 | 0.279 | 0.000 | 0.434 | 0.080 | 0.208 | 0.000 | |||
| 4 spectra, LVSQDGR | 0.000 | 0.051 | 0.000 | 0.353 | 0.371 | 0.224 | 0.000 | |||
| 1 spectrum, VPQNPHGK | 0.000 | 0.105 | 0.000 | 0.280 | 0.373 | 0.242 | 0.000 | |||
| 1 spectrum, SVAELK | 0.000 | 0.225 | 0.000 | 0.277 | 0.212 | 0.286 | 0.000 | |||
| 2 spectra, NDLAAVDVR | 0.000 | 0.011 | 0.033 | 0.288 | 0.380 | 0.288 | 0.000 | |||
| 1 spectrum, EAPEAK | 0.000 | 0.060 | 0.214 | 0.271 | 0.384 | 0.071 | 0.000 | |||
| 4 spectra, GFGFVDFNSEEDAK | 0.000 | 0.184 | 0.000 | 0.242 | 0.350 | 0.224 | 0.000 | |||
| 1 spectrum, ATTTPAK | 0.000 | 0.248 | 0.000 | 0.523 | 0.039 | 0.190 | 0.000 | |||
| 2 spectra, QGAEIDGR | 0.000 | 0.098 | 0.000 | 0.374 | 0.290 | 0.238 | 0.000 | |||
| 5 spectra, VAISELFAK | 0.000 | 0.094 | 0.000 | 0.374 | 0.334 | 0.198 | 0.000 | |||
| 1 spectrum, SEADAEK | 0.000 | 0.000 | 0.368 | 0.247 | 0.077 | 0.308 | 0.000 | |||
| 2 spectra, GIAYIEFK | 0.000 | 0.000 | 0.075 | 0.412 | 0.227 | 0.286 | 0.000 | |||
| 1 spectrum, EALNSCNK | 0.000 | 0.086 | 0.000 | 0.070 | 0.599 | 0.245 | 0.000 | |||
| 1 spectrum, ALELTGLK | 0.000 | 0.036 | 0.000 | 0.347 | 0.369 | 0.247 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
96 spectra |
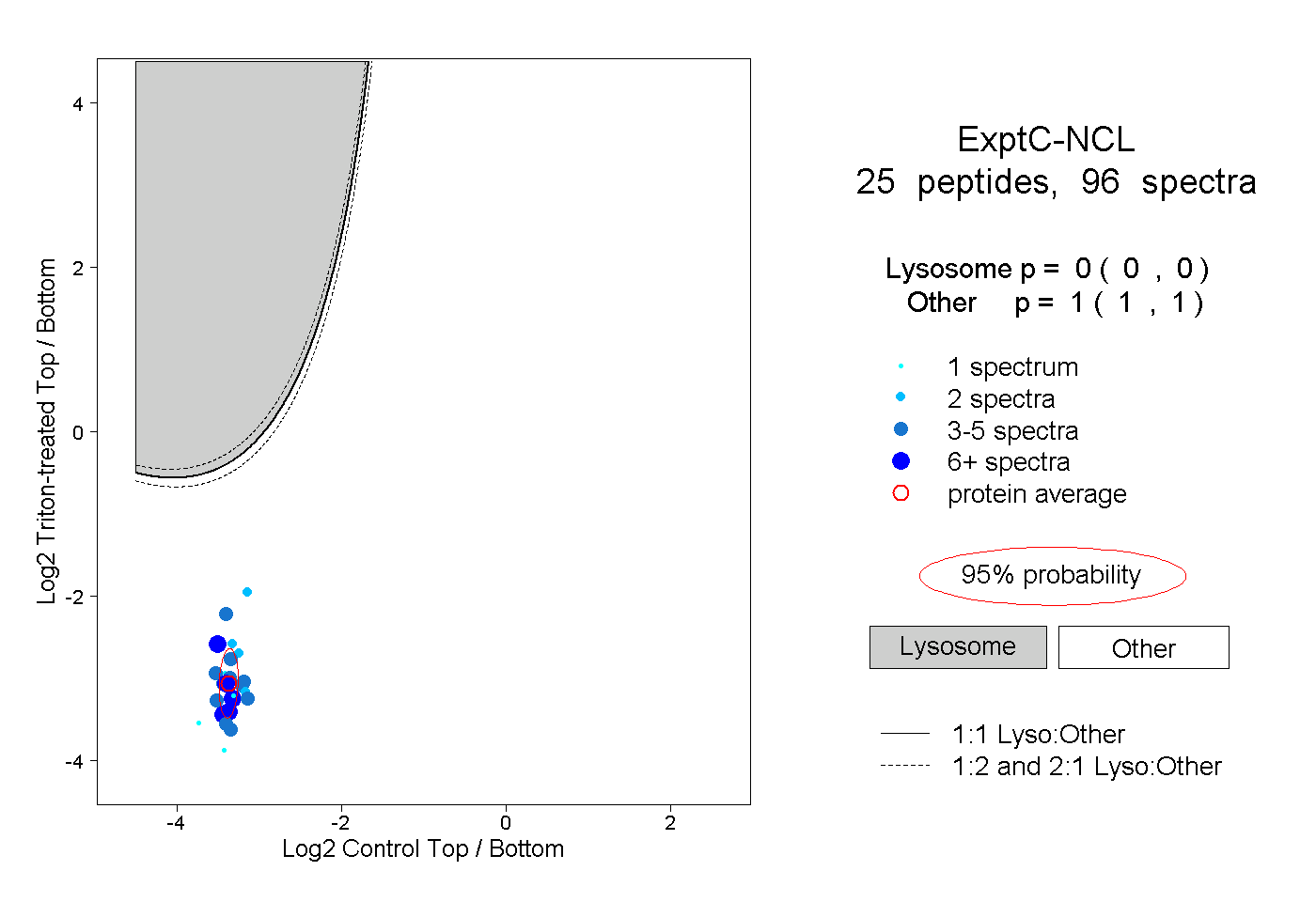 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
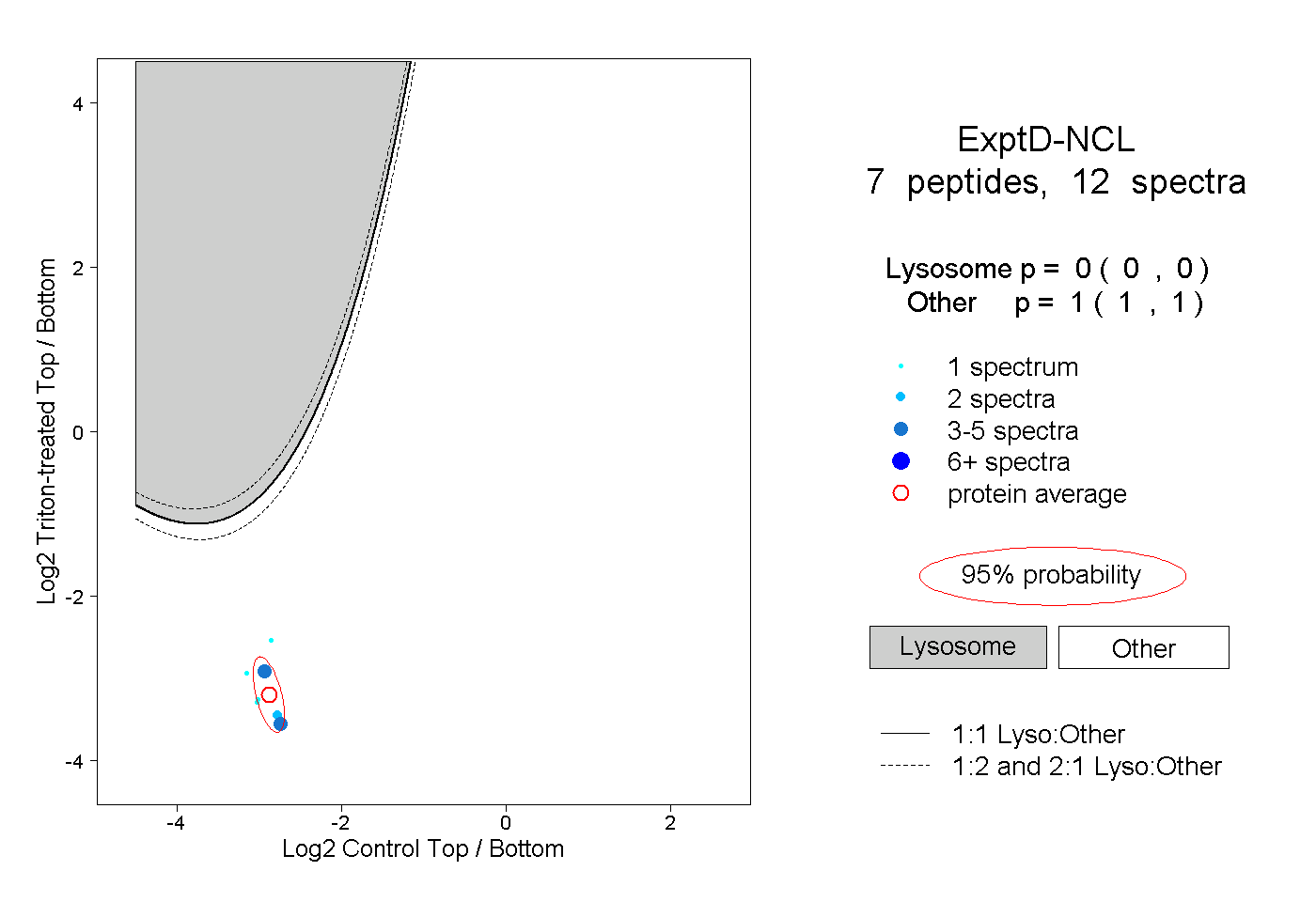 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |