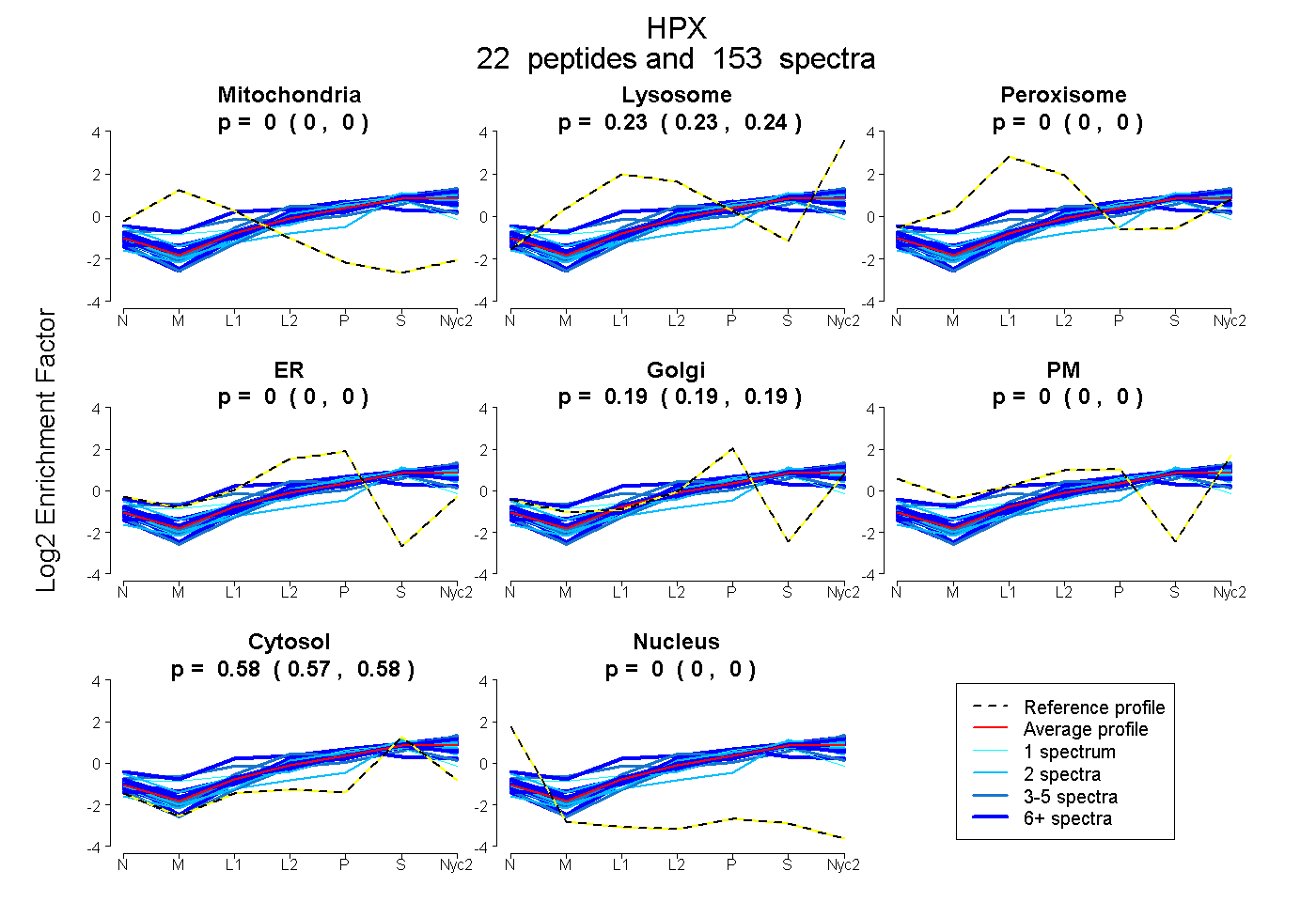
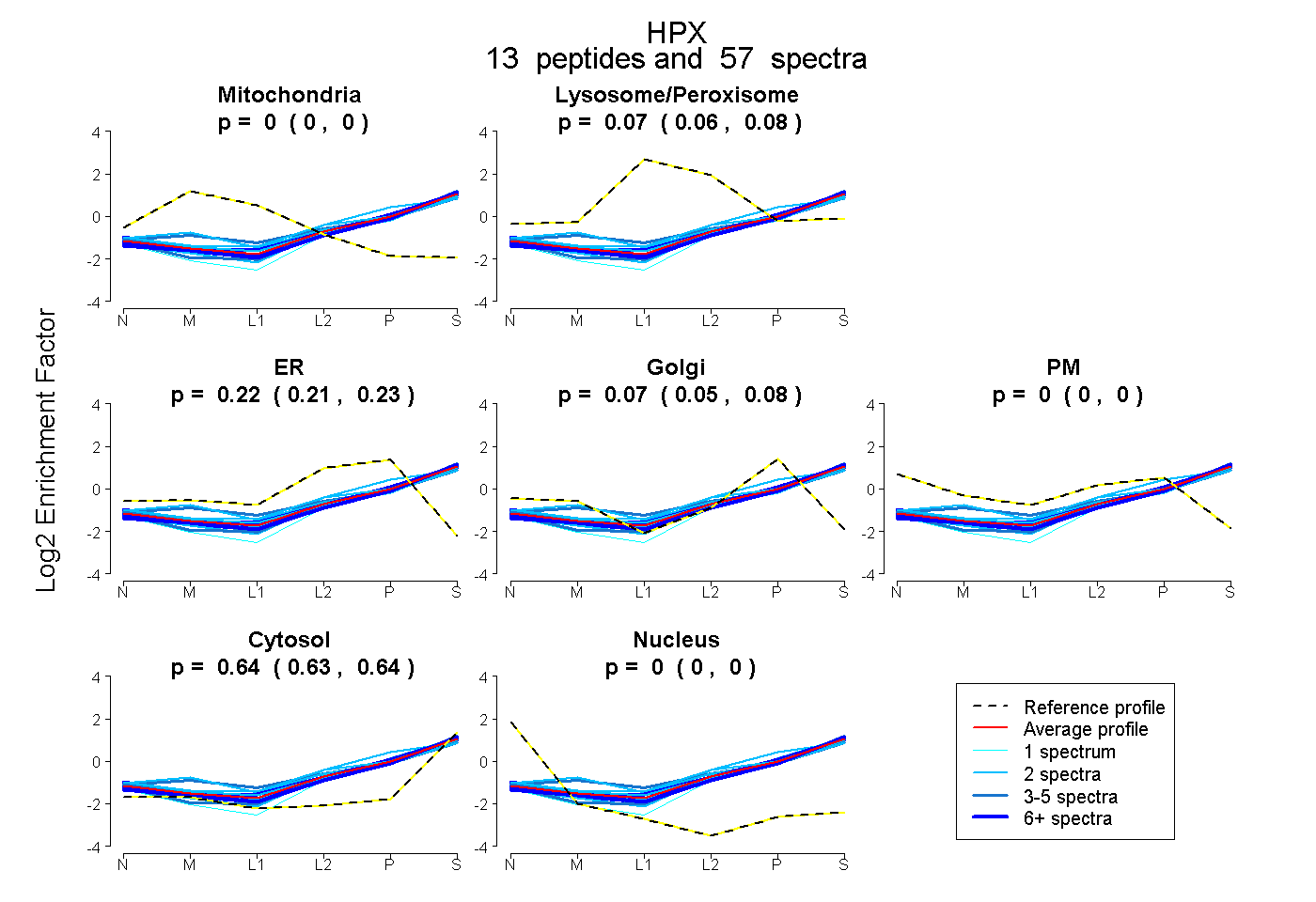
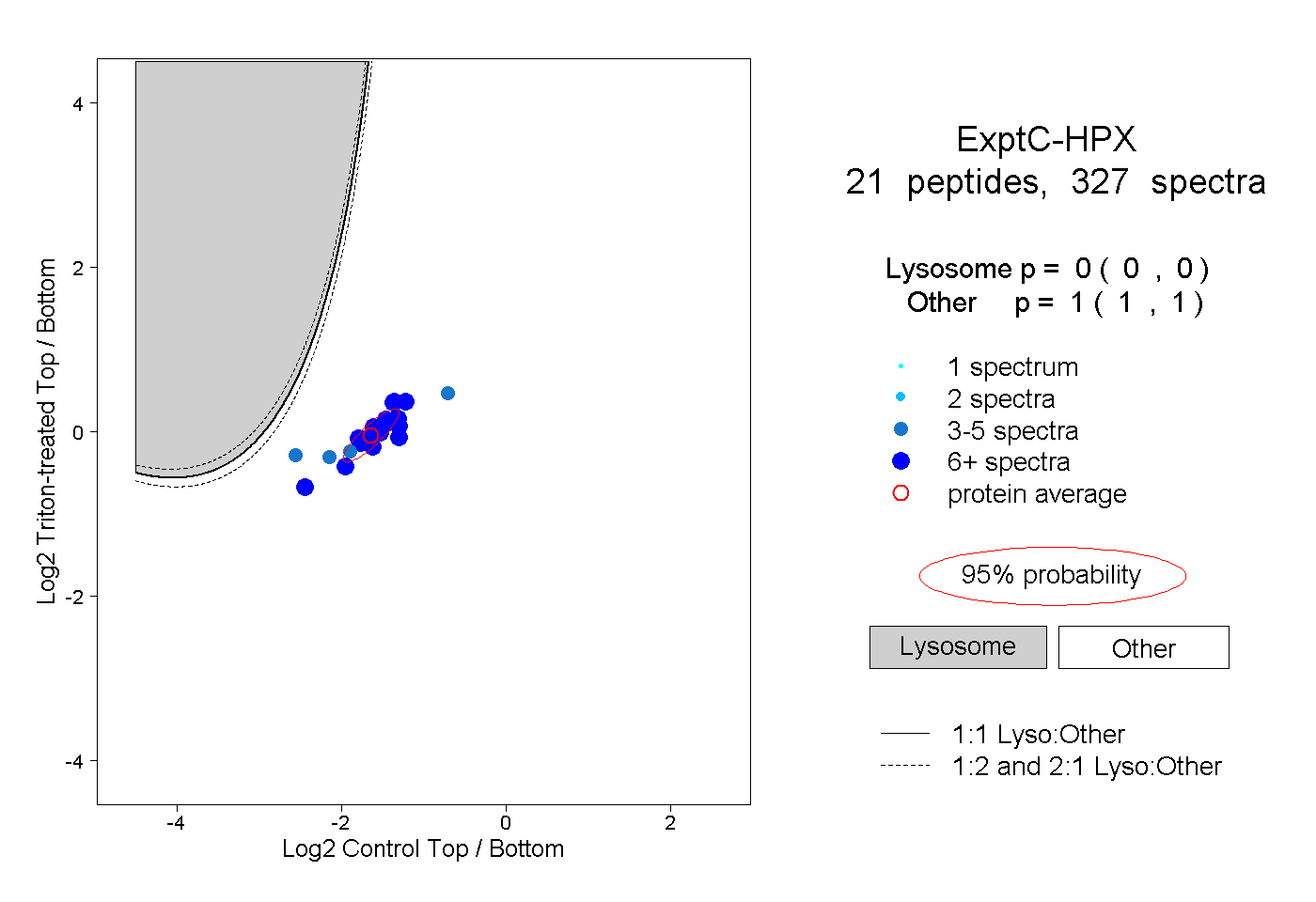
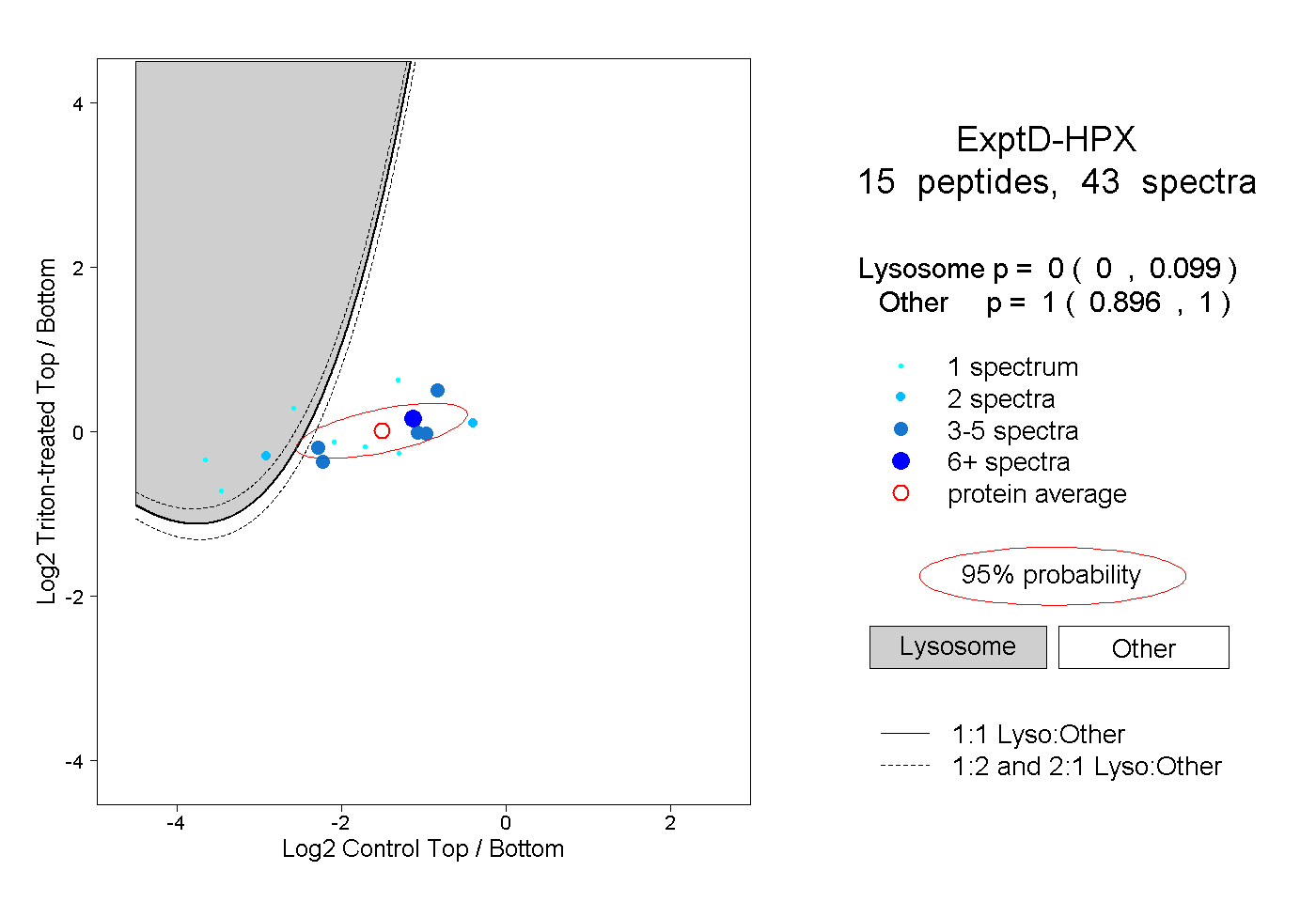
| 28 spectra, GPDSVFLIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, GGNNLVSGYPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GATYAFSGSHYWR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 4 spectra, CNADPGLSALLSDHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, DYFISCPGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, SGAQATWAELSWPHEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, ENGYPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, SLPQPQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, WFWDFATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LWWLDLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GECQSEGVLFFQGNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, FNPVTGEVPPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, YYCFQGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 37 spectra, LYVTSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, VDGALCLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, VWVYPPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, YPLDAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, GEFVWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LFQEEFPGIPYPPDAAVECHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, EDGLMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, NPVTSVDAAFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |