peptides
spectra
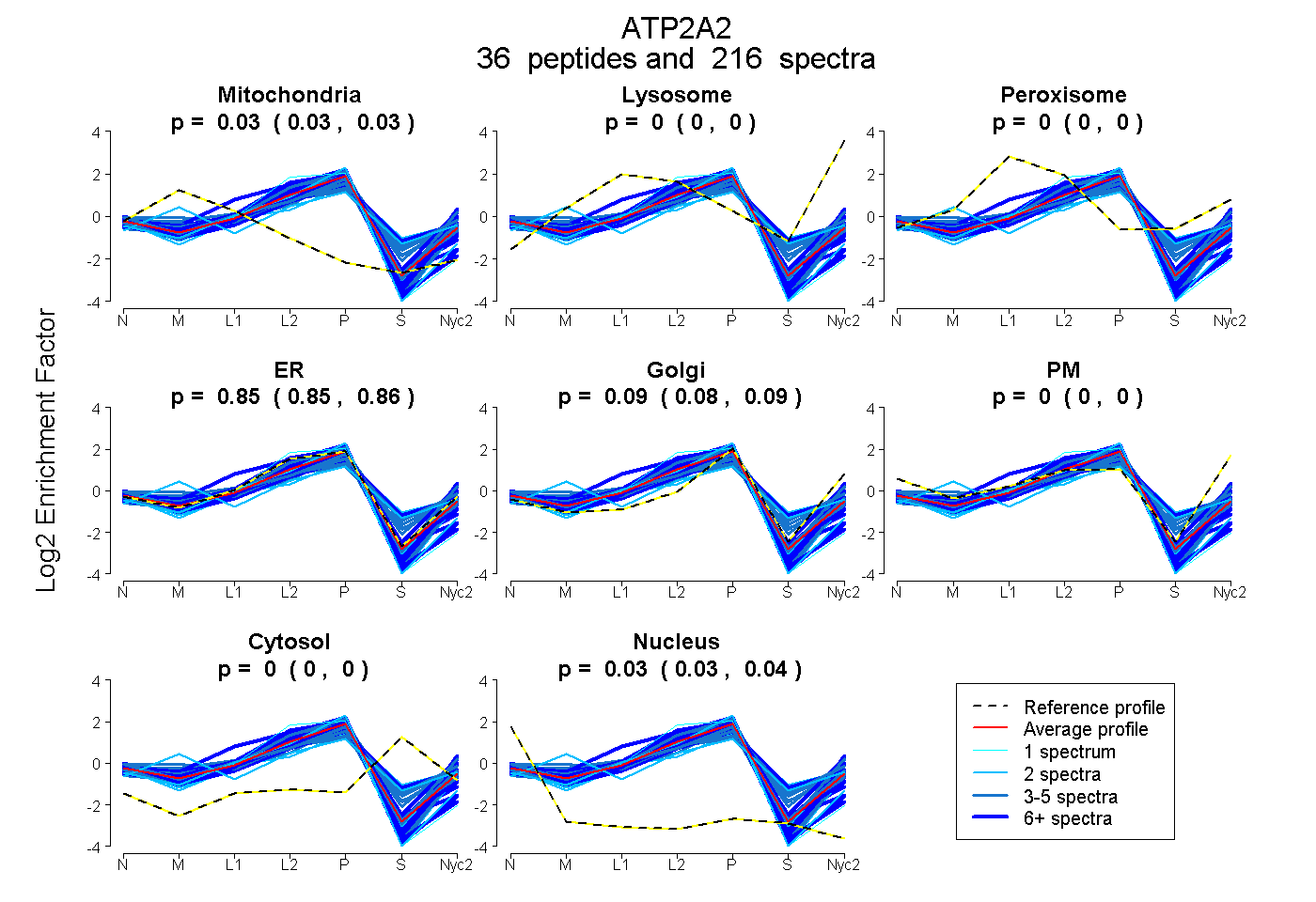
0.026 | 0.028
0.000 | 0.000
0.000 | 0.000
0.849 | 0.857
0.080 | 0.089
0.000 | 0.000
0.000 | 0.000
0.033 | 0.035
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
216 spectra |
 |
0.027 0.026 | 0.028 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.853 0.849 | 0.857 |
0.085 0.080 | 0.089 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.034 0.033 | 0.035 |
| 3 spectra, NMLFSGTNIAAGK | 0.000 | 0.014 | 0.000 | 0.793 | 0.076 | 0.116 | 0.000 | 0.000 | ||
| 17 spectra, EWGSGSDTLR | 0.000 | 0.000 | 0.000 | 0.949 | 0.000 | 0.000 | 0.000 | 0.051 | ||
| 1 spectrum, VGEATETALTCLVEK | 0.000 | 0.000 | 0.000 | 0.929 | 0.000 | 0.000 | 0.000 | 0.071 | ||
| 13 spectra, TGTLTTNQMSVCR | 0.037 | 0.000 | 0.000 | 0.918 | 0.000 | 0.000 | 0.000 | 0.045 | ||
| 8 spectra, NAENAIEALK | 0.041 | 0.034 | 0.000 | 0.624 | 0.159 | 0.143 | 0.000 | 0.000 | ||
| 2 spectra, VSFYQLSHFLQCK | 0.000 | 0.000 | 0.000 | 0.929 | 0.000 | 0.000 | 0.000 | 0.071 | ||
| 12 spectra, IMSVIR | 0.012 | 0.050 | 0.000 | 0.914 | 0.000 | 0.024 | 0.000 | 0.000 | ||
| 2 spectra, EPLISGWLFFR | 0.000 | 0.000 | 0.000 | 0.906 | 0.041 | 0.000 | 0.000 | 0.053 | ||
| 2 spectra, GAIYYFK | 0.033 | 0.000 | 0.110 | 0.406 | 0.262 | 0.000 | 0.189 | 0.000 | ||
| 5 spectra, AIYNNMK | 0.001 | 0.000 | 0.012 | 0.593 | 0.175 | 0.146 | 0.073 | 0.000 | ||
| 12 spectra, MNVFDTELK | 0.028 | 0.000 | 0.000 | 0.897 | 0.074 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LDEFGEQLSK | 0.075 | 0.000 | 0.035 | 0.711 | 0.000 | 0.000 | 0.178 | 0.000 | ||
| 7 spectra, EEMHLEDSANFIK | 0.000 | 0.000 | 0.000 | 0.929 | 0.000 | 0.000 | 0.000 | 0.071 | ||
| 9 spectra, VEPSHK | 0.000 | 0.000 | 0.000 | 0.887 | 0.024 | 0.000 | 0.000 | 0.089 | ||
| 5 spectra, HTDPVPDPR | 0.122 | 0.000 | 0.056 | 0.511 | 0.122 | 0.095 | 0.094 | 0.000 | ||
| 5 spectra, CLALATHDNPLR | 0.082 | 0.000 | 0.000 | 0.745 | 0.074 | 0.000 | 0.100 | 0.000 | ||
| 4 spectra, TPLQQK | 0.000 | 0.000 | 0.000 | 0.973 | 0.000 | 0.000 | 0.000 | 0.027 | ||
| 4 spectra, MFIIDK | 0.000 | 0.000 | 0.000 | 0.964 | 0.030 | 0.000 | 0.000 | 0.006 | ||
| 2 spectra, VPMTPGVK | 0.192 | 0.052 | 0.000 | 0.371 | 0.263 | 0.000 | 0.122 | 0.000 | ||
| 7 spectra, GAPEGVIDR | 0.000 | 0.000 | 0.000 | 0.671 | 0.112 | 0.218 | 0.000 | 0.000 | ||
| 4 spectra, IGIFGQDEDVTSK | 0.019 | 0.000 | 0.013 | 0.574 | 0.298 | 0.000 | 0.095 | 0.000 | ||
| 4 spectra, VIMITGDNK | 0.057 | 0.000 | 0.000 | 0.722 | 0.188 | 0.000 | 0.000 | 0.033 | ||
| 7 spectra, EFDELSPSAQR | 0.000 | 0.000 | 0.000 | 0.831 | 0.078 | 0.000 | 0.000 | 0.090 | ||
| 13 spectra, GTAVAICR | 0.000 | 0.000 | 0.000 | 0.874 | 0.000 | 0.000 | 0.000 | 0.126 | ||
| 5 spectra, NYLEPGK | 0.000 | 0.000 | 0.096 | 0.534 | 0.233 | 0.000 | 0.137 | 0.000 | ||
| 8 spectra, SMSVYCTPNKPSR | 0.000 | 0.000 | 0.000 | 0.937 | 0.000 | 0.000 | 0.000 | 0.063 | ||
| 7 spectra, DACLNAR | 0.000 | 0.000 | 0.000 | 0.803 | 0.158 | 0.000 | 0.000 | 0.039 | ||
| 3 spectra, ANACNSVIK | 0.089 | 0.000 | 0.000 | 0.591 | 0.117 | 0.202 | 0.000 | 0.000 | ||
| 2 spectra, IEVASSVK | 0.000 | 0.000 | 0.000 | 0.693 | 0.288 | 0.000 | 0.000 | 0.019 | ||
| 3 spectra, DEMVATEQER | 0.000 | 0.000 | 0.000 | 0.888 | 0.112 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, EYEPEMGK | 0.000 | 0.000 | 0.000 | 0.819 | 0.155 | 0.021 | 0.000 | 0.004 | ||
| 7 spectra, ISLPVILMDETLK | 0.000 | 0.000 | 0.015 | 0.634 | 0.111 | 0.000 | 0.239 | 0.000 | ||
| 6 spectra, EFTLEFSR | 0.041 | 0.000 | 0.000 | 0.923 | 0.031 | 0.000 | 0.000 | 0.005 | ||
| 4 spectra, AMGVVVATGVNTEIGK | 0.080 | 0.000 | 0.000 | 0.695 | 0.095 | 0.129 | 0.000 | 0.000 | ||
| 9 spectra, AVNQDK | 0.004 | 0.000 | 0.000 | 0.802 | 0.137 | 0.000 | 0.000 | 0.057 | ||
| 4 spectra, SEIGIAMGSGTAVAK | 0.000 | 0.000 | 0.000 | 0.872 | 0.081 | 0.000 | 0.000 | 0.047 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
59 spectra |
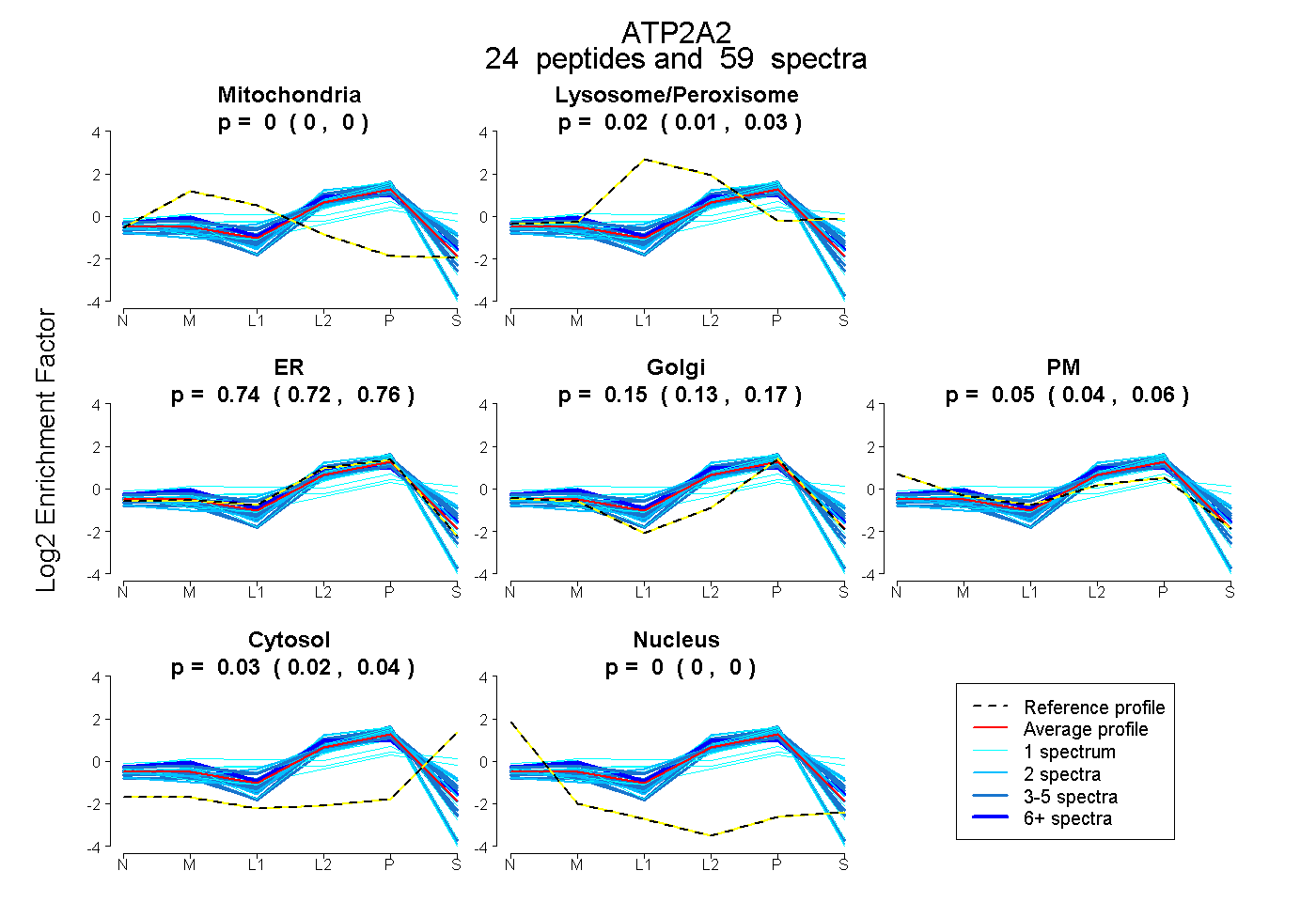 |
0.000 0.000 | 0.000 |
0.021 0.007 | 0.033 |
0.744 0.721 | 0.765 |
0.153 0.127 | 0.174 |
0.050 0.037 | 0.063 |
0.031 0.024 | 0.036 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
392 spectra |
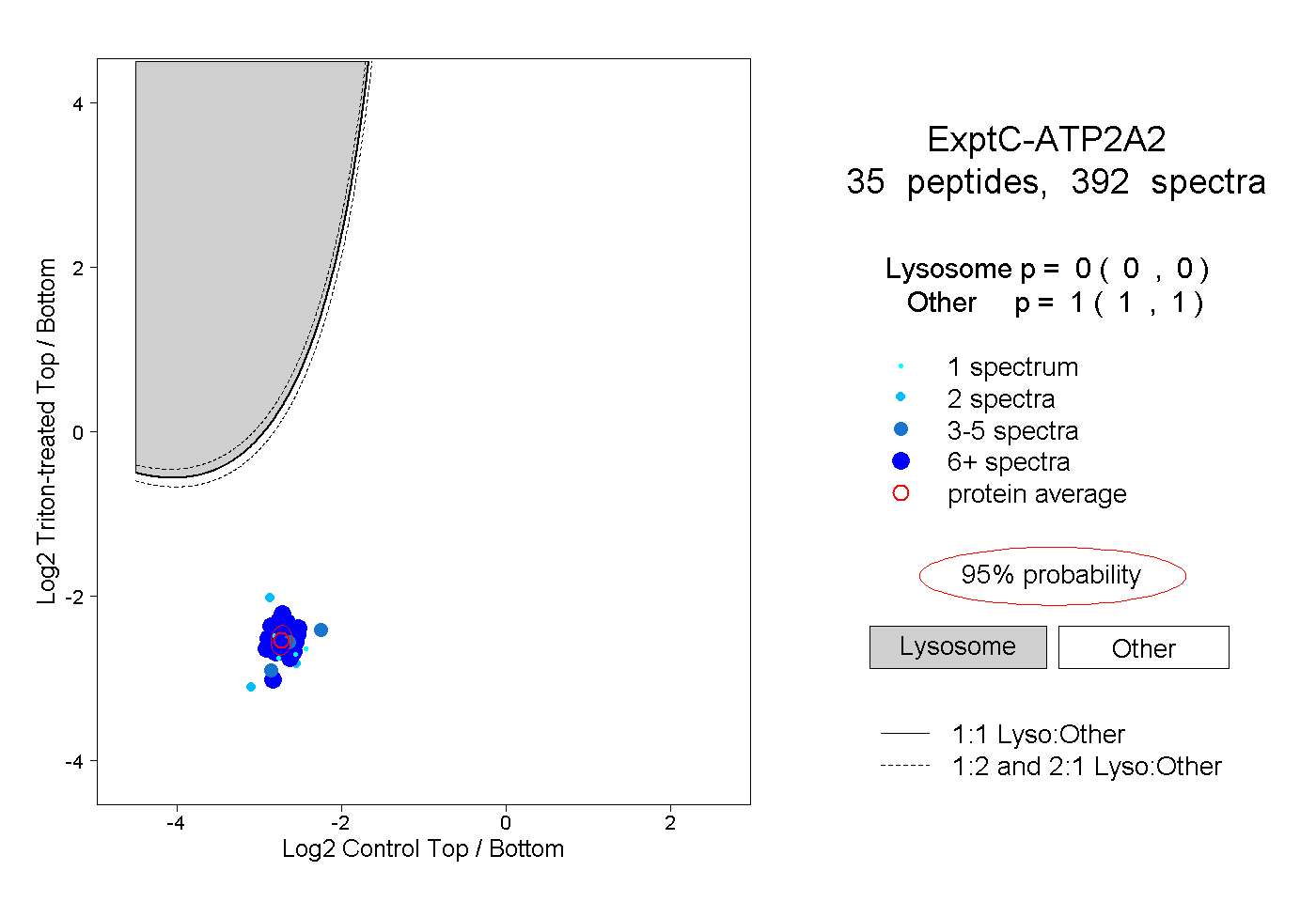 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
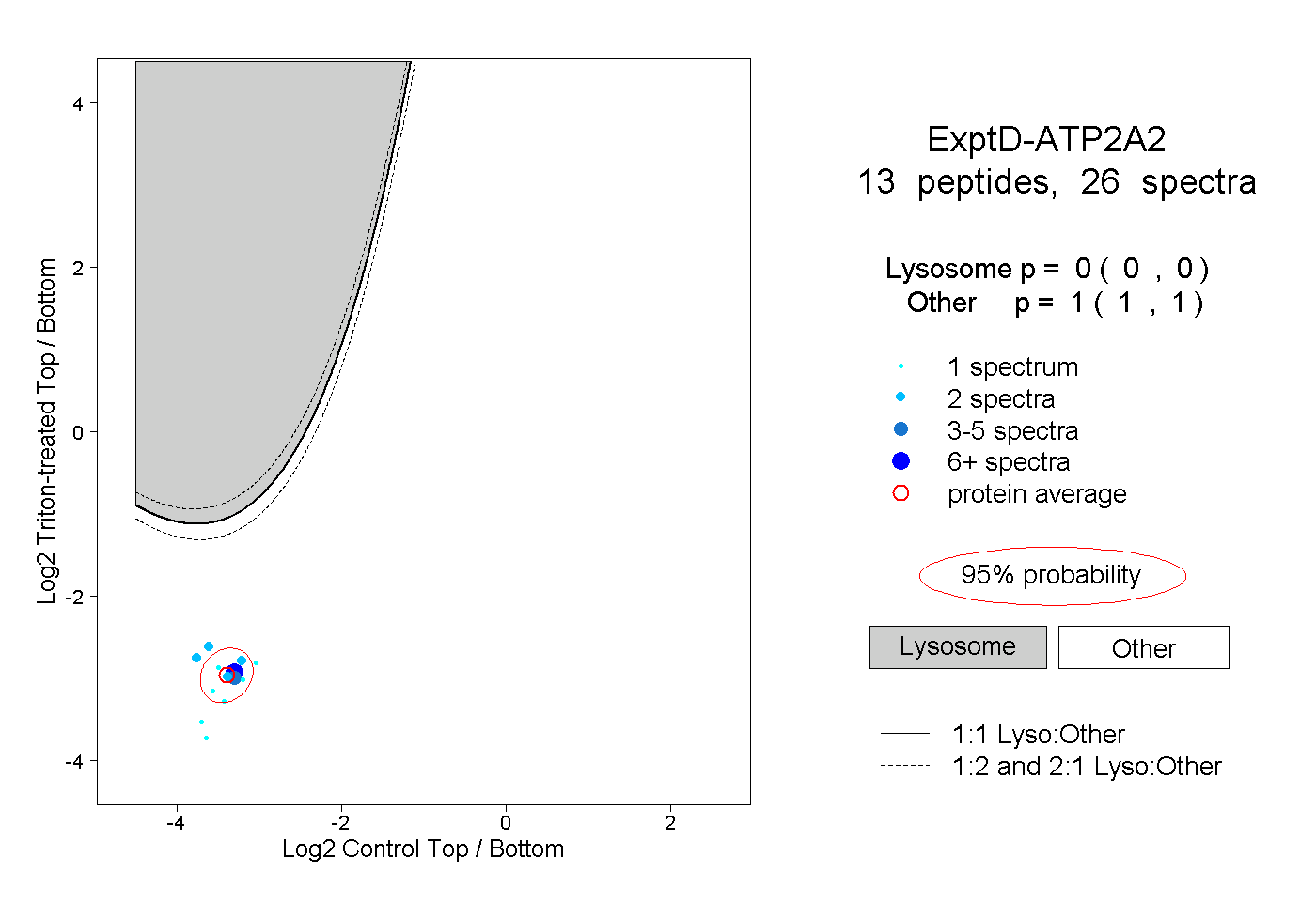 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |