peptides
spectra
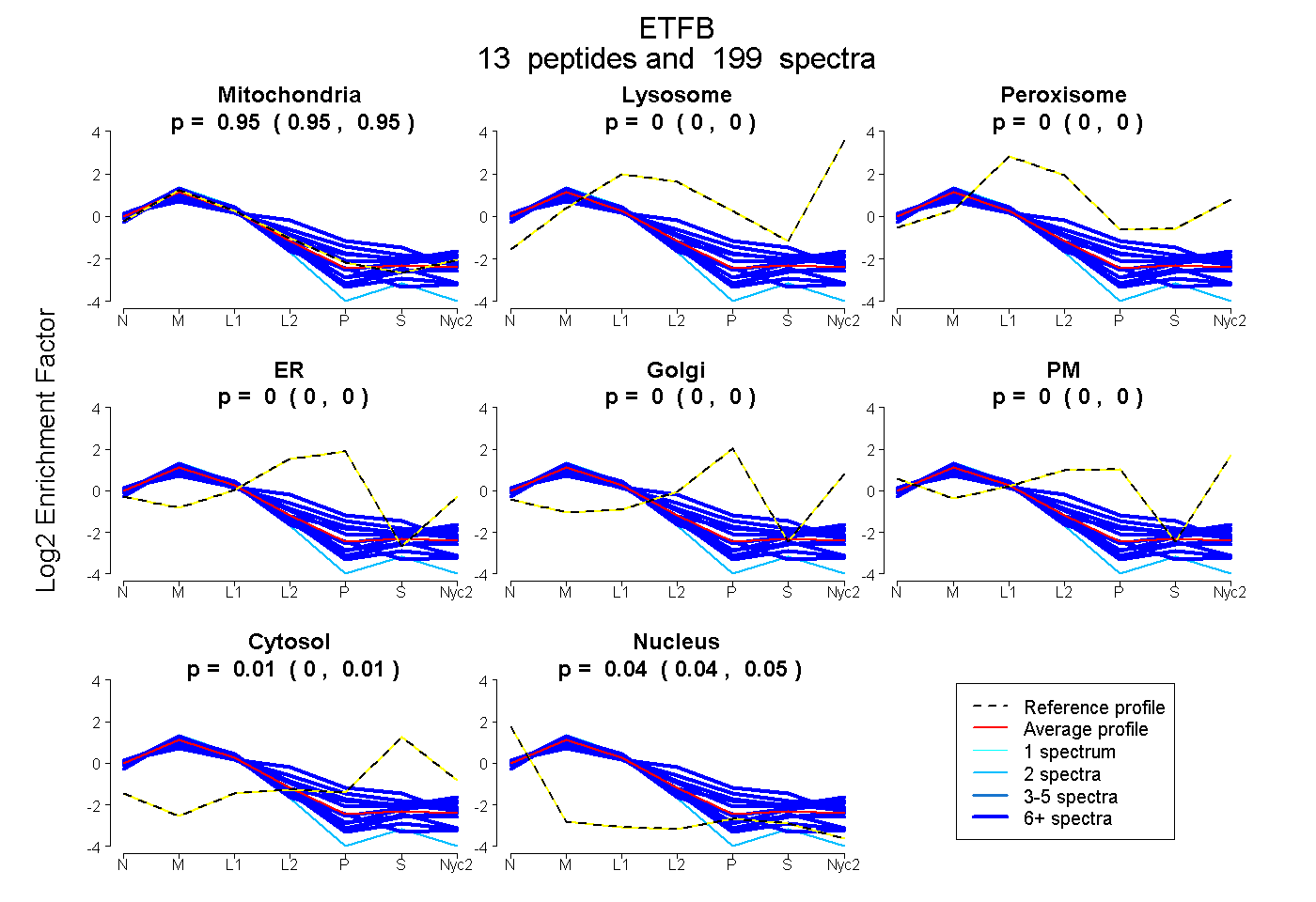
0.946 | 0.950
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.004 | 0.010
0.042 | 0.047
peptides
spectra
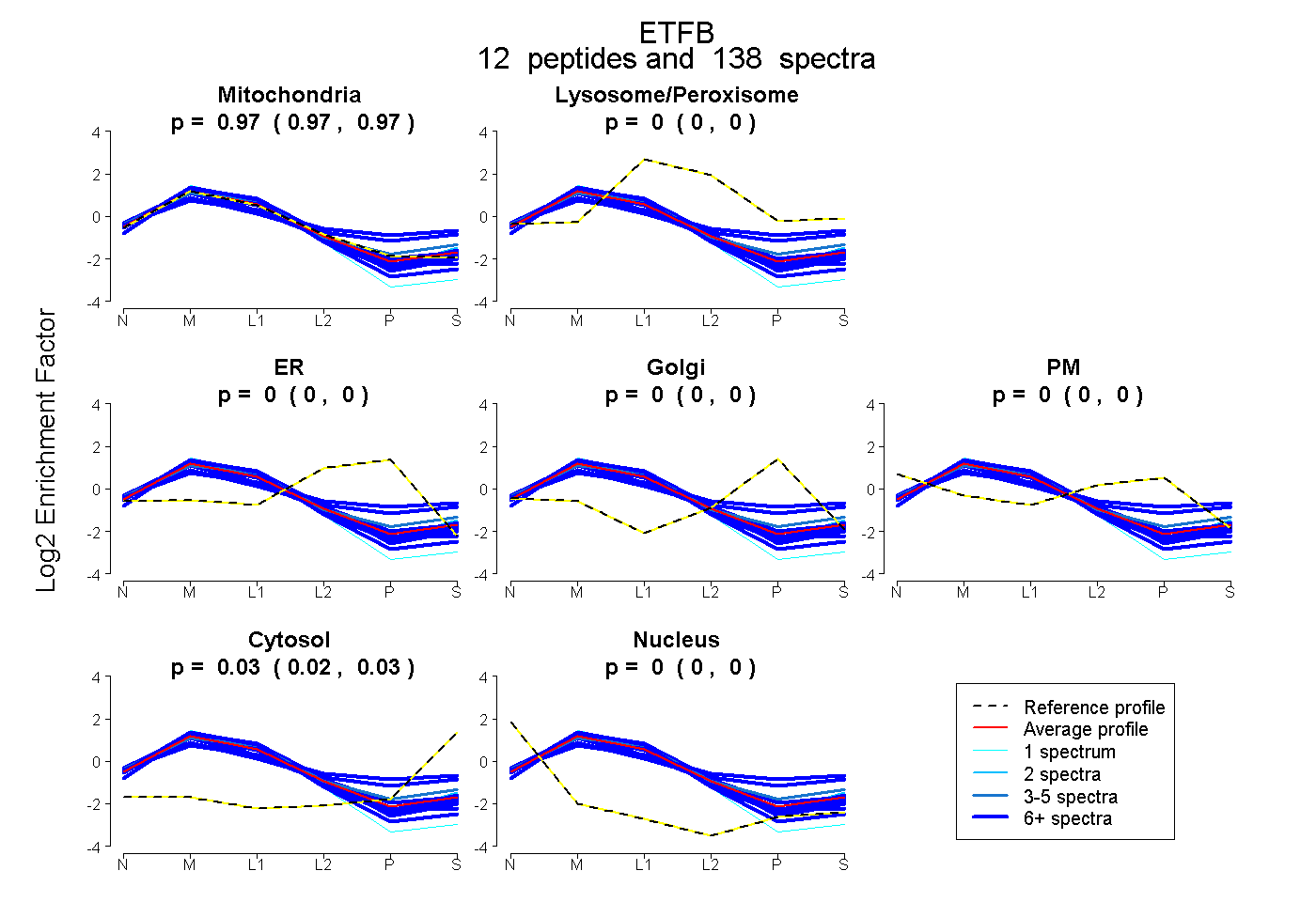
0.967 | 0.974
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.025 | 0.032
0.000 | 0.001
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
199 spectra |
 |
0.948 0.946 | 0.950 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.007 0.004 | 0.010 |
0.045 0.042 | 0.047 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
138 spectra |
 |
0.971 0.967 | 0.974 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.029 0.025 | 0.032 |
0.000 0.000 | 0.001 |
| 20 spectra, VDLLFLGK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, VIDFAVK | 0.986 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | |||
| 3 spectra, VETTEDLVAK | 0.872 | 0.070 | 0.000 | 0.000 | 0.000 | 0.058 | 0.000 | |||
| 2 spectra, ALVAVK | 0.978 | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | 0.000 | |||
| 1 spectrum, LPAVVTADLR | 0.976 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | |||
| 6 spectra, SGVVTDGVK | 0.931 | 0.000 | 0.000 | 0.000 | 0.000 | 0.053 | 0.015 | |||
| 8 spectra, AGDLGVDLTSK | 0.988 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.012 | |||
| 10 spectra, VSVISVEEPPQR | 0.523 | 0.210 | 0.000 | 0.106 | 0.021 | 0.139 | 0.000 | |||
| 17 spectra, TALAMGADR | 0.933 | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | |||
| 34 spectra, EIDGGLETIR | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.013 | |||
| 13 spectra, GIHVEVPGAEAENLGPLQVAR | 0.964 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.036 | |||
| 13 spectra, HSMNPFCEIAVEEAVR | 0.630 | 0.111 | 0.000 | 0.034 | 0.075 | 0.151 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
892 spectra |
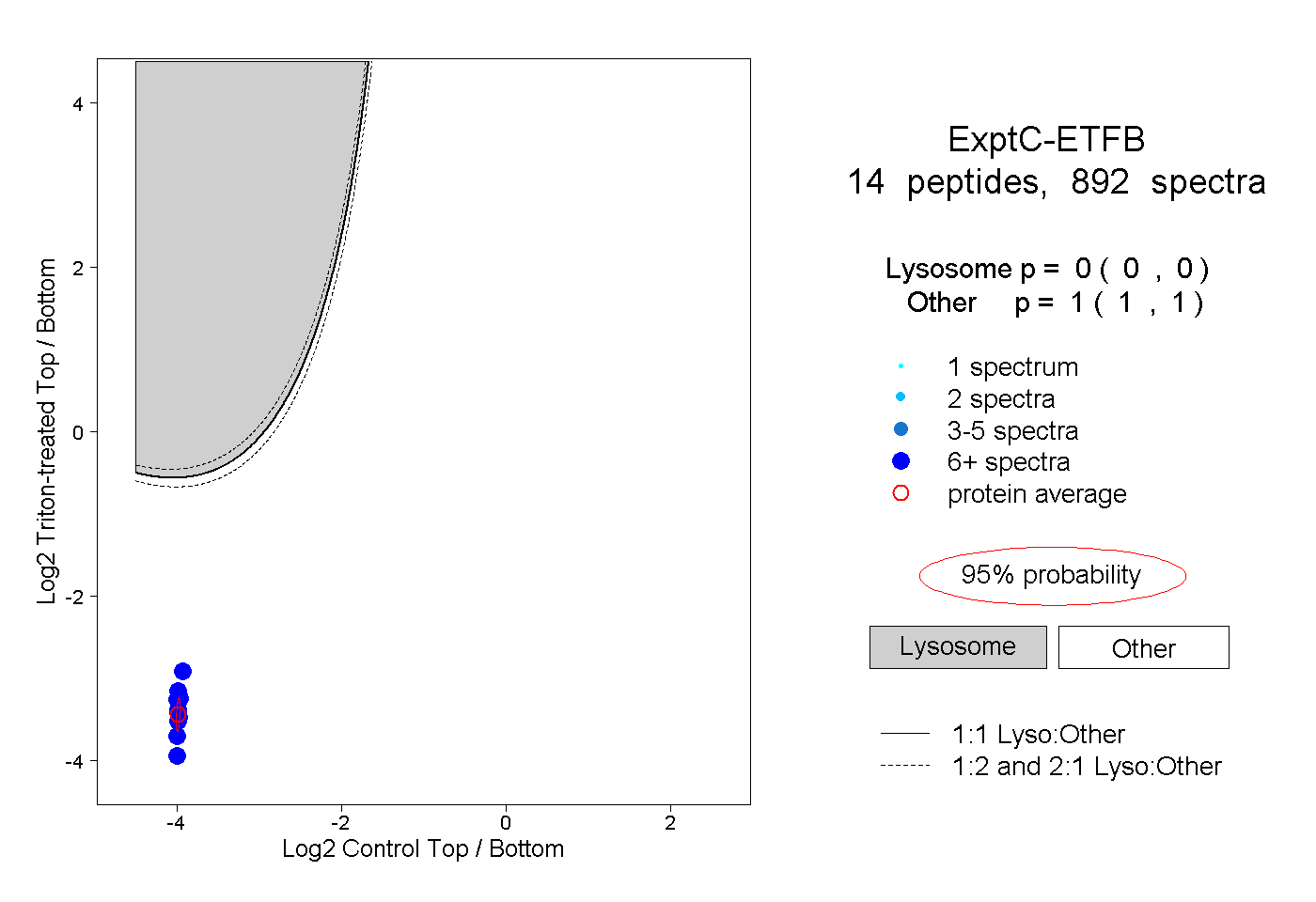 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
77 spectra |
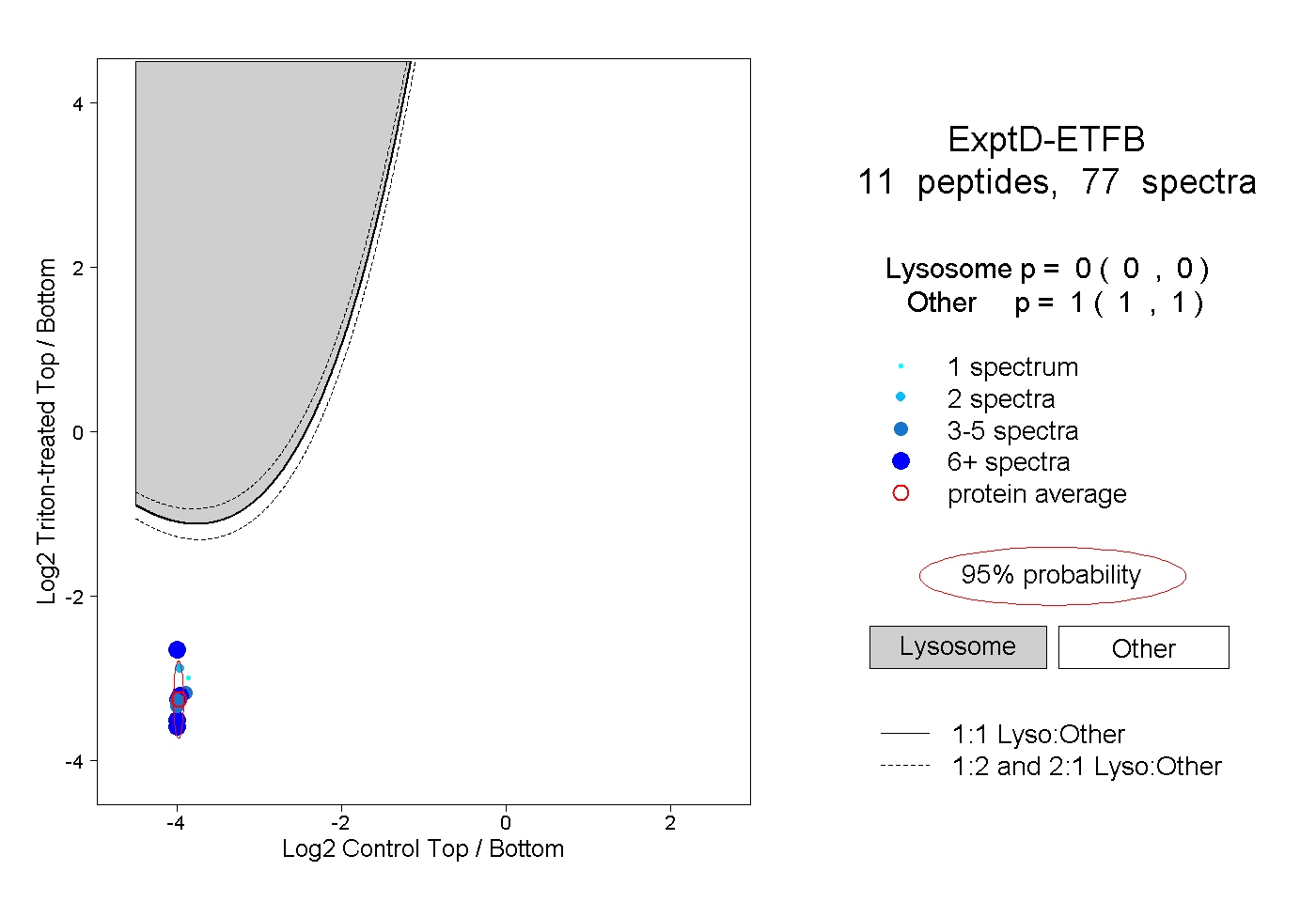 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |