peptides
spectra
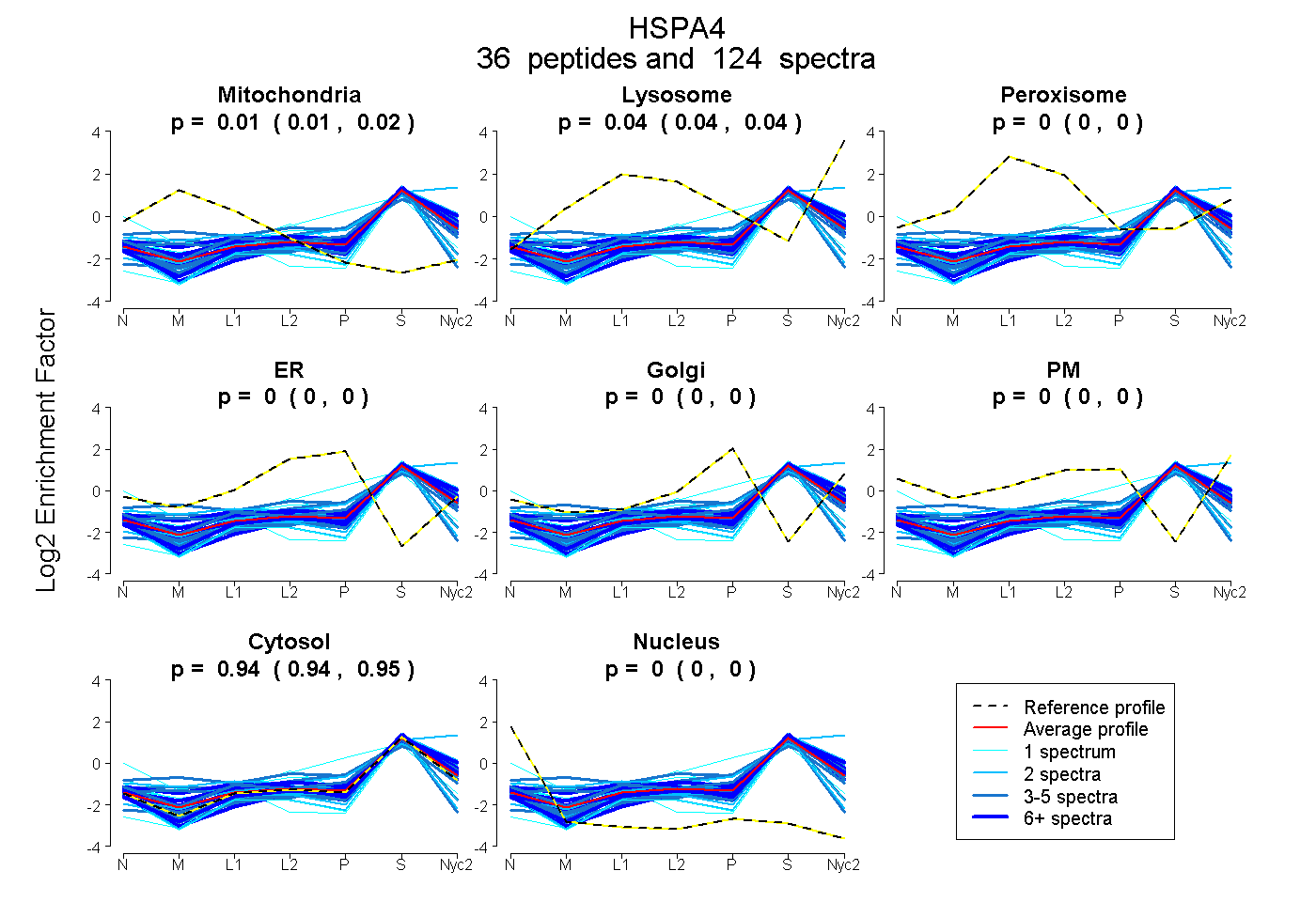
0.012 | 0.017
0.039 | 0.044
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.942 | 0.946
0.000 | 0.000
peptides
spectra
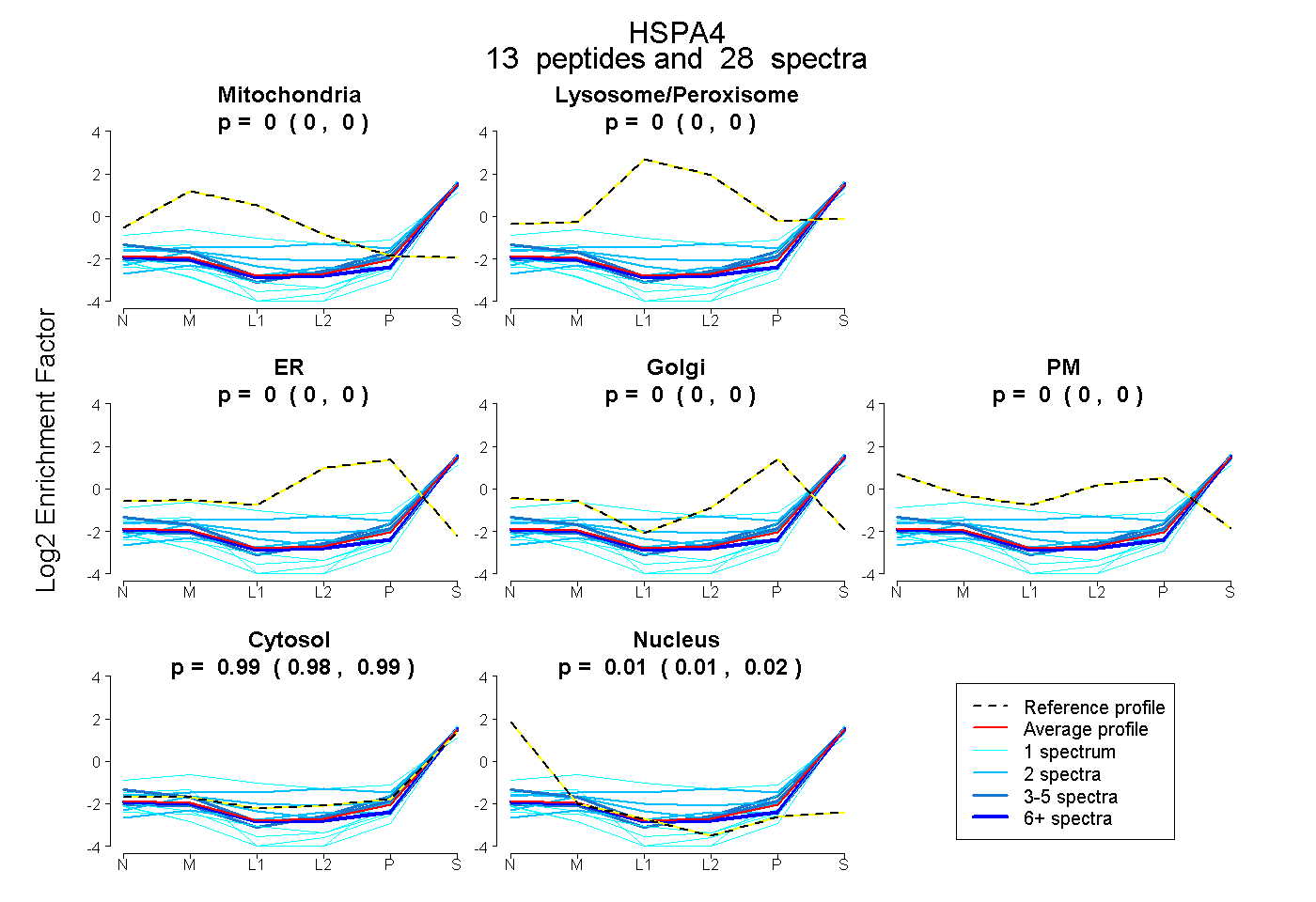
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.980 | 0.993
0.006 | 0.018
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
124 spectra |
 |
0.015 0.012 | 0.017 |
0.042 0.039 | 0.044 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.944 0.942 | 0.946 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.987 0.980 | 0.993 |
0.013 0.006 | 0.018 |
| 8 spectra, VLTFYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.983 | 0.017 | |||
| 2 spectra, NHAAPFSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, QDLPALEEKPR | 0.073 | 0.178 | 0.000 | 0.000 | 0.072 | 0.677 | 0.000 | |||
| 3 spectra, VEPPLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.925 | 0.075 | |||
| 2 spectra, QSLTADPVVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.958 | 0.042 | |||
| 1 spectrum, FLEMCDDLLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, LMNETTAVALAYGIYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VTPQSDGSSSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.951 | 0.049 | |||
| 1 spectrum, ELSTTLNADEAVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.950 | 0.050 | |||
| 1 spectrum, GCALQCAILSPAFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.916 | 0.084 | |||
| 2 spectra, TLGQPIK | 0.000 | 0.158 | 0.000 | 0.000 | 0.000 | 0.842 | 0.000 | |||
| 3 spectra, AFSDPFVEAEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, AGGIETIANEYSDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.864 | 0.136 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
119 spectra |
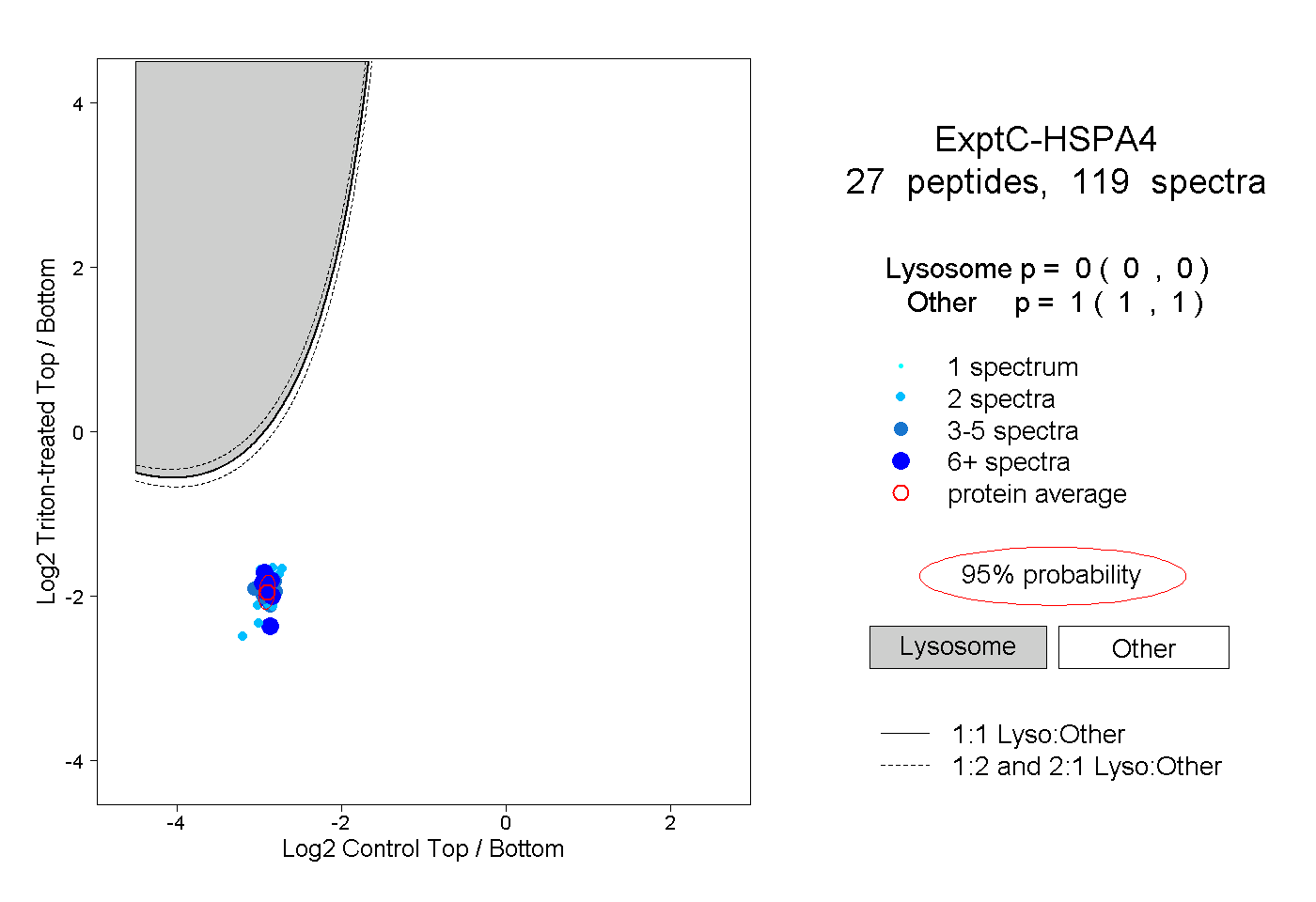 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
19 spectra |
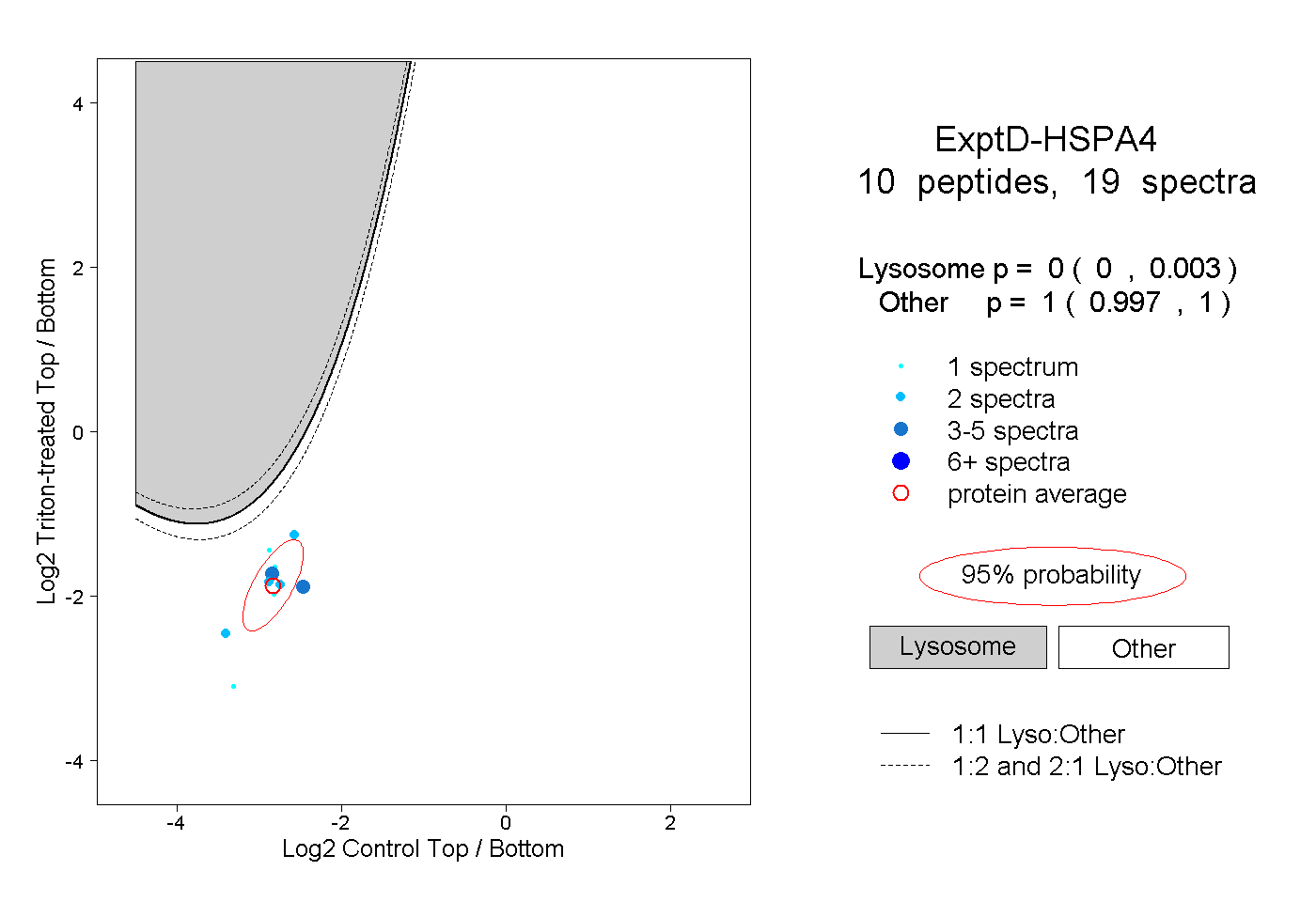 |
0.000 0.000 | 0.003 |
1.000 0.997 | 1.000 |