peptides
spectra
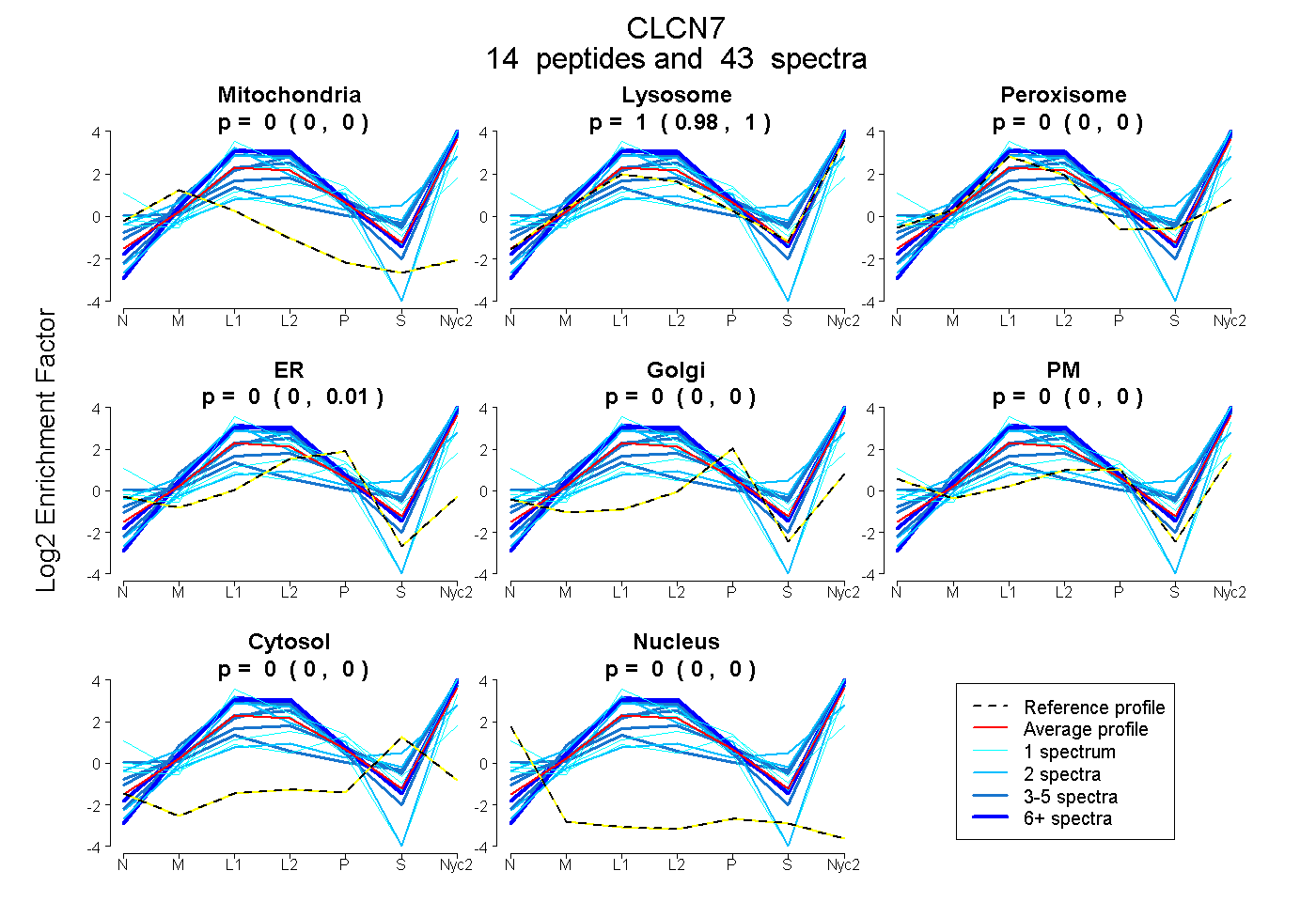
0.000 | 0.000
0.985 | 1.000
0.000 | 0.002
0.000 | 0.012
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
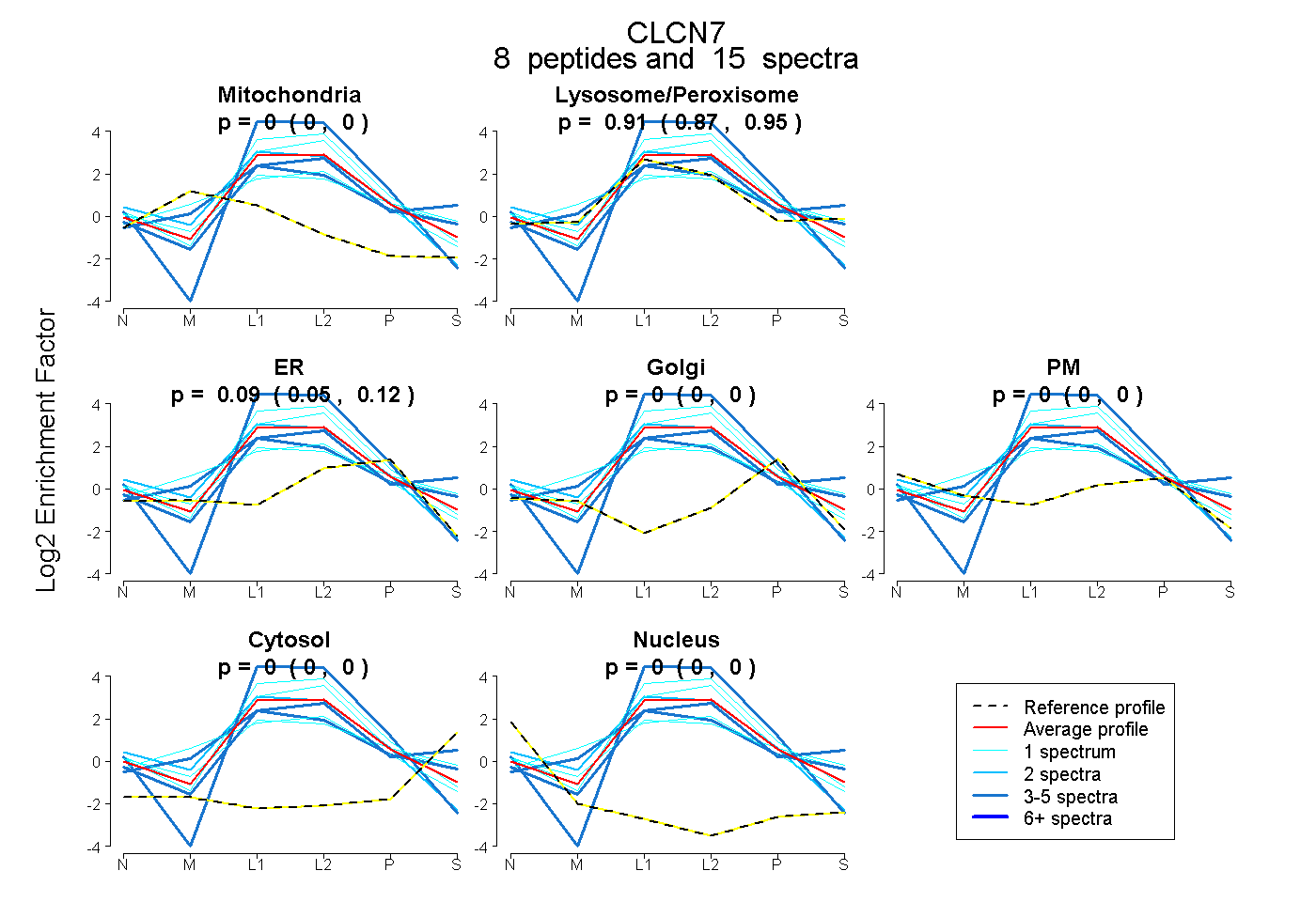
0.000 | 0.000
0.874 | 0.946
0.047 | 0.121
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
43 spectra |
 |
0.000 0.000 | 0.000 |
0.997 0.985 | 1.000 |
0.000 0.000 | 0.002 |
0.003 0.000 | 0.012 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
15 spectra |
 |
0.000 0.000 | 0.000 |
0.913 0.874 | 0.946 |
0.087 0.047 | 0.121 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, SNMGLVQR | 0.000 | 0.994 | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | |||
| 1 spectrum, IPHVVR | 0.000 | 0.774 | 0.149 | 0.000 | 0.077 | 0.000 | 0.000 | |||
| 1 spectrum, SQLIVLLK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, IFEYFR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EVMSTPVTCLR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EIPHNEK | 0.000 | 0.817 | 0.183 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QSHSALFR | 0.058 | 0.653 | 0.289 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, INHTAFR | 0.000 | 0.878 | 0.122 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
145 spectra |
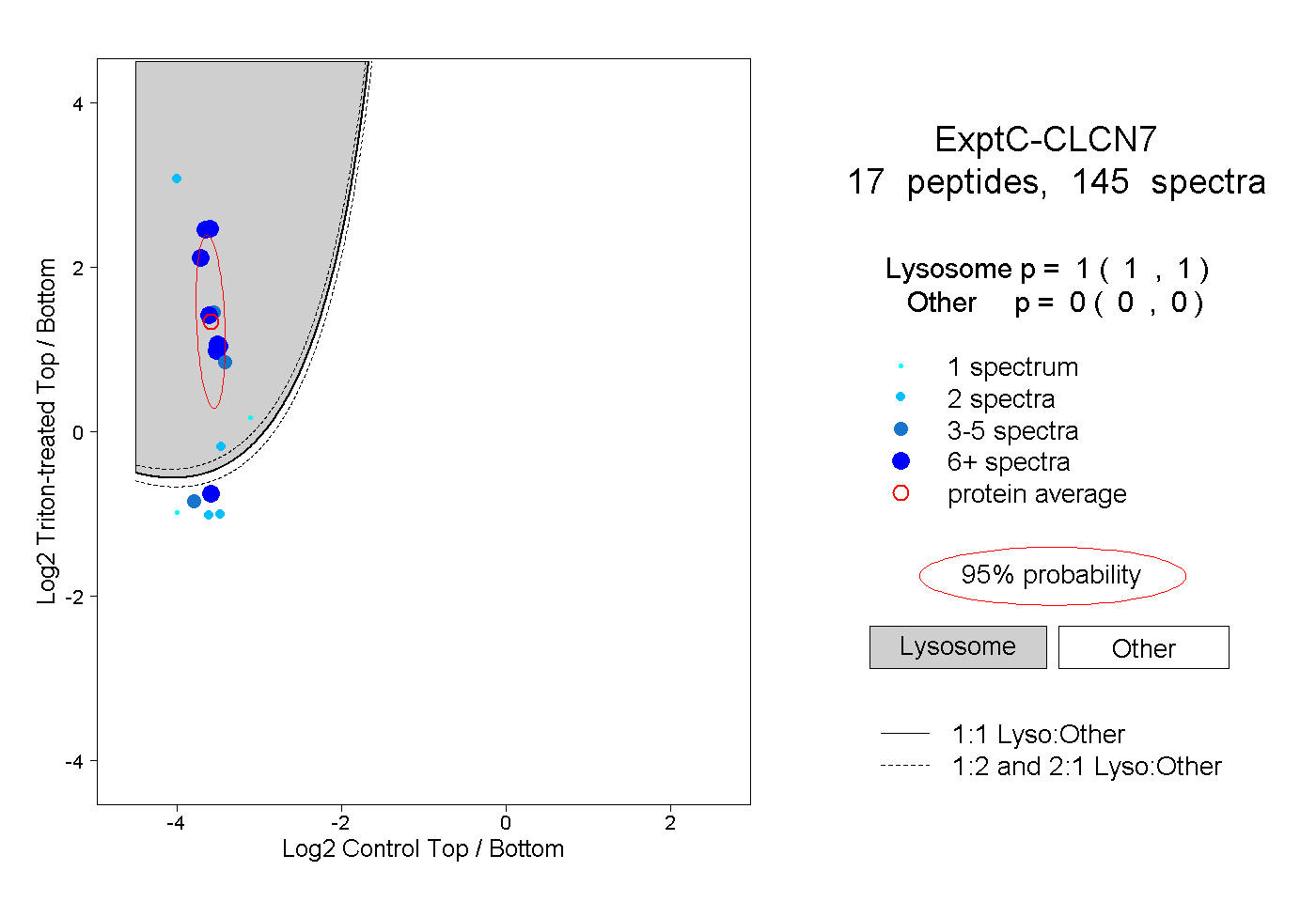 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
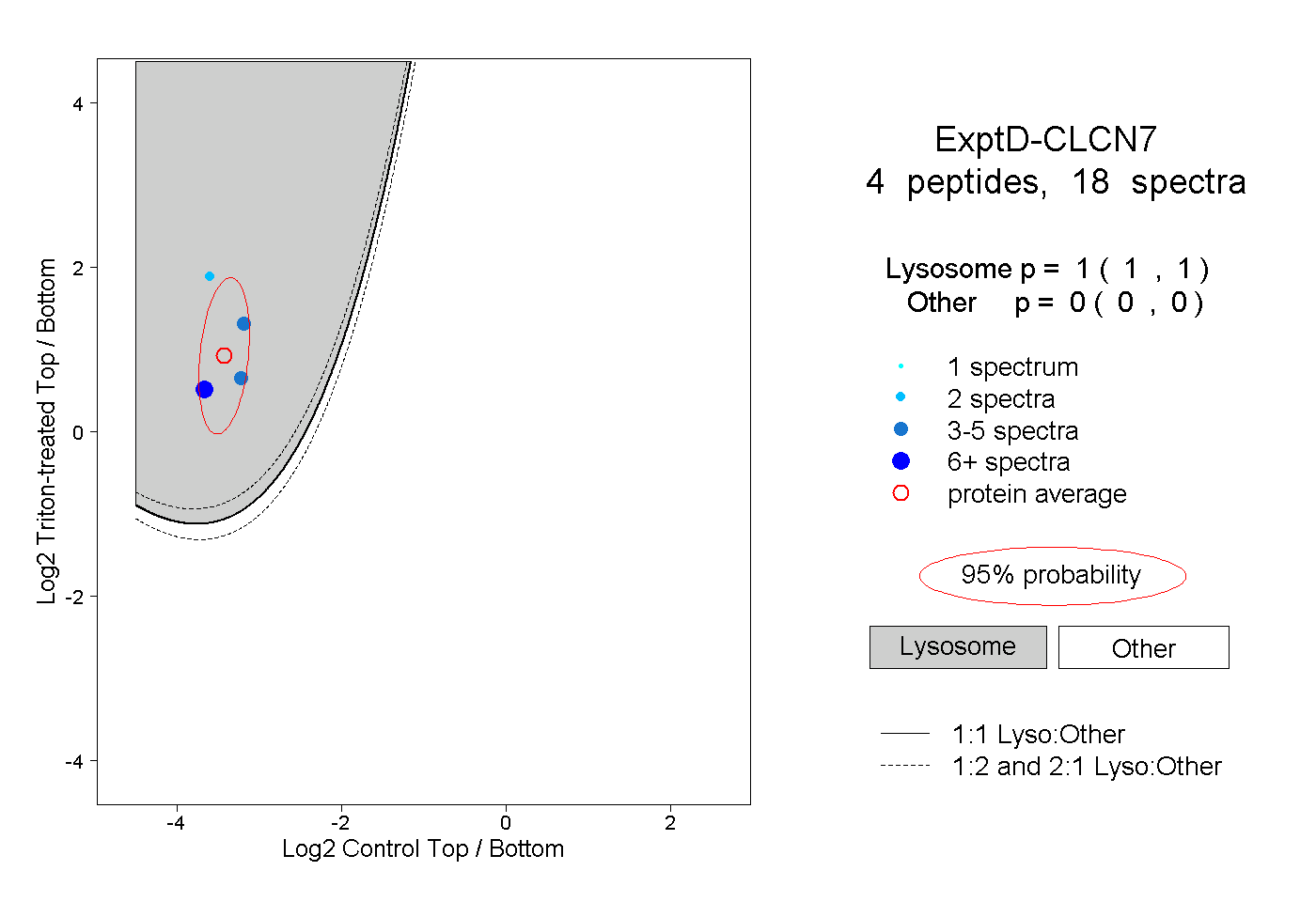 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |