peptides
spectra
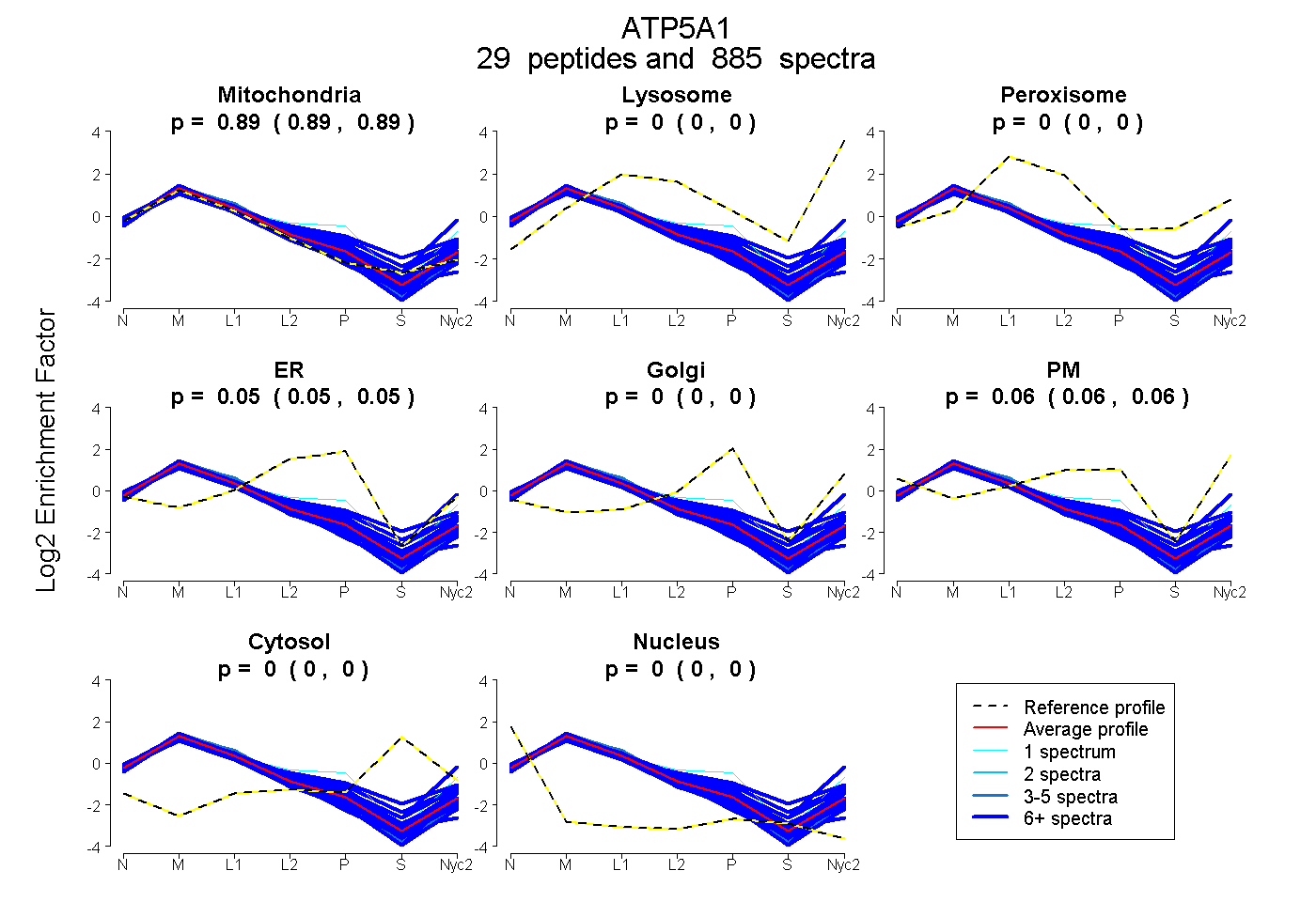
0.893 | 0.894
0.000 | 0.000
0.000 | 0.000
0.046 | 0.049
0.000 | 0.000
0.056 | 0.060
0.000 | 0.000
0.000 | 0.000
peptides
spectra
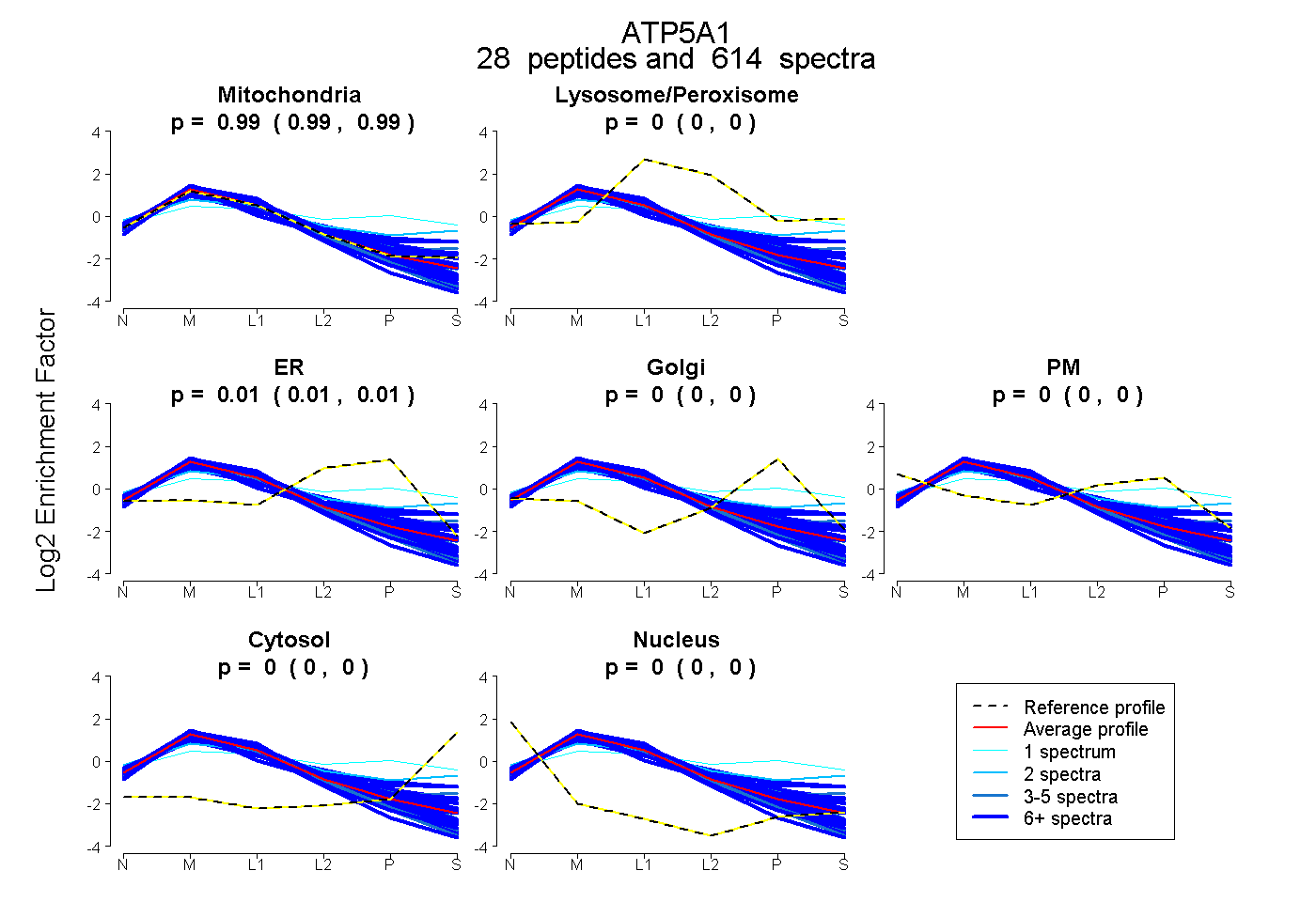
0.986 | 0.988
0.000 | 0.000
0.012 | 0.014
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
885 spectra |
 |
0.894 0.893 | 0.894 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.048 0.046 | 0.049 |
0.000 0.000 | 0.000 |
0.058 0.056 | 0.060 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
614 spectra |
 |
0.987 0.986 | 0.988 |
0.000 0.000 | 0.000 |
0.013 0.012 | 0.014 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 13 spectra, TGTAEMSSILEER | 0.966 | 0.000 | 0.000 | 0.017 | 0.000 | 0.000 | 0.016 | |||
| 3 spectra, EGDLVK | 0.905 | 0.058 | 0.000 | 0.000 | 0.000 | 0.037 | 0.000 | |||
| 19 spectra, LYCIYVAIGQK | 0.879 | 0.072 | 0.000 | 0.001 | 0.047 | 0.000 | 0.000 | |||
| 11 spectra, LTDADAMK | 0.935 | 0.000 | 0.065 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 53 spectra, VLSIGDGIAR | 0.977 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.023 | |||
| 5 spectra, TSIAIDTIINQK | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.016 | |||
| 36 spectra, QAVAYR | 0.961 | 0.000 | 0.039 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QVAGTMK | 0.522 | 0.216 | 0.000 | 0.000 | 0.142 | 0.120 | 0.000 | |||
| 64 spectra, GIRPAINVGLSVSR | 0.985 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.013 | |||
| 20 spectra, LTELLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, HALIIYDDLSK | 0.990 | 0.000 | 0.010 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, STVAQLVK | 0.935 | 0.000 | 0.000 | 0.052 | 0.000 | 0.000 | 0.013 | |||
| 36 spectra, APGIIPR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, ILGADTSVDLEETGR | 0.966 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.034 | |||
| 10 spectra, VVDALGNAIDGK | 0.838 | 0.054 | 0.030 | 0.000 | 0.077 | 0.000 | 0.000 | |||
| 8 spectra, NVQAEEMVEFSSGLK | 0.662 | 0.138 | 0.000 | 0.138 | 0.000 | 0.062 | 0.000 | |||
| 1 spectrum, FESAFLSHVVSQHQSLLGNIR | 0.240 | 0.378 | 0.000 | 0.286 | 0.000 | 0.096 | 0.000 | |||
| 26 spectra, ELIIGDR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 34 spectra, EAYPGDVFYLHSR | 0.843 | 0.074 | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, EPMQTGIK | 0.916 | 0.000 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, FNDGTDEK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 56 spectra, VGSAAQTR | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.033 | |||
| 45 spectra, LELAQYR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, GMSLNLEPDNVGVVVFGNDK | 0.693 | 0.138 | 0.000 | 0.107 | 0.000 | 0.062 | 0.000 | |||
| 5 spectra, TGAIVDVPVGDELLGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 67 spectra, QMSLLLR | 0.979 | 0.000 | 0.021 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, ISEQSDAK | 0.932 | 0.000 | 0.037 | 0.031 | 0.000 | 0.000 | 0.000 | |||
| 47 spectra, AVDSLVPIGR | 0.983 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.017 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3307 spectra |
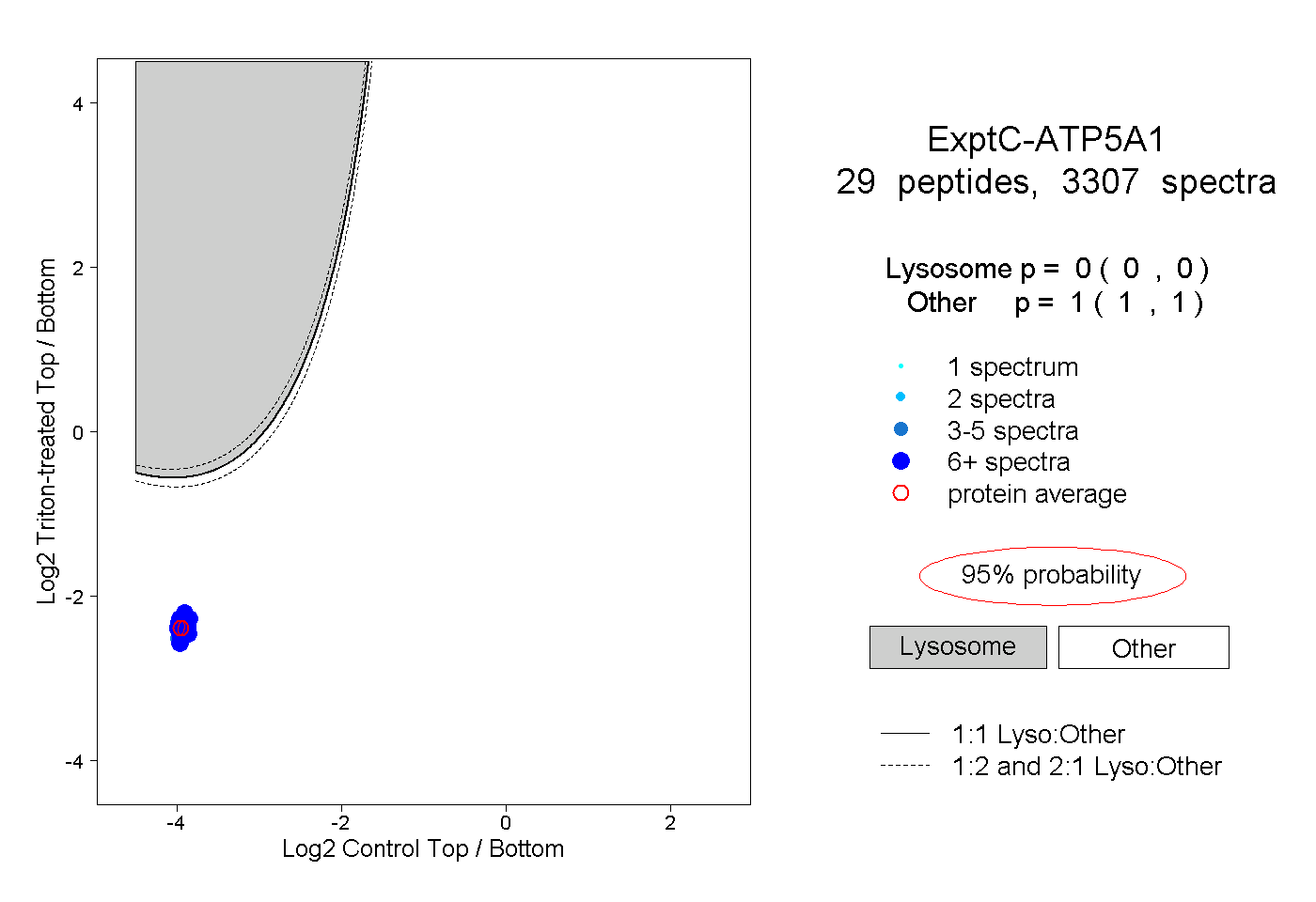 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
262 spectra |
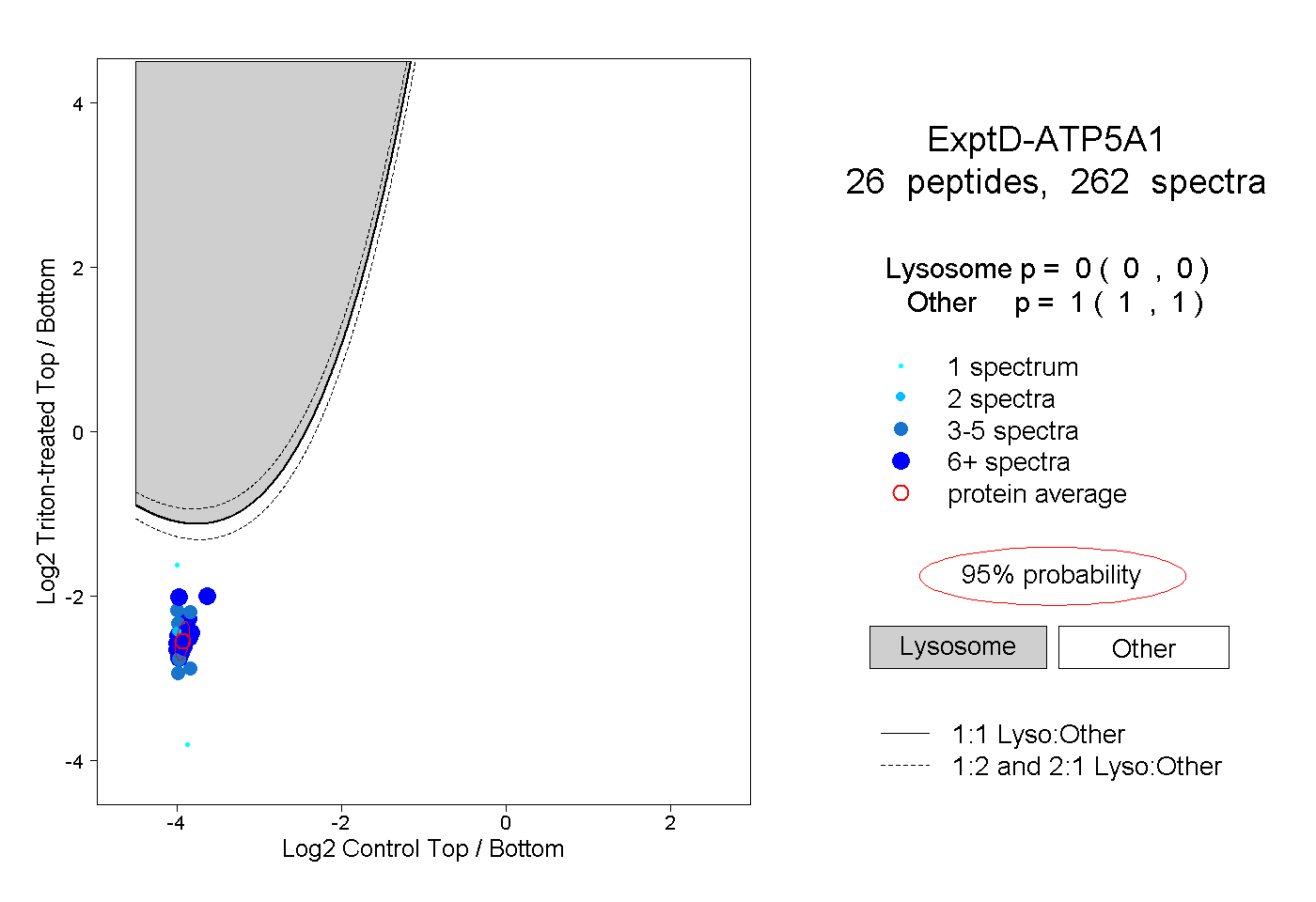 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |