peptides
spectra
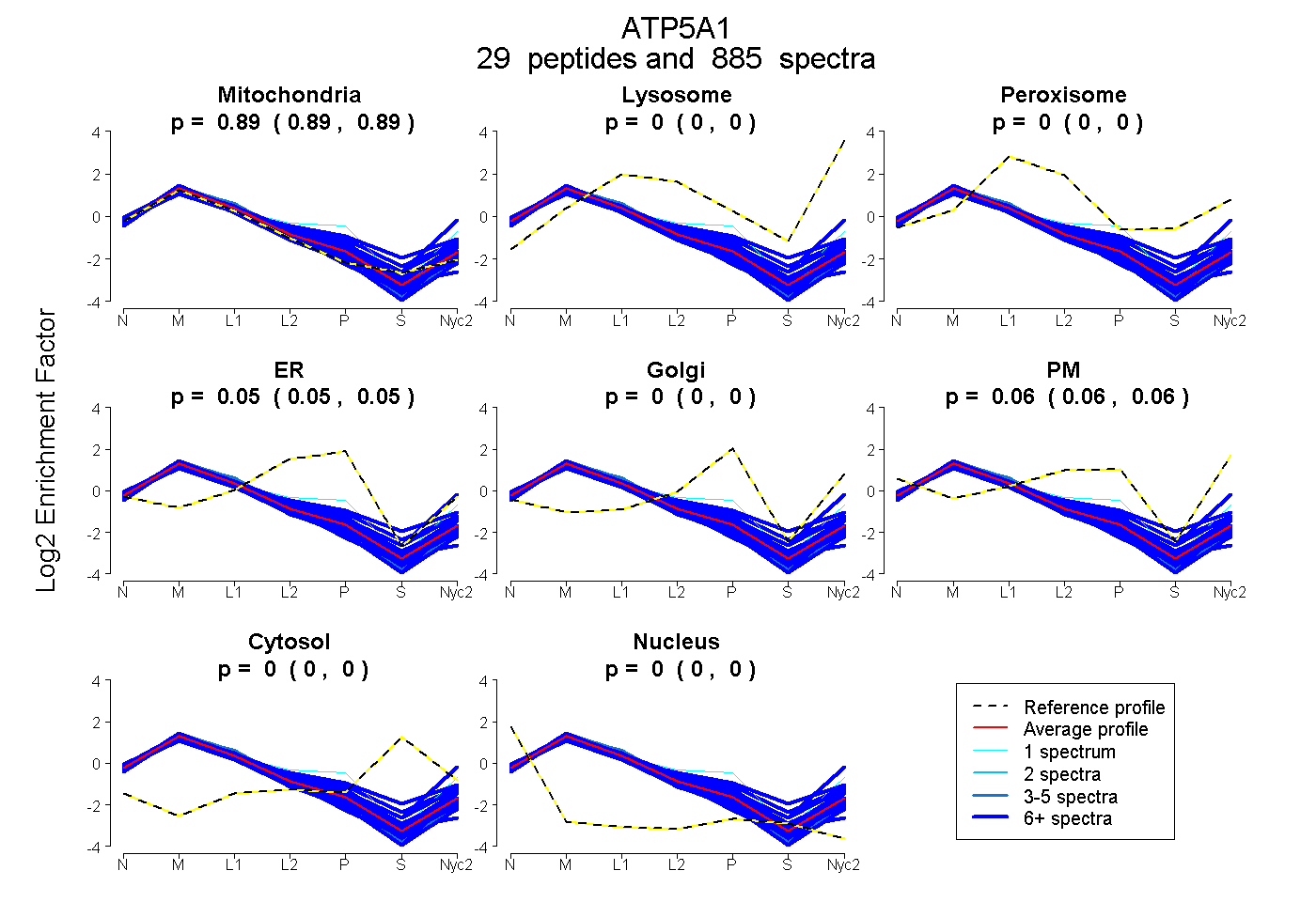
0.893 | 0.894
0.000 | 0.000
0.000 | 0.000
0.046 | 0.049
0.000 | 0.000
0.056 | 0.060
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
885 spectra |
 |
0.894 0.893 | 0.894 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.048 0.046 | 0.049 |
0.000 0.000 | 0.000 |
0.058 0.056 | 0.060 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 11 spectra, GPVGSK | 0.934 | 0.000 | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EGDLVK | 0.600 | 0.000 | 0.000 | 0.098 | 0.000 | 0.302 | 0.000 | 0.000 | ||
| 7 spectra, LYCIYVAIGQK | 0.986 | 0.000 | 0.000 | 0.011 | 0.000 | 0.000 | 0.000 | 0.002 | ||
| 38 spectra, LTDADAMK | 0.955 | 0.000 | 0.000 | 0.045 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 69 spectra, VLSIGDGIAR | 0.798 | 0.000 | 0.000 | 0.074 | 0.020 | 0.109 | 0.000 | 0.000 | ||
| 10 spectra, TSIAIDTIINQK | 0.796 | 0.018 | 0.000 | 0.000 | 0.040 | 0.147 | 0.000 | 0.000 | ||
| 90 spectra, GIRPAINVGLSVSR | 0.935 | 0.000 | 0.000 | 0.065 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 25 spectra, STVAQLVK | 0.938 | 0.000 | 0.000 | 0.062 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 58 spectra, APGIIPR | 0.915 | 0.000 | 0.000 | 0.057 | 0.000 | 0.028 | 0.000 | 0.000 | ||
| 14 spectra, NVQAEEMVEFSSGLK | 0.858 | 0.000 | 0.000 | 0.142 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, EPMQTGIK | 0.868 | 0.000 | 0.000 | 0.104 | 0.000 | 0.029 | 0.000 | 0.000 | ||
| 5 spectra, FNDGTDEK | 0.923 | 0.000 | 0.000 | 0.016 | 0.019 | 0.042 | 0.000 | 0.000 | ||
| 68 spectra, VGSAAQTR | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | ||
| 34 spectra, LELAQYR | 0.847 | 0.000 | 0.000 | 0.000 | 0.038 | 0.115 | 0.000 | 0.000 | ||
| 4 spectra, QGQYSPMAIEEQVAVIYAGVR | 0.993 | 0.000 | 0.000 | 0.007 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 32 spectra, QMSLLLR | 0.705 | 0.212 | 0.000 | 0.000 | 0.000 | 0.082 | 0.000 | 0.000 | ||
| 4 spectra, ISEQSDAK | 0.893 | 0.000 | 0.000 | 0.012 | 0.033 | 0.062 | 0.000 | 0.000 | ||
| 61 spectra, AVDSLVPIGR | 0.944 | 0.000 | 0.000 | 0.054 | 0.000 | 0.002 | 0.000 | 0.000 | ||
| 49 spectra, TGTAEMSSILEER | 0.943 | 0.041 | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 | 0.000 | ||
| 46 spectra, QAVAYR | 0.963 | 0.000 | 0.000 | 0.000 | 0.000 | 0.037 | 0.000 | 0.000 | ||
| 25 spectra, QVAGTMK | 0.949 | 0.000 | 0.000 | 0.051 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 36 spectra, LTELLK | 0.924 | 0.000 | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, HALIIYDDLSK | 0.660 | 0.016 | 0.121 | 0.000 | 0.188 | 0.005 | 0.010 | 0.000 | ||
| 19 spectra, ILGADTSVDLEETGR | 0.929 | 0.000 | 0.000 | 0.071 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 27 spectra, VVDALGNAIDGK | 0.851 | 0.000 | 0.000 | 0.076 | 0.000 | 0.073 | 0.000 | 0.000 | ||
| 58 spectra, ELIIGDR | 0.881 | 0.000 | 0.000 | 0.000 | 0.000 | 0.119 | 0.000 | 0.000 | ||
| 38 spectra, EAYPGDVFYLHSR | 0.727 | 0.009 | 0.073 | 0.000 | 0.126 | 0.065 | 0.000 | 0.000 | ||
| 3 spectra, GMSLNLEPDNVGVVVFGNDK | 0.939 | 0.000 | 0.000 | 0.061 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, TGAIVDVPVGDELLGR | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | 0.070 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
614 spectra |
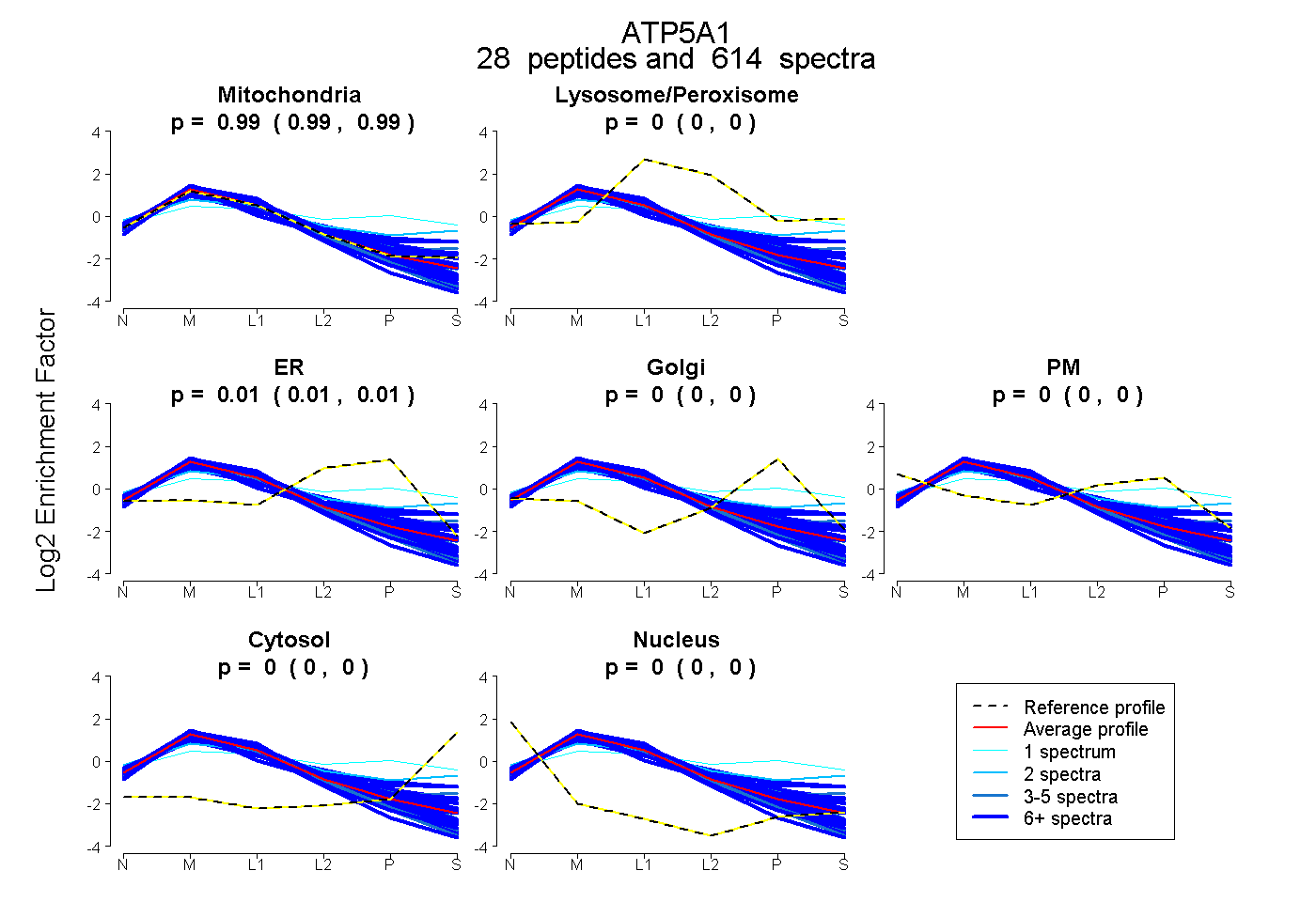 |
0.987 0.986 | 0.988 |
0.000 0.000 | 0.000 |
0.013 0.012 | 0.014 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3307 spectra |
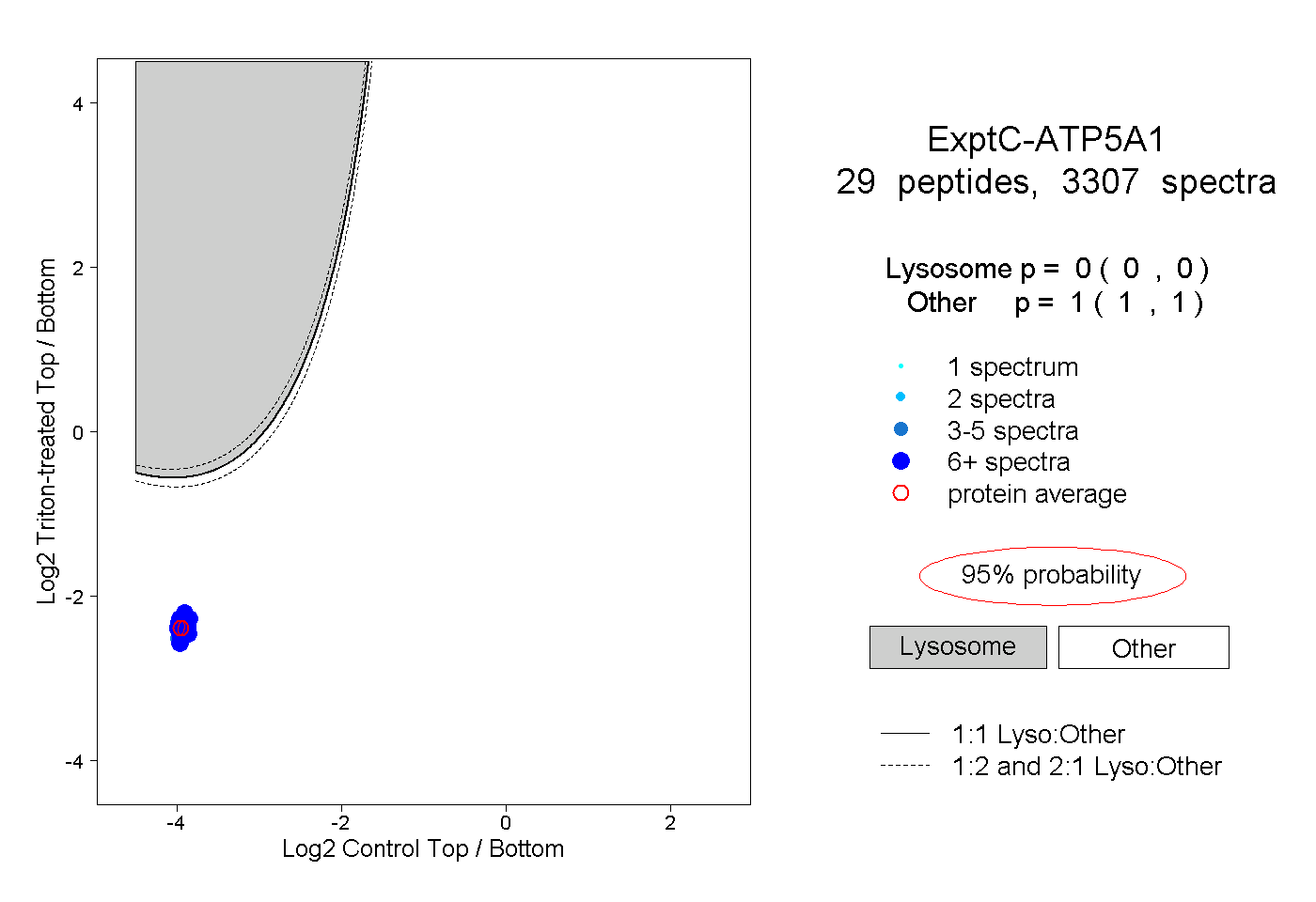 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
262 spectra |
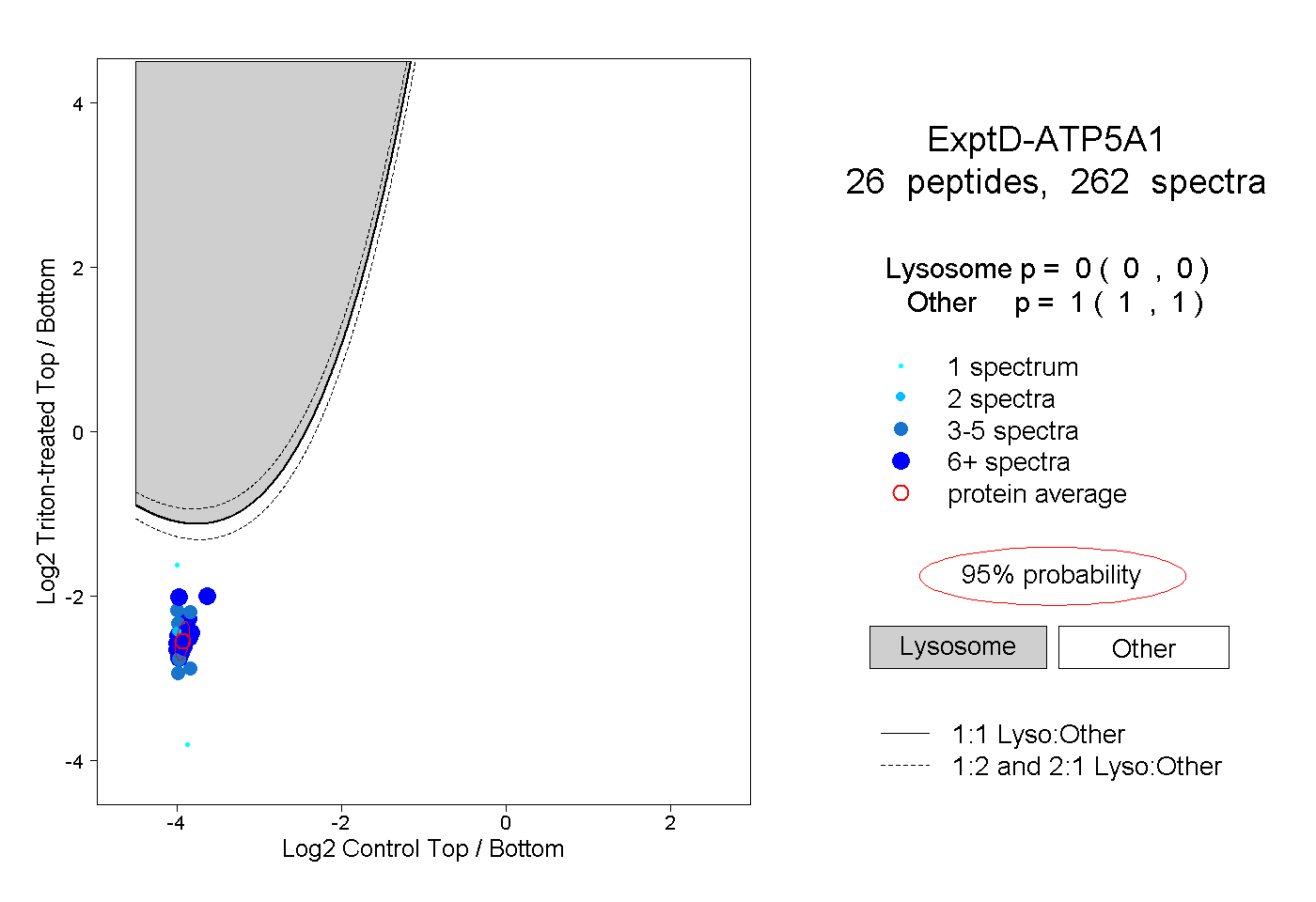 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |