peptides
spectra
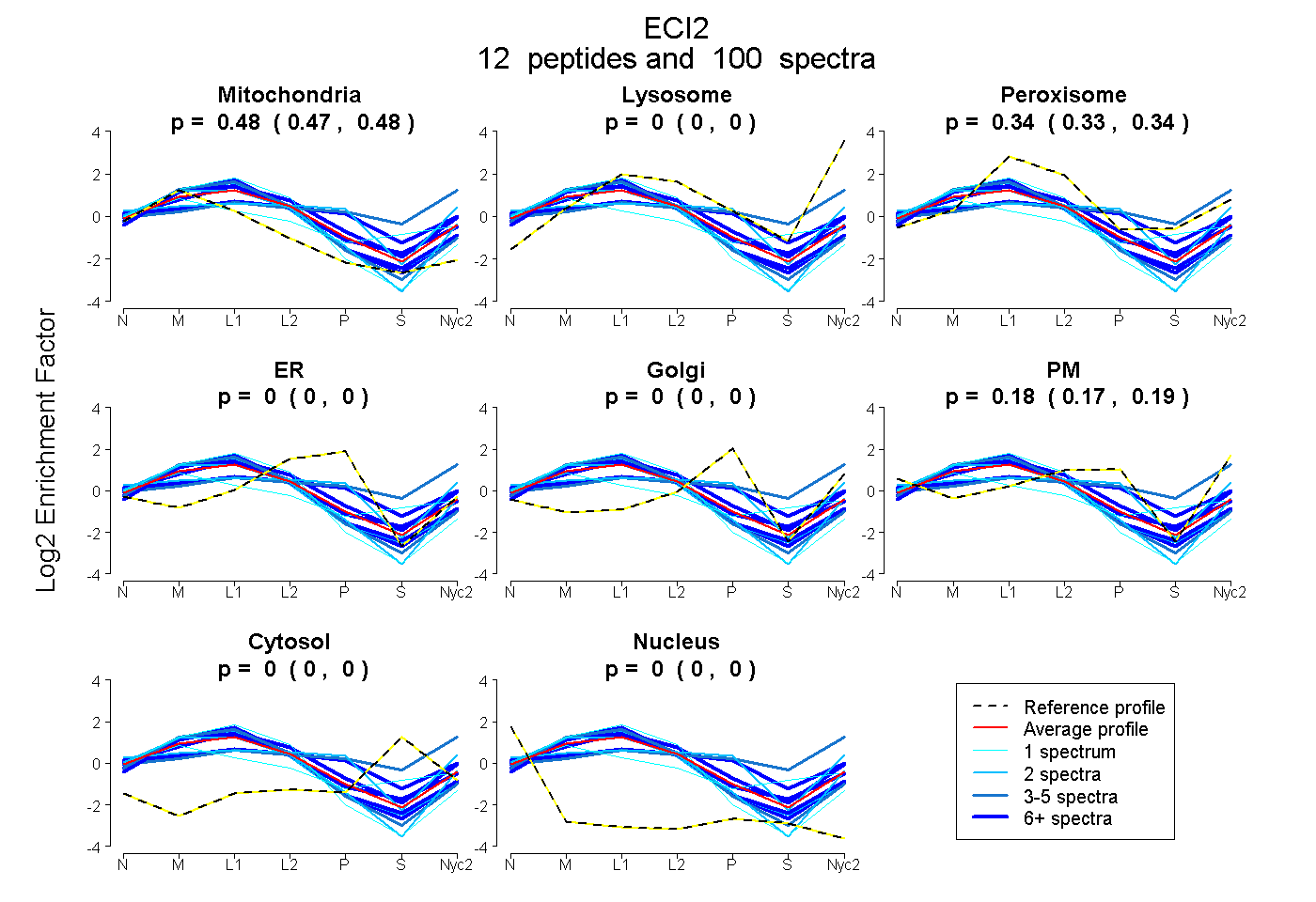
0.471 | 0.484
0.000 | 0.000
0.328 | 0.345
0.000 | 0.000
0.000 | 0.000
0.175 | 0.193
0.000 | 0.000
0.000 | 0.000
peptides
spectra
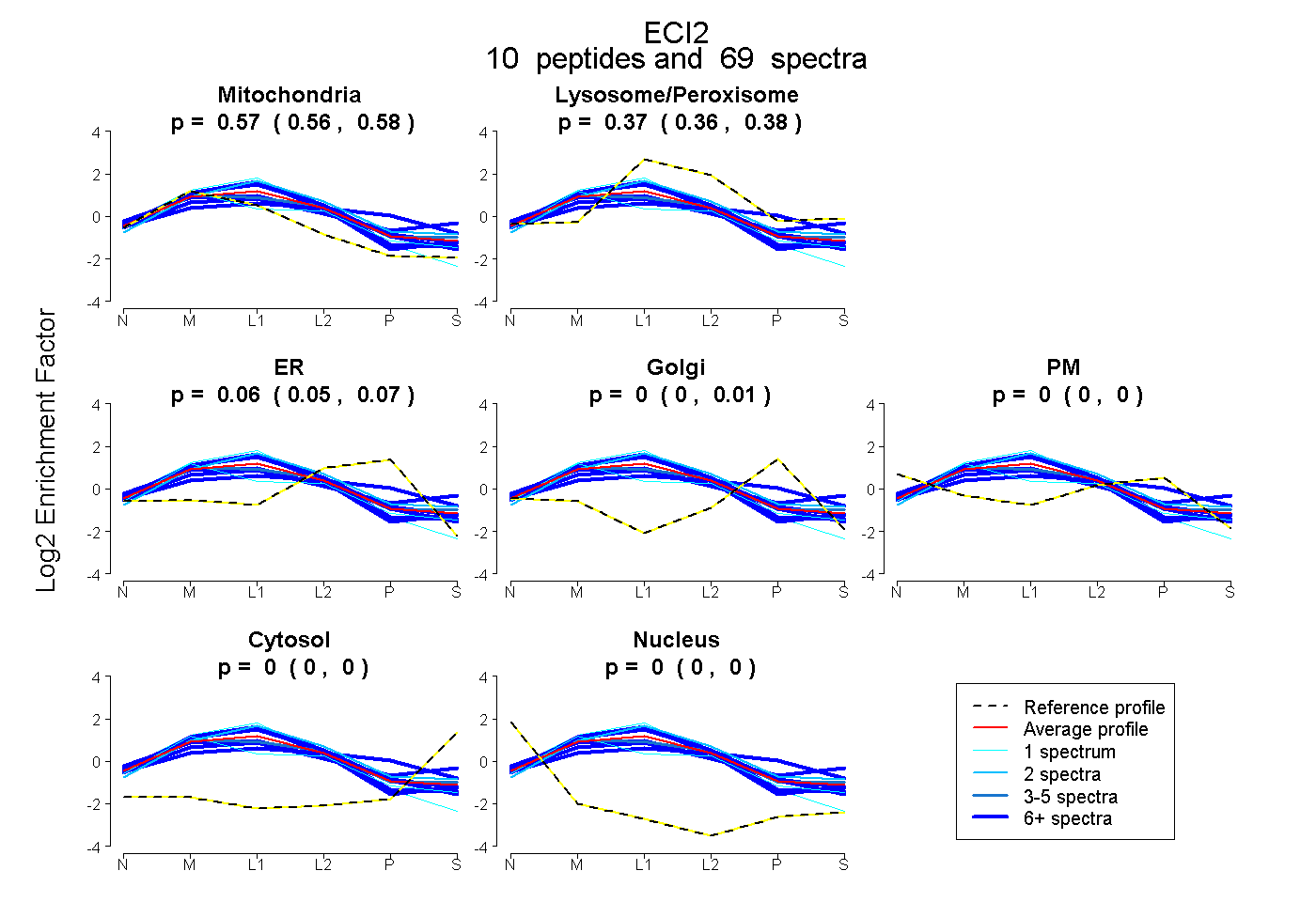
0.560 | 0.576
0.362 | 0.378
0.046 | 0.067
0.000 | 0.007
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
100 spectra |
 |
0.478 0.471 | 0.484 |
0.000 0.000 | 0.000 |
0.338 0.328 | 0.345 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.184 0.175 | 0.193 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
69 spectra |
 |
0.569 0.560 | 0.576 |
0.370 0.362 | 0.378 |
0.061 0.046 | 0.067 |
0.000 0.000 | 0.007 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, LPPNSMR | 0.561 | 0.345 | 0.054 | 0.000 | 0.033 | 0.008 | 0.000 | |||
| 8 spectra, GILVTSEGGITK | 0.549 | 0.299 | 0.000 | 0.000 | 0.151 | 0.000 | 0.000 | |||
| 14 spectra, LHAVNEEECTTLR | 0.242 | 0.450 | 0.000 | 0.302 | 0.000 | 0.006 | 0.000 | |||
| 7 spectra, ITFNRPSK | 0.620 | 0.380 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QNYVDLVSSLSSSSEASSQGK | 0.688 | 0.150 | 0.162 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, LYALYK | 0.573 | 0.406 | 0.020 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DPGNEVK | 0.696 | 0.304 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 19 spectra, GAIVLR | 0.633 | 0.367 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ATQQDFENAMNQVK | 0.374 | 0.429 | 0.000 | 0.074 | 0.000 | 0.123 | 0.000 | |||
| 2 spectra, NAITFQMYQDIILALK | 0.470 | 0.519 | 0.010 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
496 spectra |
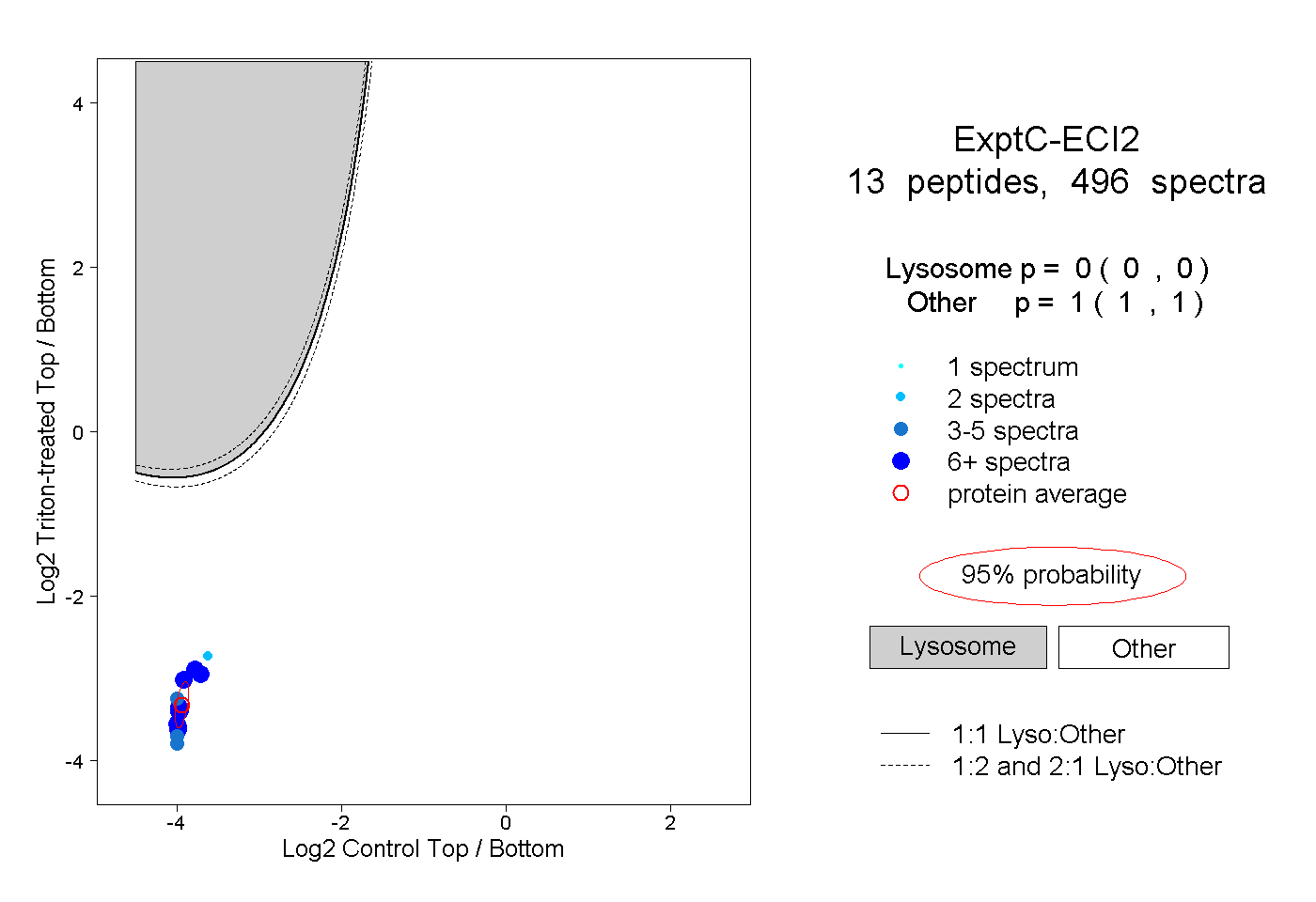 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
45 spectra |
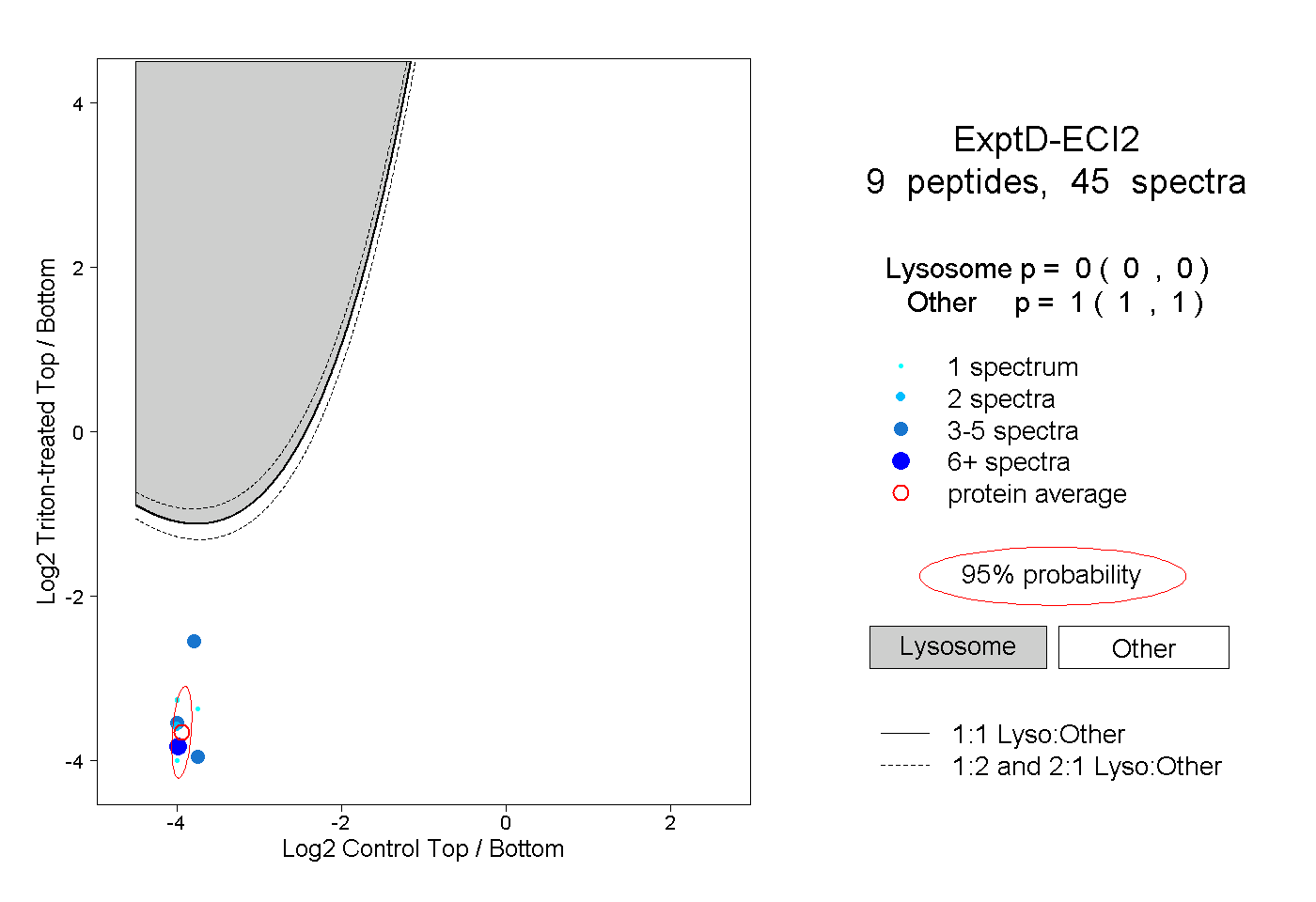 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |