peptides
spectra
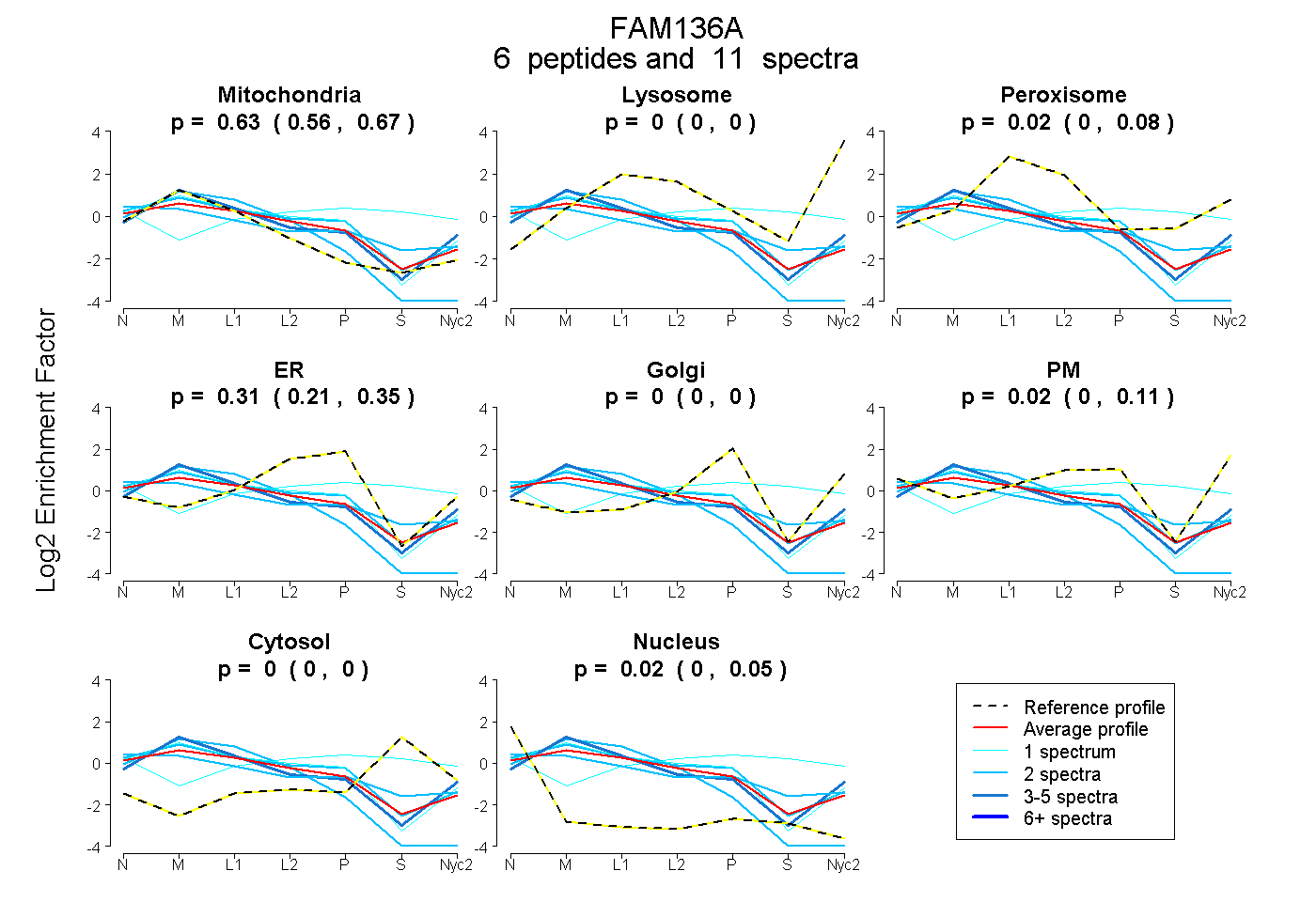
0.559 | 0.671
0.000 | 0.000
0.000 | 0.079
0.206 | 0.350
0.000 | 0.004
0.000 | 0.111
0.000 | 0.000
0.000 | 0.053
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
11 spectra |
 |
0.631 0.559 | 0.671 |
0.000 0.000 | 0.000 |
0.021 0.000 | 0.079 |
0.310 0.206 | 0.350 |
0.000 0.000 | 0.004 |
0.018 0.000 | 0.111 |
0.000 0.000 | 0.000 |
0.021 0.000 | 0.053 |
| 2 spectra, VQEAVDAMVK | 0.498 | 0.000 | 0.048 | 0.108 | 0.036 | 0.122 | 0.101 | 0.087 | ||
| 2 spectra, CTMHCNDK | 0.597 | 0.000 | 0.000 | 0.335 | 0.000 | 0.069 | 0.000 | 0.000 | ||
| 3 spectra, MQGLMFR | 0.689 | 0.038 | 0.000 | 0.055 | 0.058 | 0.159 | 0.000 | 0.000 | ||
| 1 spectrum, ESLSSIGK | 0.573 | 0.000 | 0.000 | 0.325 | 0.000 | 0.103 | 0.000 | 0.000 | ||
| 2 spectra, CSANCCEDNQASMQQVHQCIER | 0.958 | 0.000 | 0.000 | 0.034 | 0.000 | 0.000 | 0.000 | 0.008 | ||
| 1 spectrum, CHAPLAQAQALVTSELER | 0.000 | 0.000 | 0.155 | 0.158 | 0.000 | 0.244 | 0.443 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
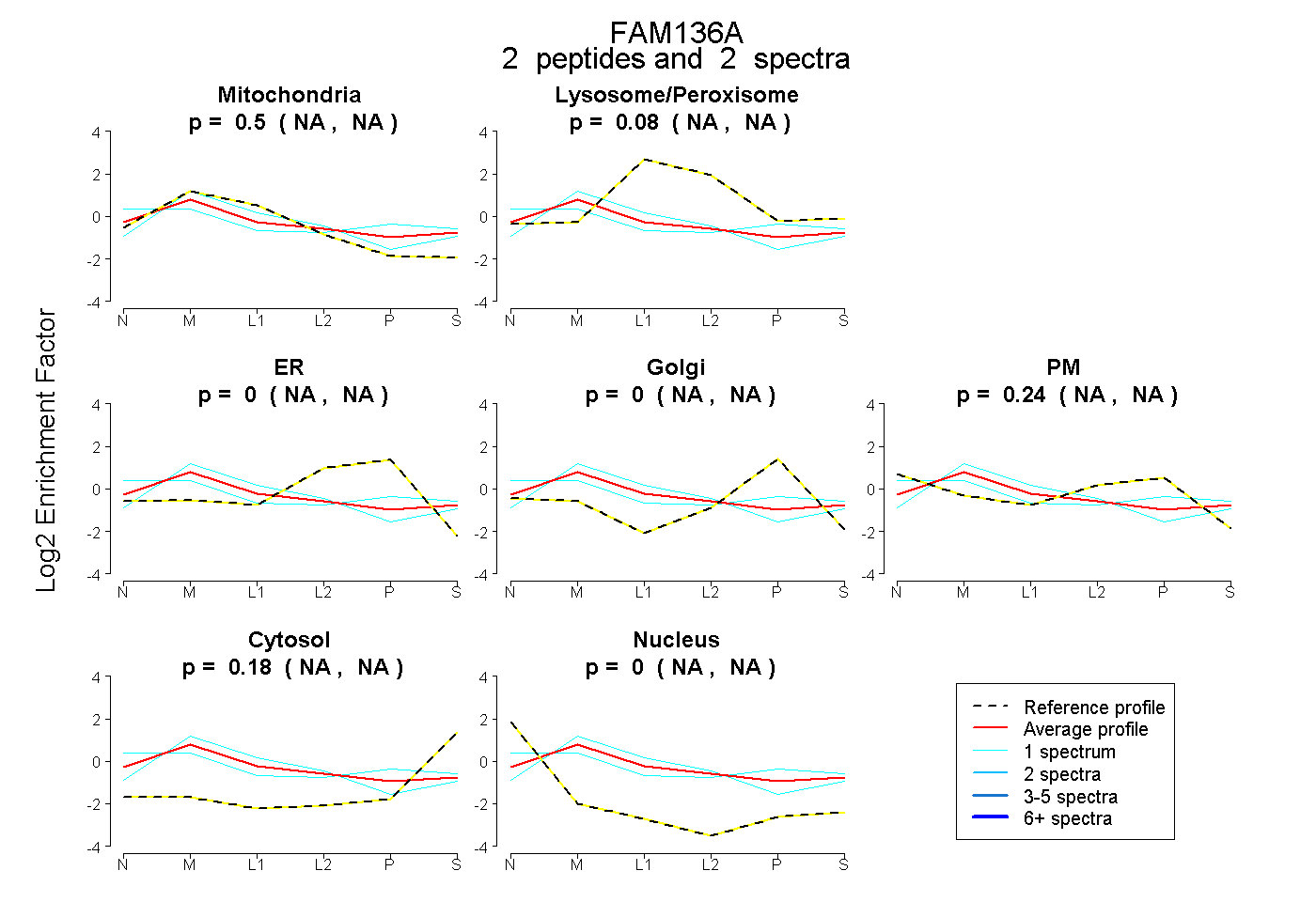 |
0.504 NA | NA |
0.077 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.240 NA | NA |
0.179 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
54 spectra |
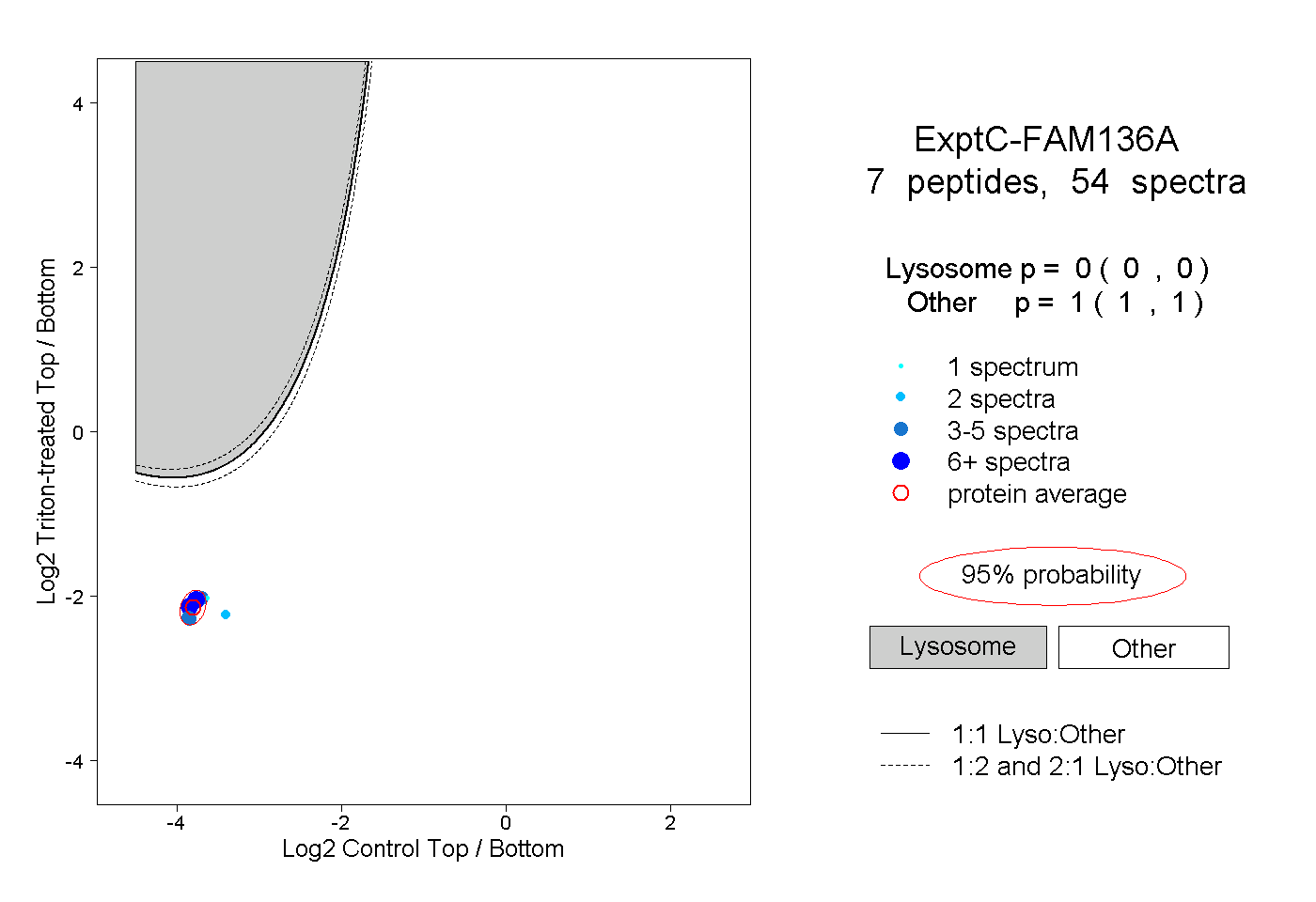 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
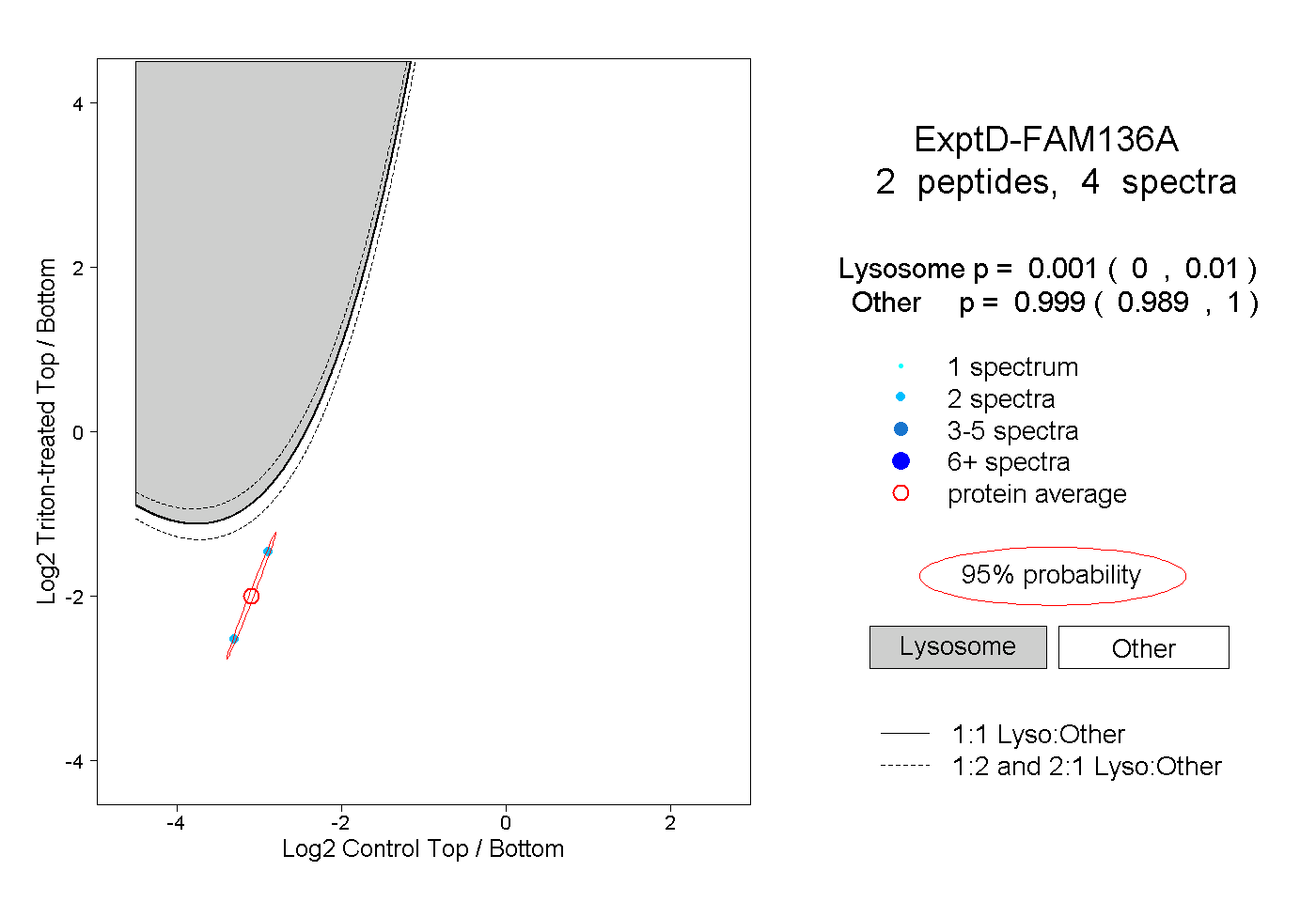 |
0.001 0.000 | 0.010 |
0.999 0.989 | 1.000 |