peptides
spectra
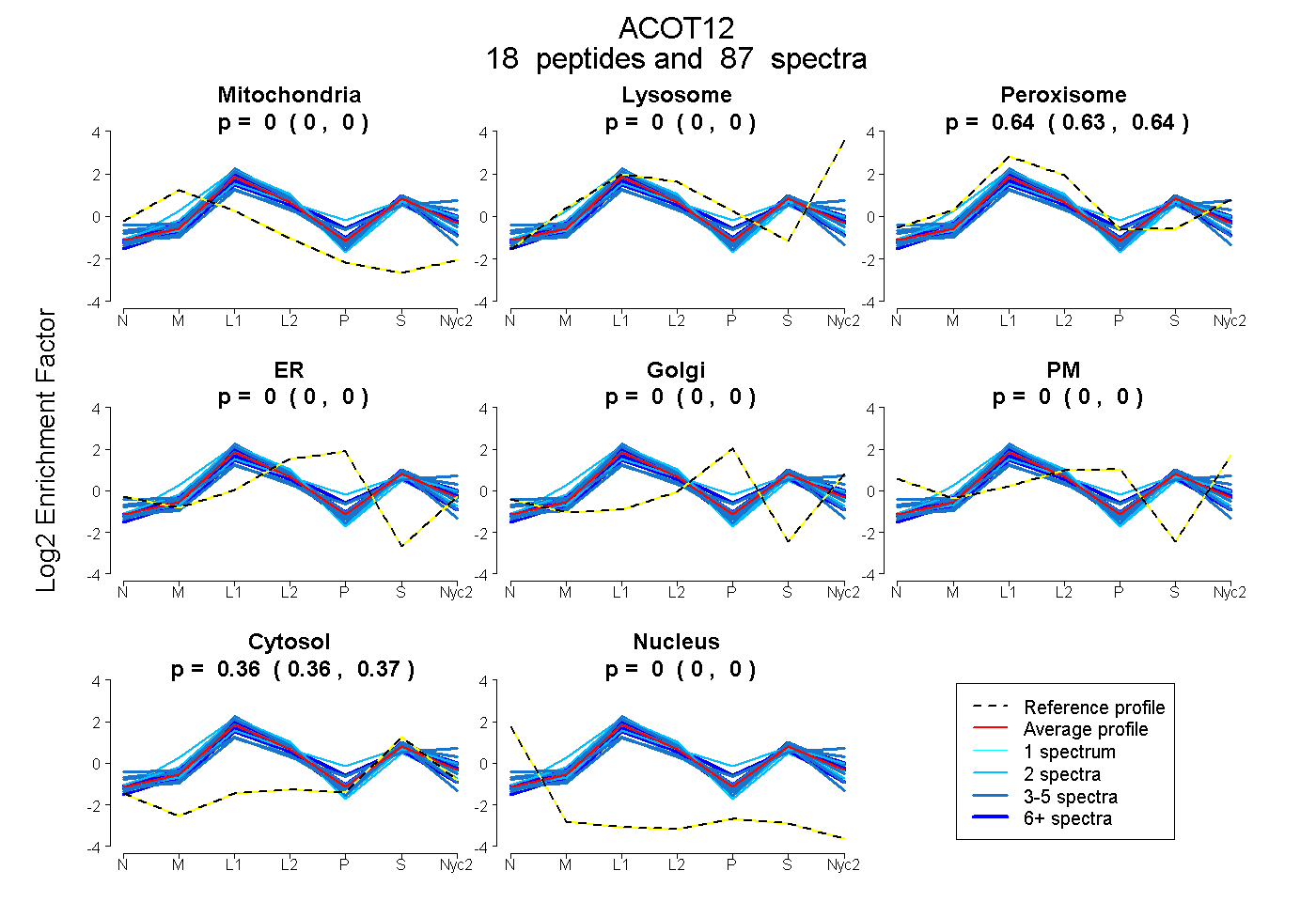
0.000 | 0.000
0.000 | 0.000
0.634 | 0.638
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.362 | 0.365
0.000 | 0.000
peptides
spectra
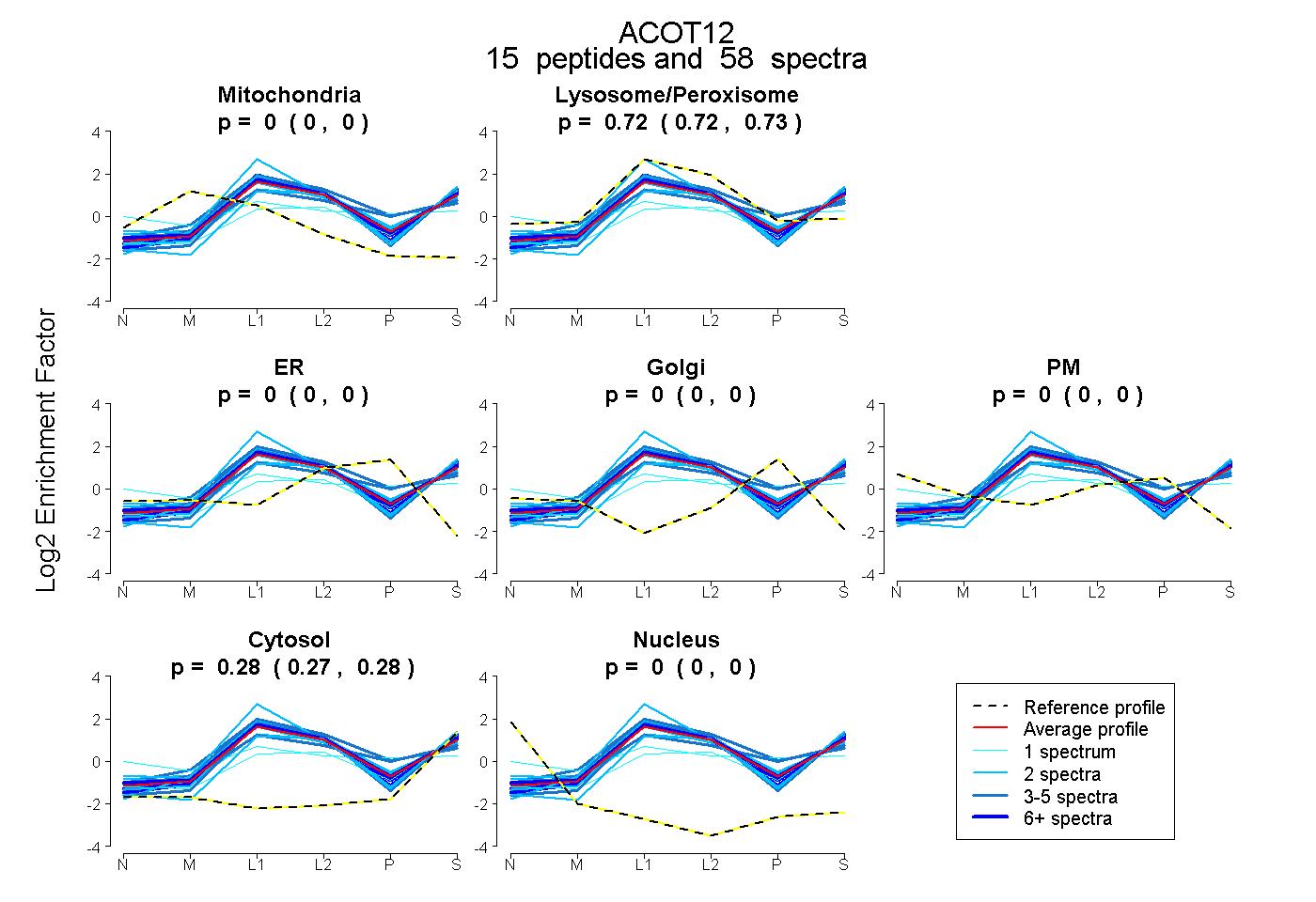
0.000 | 0.000
0.718 | 0.725
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.274 | 0.281
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
87 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.636 0.634 | 0.638 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.364 0.362 | 0.365 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.722 0.718 | 0.725 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.278 0.274 | 0.281 |
0.000 0.000 | 0.000 |
| 2 spectra, GPSTVGDR | 0.000 | 0.689 | 0.000 | 0.000 | 0.000 | 0.311 | 0.000 | |||
| 3 spectra, FIENATHDGLK | 0.000 | 0.834 | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | |||
| 1 spectrum, SVDMFK | 0.000 | 0.524 | 0.000 | 0.000 | 0.000 | 0.476 | 0.000 | |||
| 13 spectra, IGQIVTIR | 0.000 | 0.717 | 0.000 | 0.000 | 0.000 | 0.283 | 0.000 | |||
| 2 spectra, YVISHK | 0.000 | 0.618 | 0.000 | 0.000 | 0.000 | 0.382 | 0.000 | |||
| 4 spectra, VEAFDCR | 0.000 | 0.695 | 0.000 | 0.000 | 0.000 | 0.305 | 0.000 | |||
| 7 spectra, DFVVLVSQR | 0.000 | 0.748 | 0.000 | 0.000 | 0.000 | 0.252 | 0.000 | |||
| 2 spectra, EVPLGTQWDISK | 0.000 | 0.728 | 0.000 | 0.000 | 0.000 | 0.272 | 0.000 | |||
| 2 spectra, SGWEITTTLEK | 0.000 | 0.708 | 0.000 | 0.000 | 0.000 | 0.292 | 0.000 | |||
| 1 spectrum, GSISNTNVEALK | 0.000 | 0.510 | 0.000 | 0.061 | 0.216 | 0.213 | 0.000 | |||
| 2 spectra, VAYHLLSDFTK | 0.000 | 0.819 | 0.000 | 0.000 | 0.000 | 0.181 | 0.000 | |||
| 10 spectra, YQGAIAR | 0.000 | 0.740 | 0.000 | 0.000 | 0.000 | 0.260 | 0.000 | |||
| 3 spectra, SIEEAAASCIK | 0.000 | 0.692 | 0.000 | 0.022 | 0.000 | 0.286 | 0.000 | |||
| 2 spectra, QVGSPAR | 0.000 | 0.787 | 0.000 | 0.000 | 0.000 | 0.213 | 0.000 | |||
| 4 spectra, LCHGHPFLK | 0.000 | 0.772 | 0.000 | 0.000 | 0.000 | 0.228 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
324 spectra |
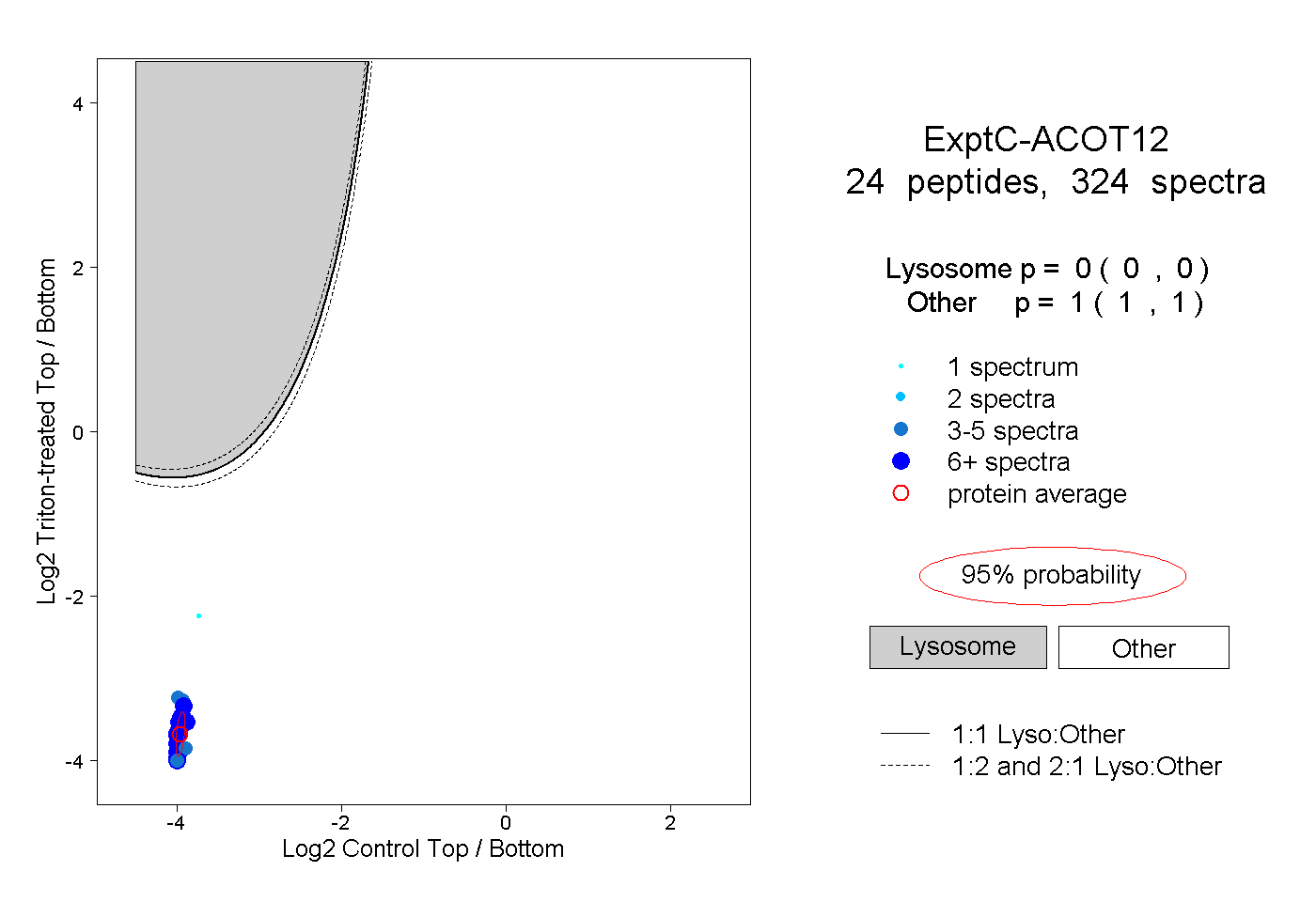 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
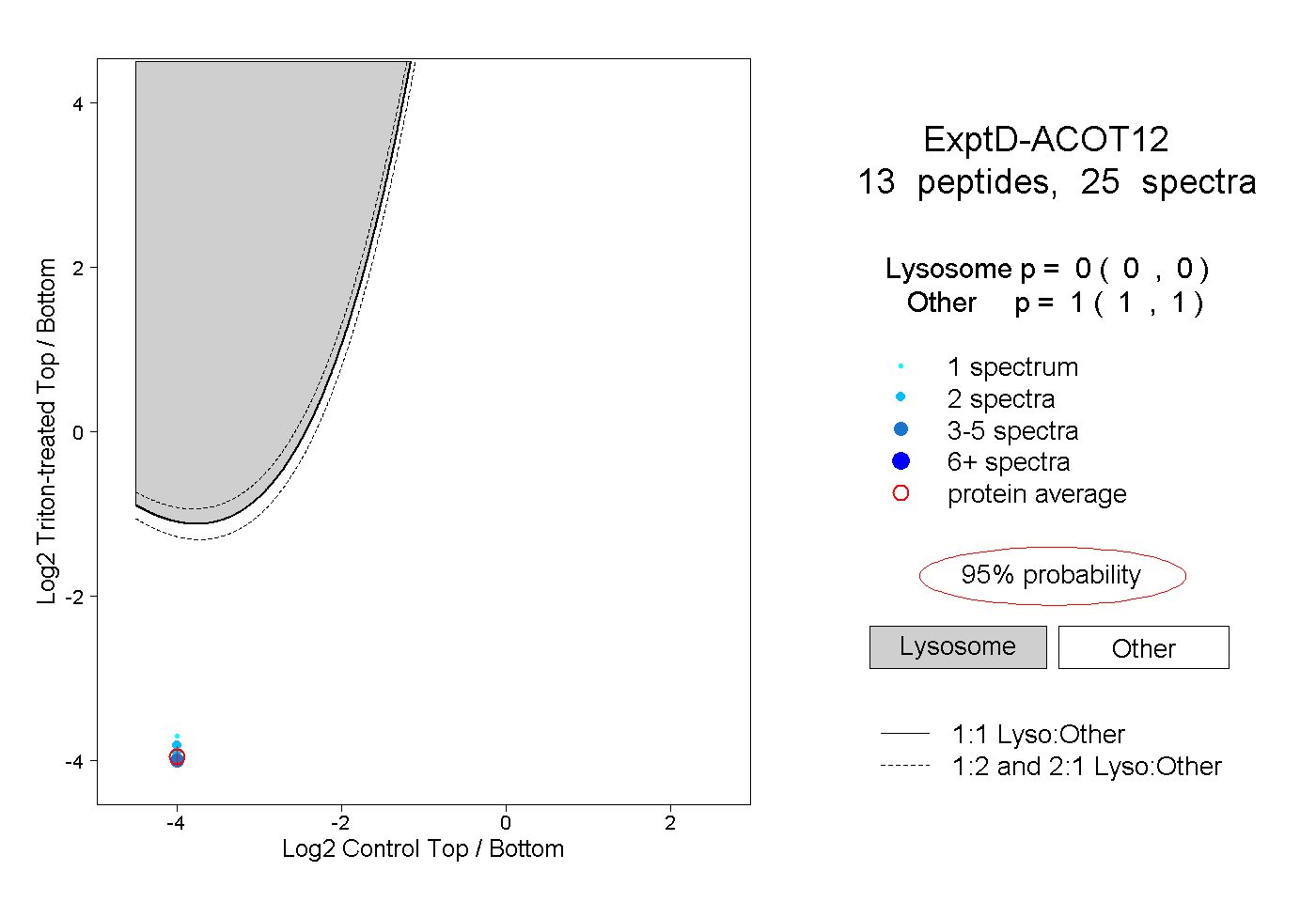 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |