peptides
spectra

0.229 | 0.257
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.668 | 0.685
0.065 | 0.089
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.245 0.229 | 0.257 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.677 0.668 | 0.685 |
0.078 0.065 | 0.089 |
| 4 spectra, LVGEIVR | 0.211 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.655 | 0.134 | ||
| 4 spectra, LVQASEELLR | 0.231 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.605 | 0.163 | ||
| 7 spectra, TFLAVKPDGVQR | 0.312 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.608 | 0.080 | ||
| 2 spectra, GDFCVEVGK | 0.234 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.600 | 0.166 | ||
| 5 spectra, EIALWFR | 0.189 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.709 | 0.102 | ||
| 2 spectra, NVIHGSDSVESAQR | 0.000 | 0.000 | 0.048 | 0.239 | 0.000 | 0.000 | 0.713 | 0.000 | ||
| 3 spectra, ERPFYSR | 0.238 | 0.000 | 0.000 | 0.154 | 0.000 | 0.000 | 0.608 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
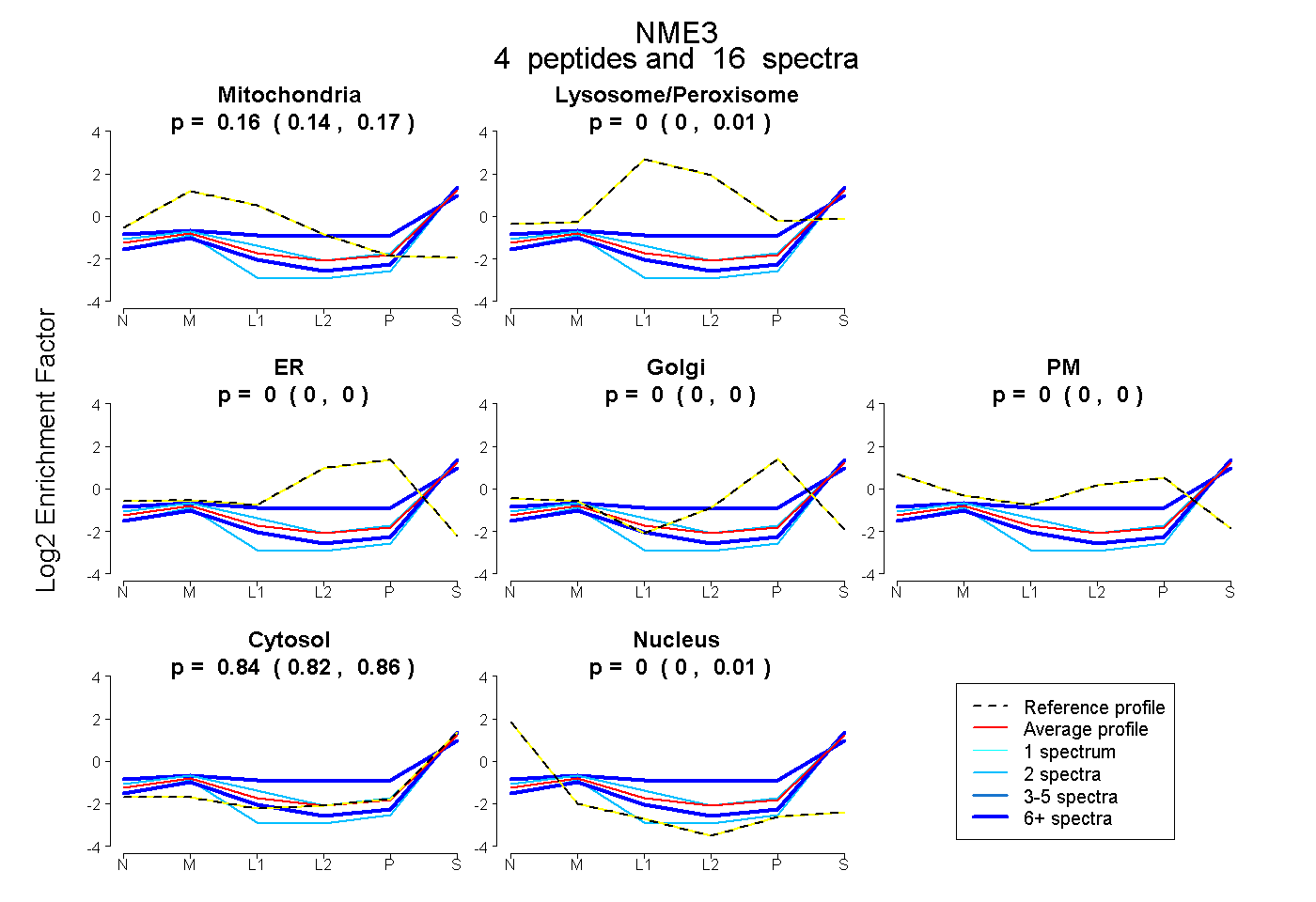 |
0.161 0.135 | 0.175 |
0.000 0.000 | 0.014 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.839 0.815 | 0.856 |
0.000 0.000 | 0.007 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
31 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
 |
0.000 NA | NA |
1.000 NA | NA |