peptides
spectra
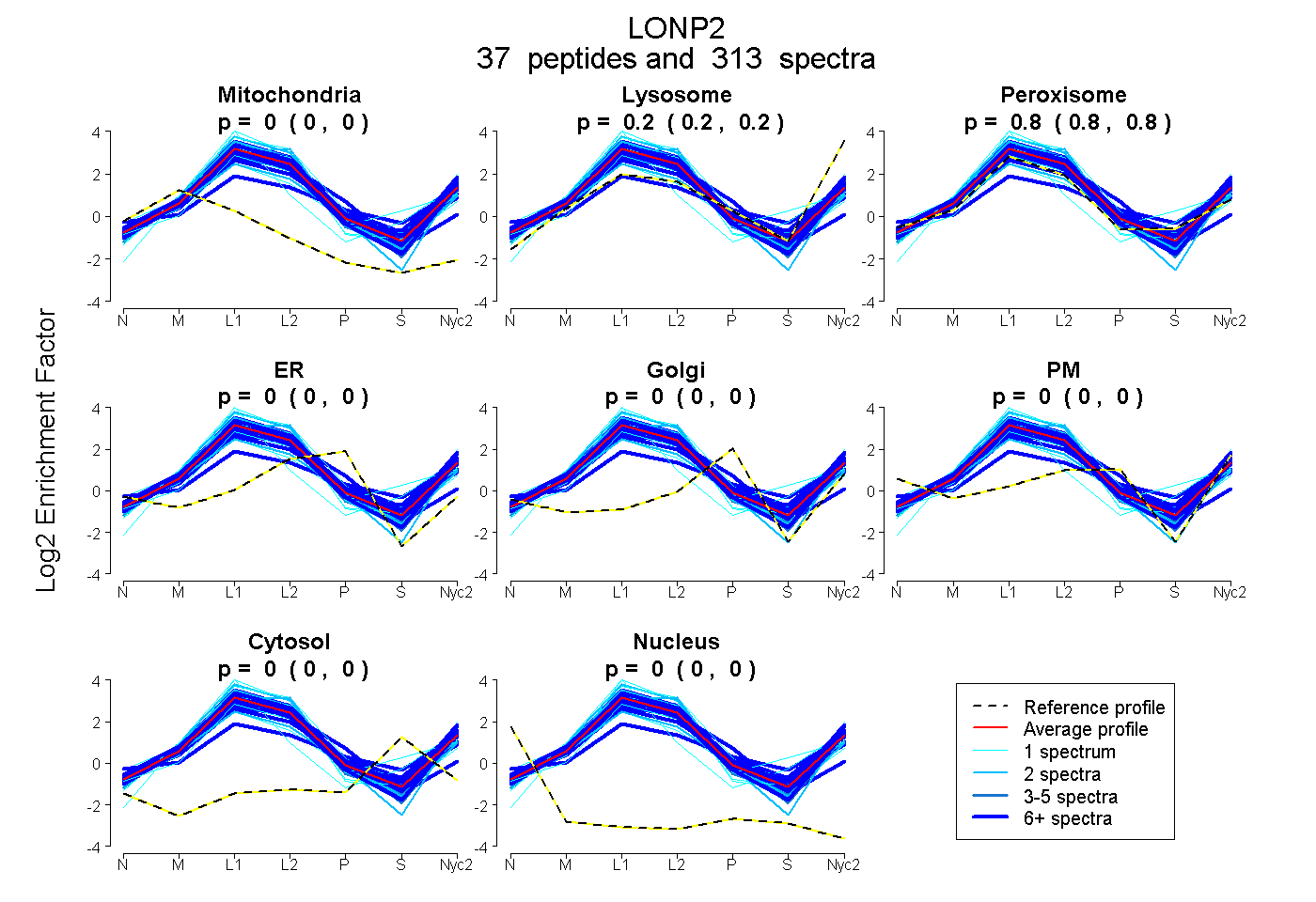
0.000 | 0.000
0.199 | 0.203
0.796 | 0.800
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
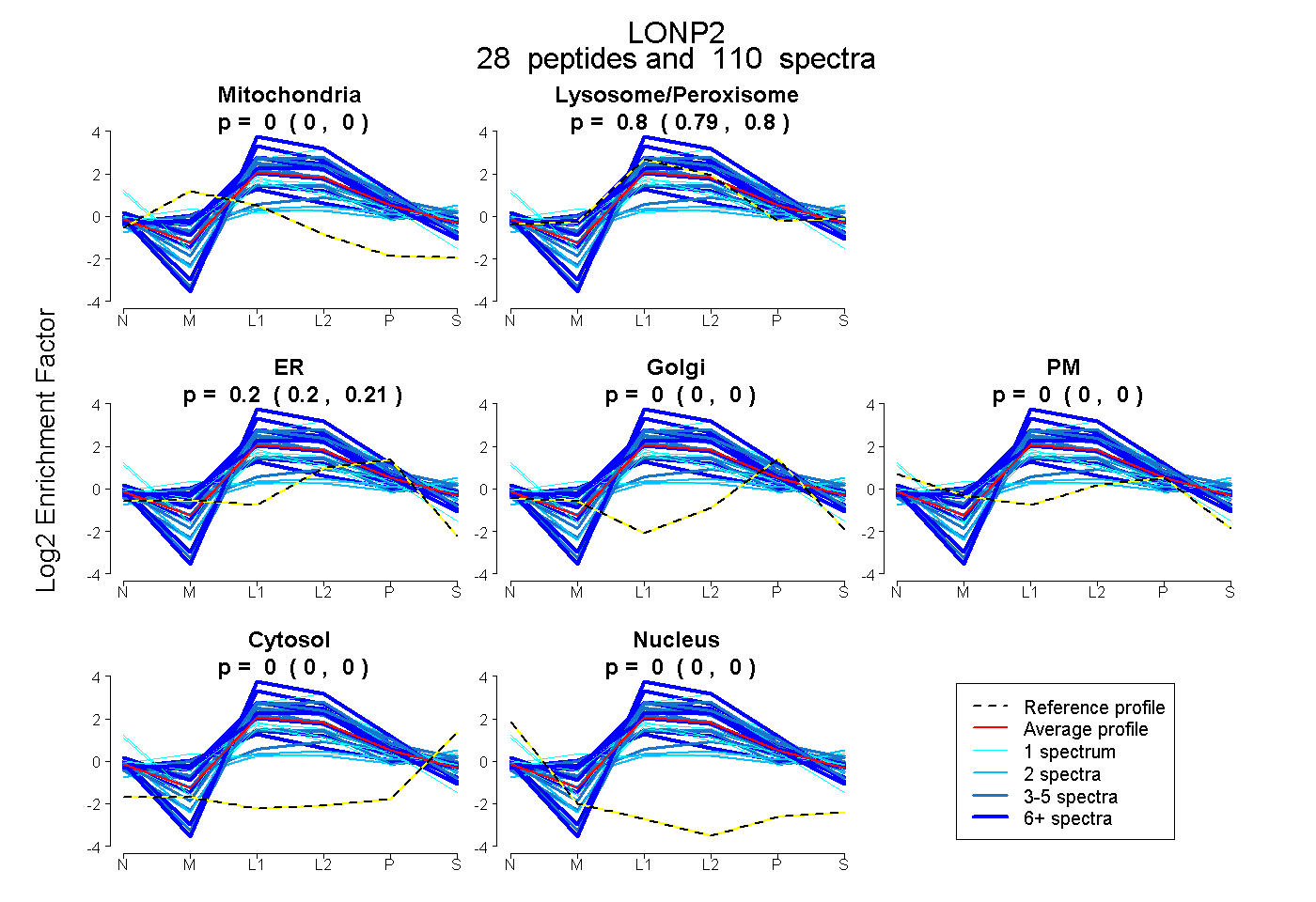
0.000 | 0.000
0.791 | 0.802
0.197 | 0.208
0.000 | 0.000
0.000 | 0.000
0.000 | 0.002
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
313 spectra |
 |
0.000 0.000 | 0.000 |
0.202 0.199 | 0.203 |
0.798 0.796 | 0.800 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
110 spectra |
 |
0.000 0.000 | 0.000 |
0.797 0.791 | 0.802 |
0.203 0.197 | 0.208 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
| 1 spectrum, LEEFPNTCK | 0.000 | 0.687 | 0.000 | 0.000 | 0.183 | 0.000 | 0.129 | |||
| 6 spectra, GLVLPVGGIK | 0.000 | 0.750 | 0.000 | 0.203 | 0.000 | 0.048 | 0.000 | |||
| 5 spectra, FGAICR | 0.000 | 0.909 | 0.045 | 0.046 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, GPILCFVGPPGVGK | 0.000 | 0.595 | 0.000 | 0.325 | 0.000 | 0.080 | 0.000 | |||
| 2 spectra, EKPYPVAEVEQLDR | 0.000 | 0.796 | 0.204 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VLAAHR | 0.000 | 0.846 | 0.154 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, EELGELSEQFYR | 0.000 | 0.762 | 0.017 | 0.190 | 0.000 | 0.031 | 0.000 | |||
| 9 spectra, NLQLVR | 0.000 | 0.953 | 0.047 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LLDGIK | 0.000 | 0.815 | 0.185 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SDVADGEGCK | 0.000 | 0.791 | 0.000 | 0.108 | 0.100 | 0.000 | 0.000 | |||
| 1 spectrum, VAEGQHK | 0.000 | 0.552 | 0.000 | 0.000 | 0.371 | 0.000 | 0.077 | |||
| 1 spectrum, TRPGLTDSK | 0.000 | 0.809 | 0.000 | 0.000 | 0.046 | 0.129 | 0.016 | |||
| 2 spectra, MPQSMPEYALTR | 0.000 | 0.896 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, IEIAHR | 0.000 | 0.854 | 0.038 | 0.000 | 0.000 | 0.108 | 0.000 | |||
| 7 spectra, ESAHLAISWLR | 0.118 | 0.622 | 0.000 | 0.197 | 0.000 | 0.063 | 0.000 | |||
| 8 spectra, VLEYLAVR | 0.000 | 0.715 | 0.285 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, TYVGSMPGR | 0.000 | 0.951 | 0.049 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, MTIPLLVR | 0.000 | 0.908 | 0.092 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IALGGVCDQSDIR | 0.141 | 0.375 | 0.000 | 0.279 | 0.173 | 0.032 | 0.000 | |||
| 11 spectra, IMFVEASR | 0.000 | 0.858 | 0.142 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LLDSLPR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TSSMPEQAHK | 0.000 | 0.920 | 0.080 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, HIIIPQR | 0.000 | 0.896 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, FQIVQVLK | 0.000 | 0.906 | 0.094 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ILLDNDHYAMEK | 0.000 | 0.759 | 0.000 | 0.039 | 0.090 | 0.112 | 0.000 | |||
| 8 spectra, VIAIRPIR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, MEIIQVPGYTQEEK | 0.000 | 0.546 | 0.000 | 0.221 | 0.000 | 0.233 | 0.000 | |||
| 2 spectra, DLEEIPSNVK | 0.000 | 0.446 | 0.000 | 0.000 | 0.244 | 0.309 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1140 spectra |
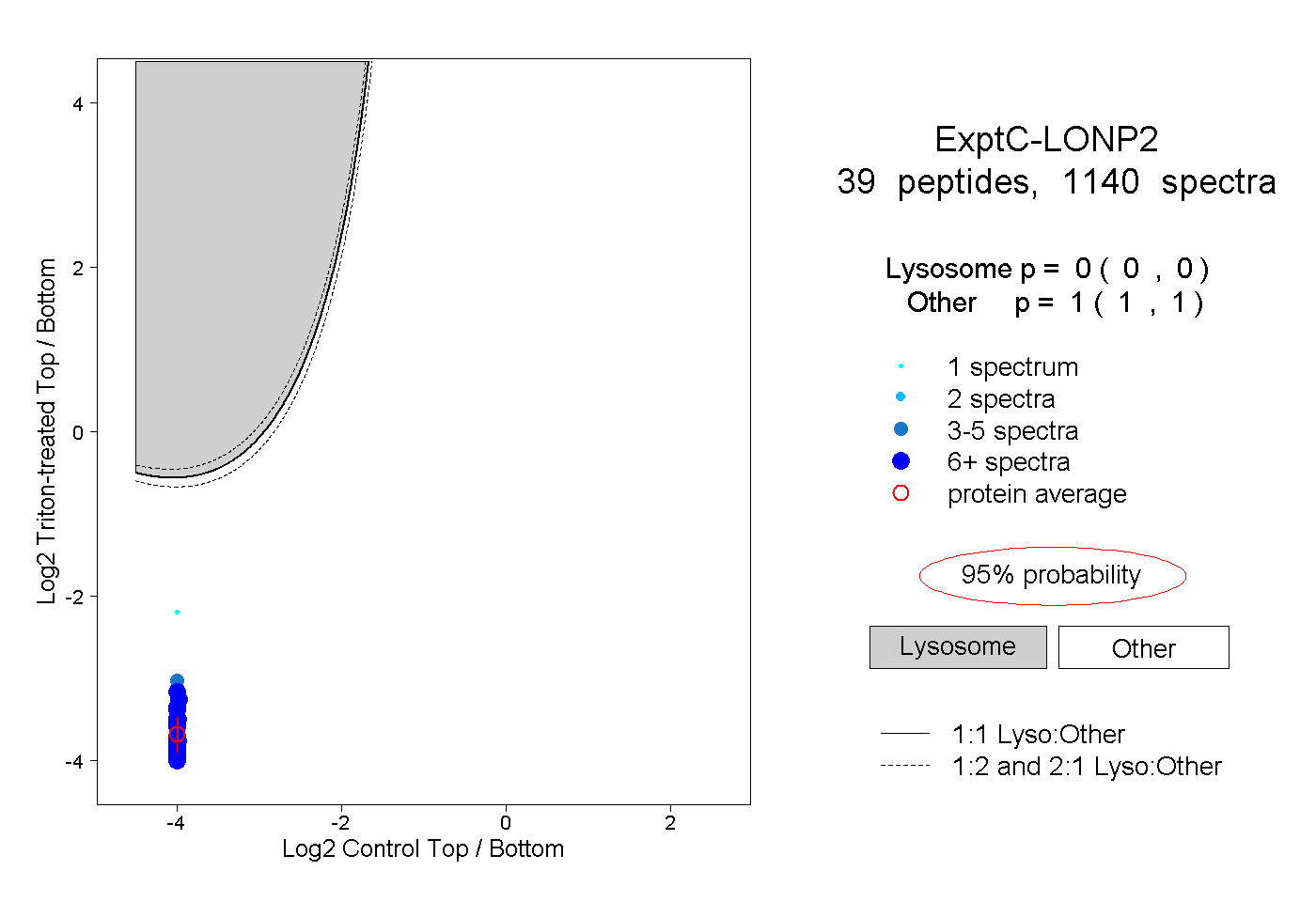 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
107 spectra |
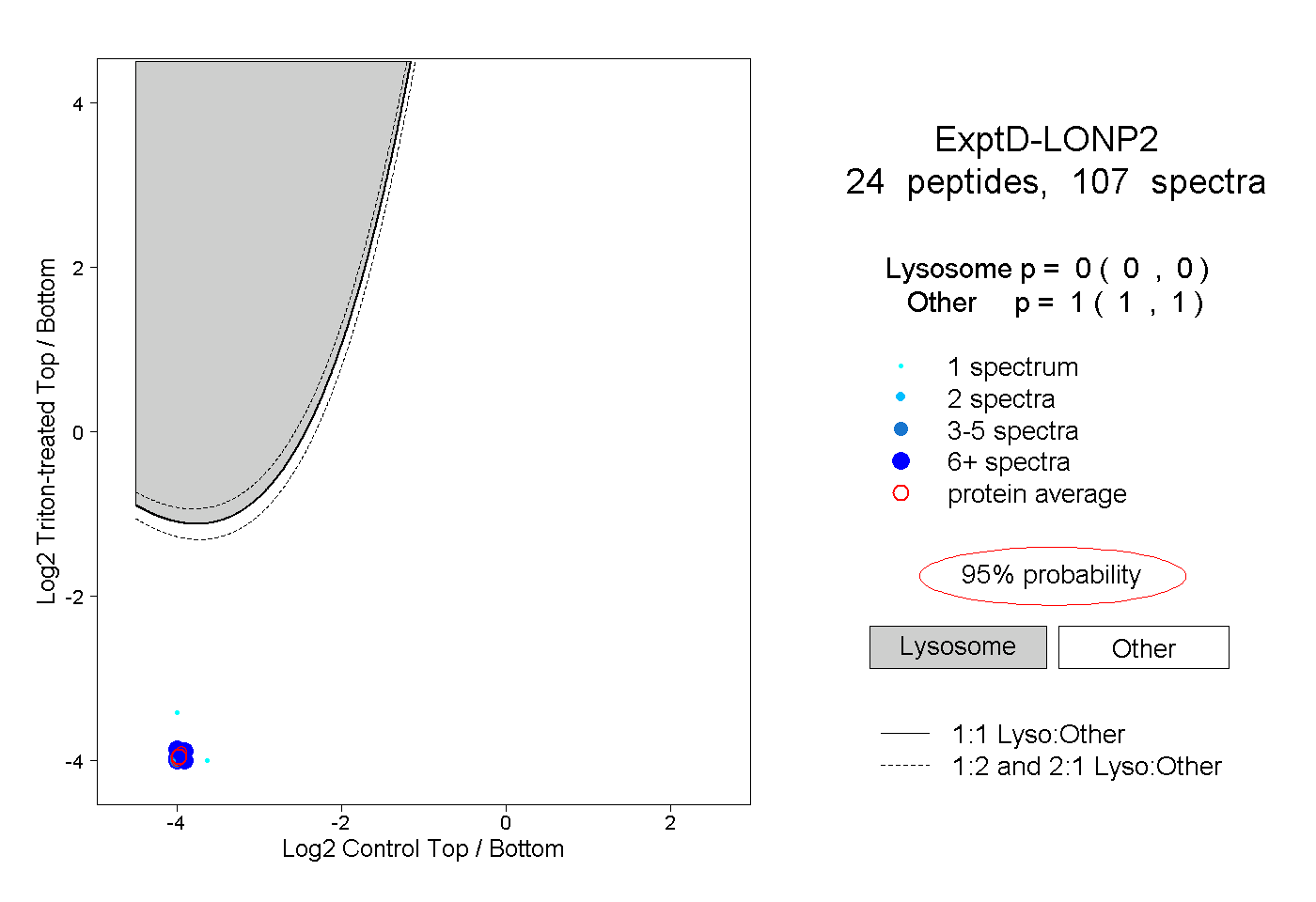 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |