peptides
spectra
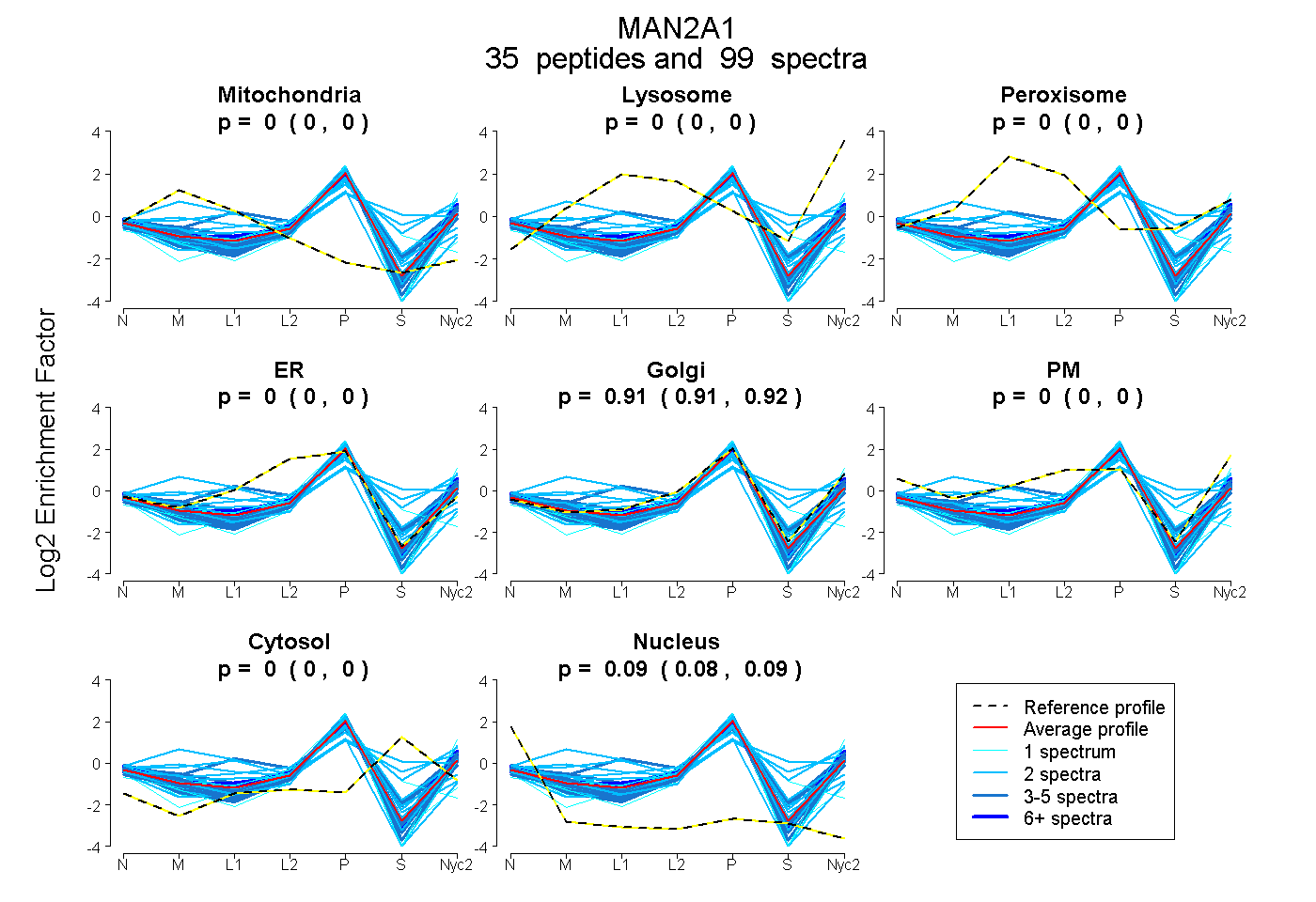
0.000 | 0.003
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.912 | 0.916
0.000 | 0.000
0.000 | 0.000
0.083 | 0.087
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
99 spectra |
 |
0.000 0.000 | 0.003 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.914 0.912 | 0.916 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.086 0.083 | 0.087 |
| 1 spectrum, IQFGTLSDYFDALEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.884 | 0.000 | 0.000 | 0.116 | ||
| 2 spectra, ICCQFDFK | 0.000 | 0.000 | 0.000 | 0.105 | 0.737 | 0.000 | 0.000 | 0.158 | ||
| 1 spectrum, LLQSSLPCDIHLVNLR | 0.000 | 0.000 | 0.000 | 0.230 | 0.599 | 0.000 | 0.000 | 0.171 | ||
| 5 spectra, AGFSHMLIQR | 0.097 | 0.000 | 0.134 | 0.076 | 0.683 | 0.000 | 0.000 | 0.009 | ||
| 2 spectra, DWVVVDYGTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.902 | 0.000 | 0.000 | 0.098 | ||
| 2 spectra, FLSSPHYTTLTEAR | 0.028 | 0.000 | 0.256 | 0.000 | 0.505 | 0.000 | 0.211 | 0.000 | ||
| 2 spectra, VQFLWYGTTNK | 0.071 | 0.000 | 0.000 | 0.000 | 0.877 | 0.000 | 0.000 | 0.052 | ||
| 2 spectra, GHLDYPR | 0.000 | 0.000 | 0.000 | 0.189 | 0.632 | 0.000 | 0.062 | 0.117 | ||
| 2 spectra, IIGDSAFLLILK | 0.000 | 0.000 | 0.000 | 0.000 | 0.842 | 0.000 | 0.095 | 0.063 | ||
| 2 spectra, YEADEWDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.930 | 0.000 | 0.000 | 0.070 | ||
| 2 spectra, VFDCQLSSR | 0.408 | 0.000 | 0.000 | 0.307 | 0.285 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YYTDLNGYQIQPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.897 | 0.000 | 0.000 | 0.103 | ||
| 2 spectra, NIIQLSAQEPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.906 | 0.000 | 0.000 | 0.094 | ||
| 4 spectra, GYSDEAALILHR | 0.010 | 0.000 | 0.000 | 0.000 | 0.899 | 0.000 | 0.092 | 0.000 | ||
| 4 spectra, WWDIIDNPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.925 | 0.000 | 0.000 | 0.075 | ||
| 1 spectrum, IYSDVTCFLEHVTHK | 0.000 | 0.000 | 0.000 | 0.516 | 0.113 | 0.000 | 0.260 | 0.110 | ||
| 3 spectra, VLSDLGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.910 | 0.000 | 0.000 | 0.090 | ||
| 2 spectra, LFQSLNSLEK | 0.211 | 0.000 | 0.000 | 0.000 | 0.789 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, AMGLPCSTTQGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.988 | 0.000 | 0.000 | 0.012 | ||
| 4 spectra, TFNDYFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.935 | 0.000 | 0.000 | 0.065 | ||
| 7 spectra, AQMLLDQYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.962 | 0.000 | 0.000 | 0.038 | ||
| 2 spectra, LPLQANVYPMSTMAYIQDAAHR | 0.000 | 0.023 | 0.078 | 0.000 | 0.562 | 0.141 | 0.196 | 0.000 | ||
| 1 spectrum, GLGQGVHDNK | 0.000 | 0.000 | 0.000 | 0.079 | 0.848 | 0.000 | 0.000 | 0.072 | ||
| 1 spectrum, VLLAPLGDDFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.878 | 0.000 | 0.000 | 0.122 | ||
| 10 spectra, ITANLFR | 0.008 | 0.000 | 0.000 | 0.000 | 0.938 | 0.000 | 0.000 | 0.054 | ||
| 1 spectrum, TQYIFNNMVLK | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, TLEFFWR | 0.000 | 0.000 | 0.000 | 0.000 | 0.931 | 0.000 | 0.000 | 0.069 | ||
| 4 spectra, NLGVKPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.906 | 0.000 | 0.000 | 0.094 | ||
| 2 spectra, TAEILYHLALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.926 | 0.000 | 0.000 | 0.074 | ||
| 4 spectra, AFLEMDTK | 0.110 | 0.000 | 0.000 | 0.000 | 0.852 | 0.000 | 0.038 | 0.000 | ||
| 2 spectra, LYQSDPSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.910 | 0.000 | 0.000 | 0.090 | ||
| 3 spectra, QSSQDSLPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.879 | 0.000 | 0.000 | 0.121 | ||
| 5 spectra, LLAENNEIISNIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.889 | 0.000 | 0.000 | 0.111 | ||
| 4 spectra, YLVVYNPFEQER | 0.000 | 0.000 | 0.000 | 0.000 | 0.906 | 0.000 | 0.000 | 0.094 | ||
| 2 spectra, LMQDDNR | 0.000 | 0.000 | 0.094 | 0.000 | 0.509 | 0.000 | 0.397 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
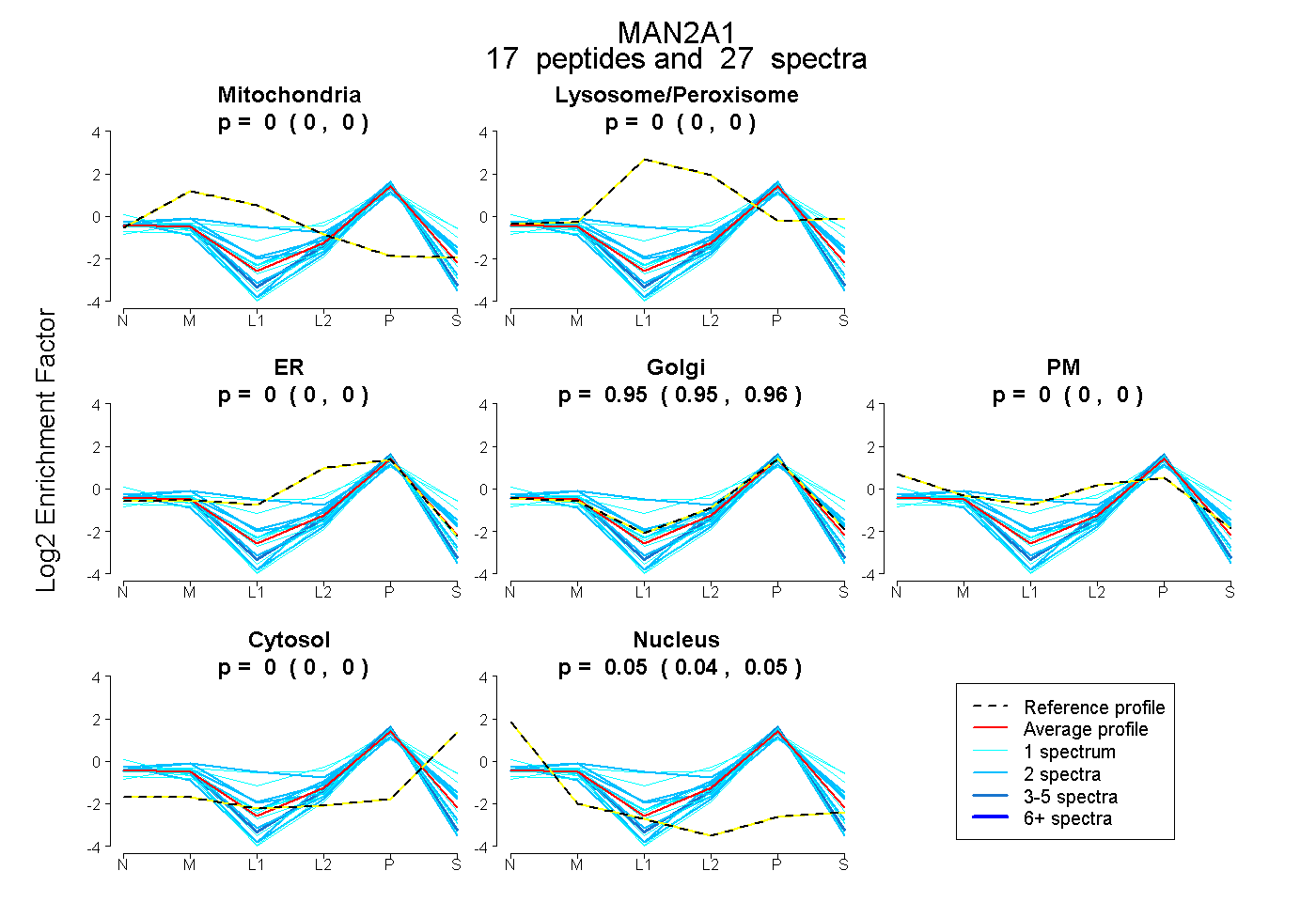 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.955 0.950 | 0.959 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.045 0.041 | 0.049 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
120 spectra |
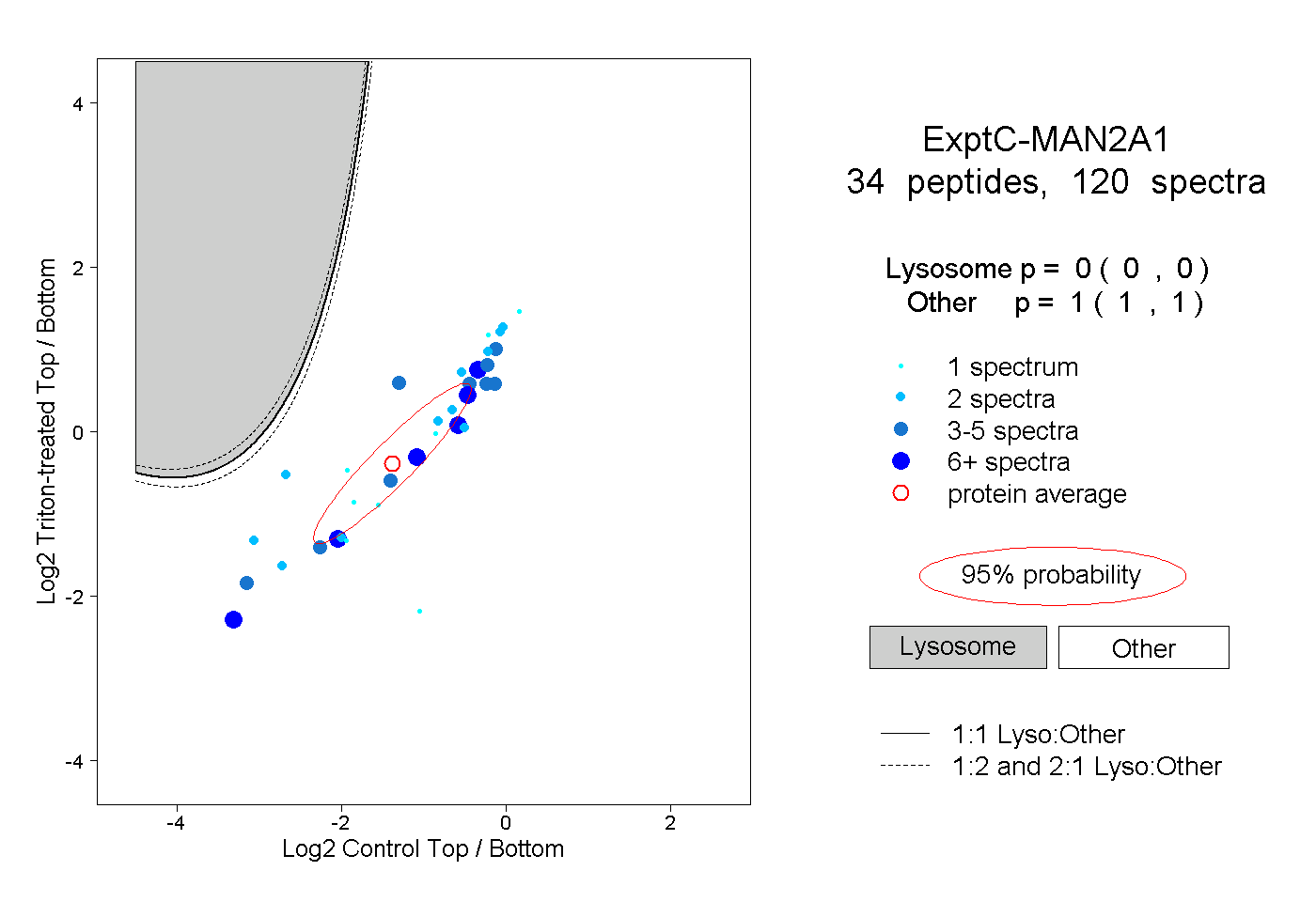 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
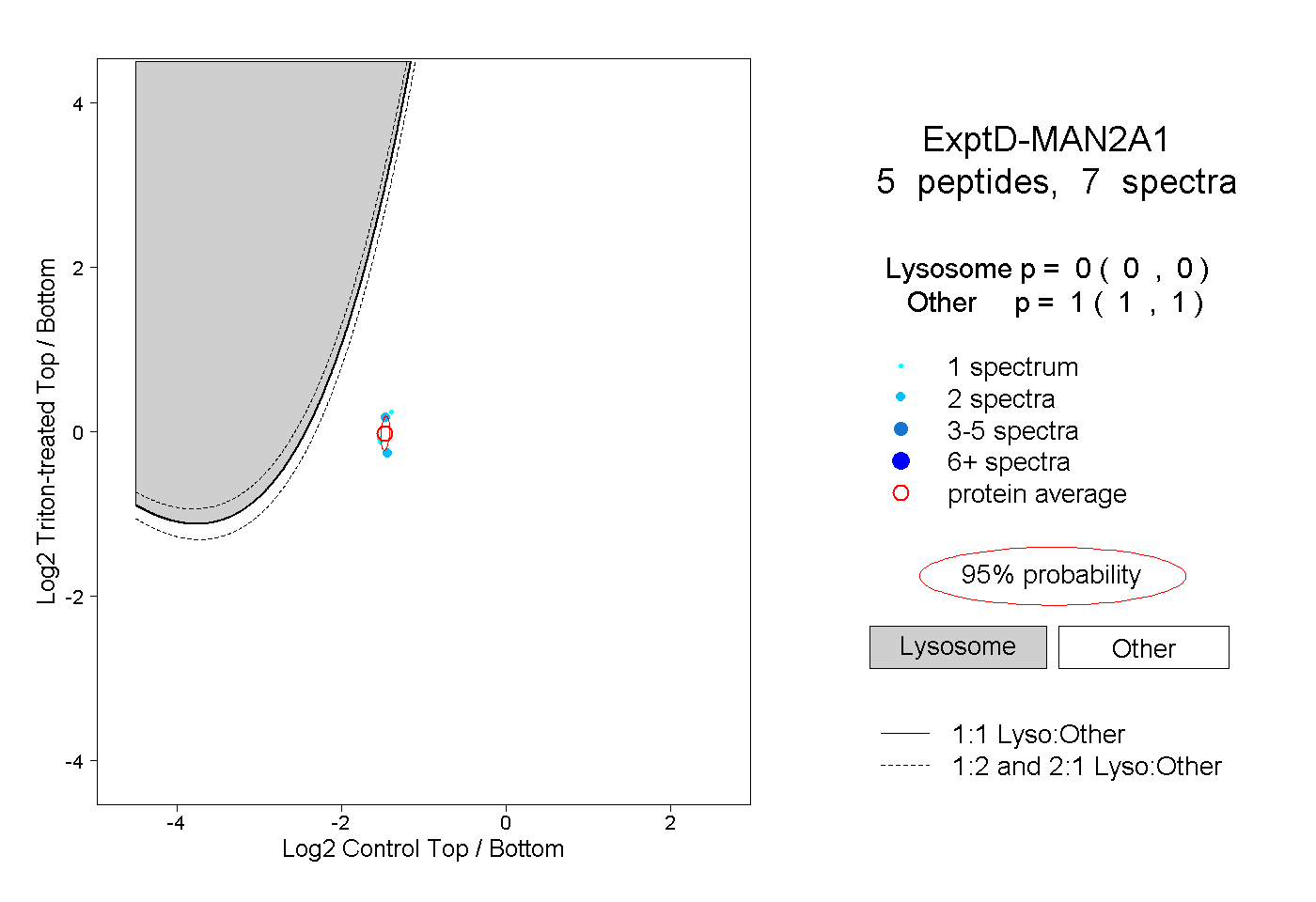 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |