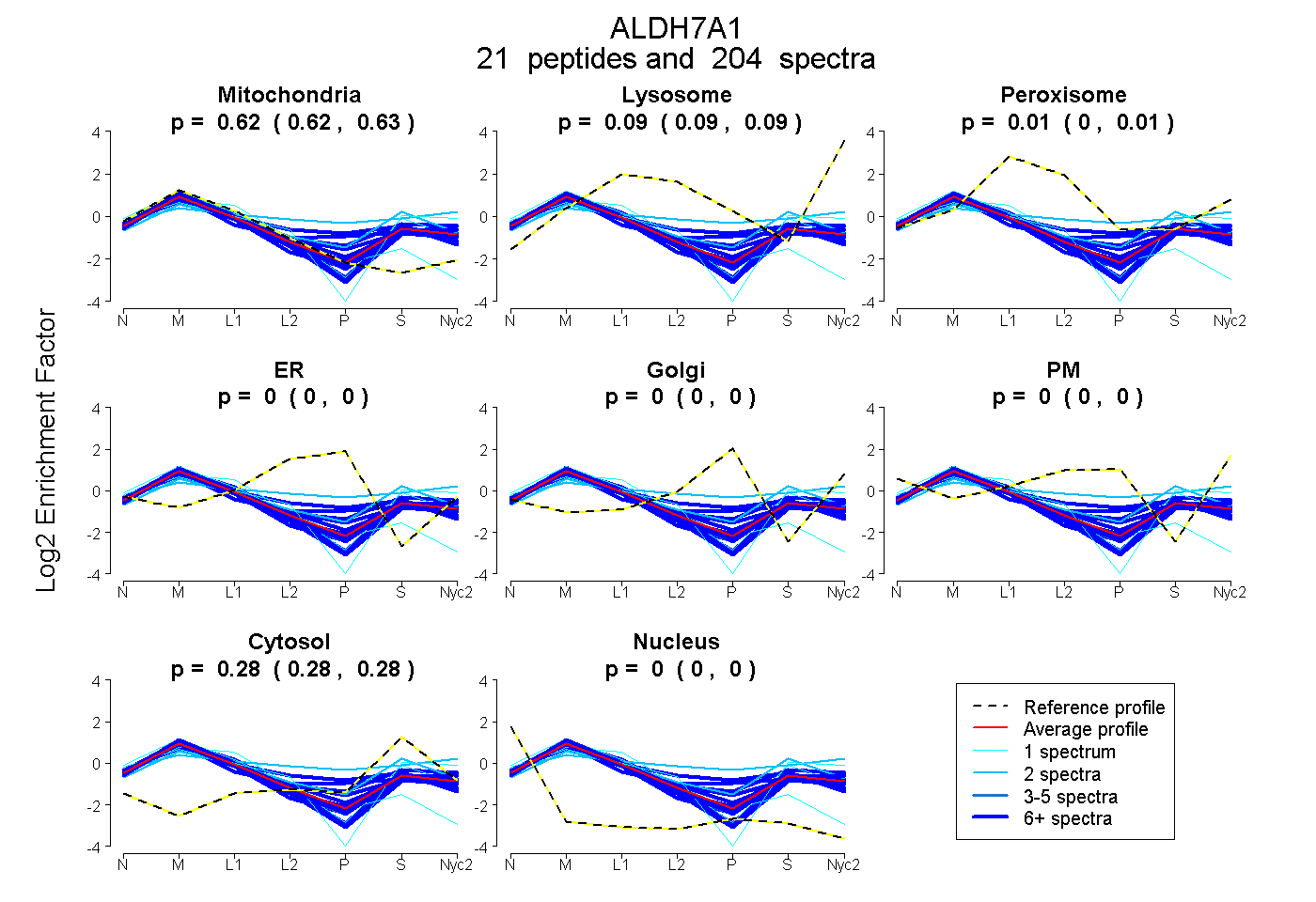
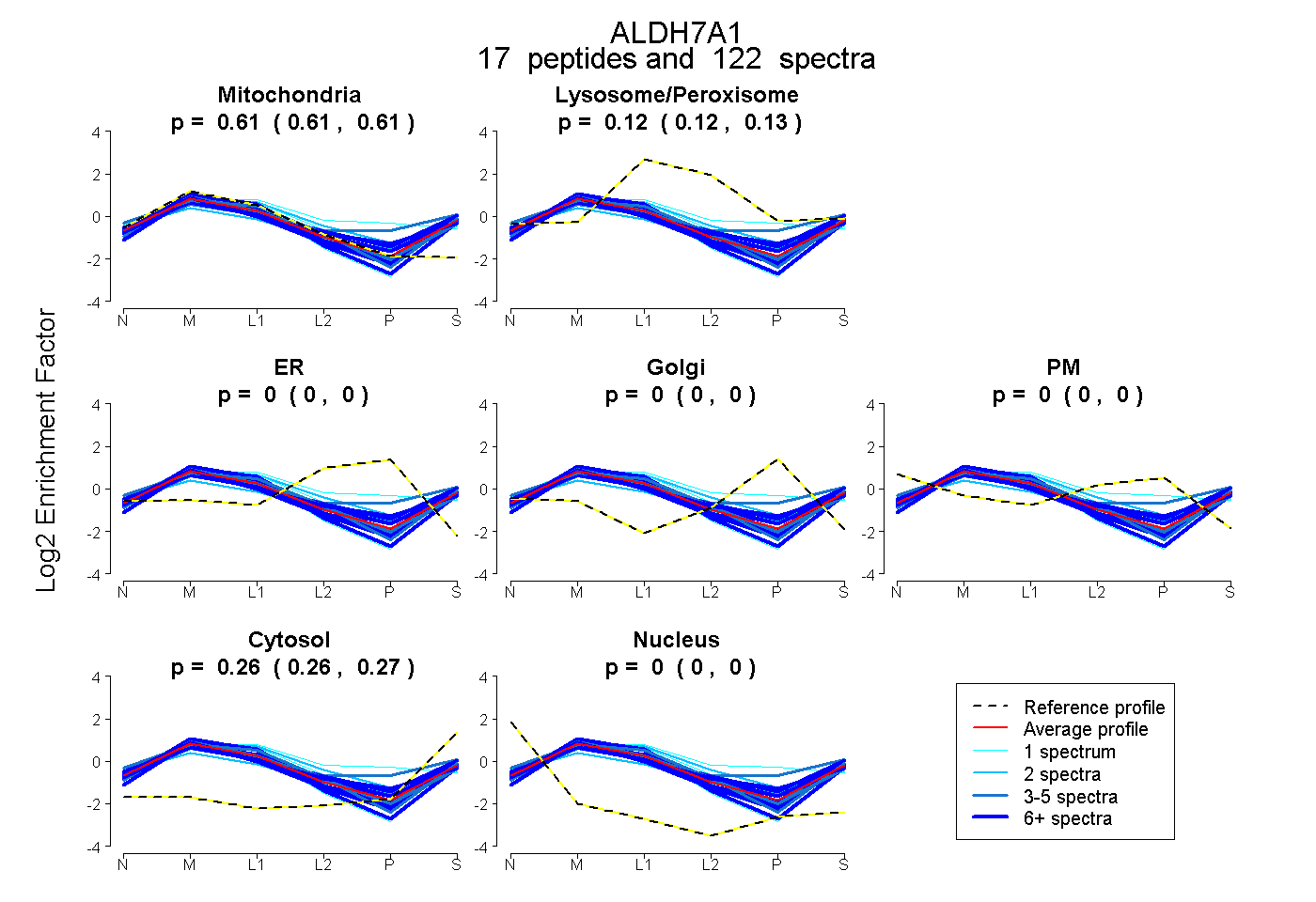
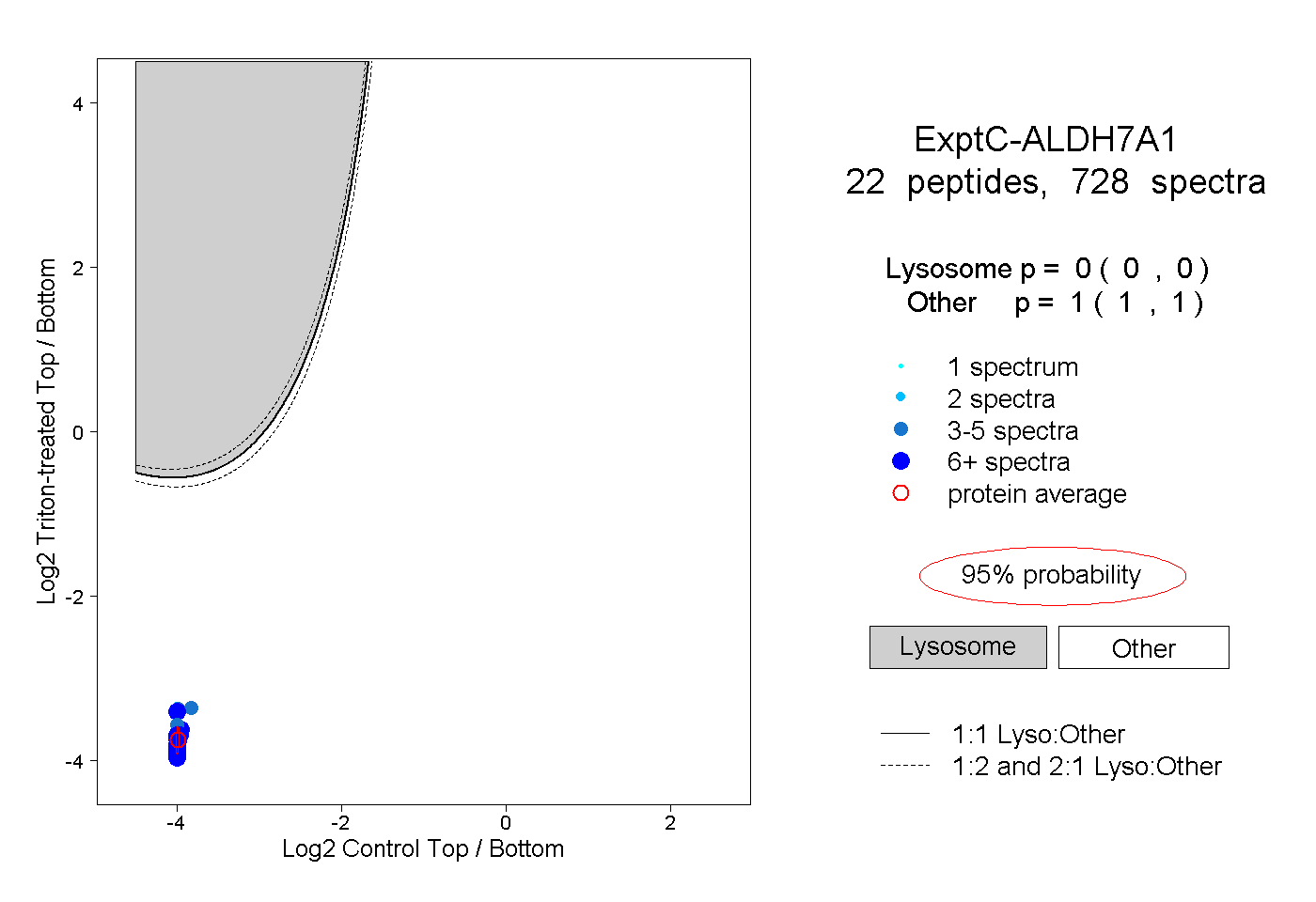
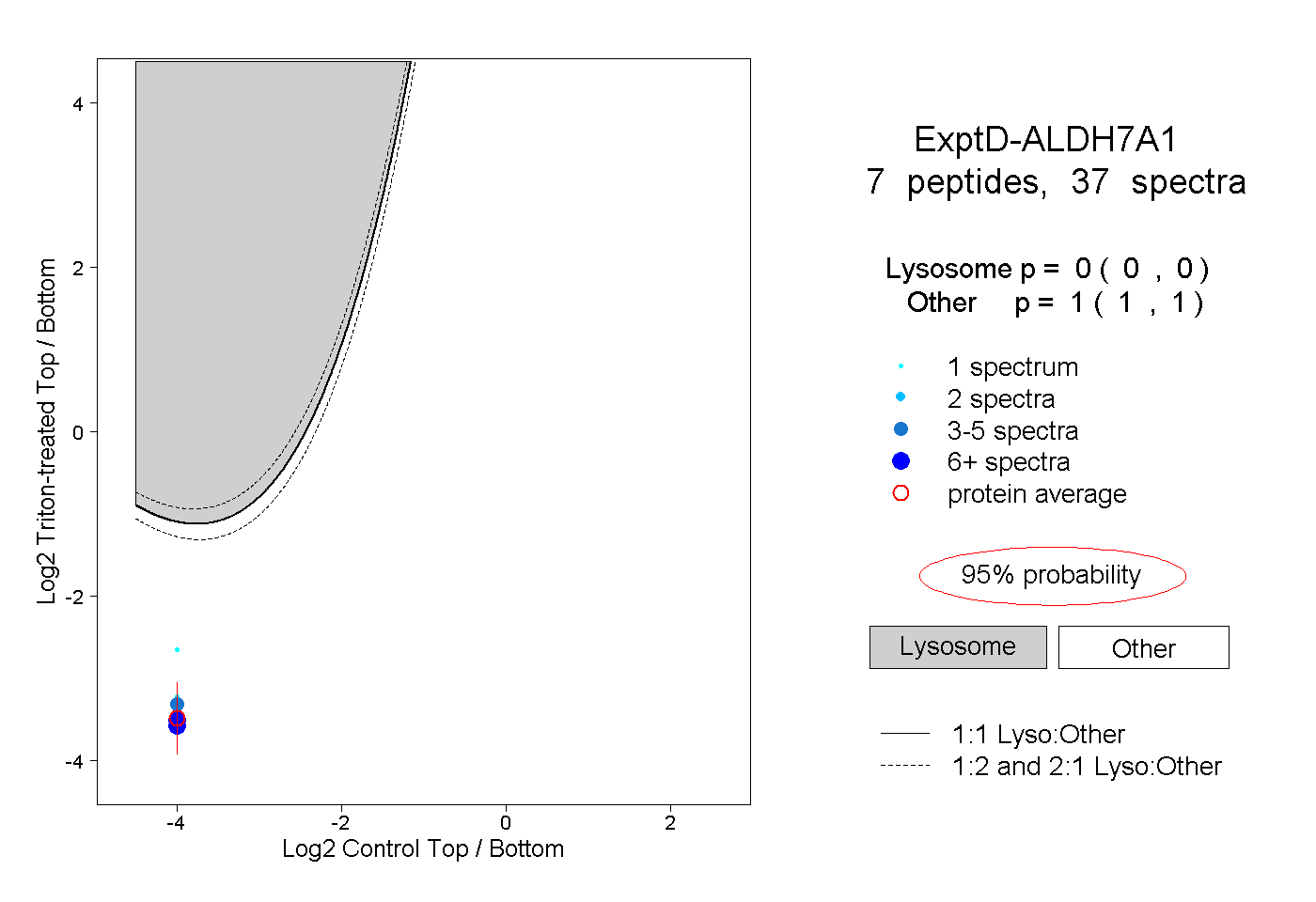
| 80 spectra, LVSLEMGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 84 spectra, NAYSQIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, GAPTTSLVSIAVTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 87 spectra, EGGTVVYGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, EDNEGVFNGSWGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 63 spectra, VGNPWDPNILYGPLHTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 33 spectra, ETFAPILYVFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, QAVSMFVQAVEEAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, IQLLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VNLLSFTGSTQVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 64 spectra, ESGSDAWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GSDCGIVNVNIPTSGAEIGGAFGGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 74 spectra, QVALMVQER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 67 spectra, DYEETIGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LELLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GEVITTYCPANNEPIAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 66 spectra, QGLSSSIFTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LGDALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GEIVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, STCTINYSTALPLAQGIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AWNIWADIPAPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, NEEEVFEWNNEVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |