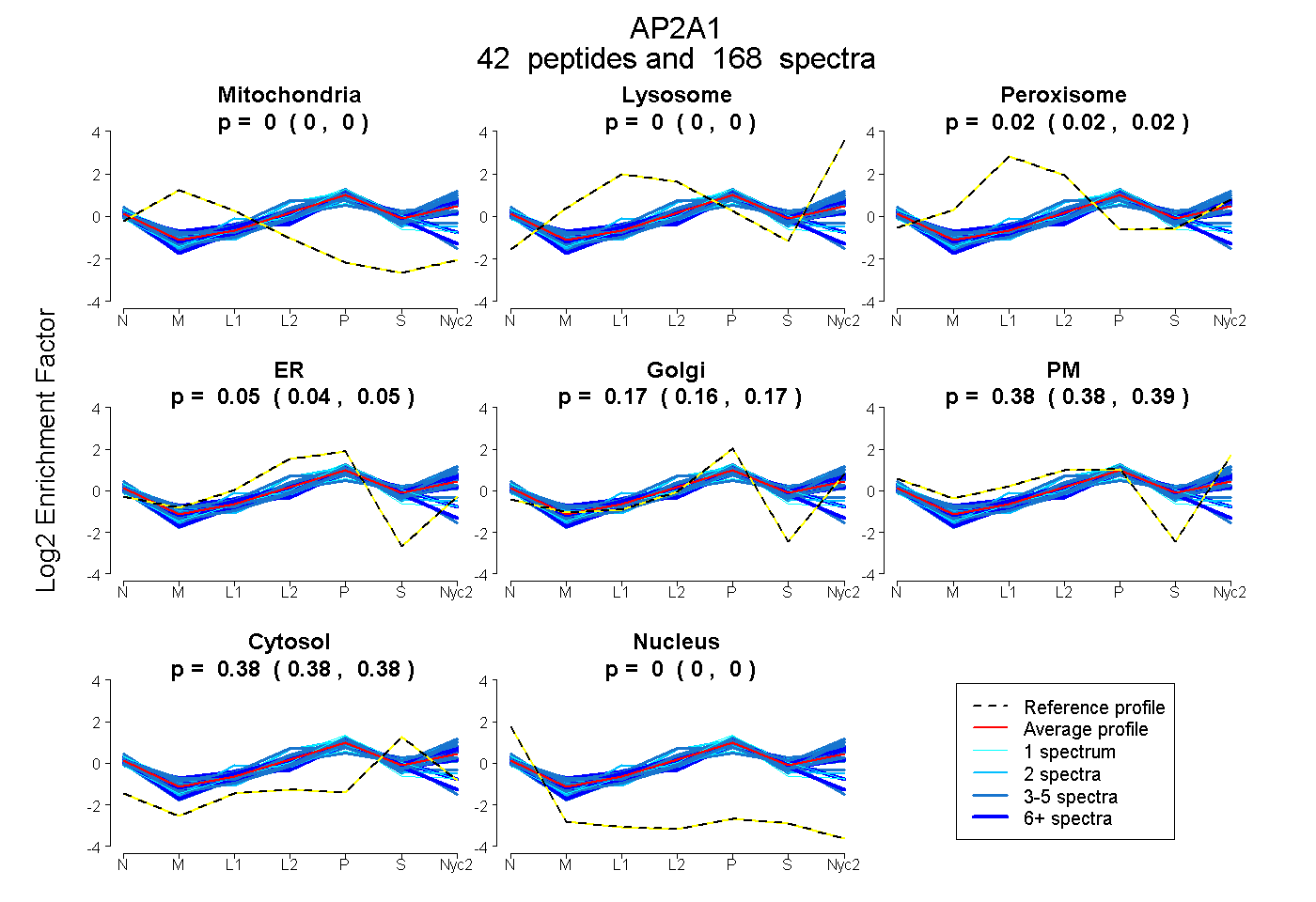
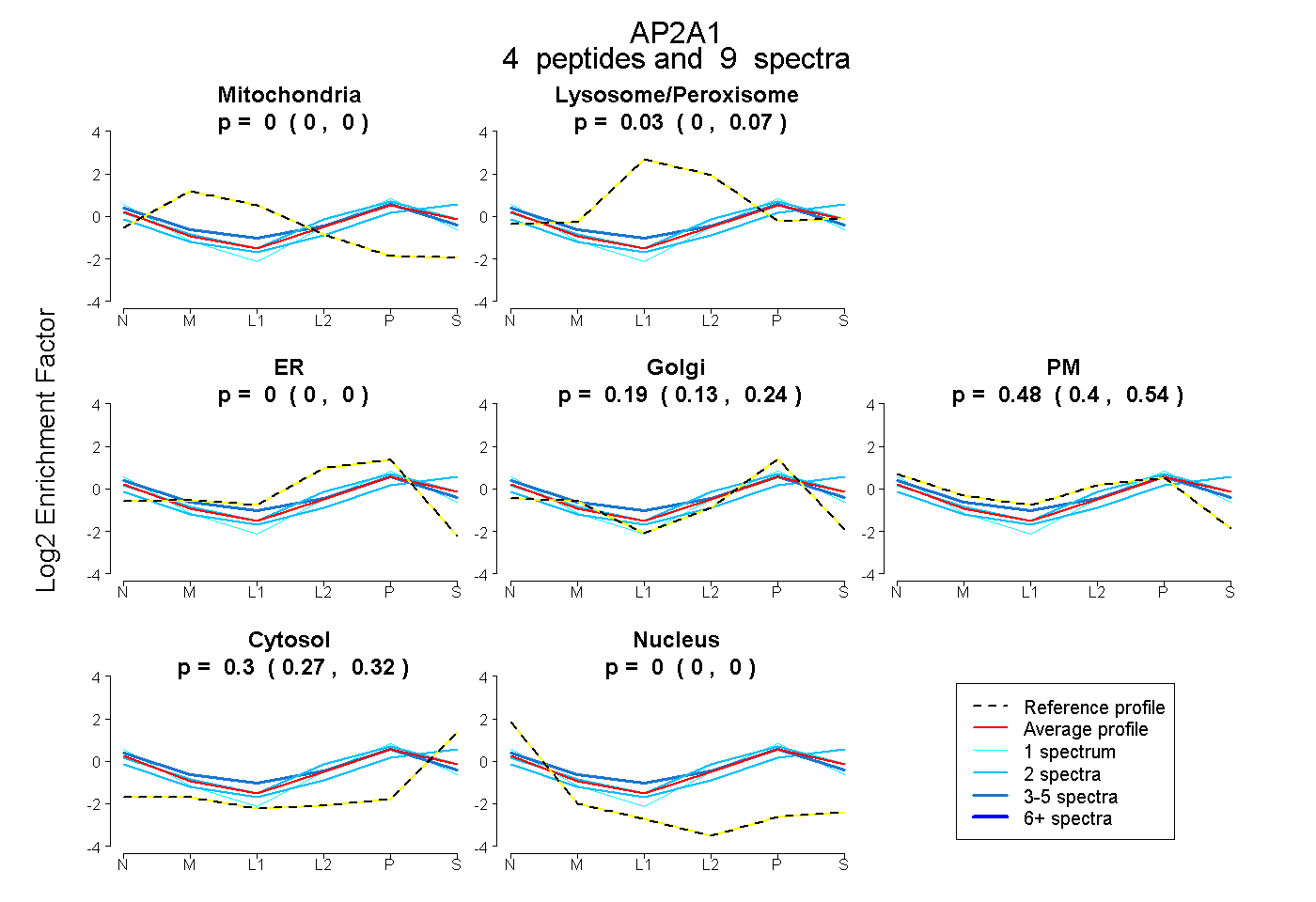
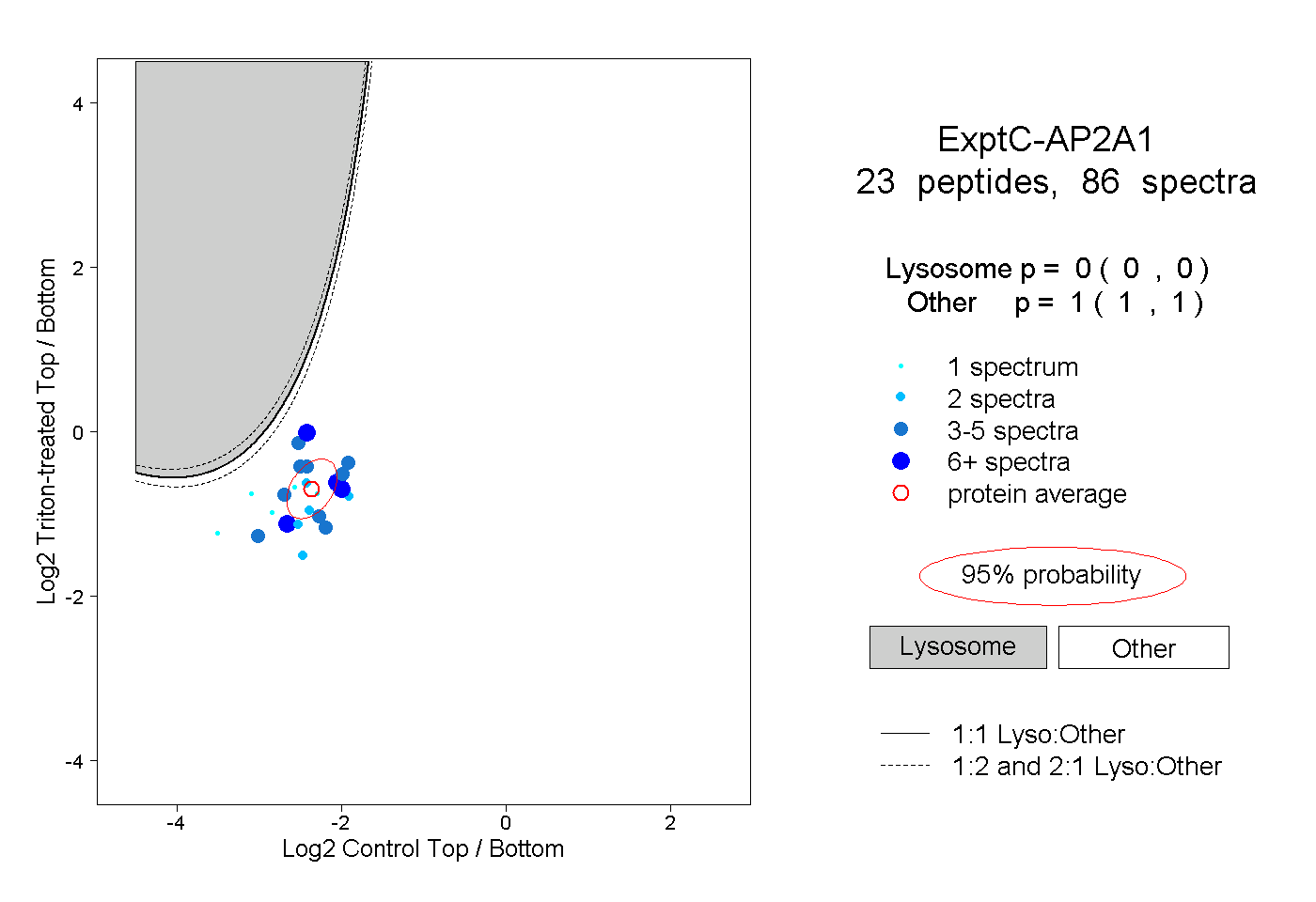
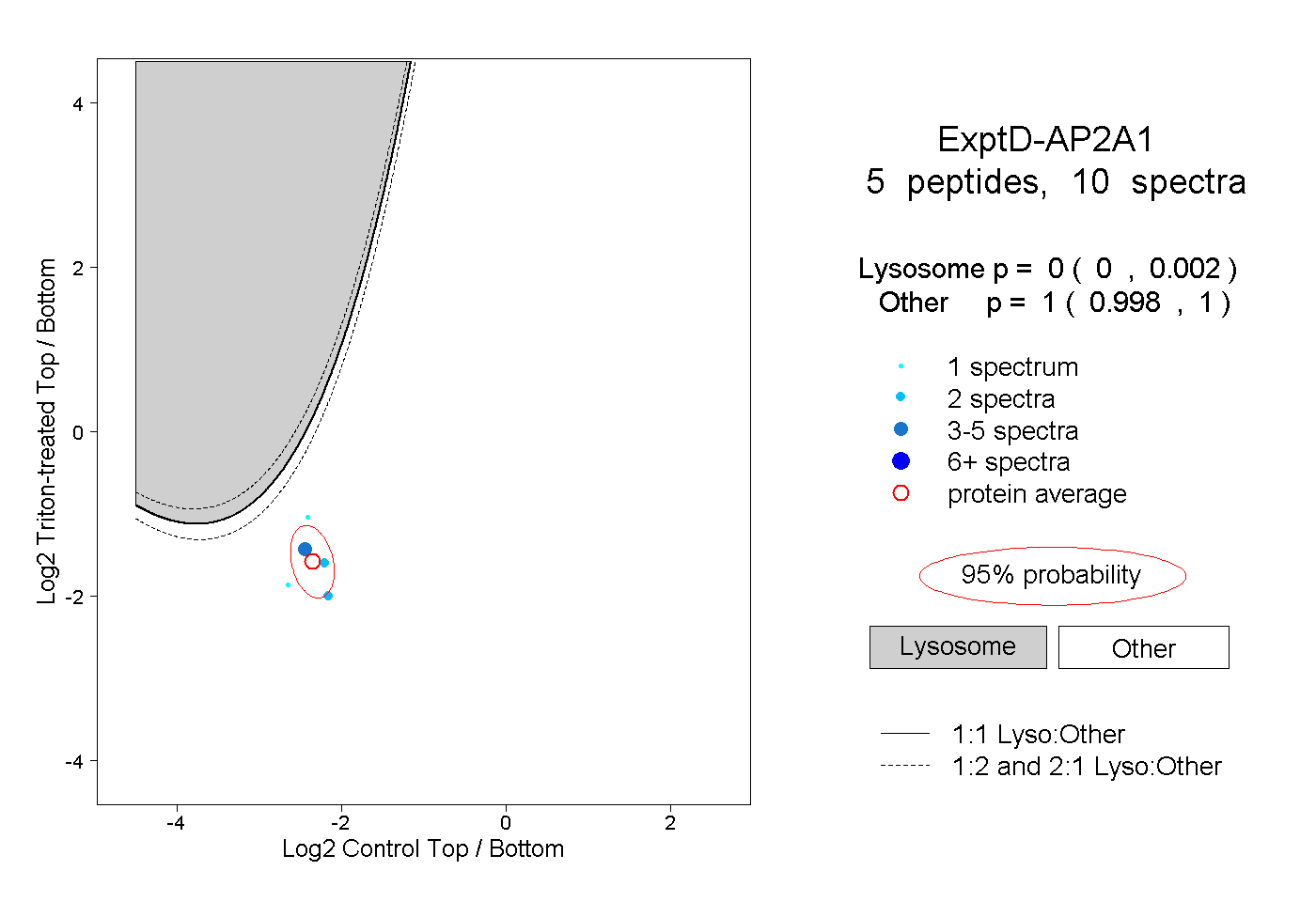
| 1 spectrum, FHLCSVATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TVFEALQAPACHENMVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, THIDTVINALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, HLCELLAQQF |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SSPPVQFSLLHSK |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 3 spectra, ATIQGVLR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 4 spectra, LEPNAQAQMYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LVECLETVLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, FINLFPETK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ASPDLVPMGEWTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, YGGTAQSLTLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LPVTINK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ALQVGCLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, YLETADYAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VLQIVTNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ILVAGDSMDSVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GPGAASALDDSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QIVSEMLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DFLTPPLLSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, AADLLYAMCDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ANHPMDAEVTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, MYLFYGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, EMGEAFAADIPR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |