peptides
spectra
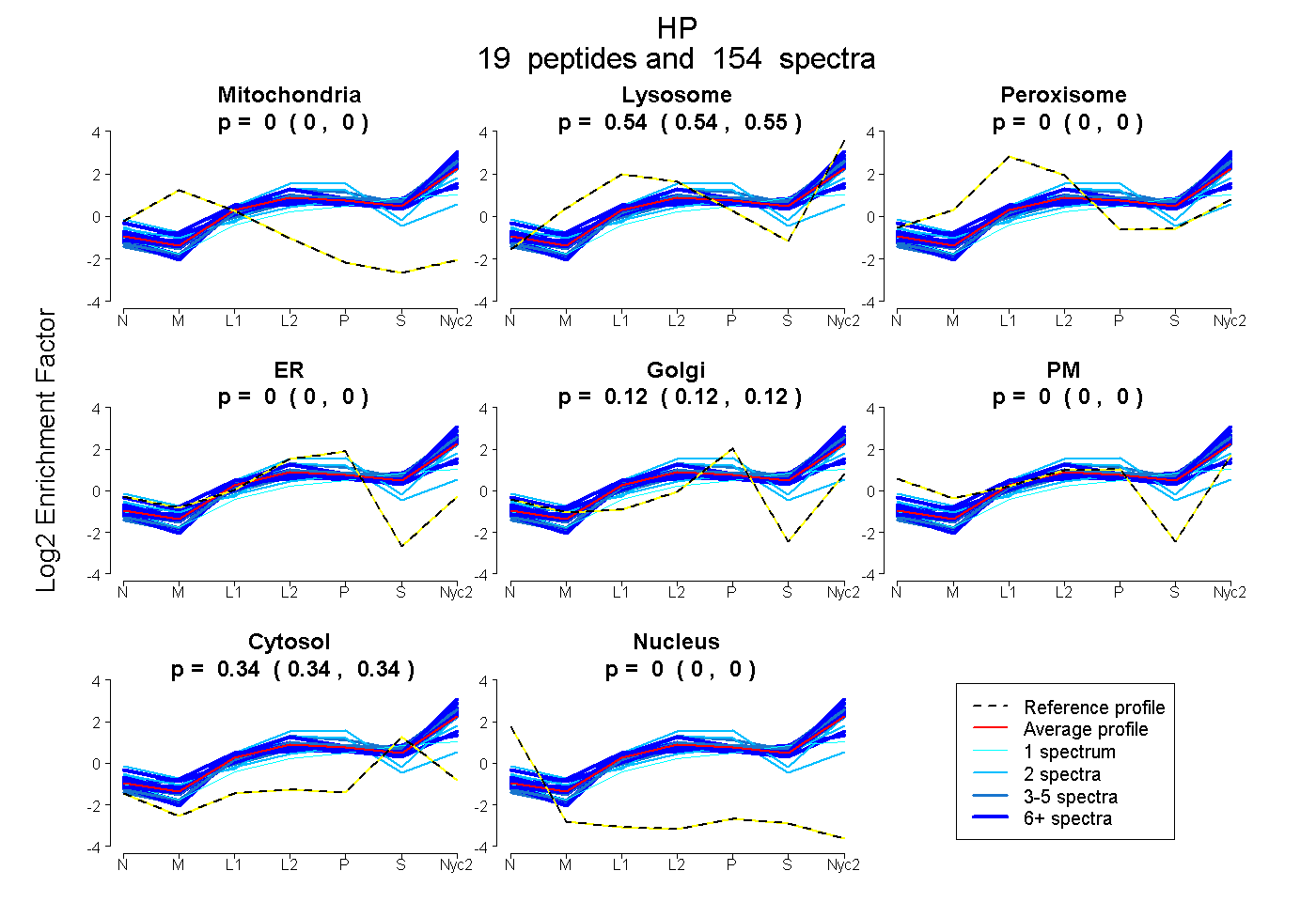
0.000 | 0.000
0.540 | 0.545
0.000 | 0.000
0.000 | 0.000
0.117 | 0.122
0.000 | 0.000
0.335 | 0.339
0.000 | 0.000
peptides
spectra
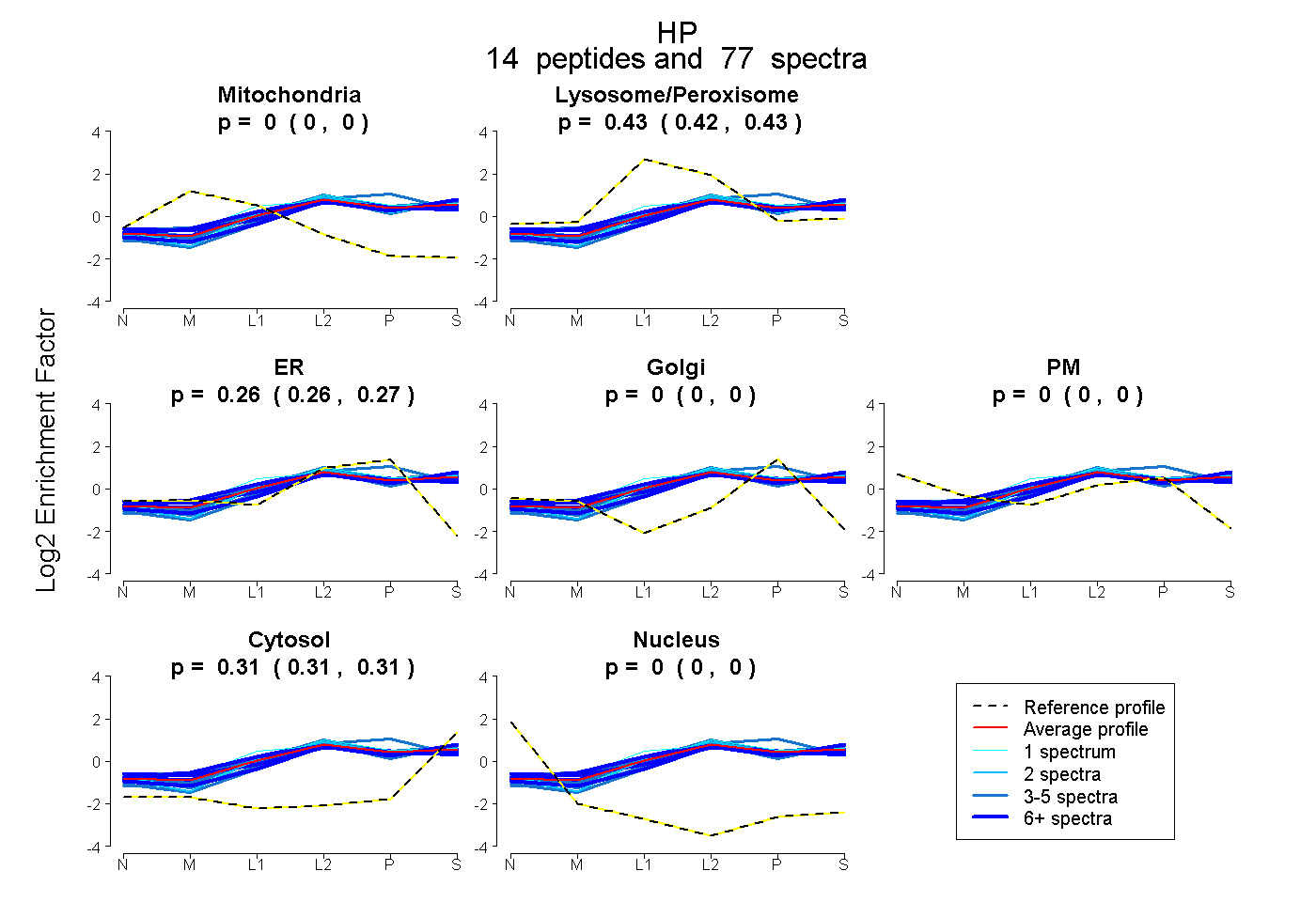
0.000 | 0.000
0.423 | 0.428
0.261 | 0.267
0.000 | 0.000
0.000 | 0.000
0.308 | 0.312
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
154 spectra |
 |
0.000 0.000 | 0.000 |
0.543 0.540 | 0.545 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.120 0.117 | 0.122 |
0.000 0.000 | 0.000 |
0.337 0.335 | 0.339 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.426 0.423 | 0.428 |
0.264 0.261 | 0.267 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.310 0.308 | 0.312 |
0.000 0.000 | 0.000 |
| 6 spectra, YVMLPVADQEK | 0.000 | 0.367 | 0.248 | 0.000 | 0.000 | 0.385 | 0.000 | |||
| 3 spectra, IIGGSMDAK | 0.000 | 0.275 | 0.444 | 0.000 | 0.000 | 0.282 | 0.000 | |||
| 7 spectra, GAVSPVGVQPILNK | 0.000 | 0.468 | 0.190 | 0.080 | 0.000 | 0.262 | 0.000 | |||
| 4 spectra, GSFPWQAK | 0.000 | 0.481 | 0.100 | 0.158 | 0.000 | 0.261 | 0.000 | |||
| 11 spectra, DYVAPGR | 0.000 | 0.463 | 0.248 | 0.000 | 0.000 | 0.289 | 0.000 | |||
| 4 spectra, CELHYEK | 0.000 | 0.476 | 0.203 | 0.041 | 0.000 | 0.280 | 0.000 | |||
| 9 spectra, SVVDIGLIK | 0.000 | 0.431 | 0.150 | 0.173 | 0.000 | 0.247 | 0.000 | |||
| 1 spectrum, VLVTEK | 0.000 | 0.436 | 0.269 | 0.000 | 0.000 | 0.295 | 0.000 | |||
| 1 spectrum, SCAVAEYGVYVR | 0.000 | 0.590 | 0.000 | 0.162 | 0.000 | 0.248 | 0.000 | |||
| 4 spectra, HTFCAGLTK | 0.000 | 0.493 | 0.164 | 0.000 | 0.000 | 0.343 | 0.000 | |||
| 2 spectra, NQLVEIEK | 0.000 | 0.462 | 0.205 | 0.000 | 0.000 | 0.333 | 0.000 | |||
| 17 spectra, VVLHPER | 0.000 | 0.490 | 0.148 | 0.102 | 0.000 | 0.259 | 0.000 | |||
| 4 spectra, MGYVSGWGR | 0.000 | 0.451 | 0.228 | 0.000 | 0.000 | 0.321 | 0.000 | |||
| 4 spectra, DIAPTLTLYVGK | 0.000 | 0.383 | 0.277 | 0.000 | 0.000 | 0.340 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
604 spectra |
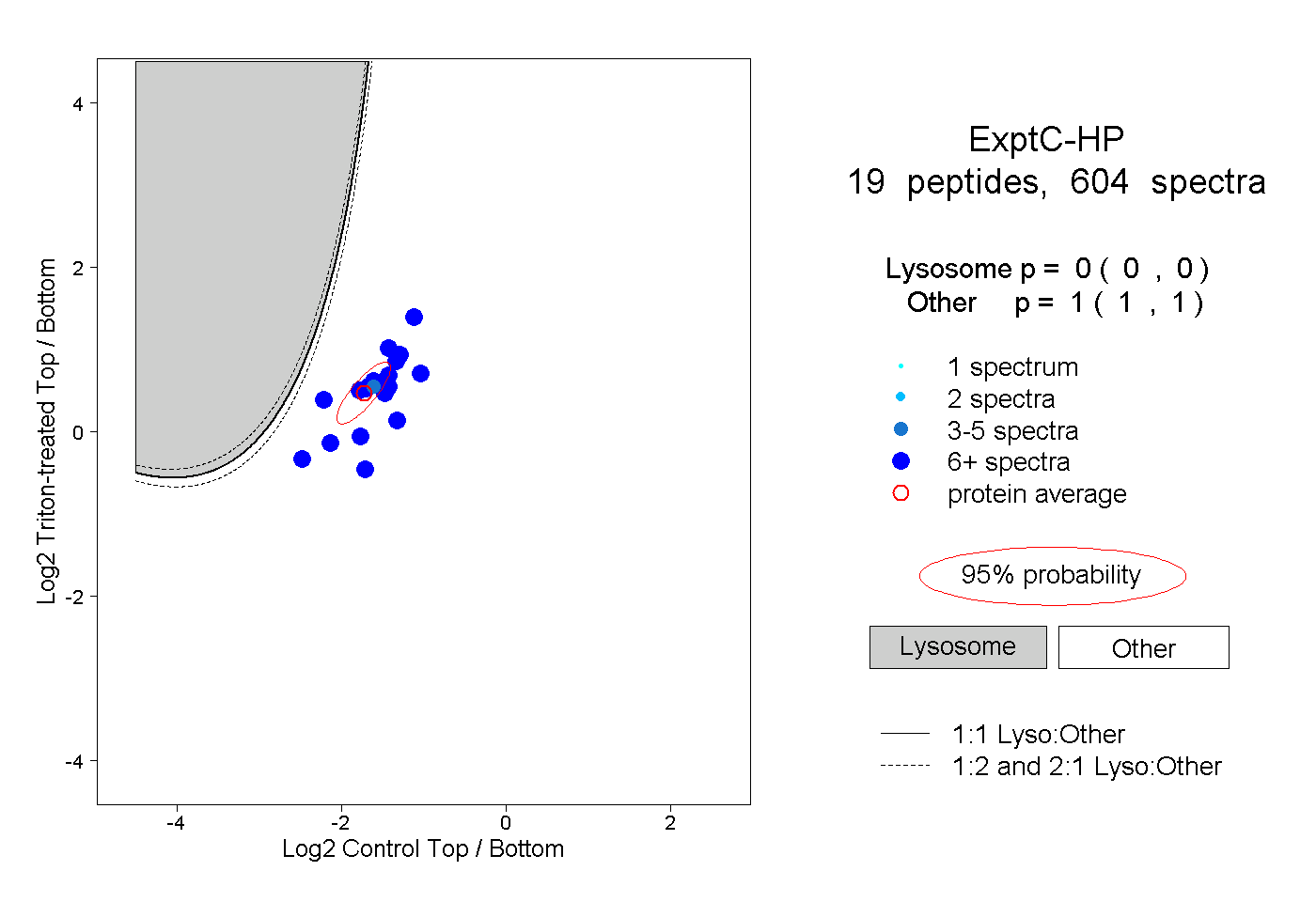 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
40 spectra |
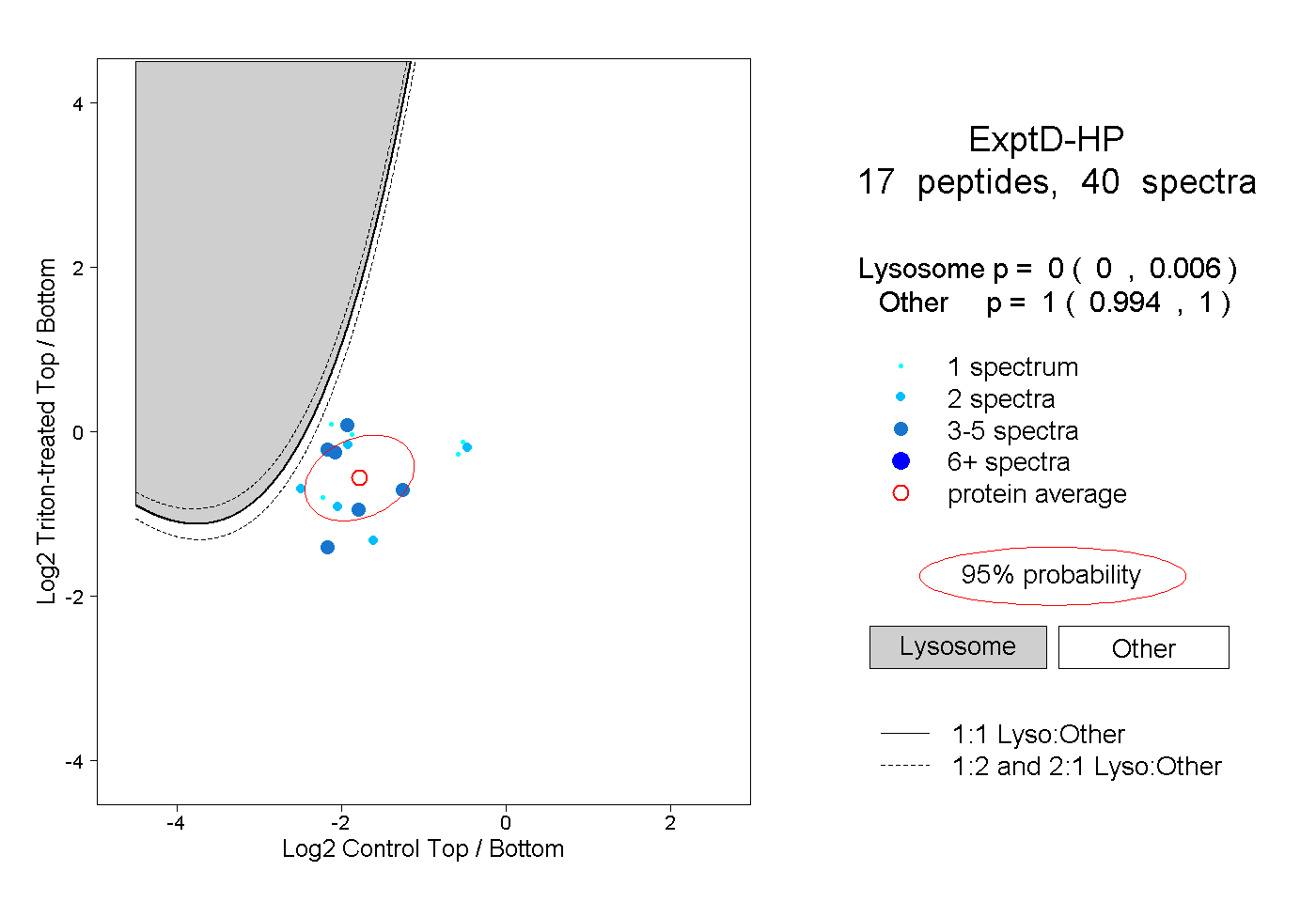 |
0.000 0.000 | 0.006 |
1.000 0.994 | 1.000 |