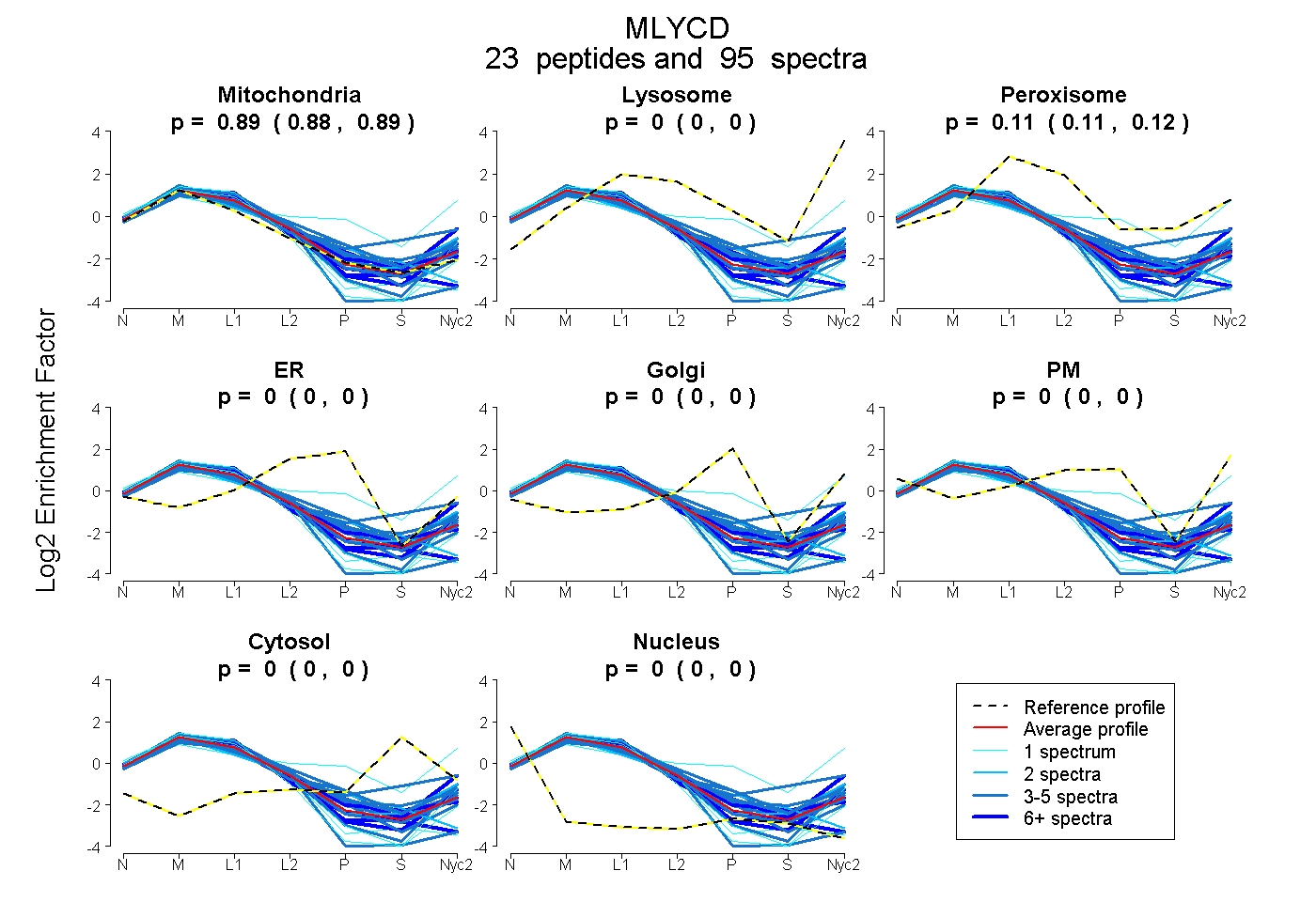
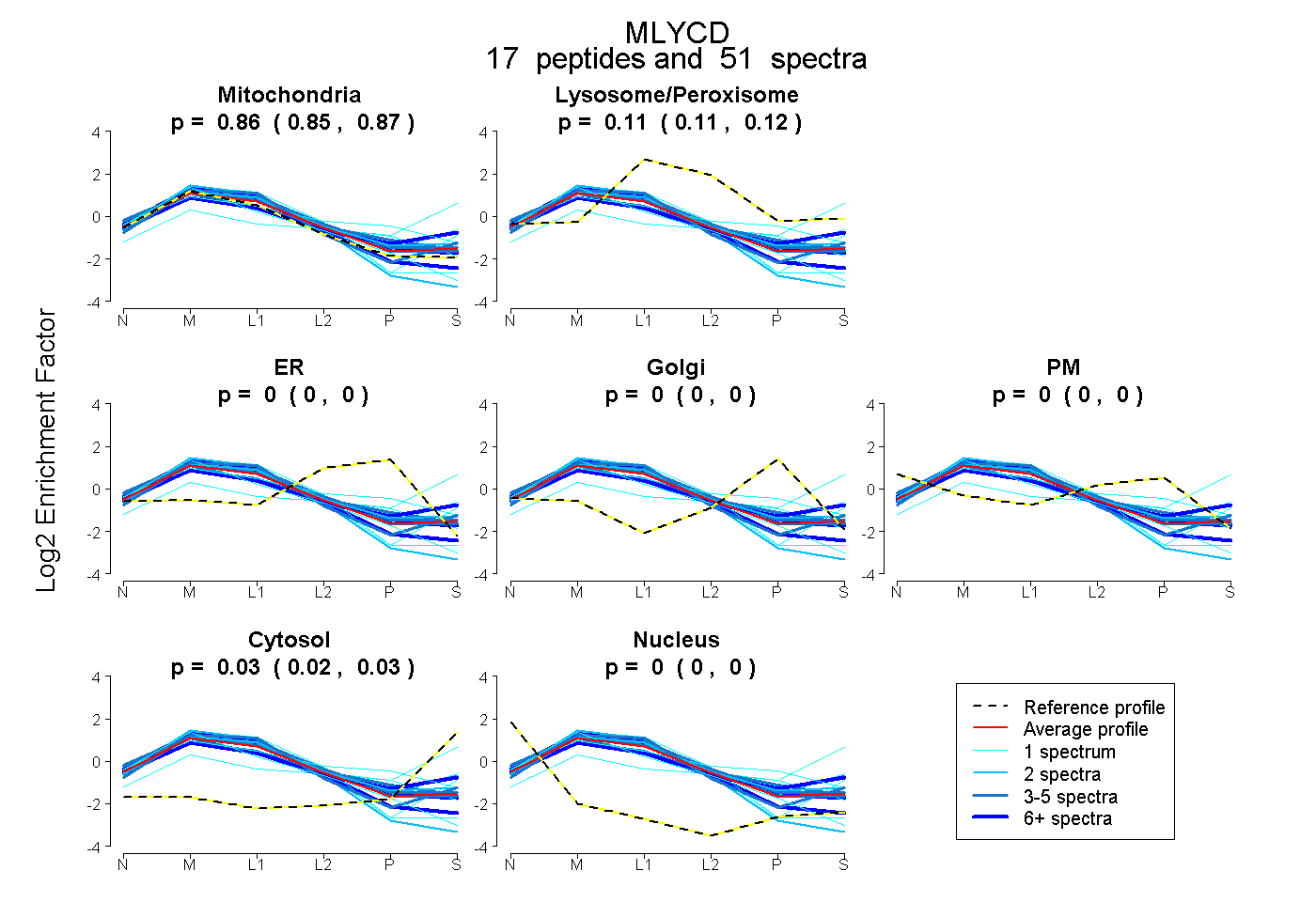
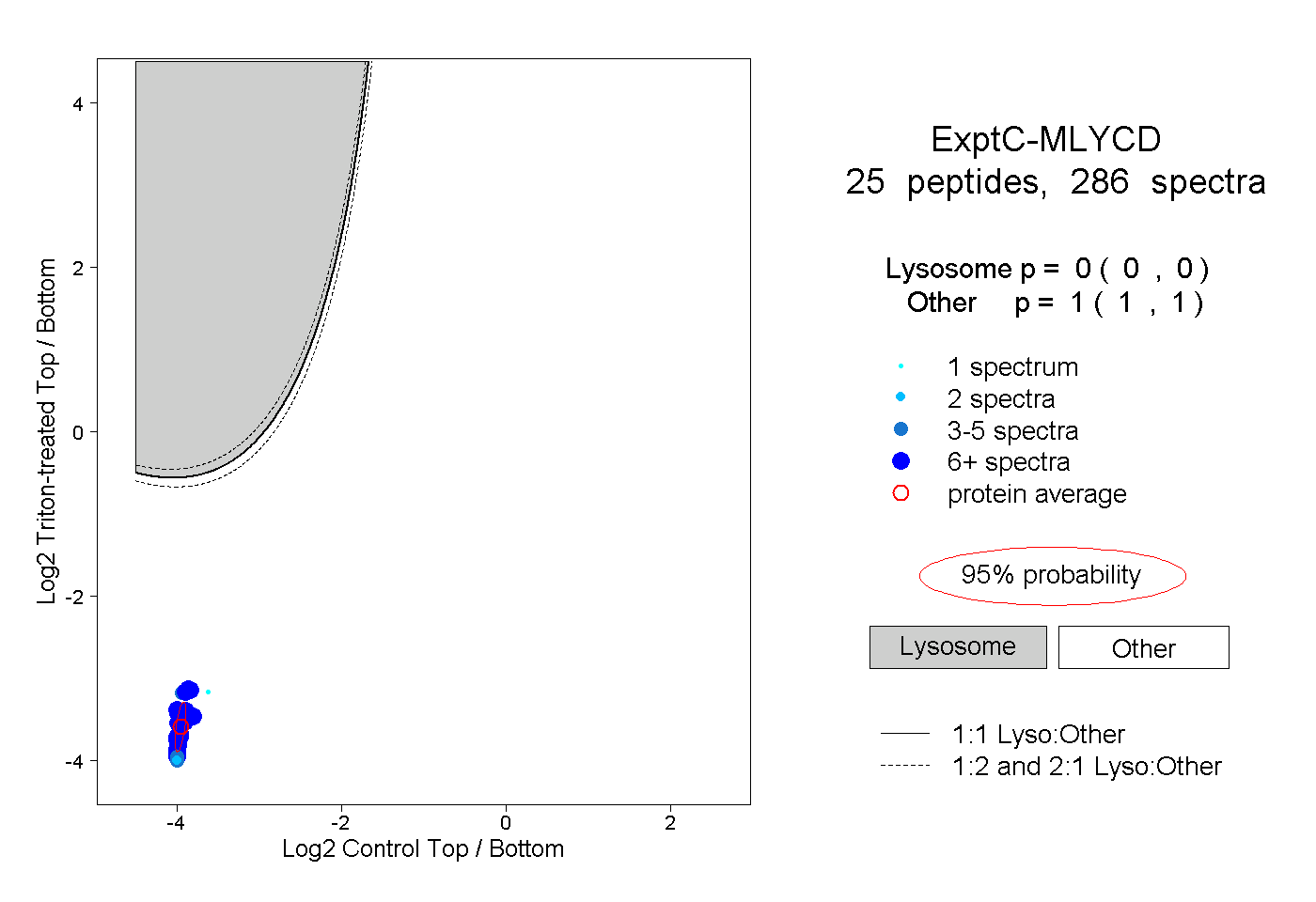
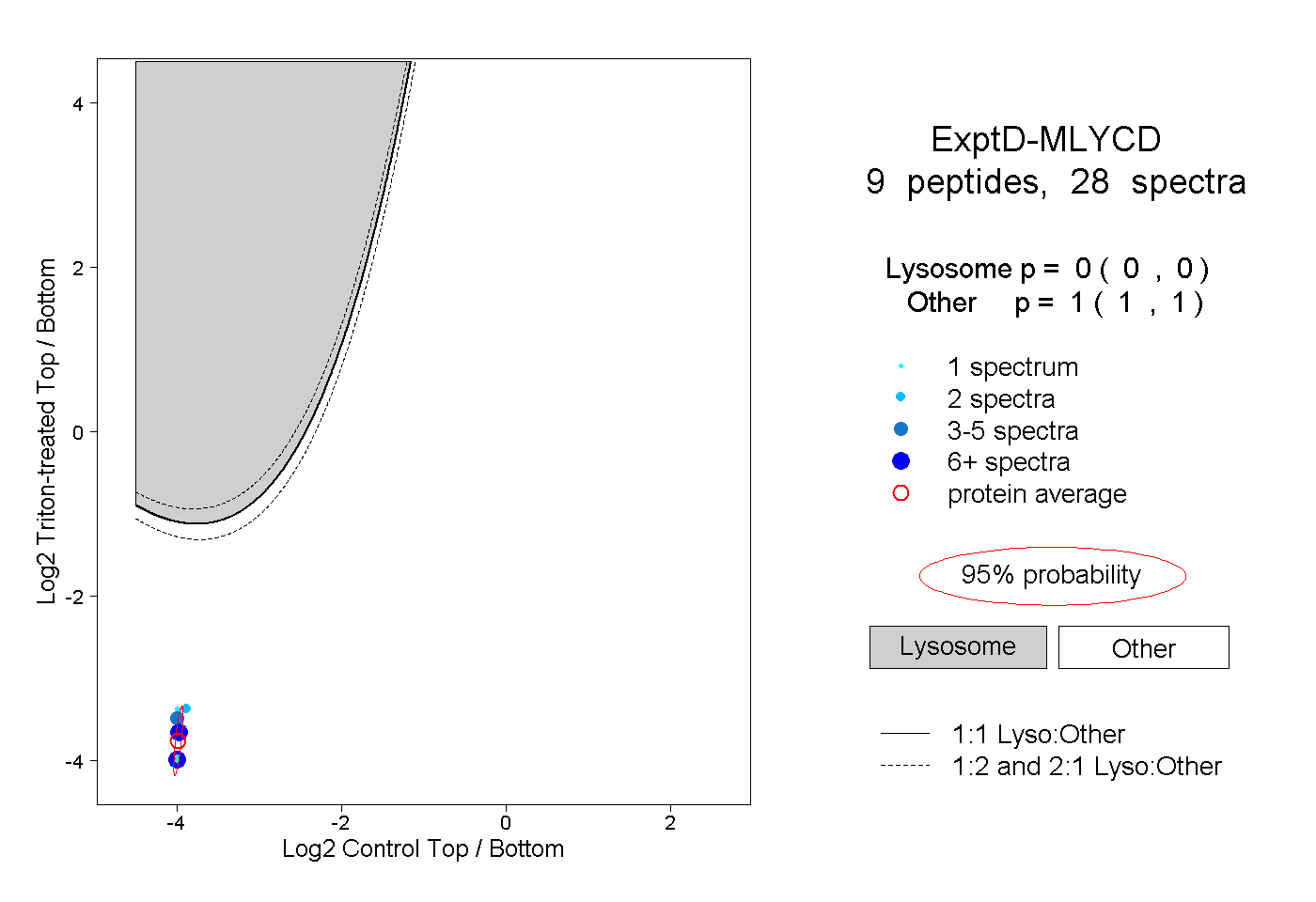
| 6 spectra, AELLGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GYALNPVANFHLQNGAVMWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, LAQALQGPLMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 33 spectra, FLVQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ASEQILSLVAQFQSNSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SMLSEWFSSGFLNLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GLFHHISK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, YALVPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GLTSSCGLMVNYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, LVEGPHVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, LDGGVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, INWMADSSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, EAAVLLQAEDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, ECPPSETEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, ADLLEAQALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, YYLEETGPNSISYLGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, VTWHSPCEVLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, AVPPTPAYELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GLLSSGEWAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LCAWYLYGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LAQGFGVDHGQVAEQSAGVLQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, ISECEAVHPVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VGPYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NELFTDSECK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, EMNGVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |