peptides
spectra
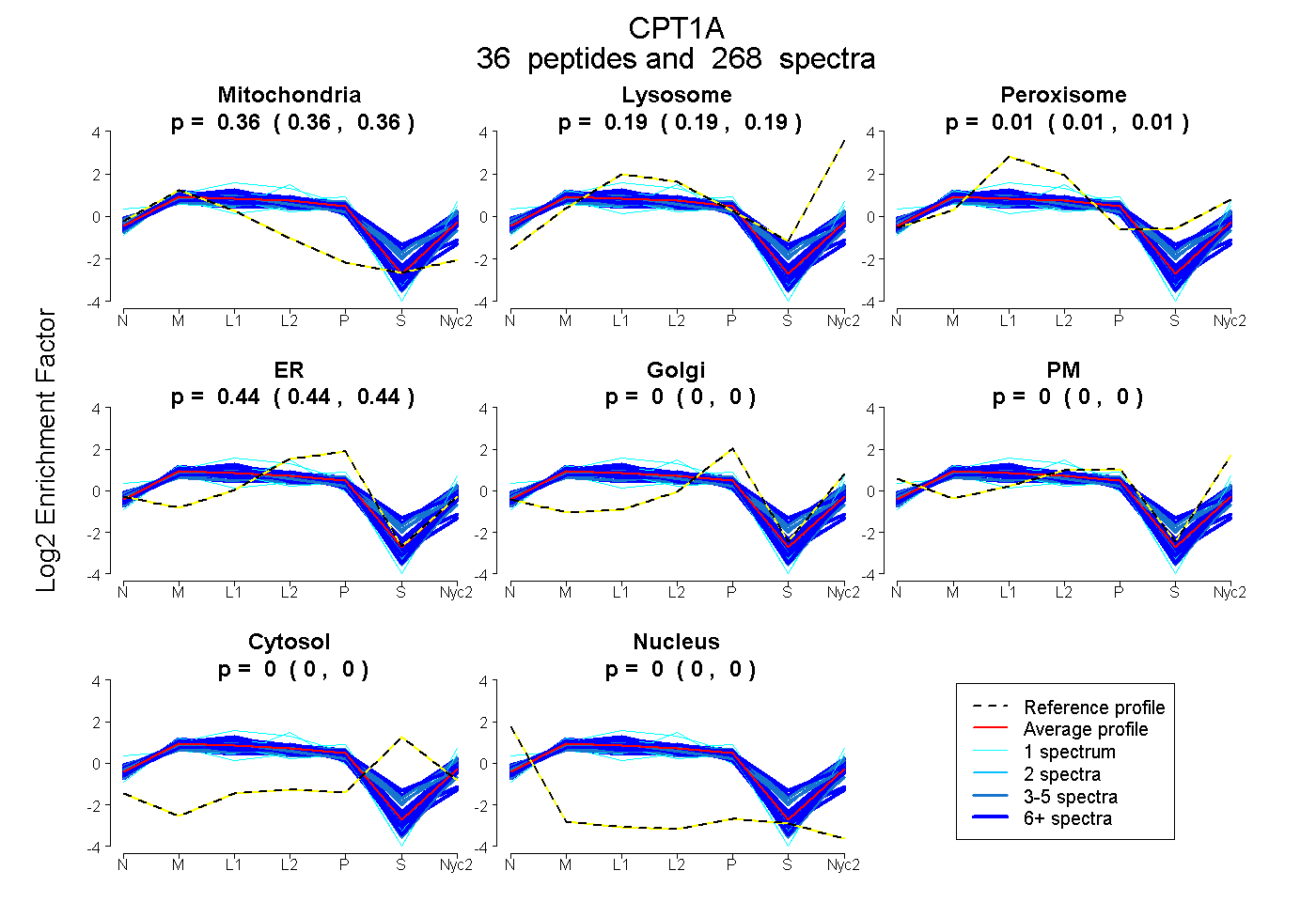
0.361 | 0.363
0.187 | 0.191
0.006 | 0.011
0.439 | 0.441
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
268 spectra |
 |
0.362 0.361 | 0.363 |
0.189 0.187 | 0.191 |
0.009 0.006 | 0.011 |
0.440 0.439 | 0.441 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 14 spectra, AGNTIHAILLYR | 0.372 | 0.146 | 0.000 | 0.482 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, EVLSEPWR | 0.350 | 0.204 | 0.000 | 0.446 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, LSHEALK | 0.248 | 0.006 | 0.262 | 0.303 | 0.112 | 0.069 | 0.000 | 0.000 | ||
| 1 spectrum, GPLMVNSNYYAMEMLYITPTHIQAAR | 0.245 | 0.268 | 0.000 | 0.325 | 0.000 | 0.162 | 0.000 | 0.000 | ||
| 4 spectra, QSLDAVEK | 0.265 | 0.171 | 0.058 | 0.319 | 0.020 | 0.167 | 0.000 | 0.000 | ||
| 9 spectra, LAMTGAGIDR | 0.353 | 0.215 | 0.000 | 0.432 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 26 spectra, KPMLYSFQTSLPR | 0.344 | 0.172 | 0.069 | 0.415 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, MTALAQDFAVNLGPK | 0.240 | 0.154 | 0.209 | 0.296 | 0.100 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, VWLYHDGR | 0.368 | 0.155 | 0.028 | 0.449 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, LQWYLK | 0.367 | 0.194 | 0.017 | 0.422 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, GDTNPNIPKPTR | 0.332 | 0.180 | 0.000 | 0.486 | 0.000 | 0.002 | 0.000 | 0.000 | ||
| 1 spectrum, SCTMESCNFVQAMMDPK | 0.373 | 0.135 | 0.000 | 0.181 | 0.000 | 0.312 | 0.000 | 0.000 | ||
| 1 spectrum, LPVPAVK | 0.336 | 0.181 | 0.000 | 0.482 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, MSSQTK | 0.349 | 0.134 | 0.000 | 0.517 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, QTYFAR | 0.237 | 0.000 | 0.382 | 0.135 | 0.246 | 0.000 | 0.000 | 0.000 | ||
| 18 spectra, TLDTTGR | 0.391 | 0.101 | 0.000 | 0.416 | 0.000 | 0.092 | 0.000 | 0.000 | ||
| 5 spectra, SLLHGR | 0.365 | 0.112 | 0.000 | 0.523 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, EEDFQR | 0.328 | 0.151 | 0.075 | 0.447 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, QICLSGLHSWK | 0.407 | 0.000 | 0.197 | 0.396 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EEDPEASIDSYAK | 0.297 | 0.183 | 0.165 | 0.355 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 15 spectra, LFNSTR | 0.364 | 0.219 | 0.000 | 0.417 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EELKPIR | 0.344 | 0.199 | 0.019 | 0.438 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, HIVVYHR | 0.408 | 0.067 | 0.000 | 0.356 | 0.000 | 0.170 | 0.000 | 0.000 | ||
| 8 spectra, IWMAMVK | 0.415 | 0.208 | 0.000 | 0.377 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HQHLYR | 0.267 | 0.000 | 0.300 | 0.354 | 0.000 | 0.074 | 0.000 | 0.004 | ||
| 8 spectra, LAALTAADR | 0.268 | 0.200 | 0.165 | 0.234 | 0.133 | 0.000 | 0.000 | 0.000 | ||
| 16 spectra, YLESVRPLMK | 0.361 | 0.173 | 0.000 | 0.465 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, SITFVVFK | 0.364 | 0.206 | 0.000 | 0.430 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HLFCLYVVSK | 0.324 | 0.000 | 0.184 | 0.299 | 0.139 | 0.000 | 0.055 | 0.000 | ||
| 6 spectra, FSSPETDSHR | 0.270 | 0.000 | 0.294 | 0.013 | 0.293 | 0.130 | 0.000 | 0.000 | ||
| 9 spectra, FCLTYEASMTR | 0.425 | 0.000 | 0.067 | 0.508 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, LFNTSR | 0.379 | 0.190 | 0.000 | 0.431 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, YLAVDSPFLK | 0.347 | 0.115 | 0.202 | 0.304 | 0.022 | 0.010 | 0.000 | 0.000 | ||
| 1 spectrum, AAFFVTLDESEQGYR | 0.271 | 0.206 | 0.000 | 0.464 | 0.000 | 0.059 | 0.000 | 0.000 | ||
| 8 spectra, IPGEETDTIQHIK | 0.300 | 0.125 | 0.110 | 0.377 | 0.000 | 0.087 | 0.000 | 0.000 | ||
| 4 spectra, LLGSTIPLCSAQWER | 0.373 | 0.122 | 0.000 | 0.505 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
105 spectra |
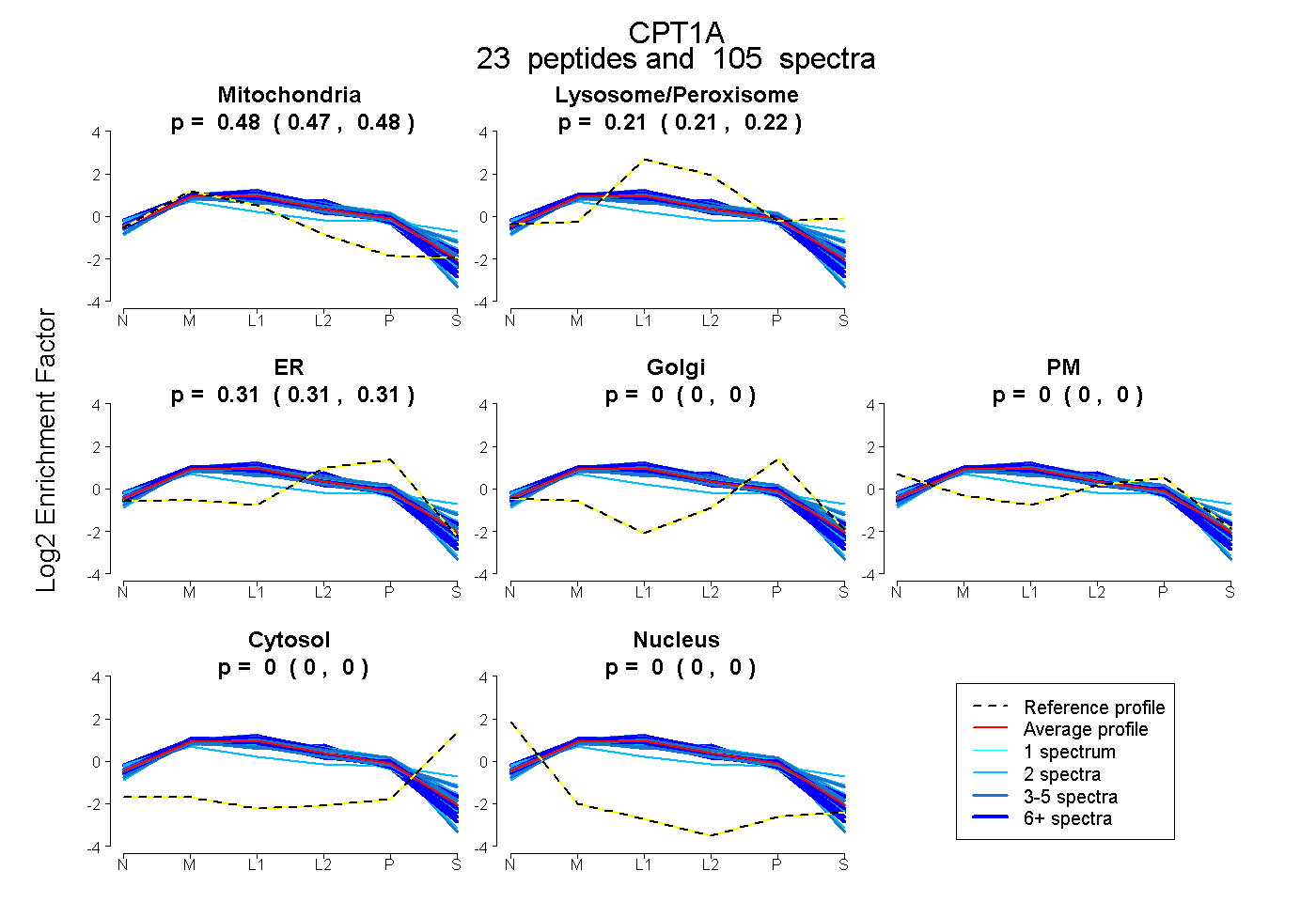 |
0.476 0.474 | 0.478 |
0.213 0.210 | 0.216 |
0.311 0.308 | 0.313 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
860 spectra |
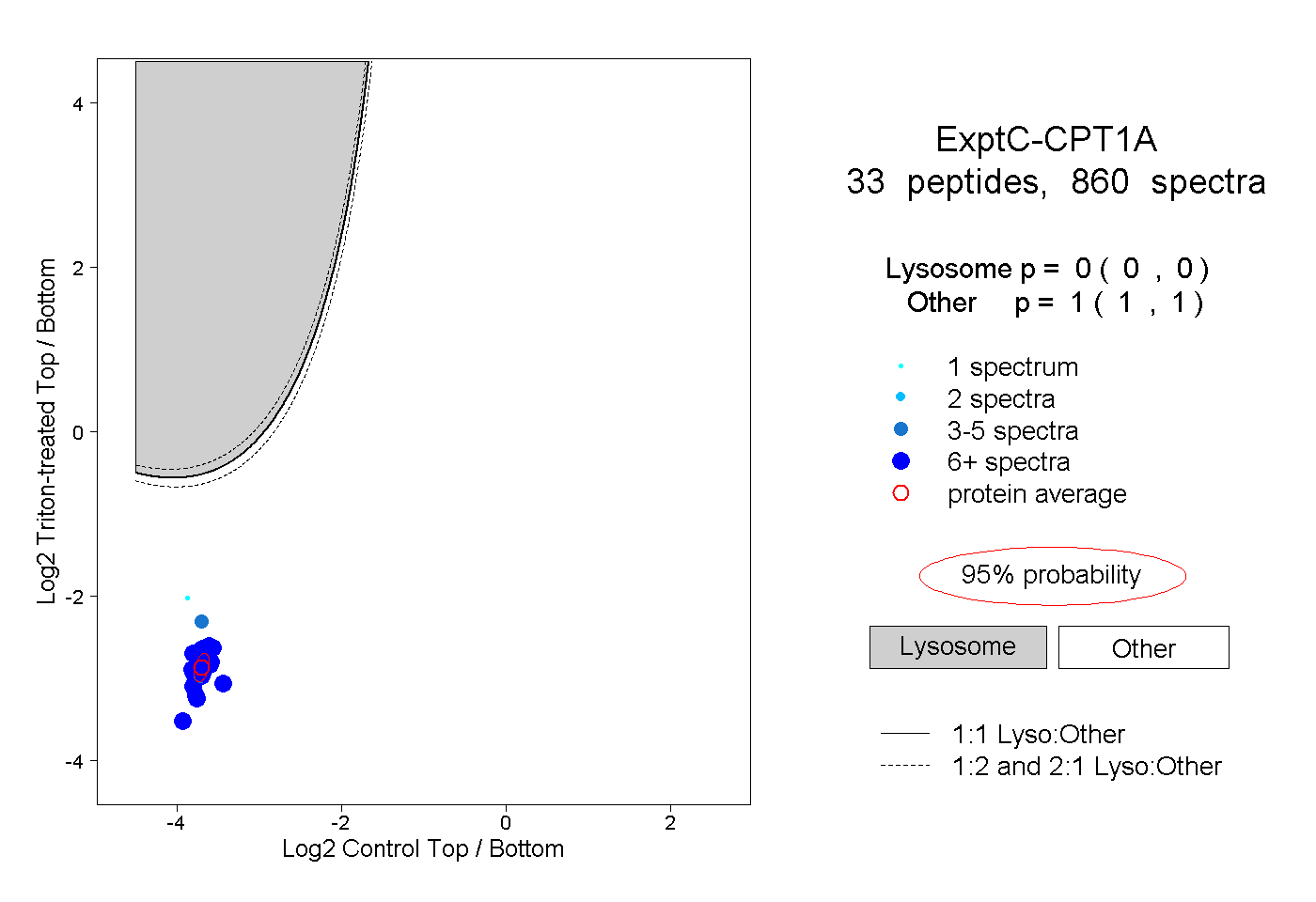 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
43 spectra |
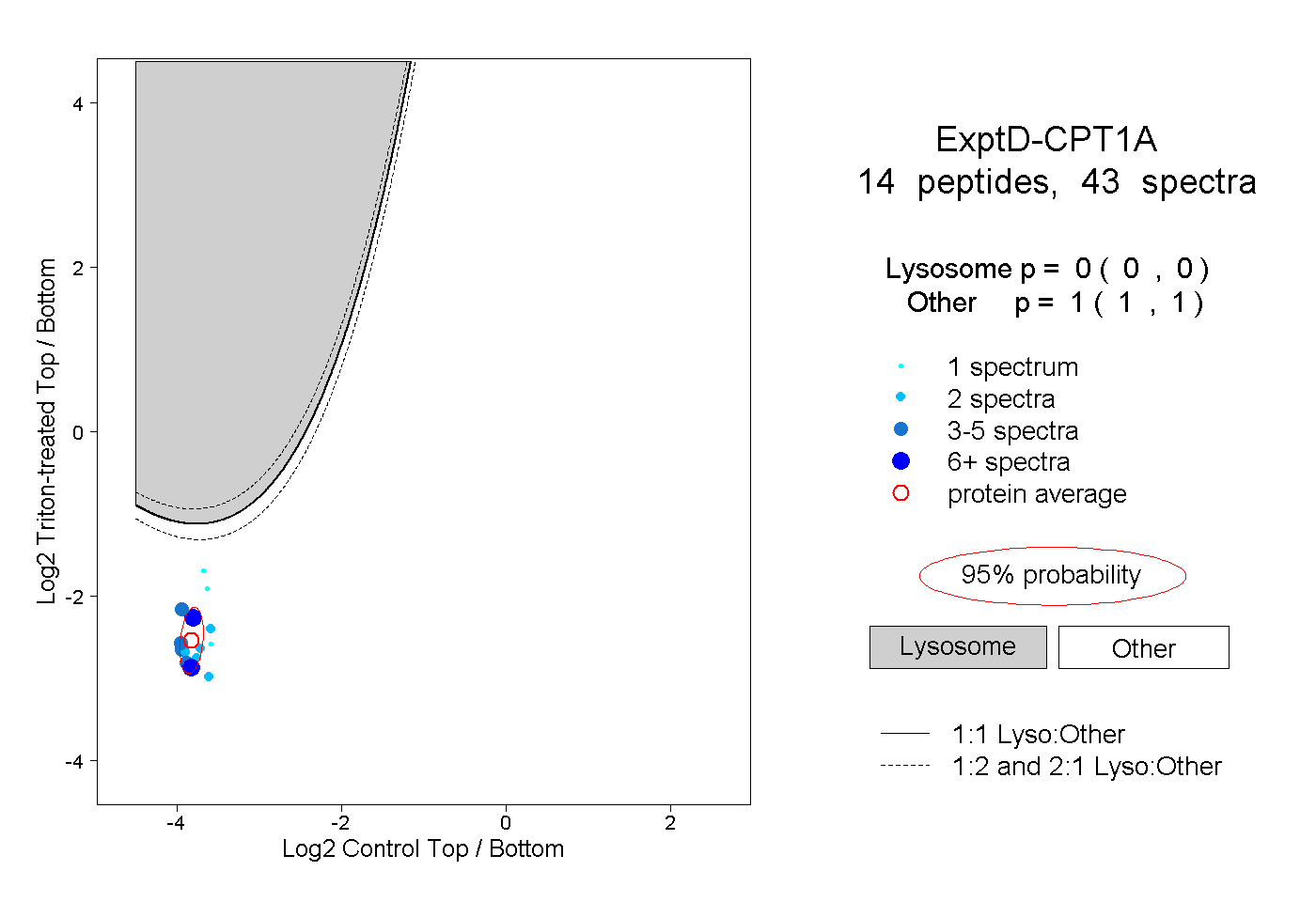 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |