peptides
spectra
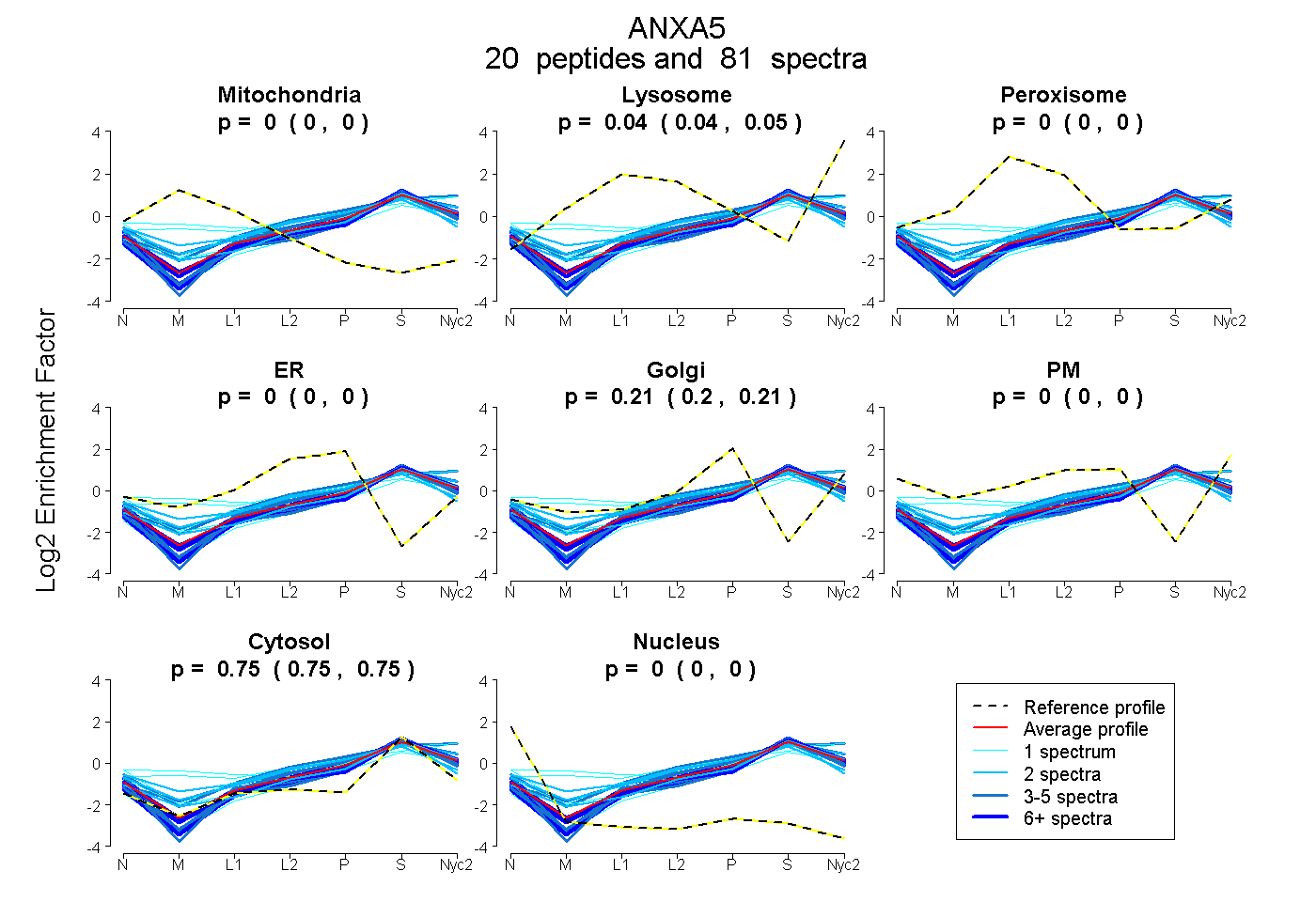
0.000 | 0.000
0.038 | 0.045
0.000 | 0.000
0.000 | 0.000
0.203 | 0.208
0.000 | 0.000
0.749 | 0.754
0.000 | 0.000
peptides
spectra
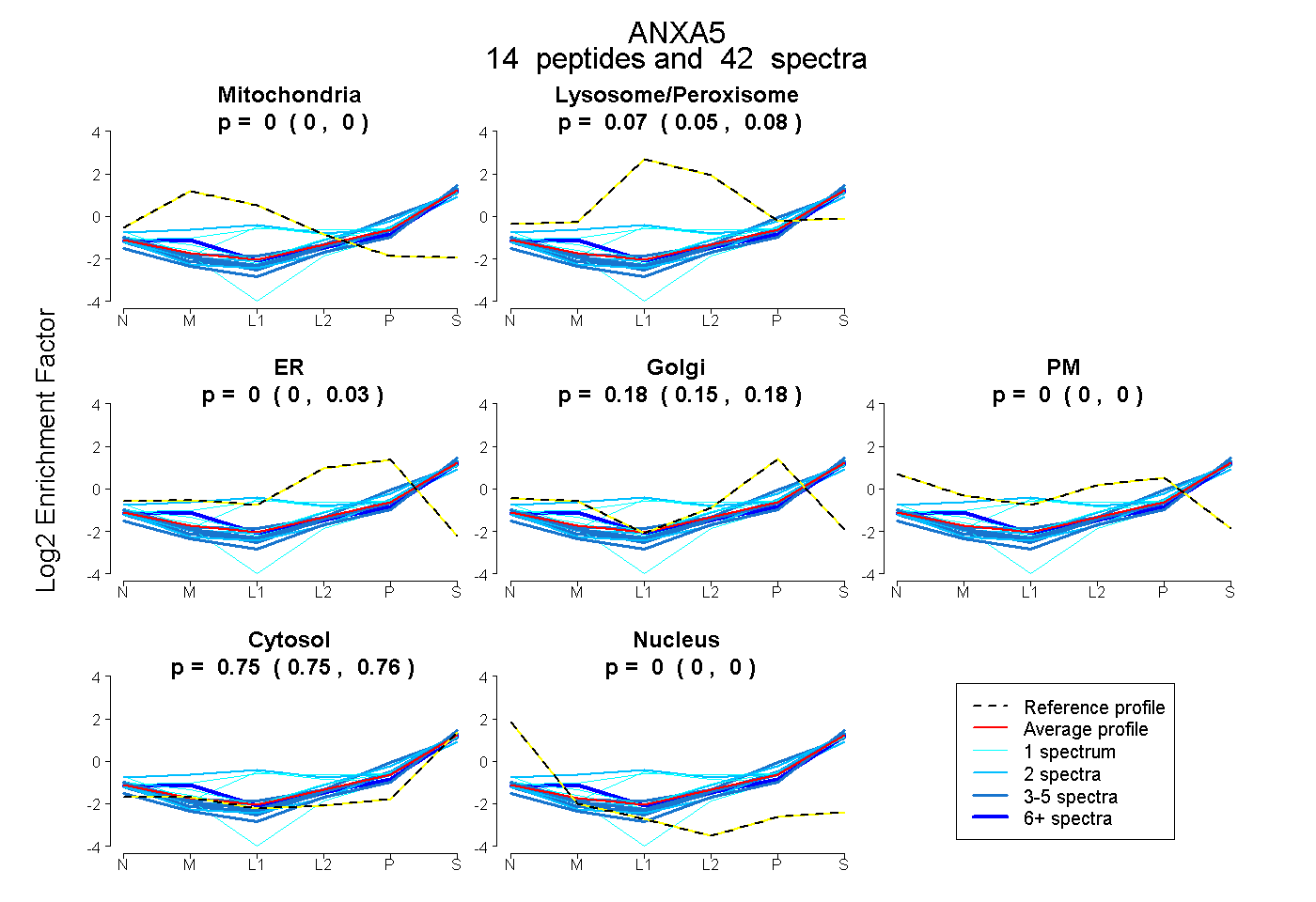
0.000 | 0.000
0.050 | 0.077
0.000 | 0.028
0.153 | 0.183
0.000 | 0.000
0.747 | 0.761
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
81 spectra |
 |
0.000 0.000 | 0.000 |
0.042 0.038 | 0.045 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.206 0.203 | 0.208 |
0.000 0.000 | 0.000 |
0.752 0.749 | 0.754 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.069 0.050 | 0.077 |
0.000 0.000 | 0.028 |
0.179 0.153 | 0.183 |
0.000 0.000 | 0.000 |
0.752 0.747 | 0.761 |
0.000 0.000 | 0.000 |
| 1 spectrum, ALLLLCGGEDD | 0.000 | 0.000 | 0.000 | 0.126 | 0.000 | 0.796 | 0.077 | |||
| 2 spectra, SIPAYLAETLYYAMK | 0.000 | 0.000 | 0.212 | 0.035 | 0.000 | 0.753 | 0.000 | |||
| 4 spectra, ADAEVLR | 0.000 | 0.000 | 0.019 | 0.178 | 0.000 | 0.803 | 0.000 | |||
| 1 spectrum, GLGTDEDSILNLLTAR | 0.000 | 0.043 | 0.000 | 0.200 | 0.000 | 0.757 | 0.000 | |||
| 5 spectra, SEIDLFNIR | 0.000 | 0.000 | 0.000 | 0.087 | 0.000 | 0.913 | 0.000 | |||
| 1 spectrum, NFATSLYSMIK | 0.000 | 0.339 | 0.000 | 0.071 | 0.000 | 0.590 | 0.000 | |||
| 5 spectra, GTVTDFSGFDGR | 0.000 | 0.000 | 0.017 | 0.189 | 0.000 | 0.794 | 0.000 | |||
| 2 spectra, LYDAYELK | 0.000 | 0.000 | 0.000 | 0.188 | 0.000 | 0.812 | 0.000 | |||
| 1 spectrum, FITILGTR | 0.000 | 0.311 | 0.000 | 0.000 | 0.000 | 0.689 | 0.000 | |||
| 8 spectra, GAGTDDHTLIR | 0.000 | 0.063 | 0.000 | 0.170 | 0.011 | 0.756 | 0.000 | |||
| 5 spectra, VLTEIIASR | 0.000 | 0.011 | 0.048 | 0.146 | 0.001 | 0.794 | 0.000 | |||
| 1 spectrum, TPEEIR | 0.000 | 0.092 | 0.012 | 0.198 | 0.000 | 0.698 | 0.000 | |||
| 4 spectra, LIVALMKPSR | 0.000 | 0.074 | 0.000 | 0.260 | 0.000 | 0.666 | 0.000 | |||
| 2 spectra, ETSGNLENLLLAVVK | 0.000 | 0.344 | 0.000 | 0.087 | 0.034 | 0.535 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
69 spectra |
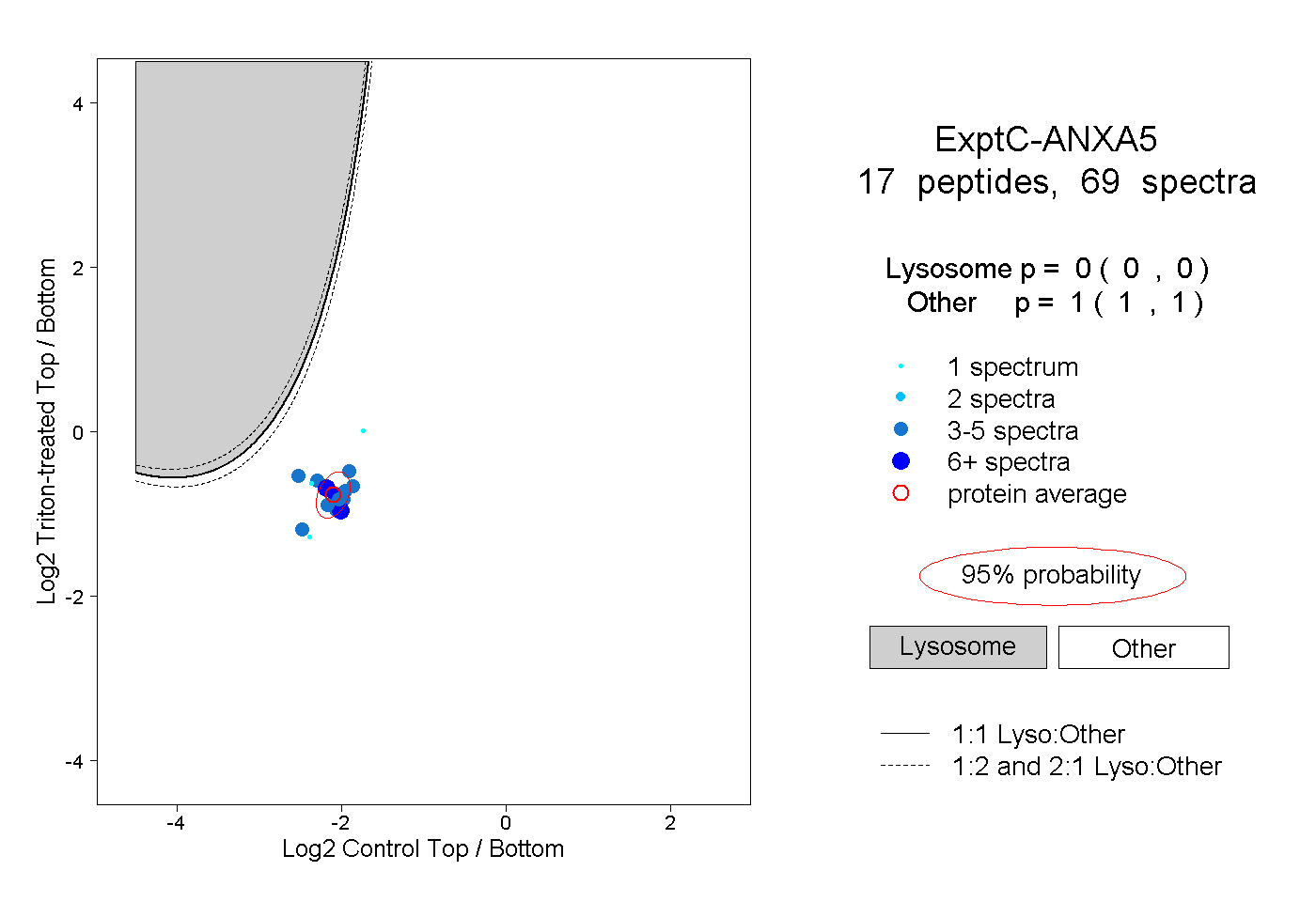 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
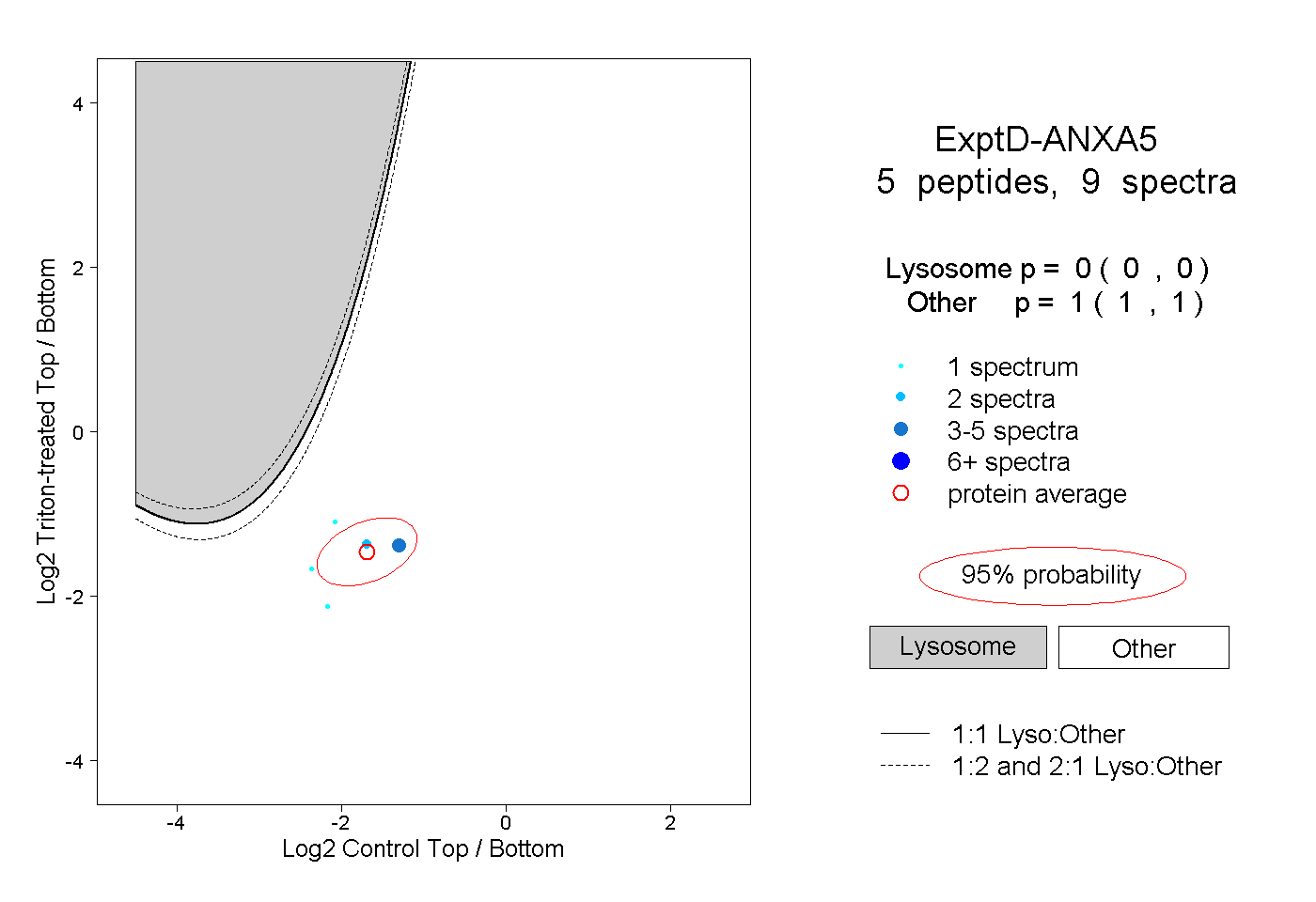 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |