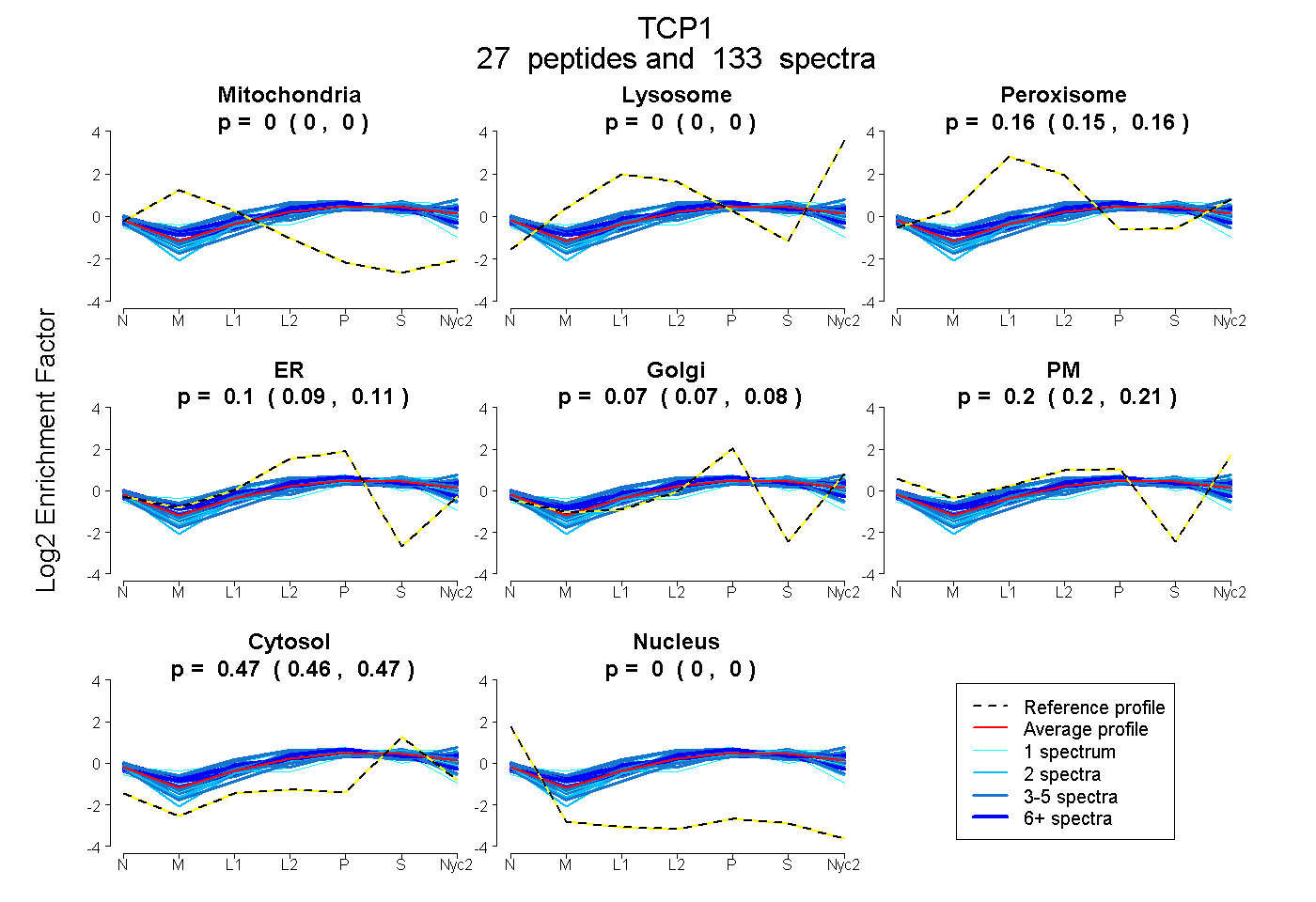
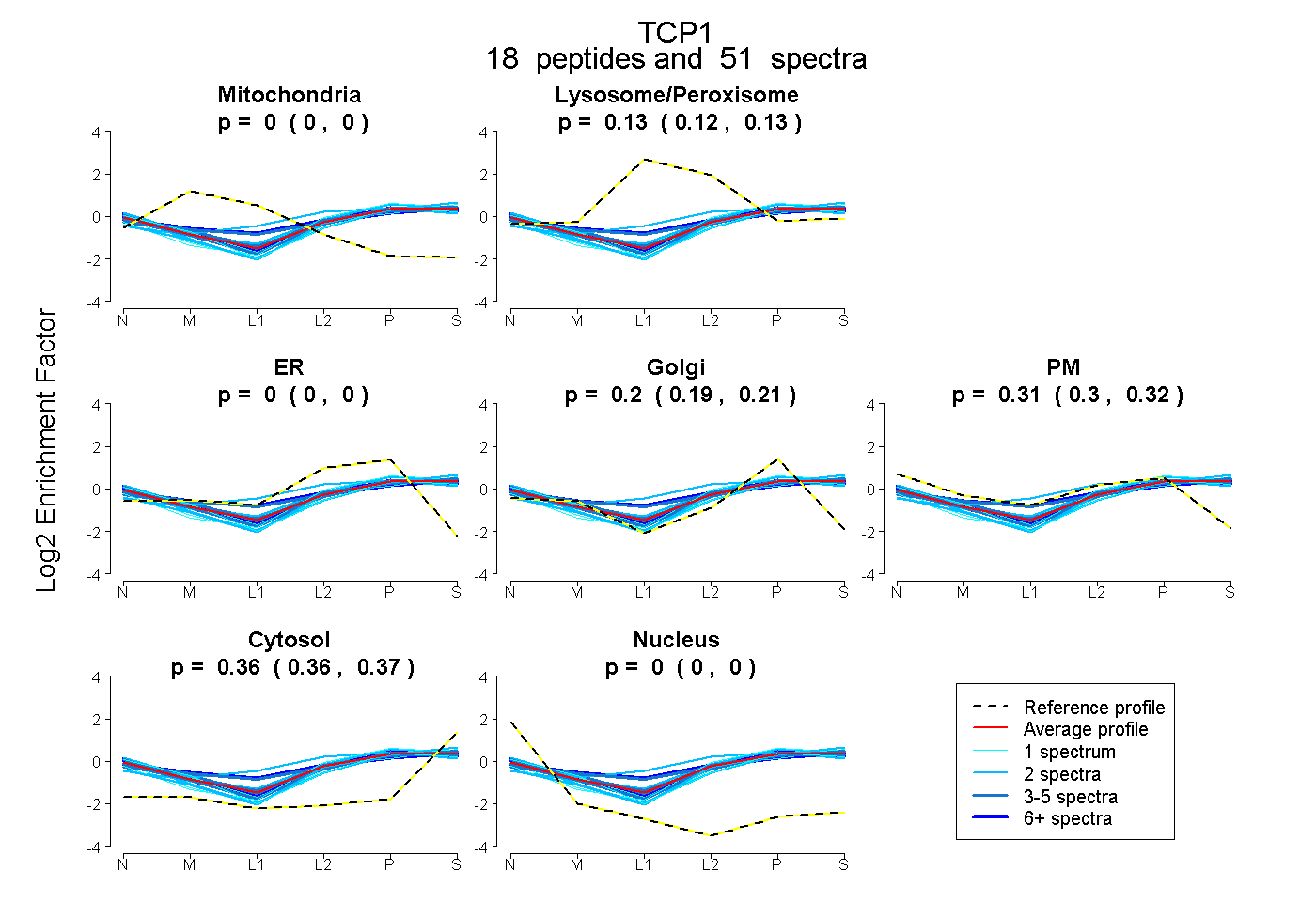
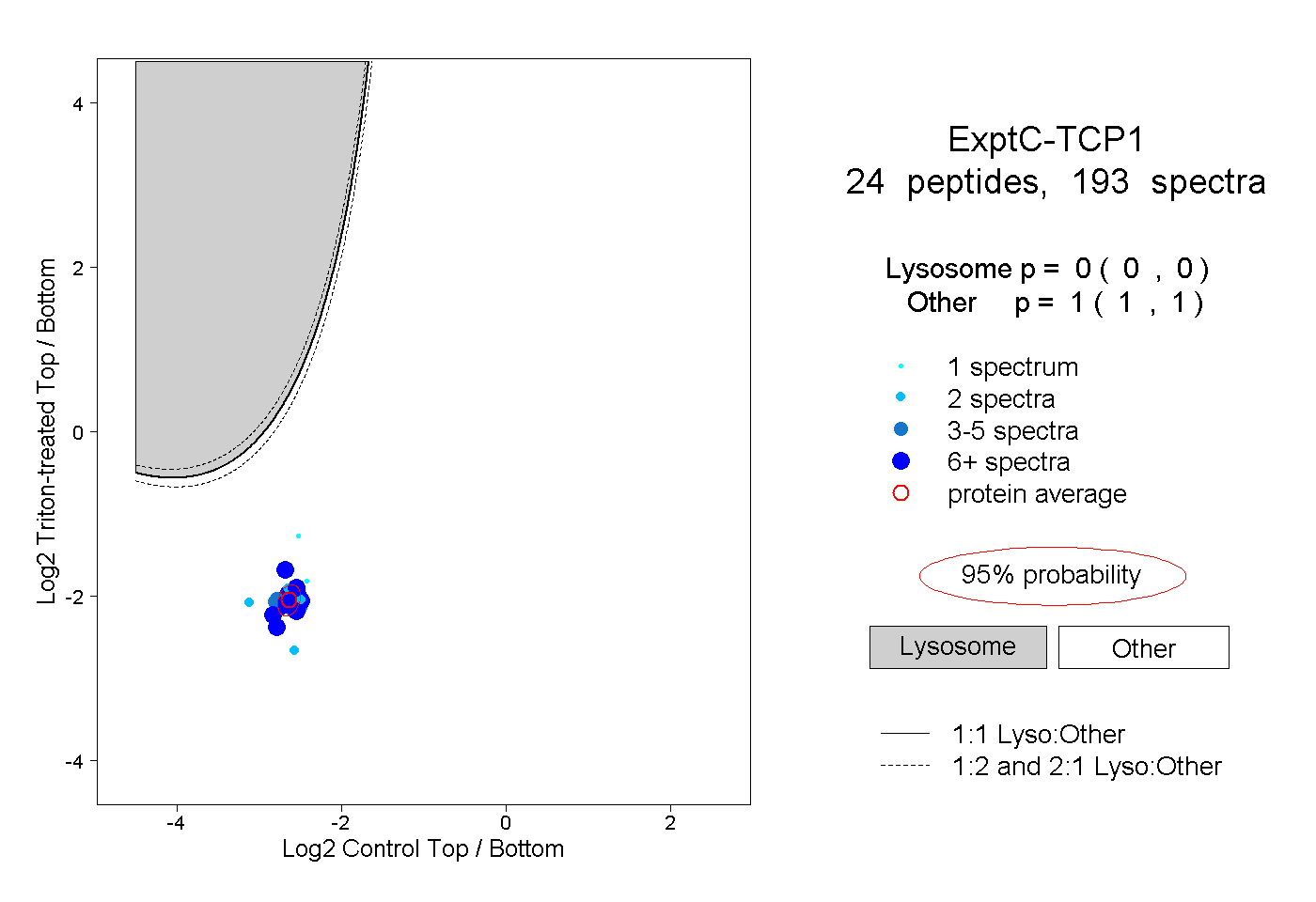
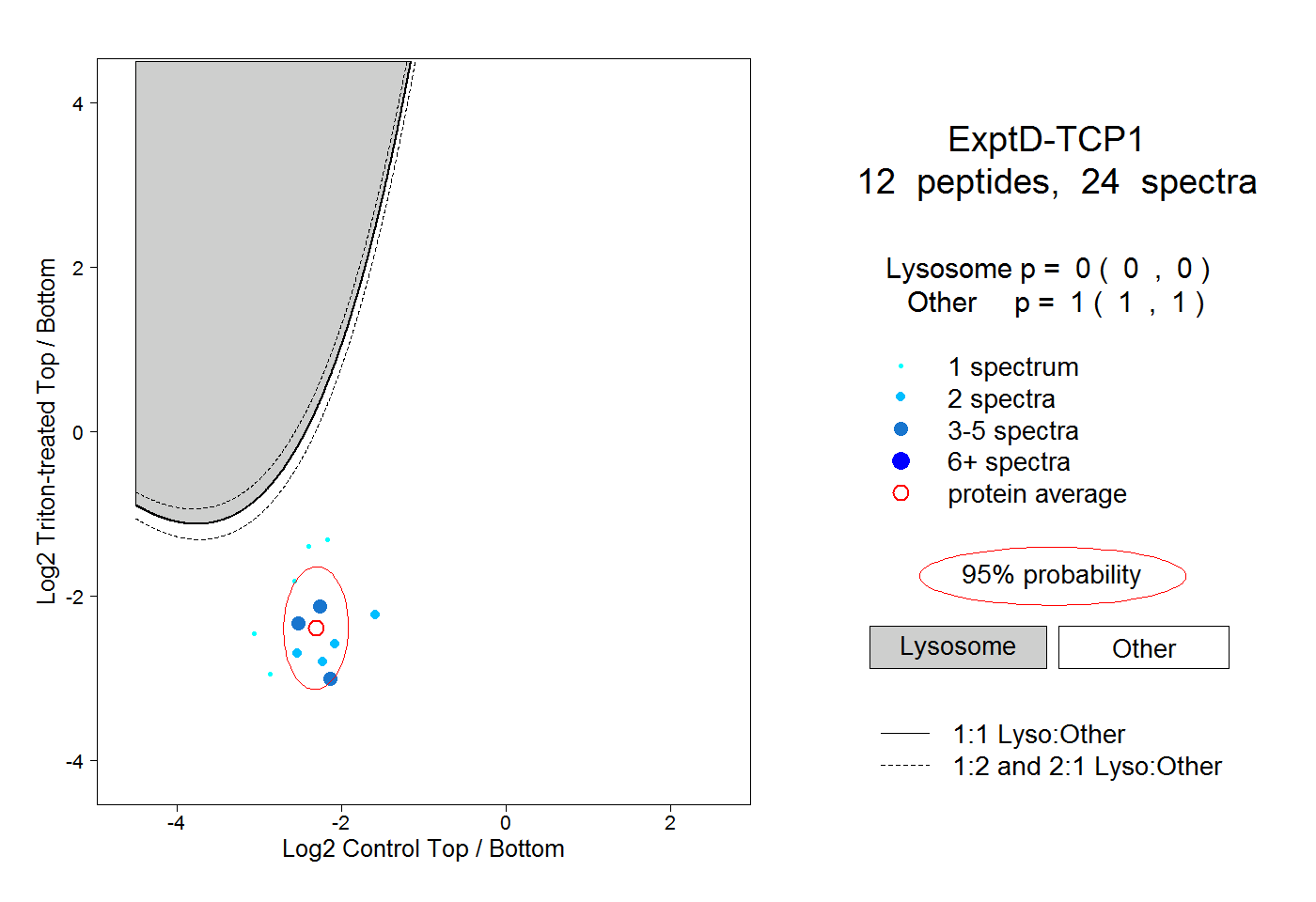
| 5 spectra, SSLGPVGLDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, FATEAAITILR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LGVQVVITDPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ICDDELILIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QAGVFEPTIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YINENLIINTDELGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ILATGANVILTTGGIDDMCLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, ESDLTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, YPVNSVNILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TSMSSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IACLDFSLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TSASIILR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, STGEAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, LLEVEHPAAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, EQLAIAEFAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LHPESK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, YFVEAGAMAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, AFHNEAQVNPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, HGGYENAVHSGALDD |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, NADELVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, DCLINAAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SQNVMAAASIANIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, WIGLDLVHGKPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, GANDFMCDEMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |