peptides
spectra
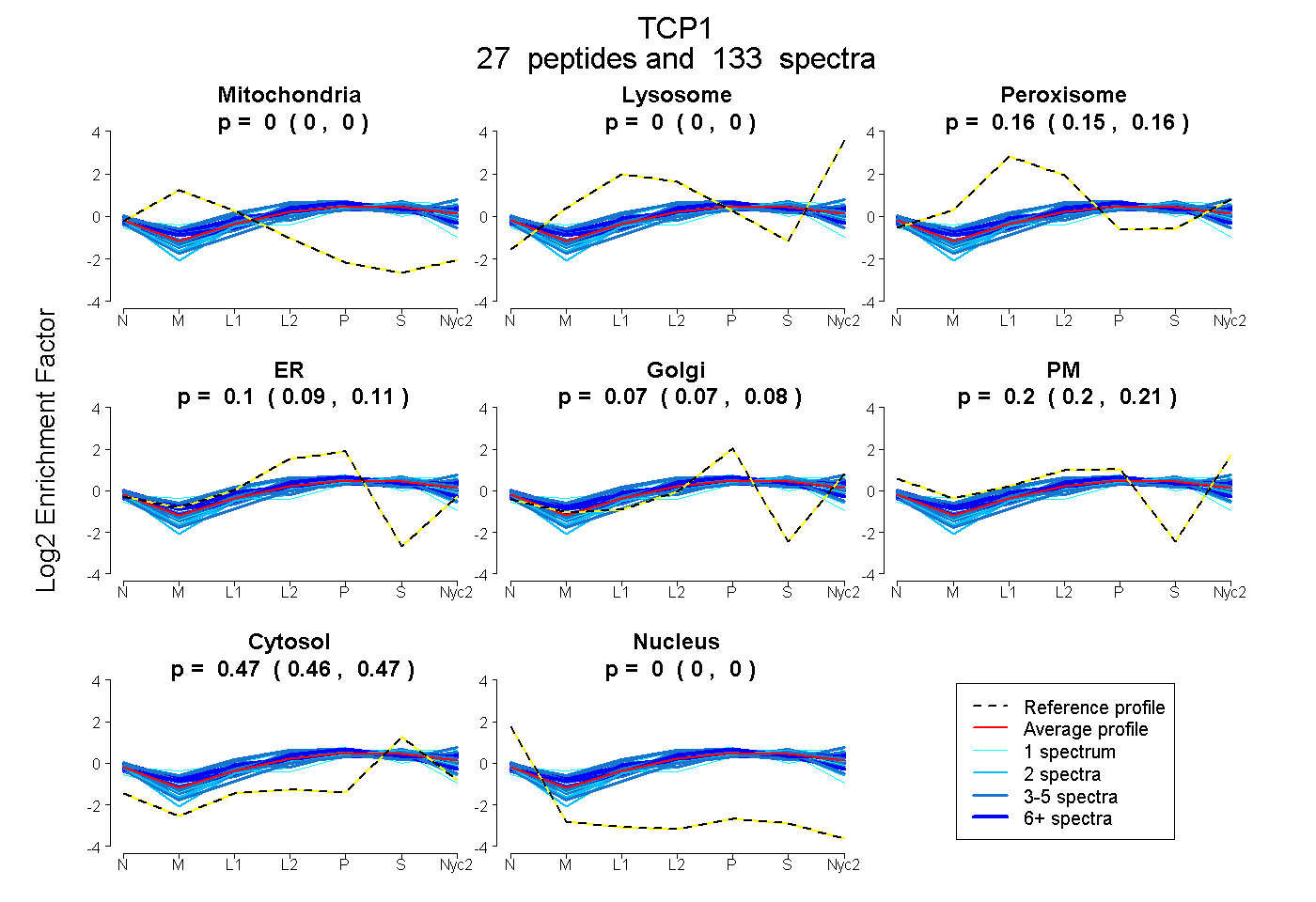
0.000 | 0.000
0.000 | 0.000
0.152 | 0.159
0.094 | 0.106
0.067 | 0.080
0.198 | 0.207
0.464 | 0.468
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
133 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.156 0.152 | 0.159 |
0.101 0.094 | 0.106 |
0.074 0.067 | 0.080 |
0.203 0.198 | 0.207 |
0.466 0.464 | 0.468 |
0.000 0.000 | 0.000 |
| 8 spectra, SSLGPVGLDK | 0.000 | 0.000 | 0.186 | 0.000 | 0.028 | 0.374 | 0.412 | 0.000 | ||
| 3 spectra, FATEAAITILR | 0.000 | 0.021 | 0.120 | 0.070 | 0.000 | 0.355 | 0.435 | 0.000 | ||
| 4 spectra, ICDDELILIK | 0.000 | 0.000 | 0.129 | 0.294 | 0.000 | 0.093 | 0.485 | 0.000 | ||
| 1 spectrum, QAGVFEPTIVK | 0.000 | 0.000 | 0.095 | 0.185 | 0.000 | 0.194 | 0.526 | 0.000 | ||
| 2 spectra, YINENLIINTDELGR | 0.000 | 0.000 | 0.096 | 0.086 | 0.036 | 0.233 | 0.550 | 0.000 | ||
| 2 spectra, ESDLTK | 0.000 | 0.000 | 0.086 | 0.080 | 0.069 | 0.225 | 0.540 | 0.000 | ||
| 4 spectra, YPVNSVNILK | 0.000 | 0.000 | 0.152 | 0.000 | 0.084 | 0.257 | 0.507 | 0.000 | ||
| 4 spectra, TSMSSK | 0.000 | 0.047 | 0.243 | 0.000 | 0.007 | 0.364 | 0.339 | 0.000 | ||
| 1 spectrum, IACLDFSLQK | 0.000 | 0.000 | 0.303 | 0.000 | 0.272 | 0.158 | 0.266 | 0.000 | ||
| 5 spectra, TSASIILR | 0.000 | 0.000 | 0.108 | 0.025 | 0.032 | 0.432 | 0.402 | 0.000 | ||
| 5 spectra, STGEAIR | 0.000 | 0.000 | 0.102 | 0.142 | 0.000 | 0.258 | 0.498 | 0.000 | ||
| 7 spectra, SLHDALCVVK | 0.000 | 0.000 | 0.246 | 0.198 | 0.091 | 0.036 | 0.430 | 0.000 | ||
| 5 spectra, LLEVEHPAAK | 0.000 | 0.000 | 0.075 | 0.150 | 0.000 | 0.264 | 0.511 | 0.000 | ||
| 7 spectra, EQLAIAEFAR | 0.000 | 0.000 | 0.119 | 0.019 | 0.063 | 0.318 | 0.480 | 0.000 | ||
| 5 spectra, LHPESK | 0.000 | 0.000 | 0.092 | 0.226 | 0.064 | 0.140 | 0.478 | 0.000 | ||
| 1 spectrum, MLVDDIGDVTITNDGATILK | 0.000 | 0.000 | 0.172 | 0.118 | 0.144 | 0.000 | 0.566 | 0.000 | ||
| 15 spectra, YFVEAGAMAVR | 0.000 | 0.000 | 0.172 | 0.000 | 0.141 | 0.239 | 0.448 | 0.000 | ||
| 1 spectrum, AFHNEAQVNPER | 0.000 | 0.000 | 0.145 | 0.338 | 0.000 | 0.000 | 0.517 | 0.000 | ||
| 2 spectra, HGGYENAVHSGALDD | 0.000 | 0.000 | 0.046 | 0.000 | 0.118 | 0.278 | 0.558 | 0.000 | ||
| 4 spectra, NADELVK | 0.000 | 0.000 | 0.014 | 0.113 | 0.000 | 0.262 | 0.611 | 0.000 | ||
| 2 spectra, DCLINAAK | 0.000 | 0.000 | 0.136 | 0.328 | 0.000 | 0.014 | 0.522 | 0.000 | ||
| 3 spectra, SQNVMAAASIANIVK | 0.000 | 0.000 | 0.188 | 0.127 | 0.000 | 0.301 | 0.384 | 0.000 | ||
| 8 spectra, WIGLDLVHGKPR | 0.000 | 0.009 | 0.121 | 0.127 | 0.083 | 0.219 | 0.440 | 0.000 | ||
| 27 spectra, GANDFMCDEMER | 0.000 | 0.000 | 0.230 | 0.095 | 0.175 | 0.045 | 0.455 | 0.000 | ||
| 1 spectrum, EVGDGTTSVVIIAAELLK | 0.000 | 0.134 | 0.039 | 0.028 | 0.086 | 0.203 | 0.511 | 0.000 | ||
| 3 spectra, VLCELADLQDK | 0.000 | 0.000 | 0.181 | 0.308 | 0.000 | 0.000 | 0.511 | 0.000 | ||
| 3 spectra, IHPTSVISGYR | 0.000 | 0.000 | 0.299 | 0.000 | 0.287 | 0.037 | 0.378 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
51 spectra |
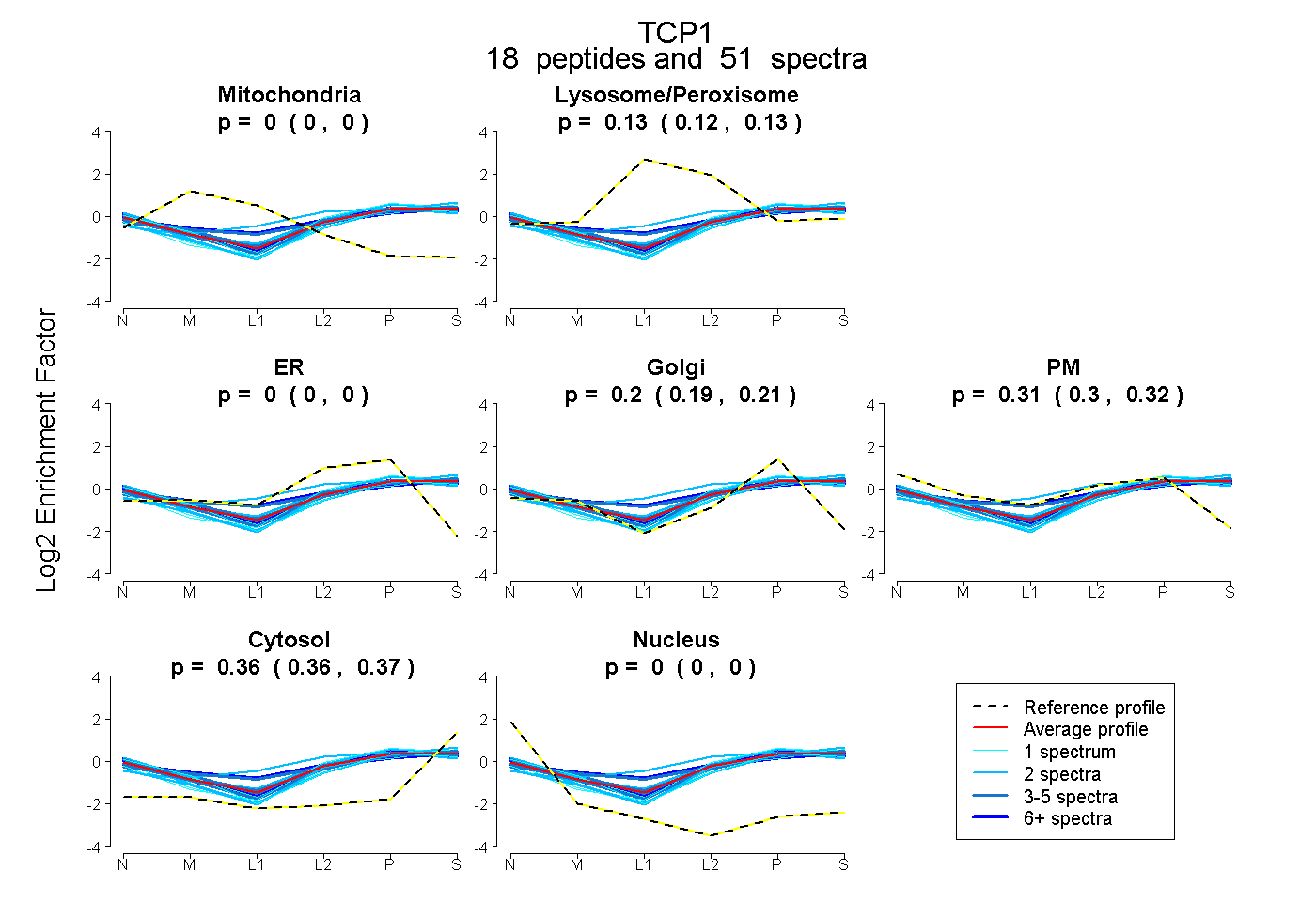 |
0.000 0.000 | 0.000 |
0.128 0.122 | 0.133 |
0.000 0.000 | 0.000 |
0.200 0.193 | 0.205 |
0.308 0.299 | 0.316 |
0.364 0.362 | 0.366 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
193 spectra |
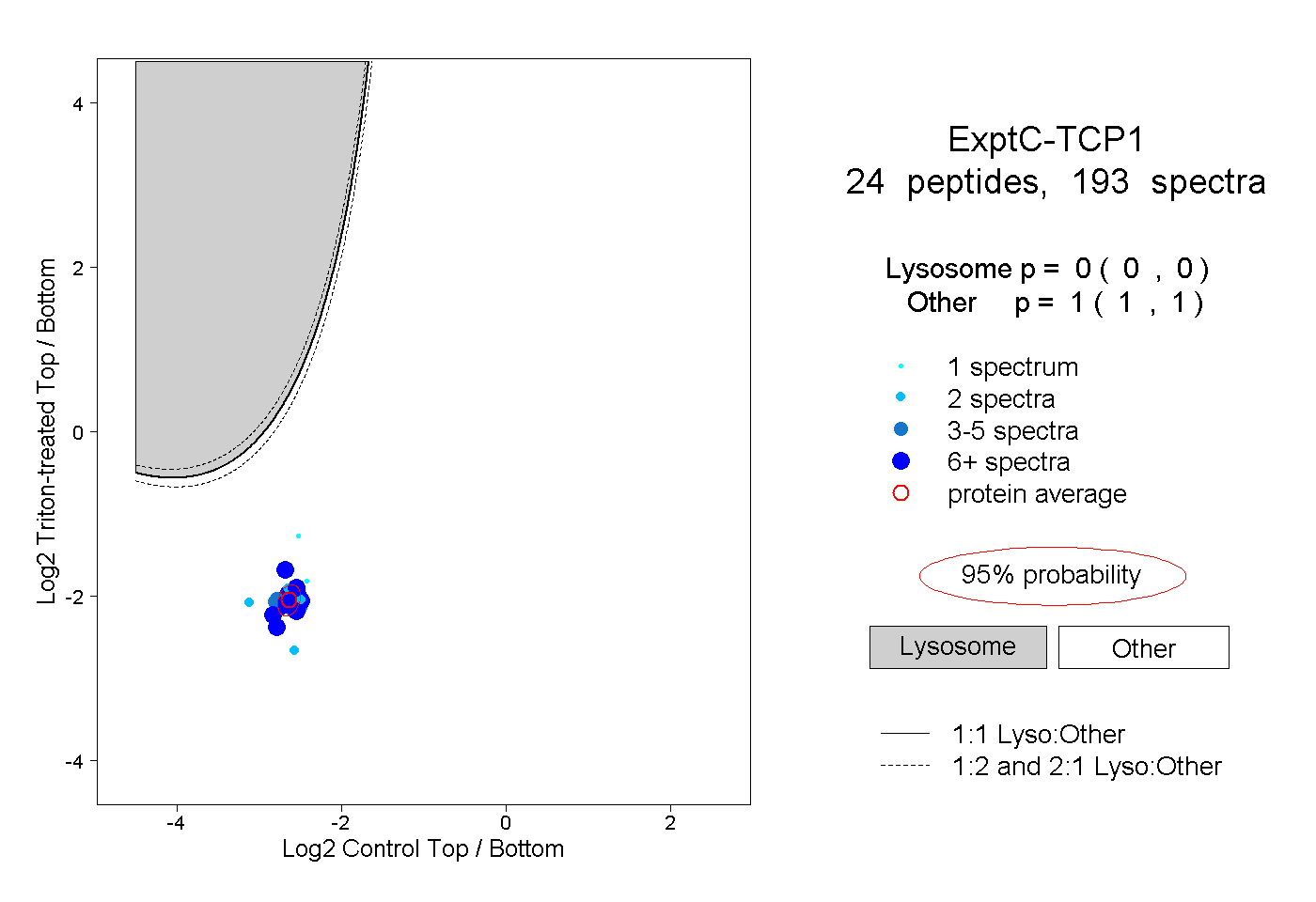 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
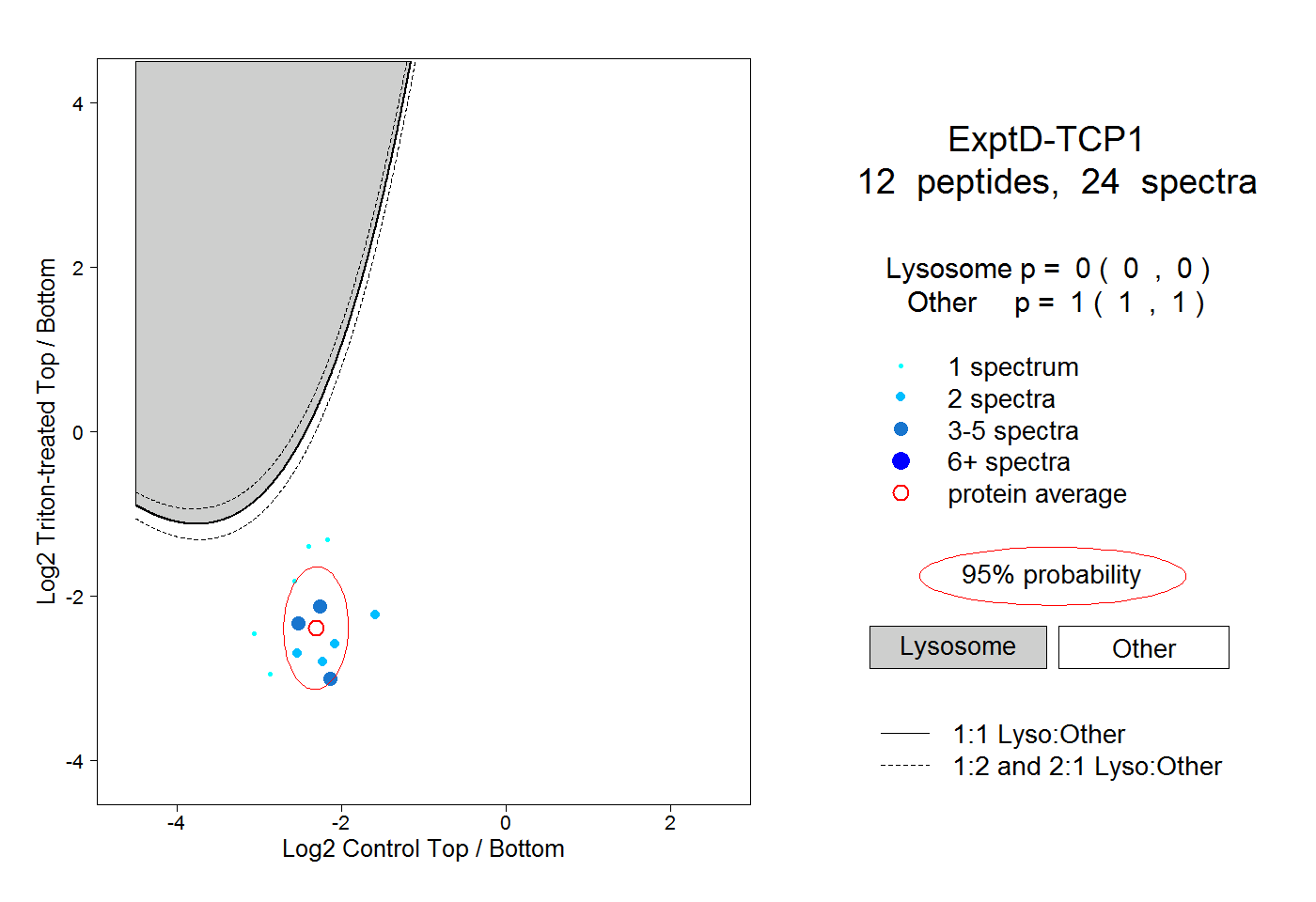 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |