peptides
spectra
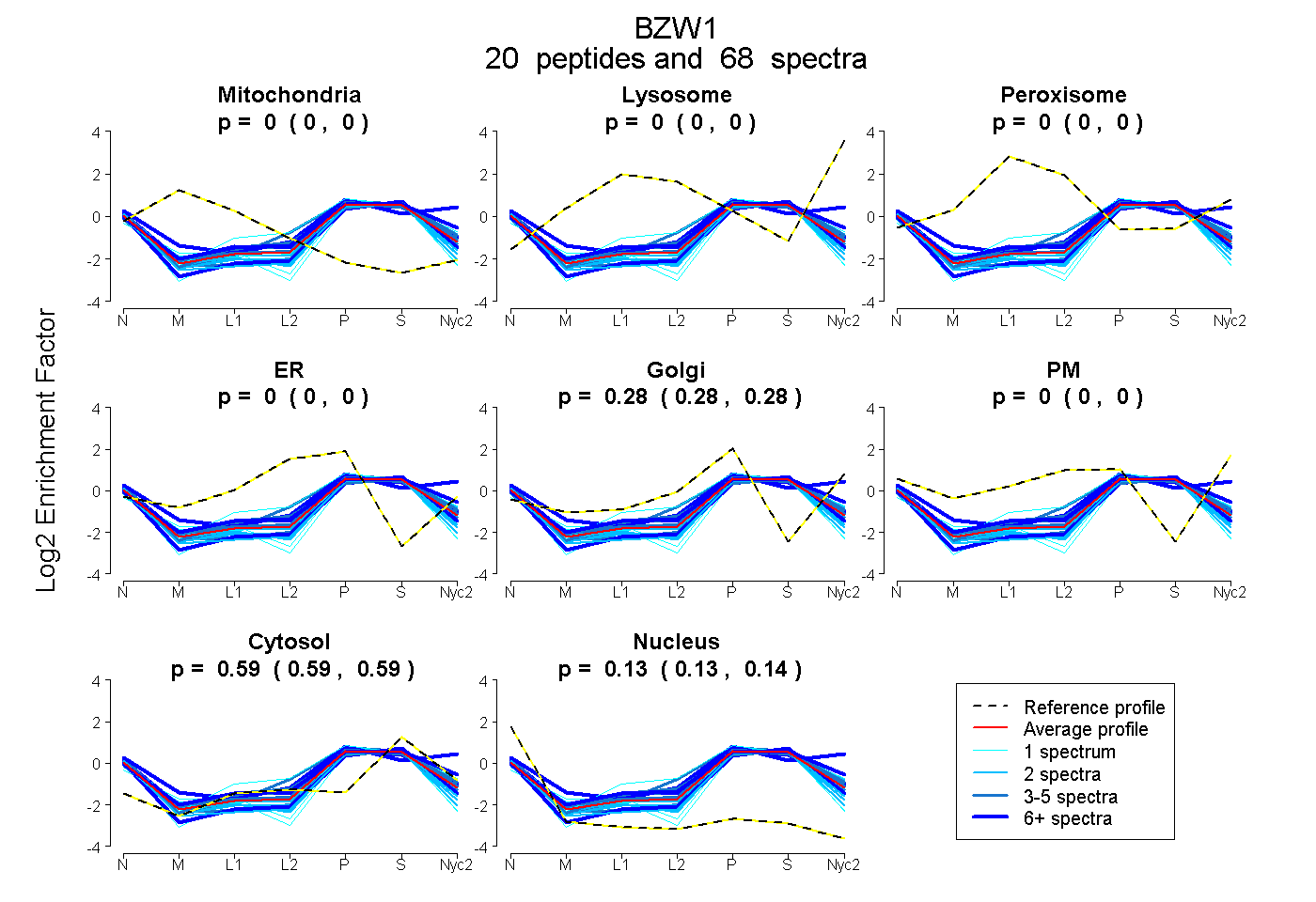
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.276 | 0.281
0.000 | 0.000
0.587 | 0.590
0.129 | 0.135
peptides
spectra
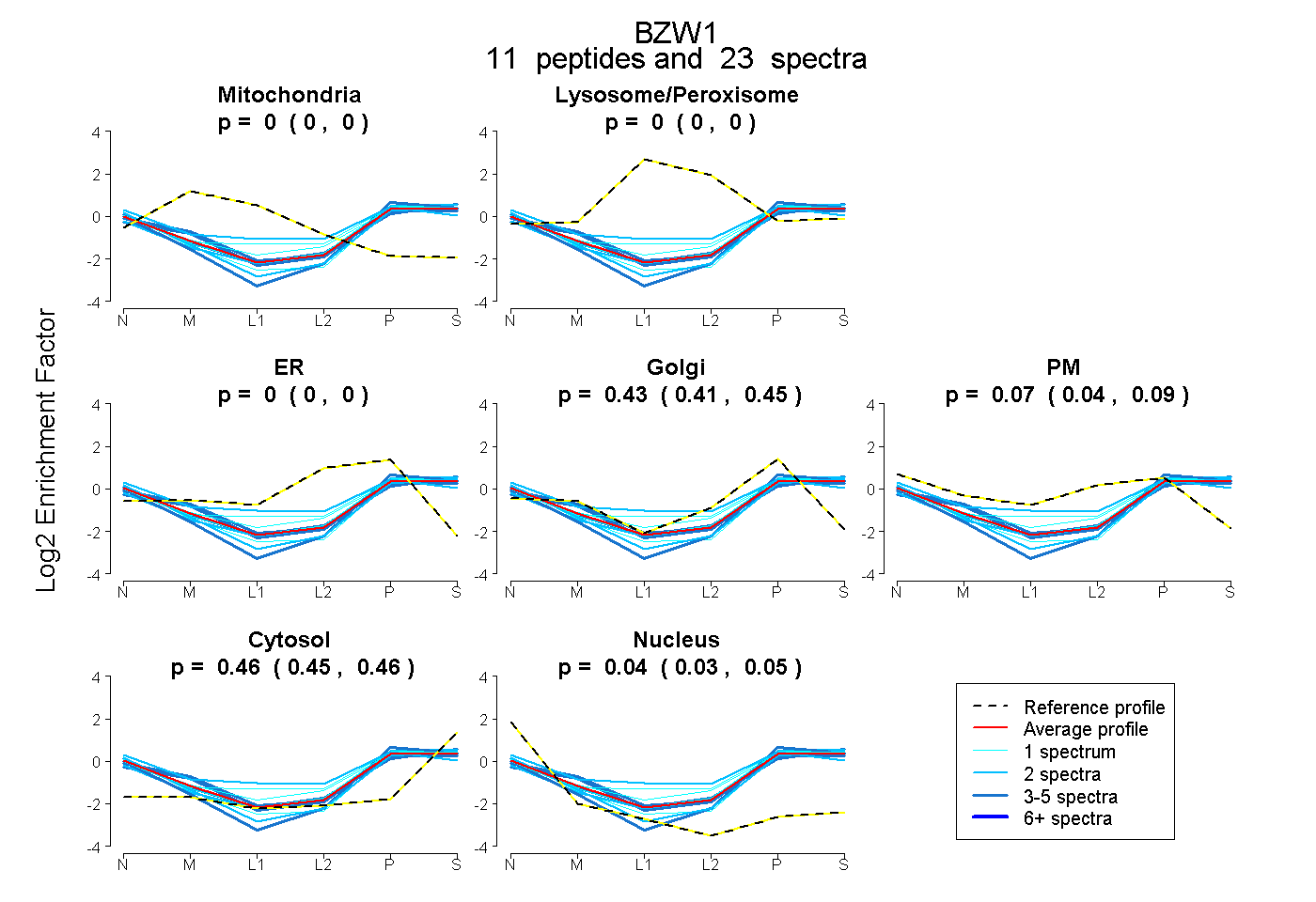
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.411 | 0.454
0.040 | 0.089
0.452 | 0.462
0.035 | 0.049
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
68 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.279 0.276 | 0.281 |
0.000 0.000 | 0.000 |
0.589 0.587 | 0.590 |
0.133 0.129 | 0.135 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.433 0.411 | 0.454 |
0.067 0.040 | 0.089 |
0.457 0.452 | 0.462 |
0.042 0.035 | 0.049 |
| 1 spectrum, LLLFLK | 0.000 | 0.074 | 0.000 | 0.235 | 0.263 | 0.428 | 0.000 | |||
| 1 spectrum, EGVSAAFAVK | 0.000 | 0.000 | 0.000 | 0.418 | 0.000 | 0.445 | 0.137 | |||
| 4 spectra, DINAVAASLR | 0.000 | 0.000 | 0.000 | 0.505 | 0.000 | 0.474 | 0.021 | |||
| 2 spectra, NQQTIGAR | 0.000 | 0.055 | 0.000 | 0.120 | 0.479 | 0.346 | 0.000 | |||
| 3 spectra, AEVLSEEPILK | 0.000 | 0.000 | 0.000 | 0.296 | 0.148 | 0.508 | 0.047 | |||
| 3 spectra, FLDASGAK | 0.000 | 0.000 | 0.000 | 0.411 | 0.106 | 0.445 | 0.037 | |||
| 2 spectra, ELQEQMSR | 0.000 | 0.000 | 0.000 | 0.485 | 0.000 | 0.507 | 0.008 | |||
| 2 spectra, IVVLFYK | 0.000 | 0.000 | 0.000 | 0.415 | 0.000 | 0.458 | 0.127 | |||
| 3 spectra, ELSEYVR | 0.000 | 0.000 | 0.000 | 0.467 | 0.000 | 0.440 | 0.093 | |||
| 1 spectrum, FVEWLK | 0.000 | 0.000 | 0.000 | 0.246 | 0.283 | 0.471 | 0.000 | |||
| 1 spectrum, GFEDEVK | 0.000 | 0.000 | 0.000 | 0.450 | 0.064 | 0.463 | 0.023 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
37 spectra |
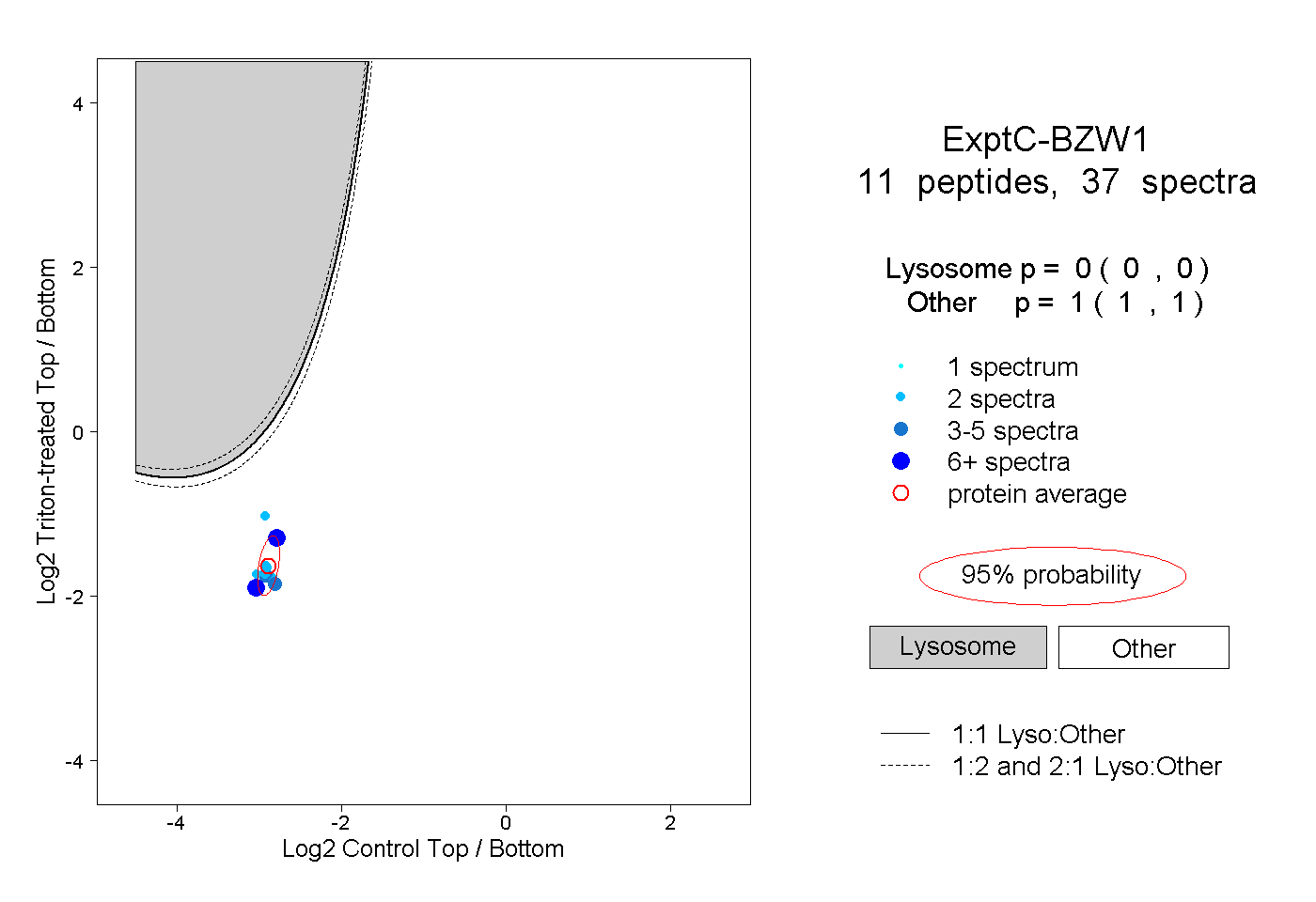 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
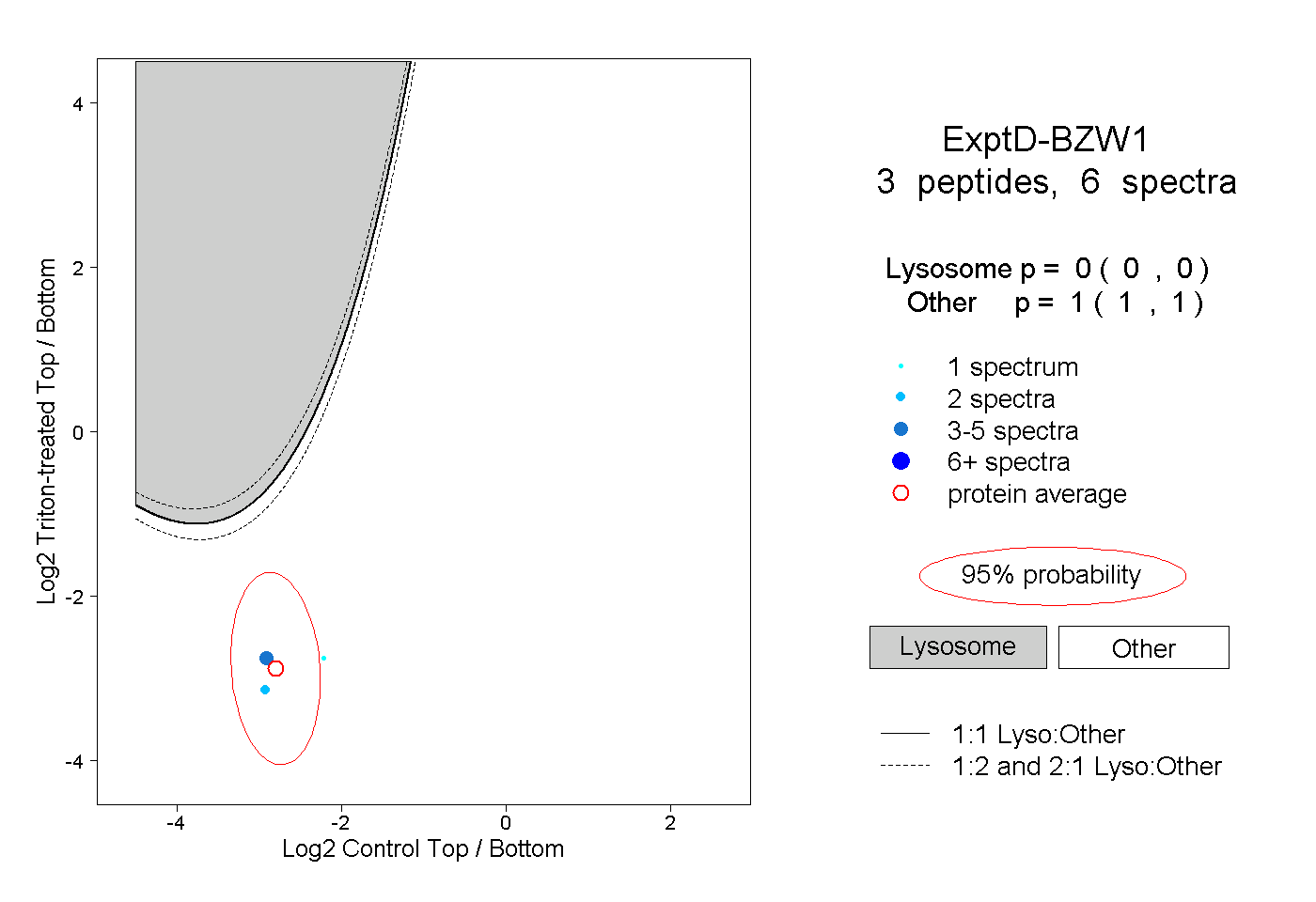 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |