peptides
spectra
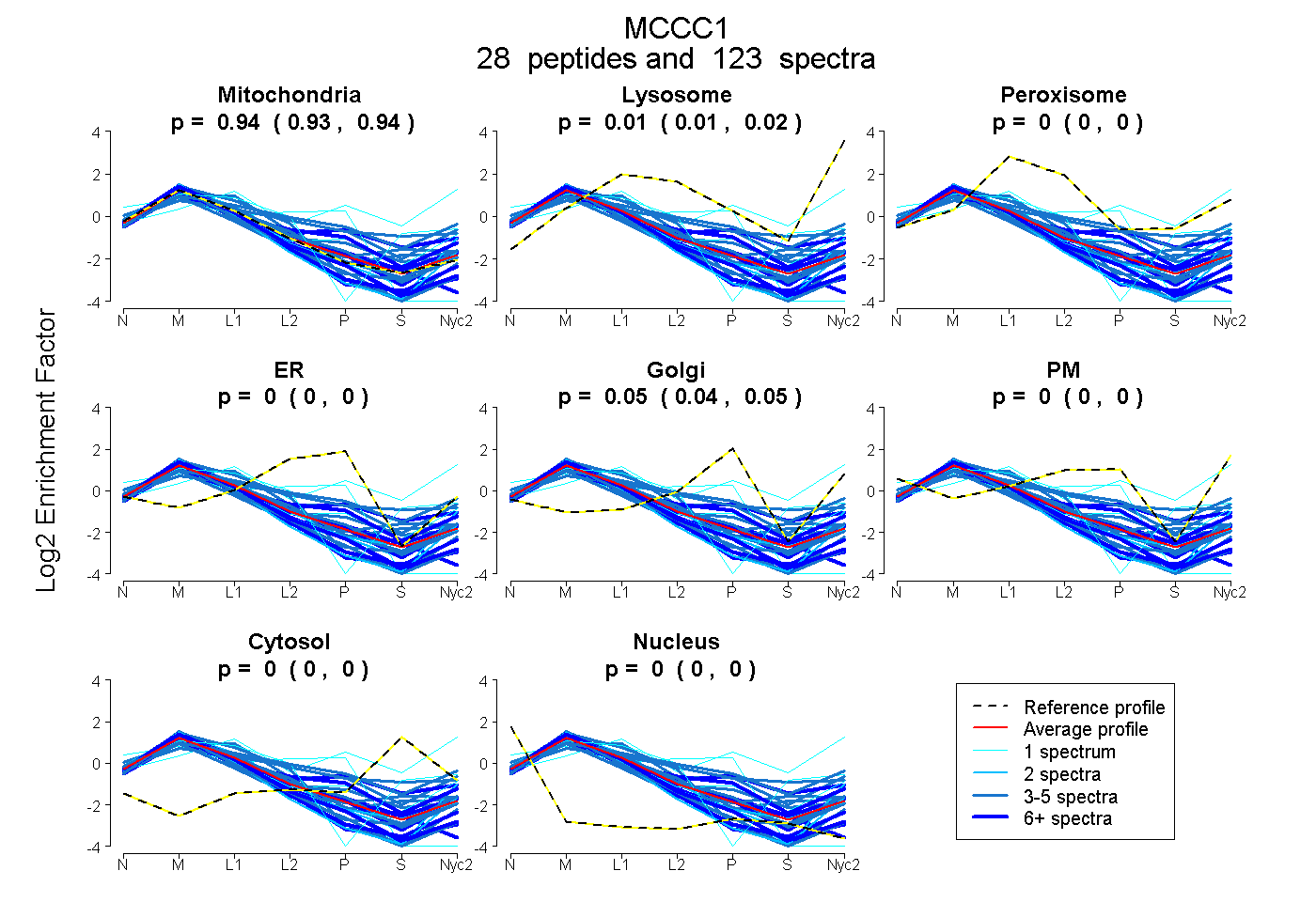
0.934 | 0.943
0.007 | 0.016
0.000 | 0.000
0.000 | 0.003
0.043 | 0.053
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
123 spectra |
 |
0.939 0.934 | 0.943 |
0.012 0.007 | 0.016 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.003 |
0.049 0.043 | 0.053 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, LHTQDQFSPFSFSSGR | 0.444 | 0.000 | 0.277 | 0.000 | 0.132 | 0.000 | 0.146 | 0.000 | ||
| 10 spectra, VLIANR | 0.953 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.047 | ||
| 4 spectra, SFNDDAMLIEK | 0.916 | 0.000 | 0.000 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, IPLSQEEIPLQGHAFEAR | 0.970 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.030 | ||
| 8 spectra, LVVWASDR | 0.925 | 0.000 | 0.000 | 0.000 | 0.032 | 0.043 | 0.000 | 0.000 | ||
| 5 spectra, AVNYVGAGTVEFIMDSK | 0.842 | 0.000 | 0.021 | 0.014 | 0.094 | 0.000 | 0.028 | 0.000 | ||
| 8 spectra, HNFYFMEMNTR | 0.595 | 0.049 | 0.056 | 0.000 | 0.193 | 0.000 | 0.107 | 0.000 | ||
| 4 spectra, YSLHQYNIVGLR | 0.467 | 0.051 | 0.221 | 0.000 | 0.165 | 0.071 | 0.025 | 0.000 | ||
| 3 spectra, DLLPTHSTIAK | 0.585 | 0.017 | 0.174 | 0.000 | 0.105 | 0.120 | 0.000 | 0.000 | ||
| 9 spectra, GEIACR | 0.920 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.080 | ||
| 2 spectra, TNVDFLLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, VLNLAR | 0.620 | 0.000 | 0.276 | 0.000 | 0.000 | 0.000 | 0.104 | 0.000 | ||
| 6 spectra, NDIIIAVTYNR | 0.746 | 0.056 | 0.000 | 0.016 | 0.182 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LQVEHPVTEMITGTDLVEWQLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, QEGIIFIGPPSTAIR | 0.976 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | ||
| 2 spectra, EFQEQLESAR | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | ||
| 1 spectrum, IIEEAPAPGIDPEVR | 0.115 | 0.314 | 0.200 | 0.000 | 0.228 | 0.000 | 0.143 | 0.000 | ||
| 6 spectra, ESVCQAALGLILK | 0.895 | 0.029 | 0.000 | 0.000 | 0.075 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, FVDTPR | 0.880 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.120 | 0.000 | ||
| 3 spectra, LGEAAVR | 0.798 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.202 | 0.000 | ||
| 5 spectra, QGDEVSVHYDPMIAK | 0.964 | 0.000 | 0.000 | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, HAPLVEFEEEEV | 0.943 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.057 | ||
| 5 spectra, VFFSEGAQANR | 0.988 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.012 | ||
| 1 spectrum, HVEVQVFGDHHGNAVYLFER | 0.547 | 0.000 | 0.000 | 0.352 | 0.000 | 0.000 | 0.000 | 0.101 | ||
| 6 spectra, MGVQSVAVYSEADR | 0.962 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.038 | ||
| 2 spectra, IETGVR | 0.898 | 0.019 | 0.000 | 0.000 | 0.000 | 0.083 | 0.000 | 0.000 | ||
| 1 spectrum, LNISYTR | 0.746 | 0.081 | 0.000 | 0.000 | 0.173 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, IGYPVMIK | 0.993 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.007 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
63 spectra |
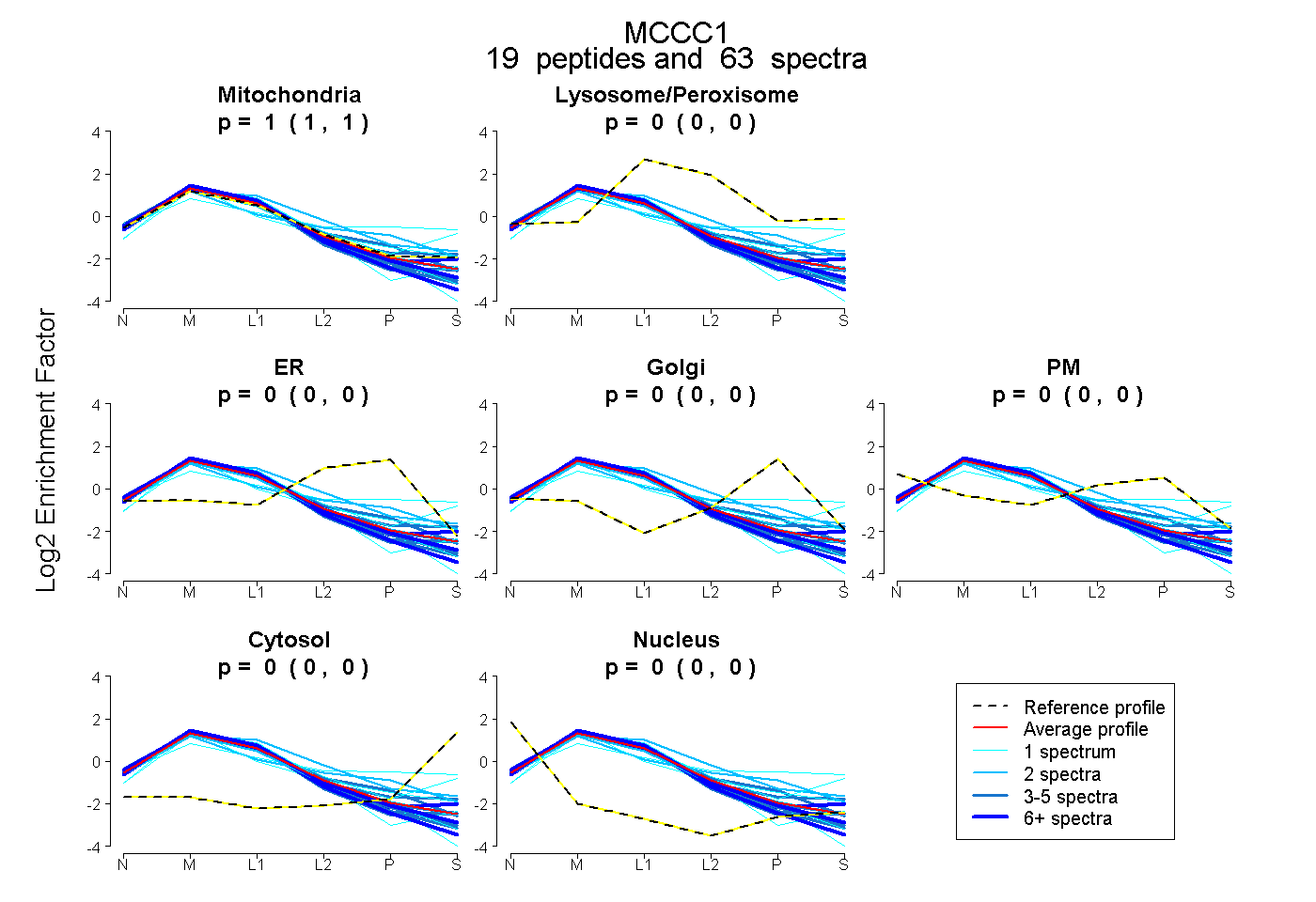 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
400 spectra |
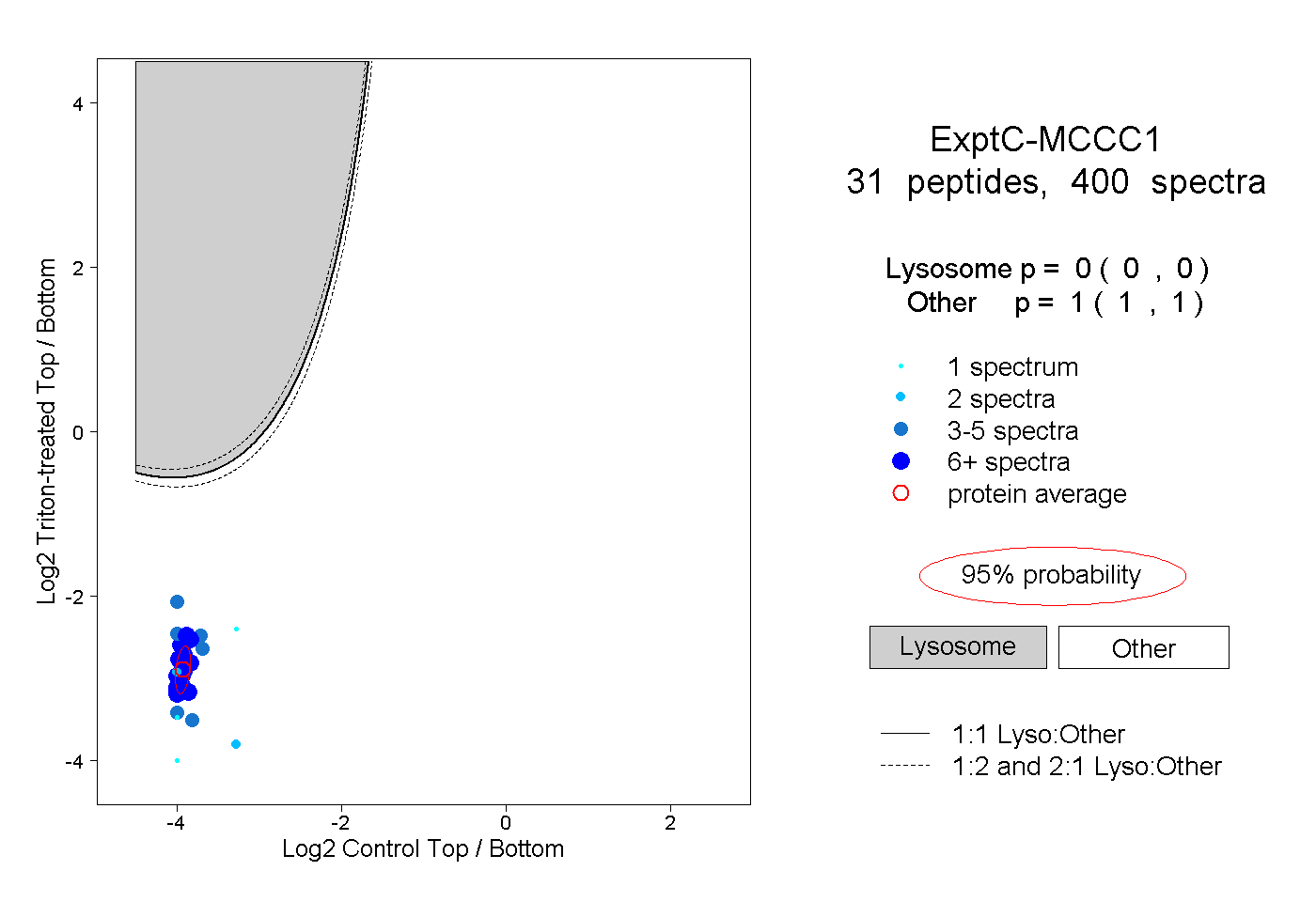 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
52 spectra |
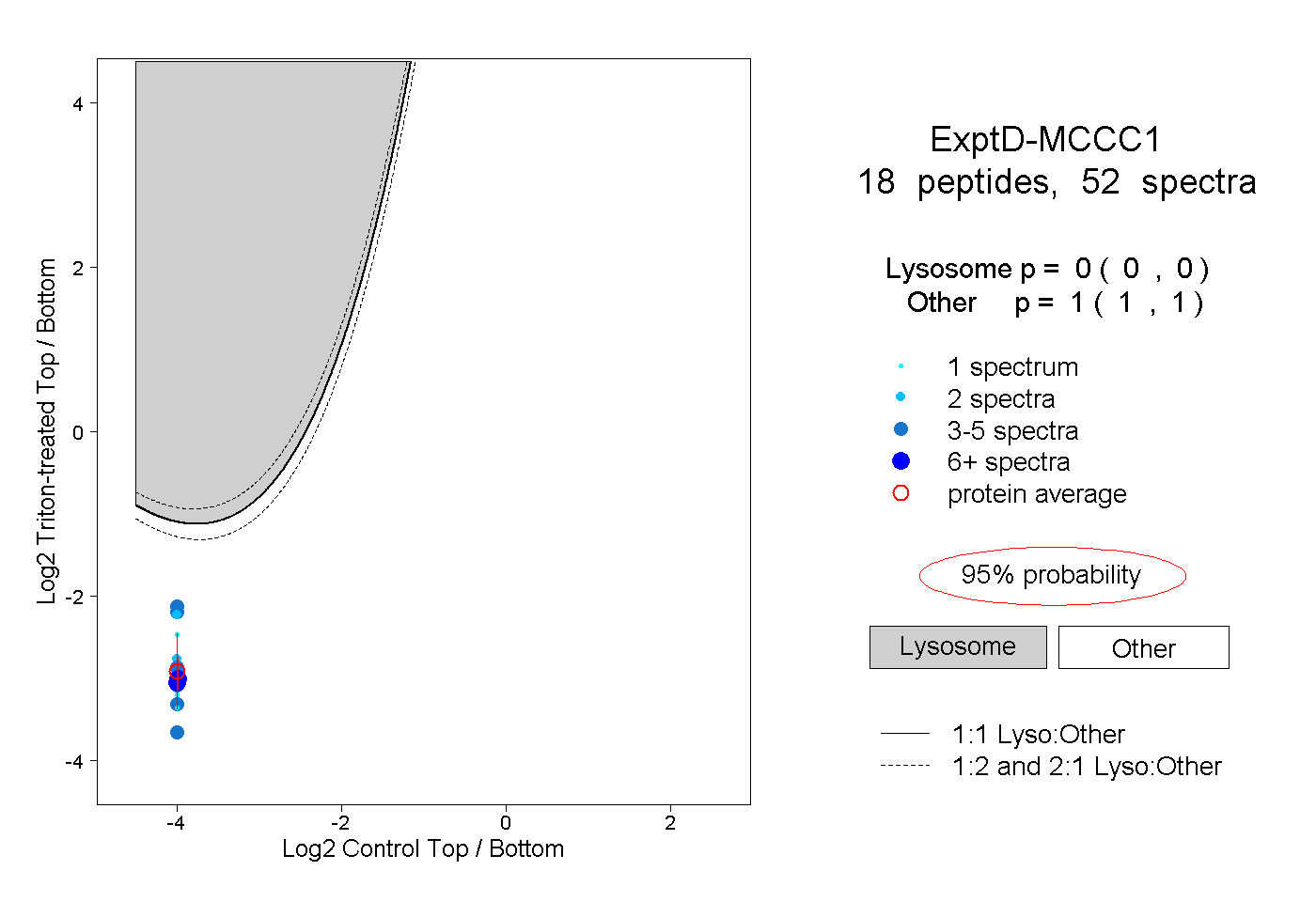 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |