peptides
spectra
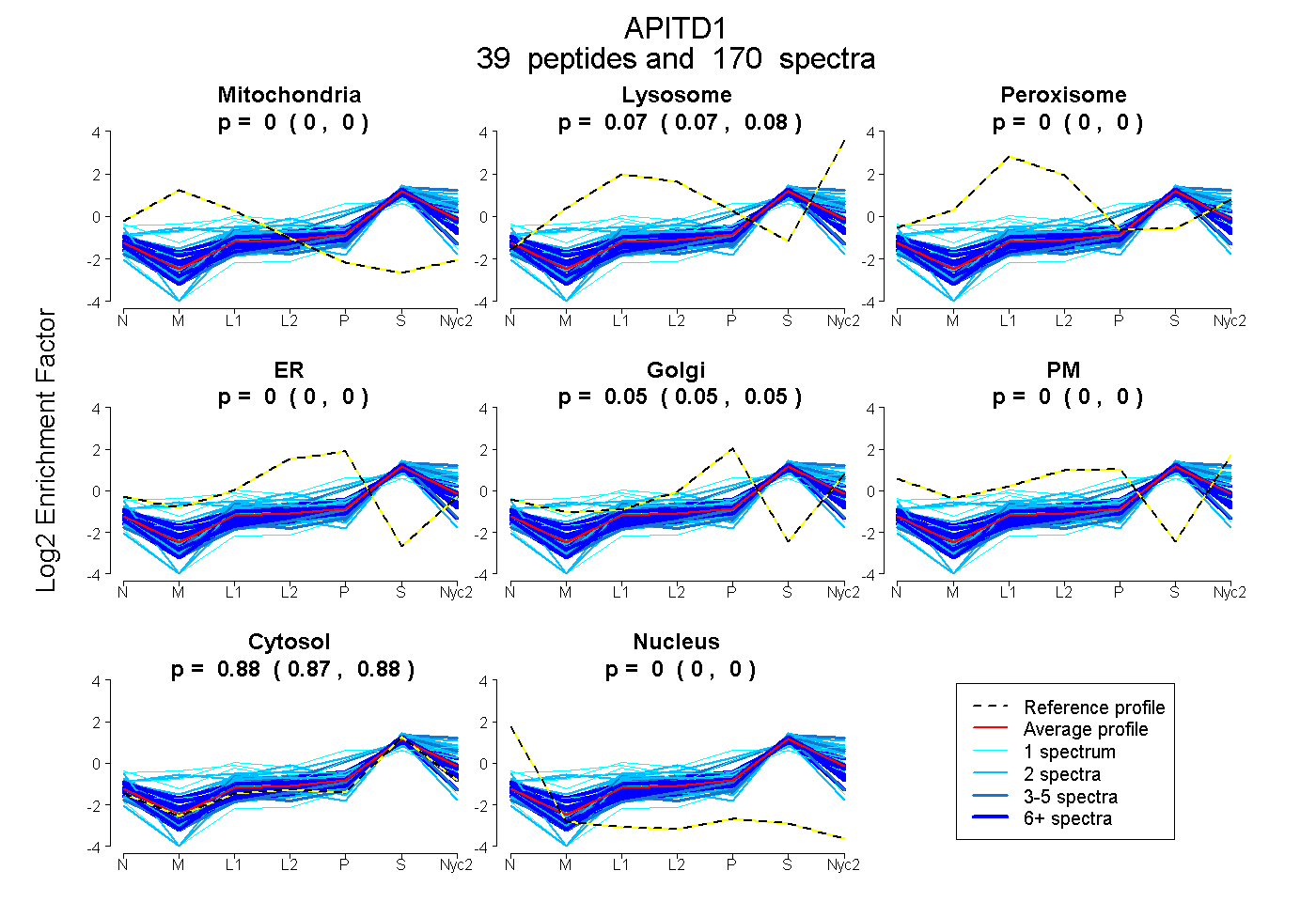
0.000 | 0.000
0.072 | 0.077
0.000 | 0.000
0.000 | 0.000
0.048 | 0.052
0.000 | 0.000
0.874 | 0.877
0.000 | 0.000
peptides
spectra
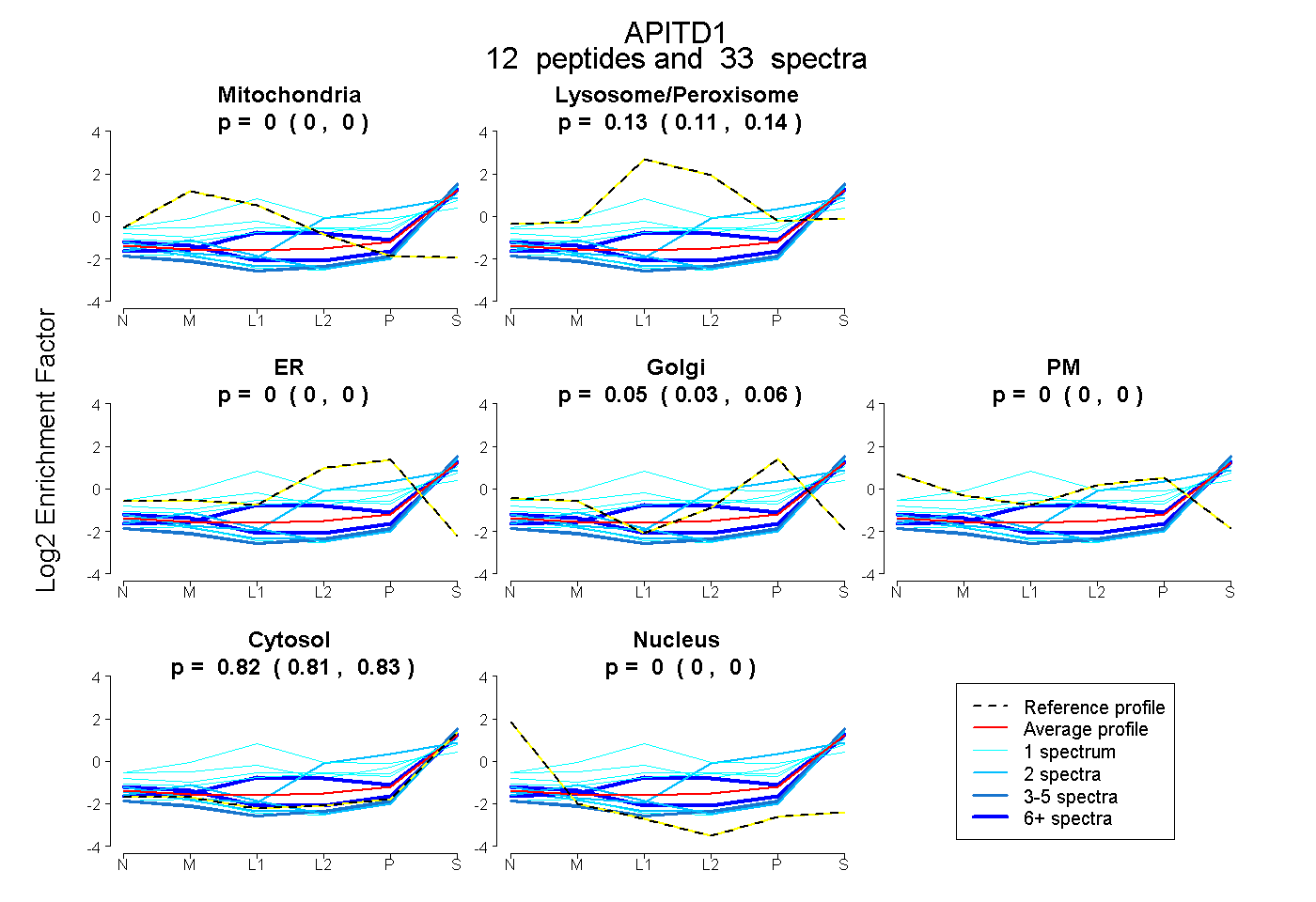
0.000 | 0.000
0.111 | 0.141
0.000 | 0.000
0.033 | 0.063
0.000 | 0.000
0.809 | 0.835
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
170 spectra |
 |
0.000 0.000 | 0.000 |
0.075 0.072 | 0.077 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.050 0.048 | 0.052 |
0.000 0.000 | 0.000 |
0.875 0.874 | 0.877 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.000 0.000 | 0.000 |
0.128 0.111 | 0.141 |
0.000 0.000 | 0.000 |
0.050 0.033 | 0.063 |
0.000 0.000 | 0.000 |
0.823 0.809 | 0.835 |
0.000 0.000 | 0.000 |
| 2 spectra, SAVDDCQDSWR | 0.068 | 0.000 | 0.000 | 0.000 | 0.000 | 0.932 | 0.000 | |||
| 2 spectra, EAWPHIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.957 | 0.043 | |||
| 7 spectra, HFLLLR | 0.000 | 0.280 | 0.000 | 0.000 | 0.000 | 0.720 | 0.000 | |||
| 4 spectra, QAFLEDVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VAHPVQLR | 0.064 | 0.547 | 0.000 | 0.130 | 0.000 | 0.259 | 0.000 | |||
| 2 spectra, TIFQAIAAK | 0.000 | 0.013 | 0.406 | 0.000 | 0.000 | 0.580 | 0.000 | |||
| 1 spectrum, GILFVGSGVSGGEEGAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 6 spectra, AGQAVDDFIEK | 0.017 | 0.009 | 0.000 | 0.000 | 0.040 | 0.894 | 0.040 | |||
| 1 spectrum, HEMLPANLIQAQR | 0.000 | 0.363 | 0.000 | 0.141 | 0.037 | 0.459 | 0.000 | |||
| 5 spectra, NPELQNLLLDDFFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, VISALAEVSK | 0.000 | 0.357 | 0.000 | 0.086 | 0.000 | 0.557 | 0.000 | |||
| 1 spectrum, TVVAVEVQDLK | 0.000 | 0.320 | 0.000 | 0.053 | 0.000 | 0.627 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
143 spectra |
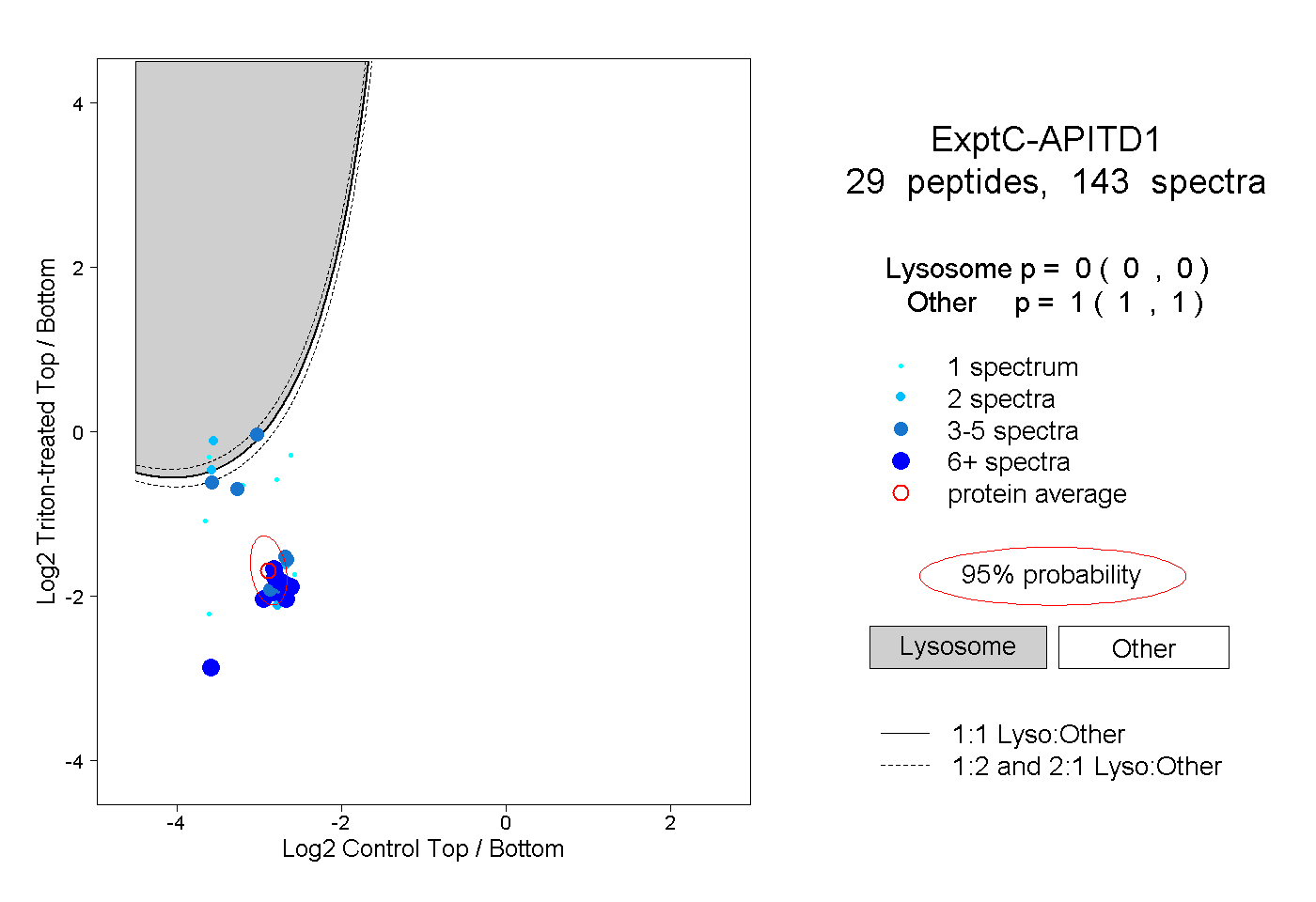 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
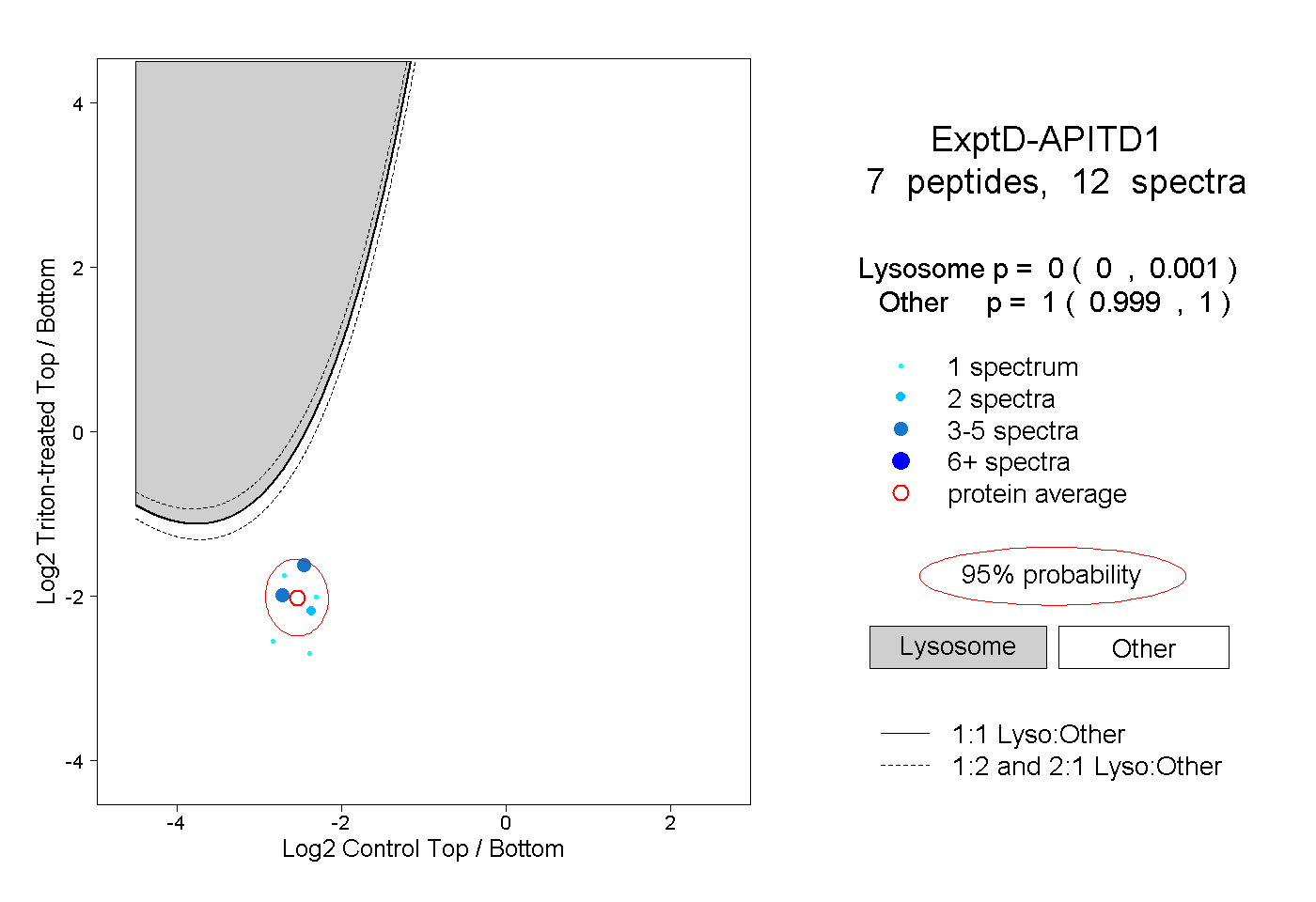 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |