peptides
spectra
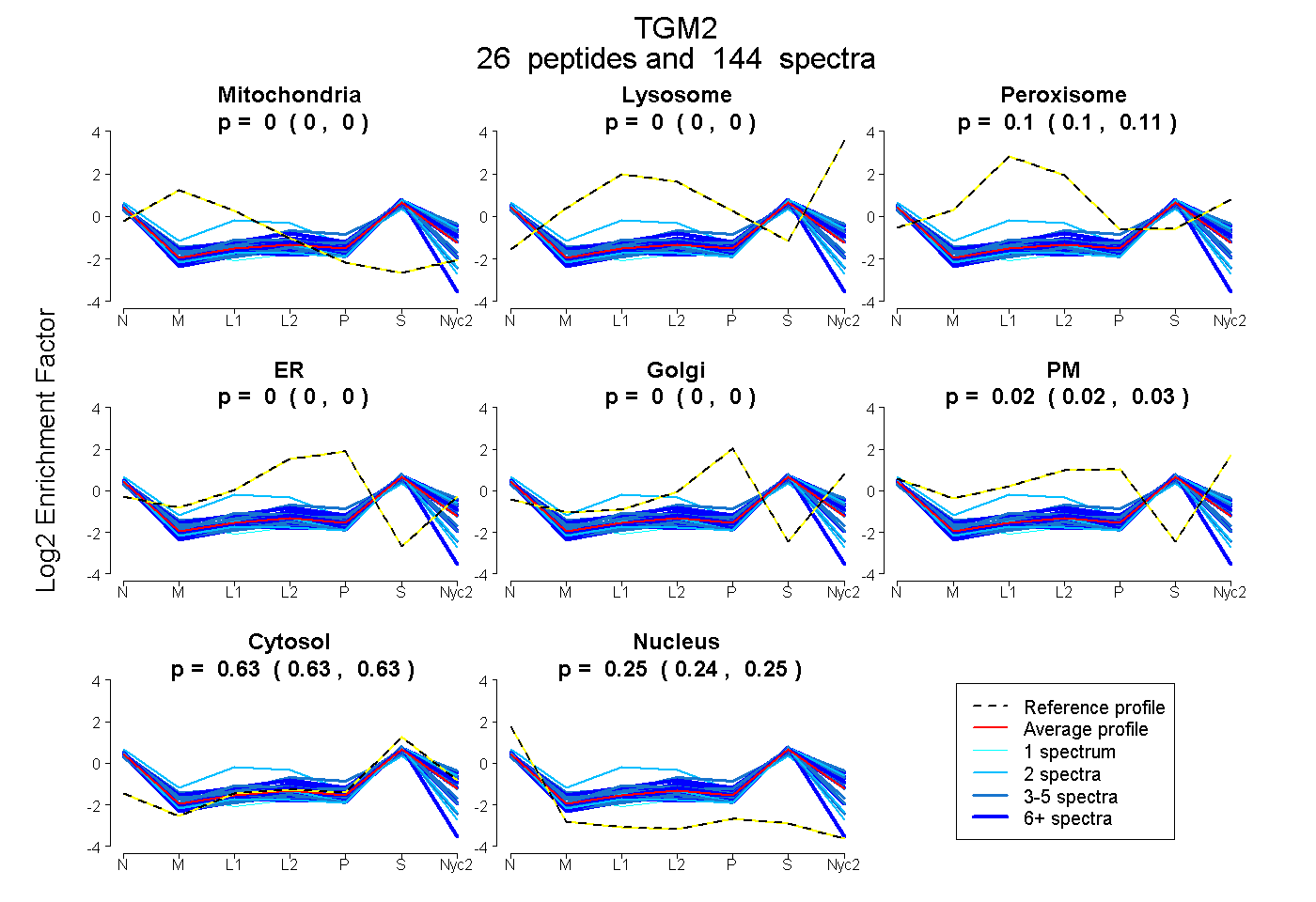
0.000 | 0.000
0.000 | 0.000
0.100 | 0.108
0.000 | 0.000
0.000 | 0.000
0.019 | 0.027
0.625 | 0.629
0.242 | 0.247
peptides
spectra
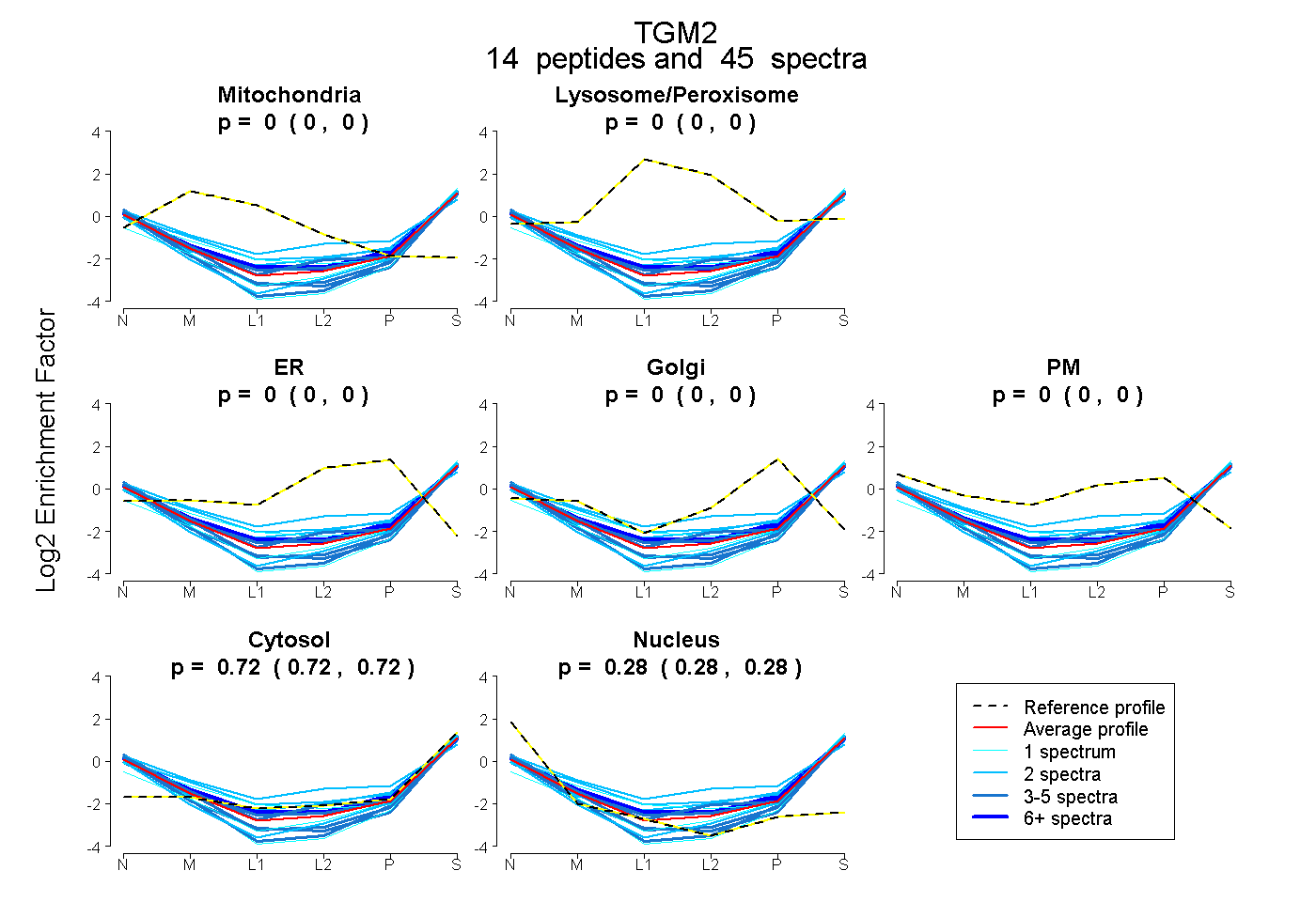
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.718 | 0.724
0.276 | 0.282
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
144 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.105 0.100 | 0.108 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.023 0.019 | 0.027 |
0.627 0.625 | 0.629 |
0.245 0.242 | 0.247 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.721 0.718 | 0.724 |
0.279 0.276 | 0.282 |
| 3 spectra, YSGCLTESNLIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.041 | 0.701 | 0.258 | |||
| 6 spectra, GYEASVDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.044 | 0.703 | 0.253 | |||
| 4 spectra, LLLCAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.644 | 0.356 | |||
| 2 spectra, SVEVSDPVPAGDAVK | 0.000 | 0.066 | 0.000 | 0.000 | 0.259 | 0.567 | 0.108 | |||
| 4 spectra, SSPIYVGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.649 | 0.351 | |||
| 1 spectrum, VGDGMSLGNDFDVFAHIGNDTSESR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.797 | 0.203 | |||
| 10 spectra, LTLYFEGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.043 | 0.704 | 0.252 | |||
| 2 spectra, EYVLTQQGFIYQGSVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.108 | 0.709 | 0.184 | |||
| 3 spectra, CLGIPTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.671 | 0.329 | |||
| 2 spectra, LTFGAVTGPDPSEEAGTK | 0.000 | 0.044 | 0.000 | 0.000 | 0.121 | 0.662 | 0.173 | |||
| 2 spectra, YPEGSPEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.712 | 0.288 | |||
| 4 spectra, VDLFPTDIGLHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.751 | 0.249 | |||
| 1 spectrum, DLYLENPEIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.635 | 0.365 | |||
| 1 spectrum, VVTNYNSAHDQNSNLLIEYFR | 0.000 | 0.061 | 0.000 | 0.000 | 0.000 | 0.714 | 0.225 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
123 spectra |
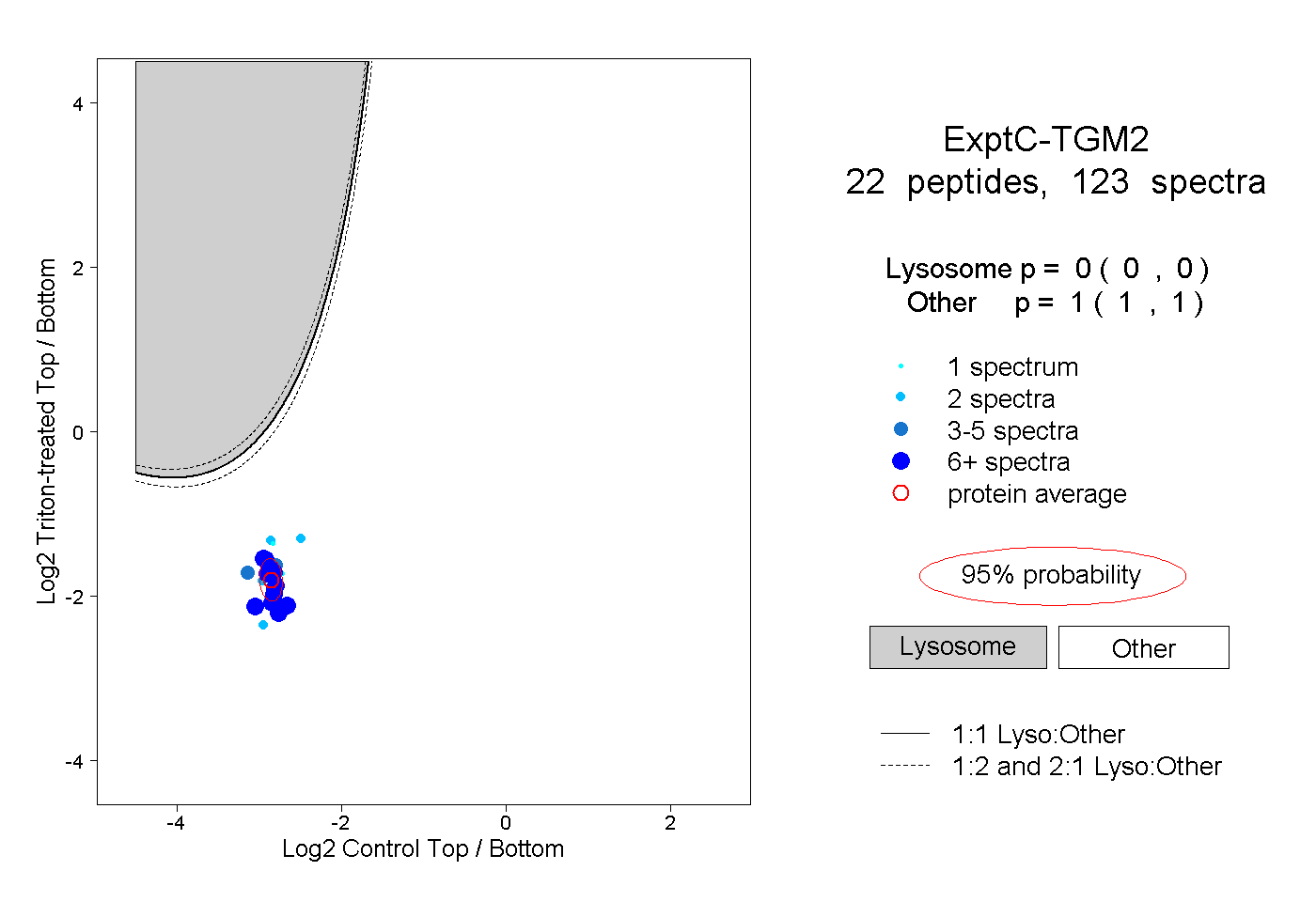 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
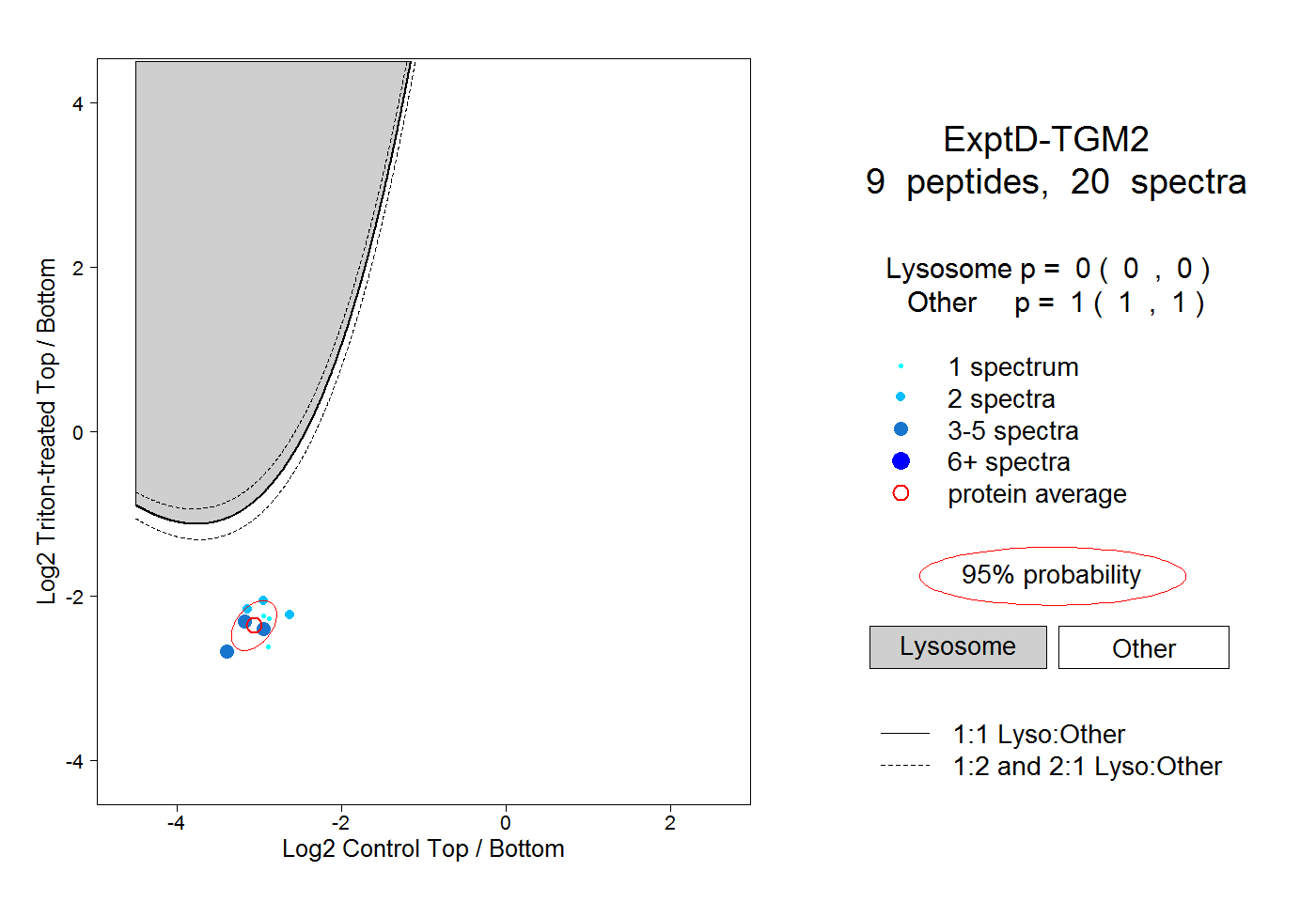 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |