peptides
spectra
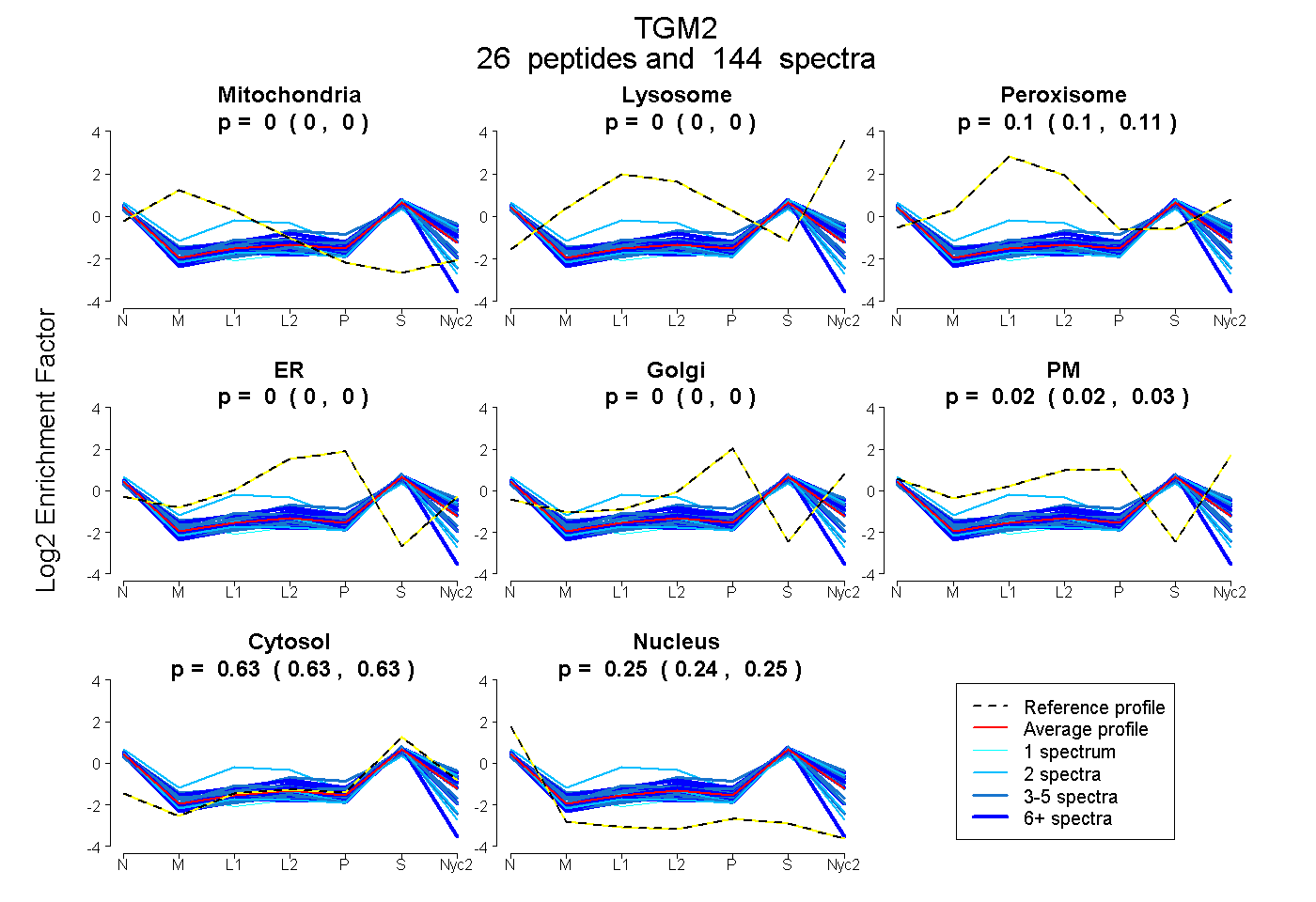
0.000 | 0.000
0.000 | 0.000
0.100 | 0.108
0.000 | 0.000
0.000 | 0.000
0.019 | 0.027
0.625 | 0.629
0.242 | 0.247
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
144 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.105 0.100 | 0.108 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.023 0.019 | 0.027 |
0.627 0.625 | 0.629 |
0.245 0.242 | 0.247 |
| 2 spectra, YSGCLTESNLIK | 0.000 | 0.000 | 0.028 | 0.000 | 0.000 | 0.000 | 0.629 | 0.343 | ||
| 16 spectra, GYEASVDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.168 | 0.673 | 0.159 | ||
| 5 spectra, LVVNFQCDK | 0.000 | 0.000 | 0.048 | 0.000 | 0.000 | 0.000 | 0.600 | 0.352 | ||
| 19 spectra, LLLCAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.595 | 0.405 | ||
| 3 spectra, SVEVSDPVPAGDAVK | 0.000 | 0.000 | 0.138 | 0.000 | 0.000 | 0.058 | 0.627 | 0.177 | ||
| 7 spectra, EHGCQQVK | 0.000 | 0.000 | 0.104 | 0.000 | 0.000 | 0.069 | 0.605 | 0.223 | ||
| 7 spectra, SSPIYVGR | 0.000 | 0.000 | 0.035 | 0.000 | 0.000 | 0.101 | 0.675 | 0.189 | ||
| 2 spectra, EGDLSTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | 0.708 | 0.204 | ||
| 6 spectra, NEYGELESNK | 0.000 | 0.000 | 0.149 | 0.000 | 0.000 | 0.099 | 0.564 | 0.187 | ||
| 5 spectra, EDITYTYK | 0.000 | 0.000 | 0.062 | 0.000 | 0.000 | 0.230 | 0.567 | 0.142 | ||
| 1 spectrum, ANHLNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.145 | 0.637 | 0.218 | ||
| 2 spectra, VGDGMSLGNDFDVFAHIGNDTSESR | 0.000 | 0.000 | 0.067 | 0.000 | 0.000 | 0.053 | 0.688 | 0.191 | ||
| 7 spectra, SEGTYCCGPVSVR | 0.000 | 0.000 | 0.034 | 0.000 | 0.000 | 0.000 | 0.667 | 0.299 | ||
| 7 spectra, LTLYFEGR | 0.000 | 0.000 | 0.032 | 0.000 | 0.000 | 0.073 | 0.678 | 0.217 | ||
| 2 spectra, DHHTADLCQQK | 0.000 | 0.000 | 0.387 | 0.000 | 0.000 | 0.000 | 0.336 | 0.277 | ||
| 3 spectra, ILGEPK | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.171 | 0.666 | 0.162 | ||
| 7 spectra, EETGVAMR | 0.000 | 0.000 | 0.042 | 0.000 | 0.000 | 0.152 | 0.672 | 0.134 | ||
| 3 spectra, EYVLTQQGFIYQGSVK | 0.000 | 0.000 | 0.122 | 0.000 | 0.000 | 0.000 | 0.641 | 0.237 | ||
| 14 spectra, YPEGSPEER | 0.000 | 0.000 | 0.055 | 0.000 | 0.000 | 0.088 | 0.646 | 0.211 | ||
| 2 spectra, CLGIPTR | 0.000 | 0.000 | 0.037 | 0.000 | 0.000 | 0.000 | 0.620 | 0.342 | ||
| 5 spectra, SINNSLVVGQK | 0.000 | 0.000 | 0.068 | 0.000 | 0.000 | 0.109 | 0.616 | 0.206 | ||
| 4 spectra, LVAEVSLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.110 | 0.692 | 0.198 | ||
| 3 spectra, VDLFPTDIGLHK | 0.000 | 0.000 | 0.136 | 0.000 | 0.000 | 0.000 | 0.613 | 0.251 | ||
| 4 spectra, QSDGSVLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.691 | 0.241 | ||
| 5 spectra, DLYLENPEIK | 0.000 | 0.000 | 0.152 | 0.000 | 0.000 | 0.051 | 0.572 | 0.226 | ||
| 3 spectra, VVSGMVNCNDDQGVLLGR | 0.000 | 0.000 | 0.043 | 0.000 | 0.000 | 0.000 | 0.662 | 0.295 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
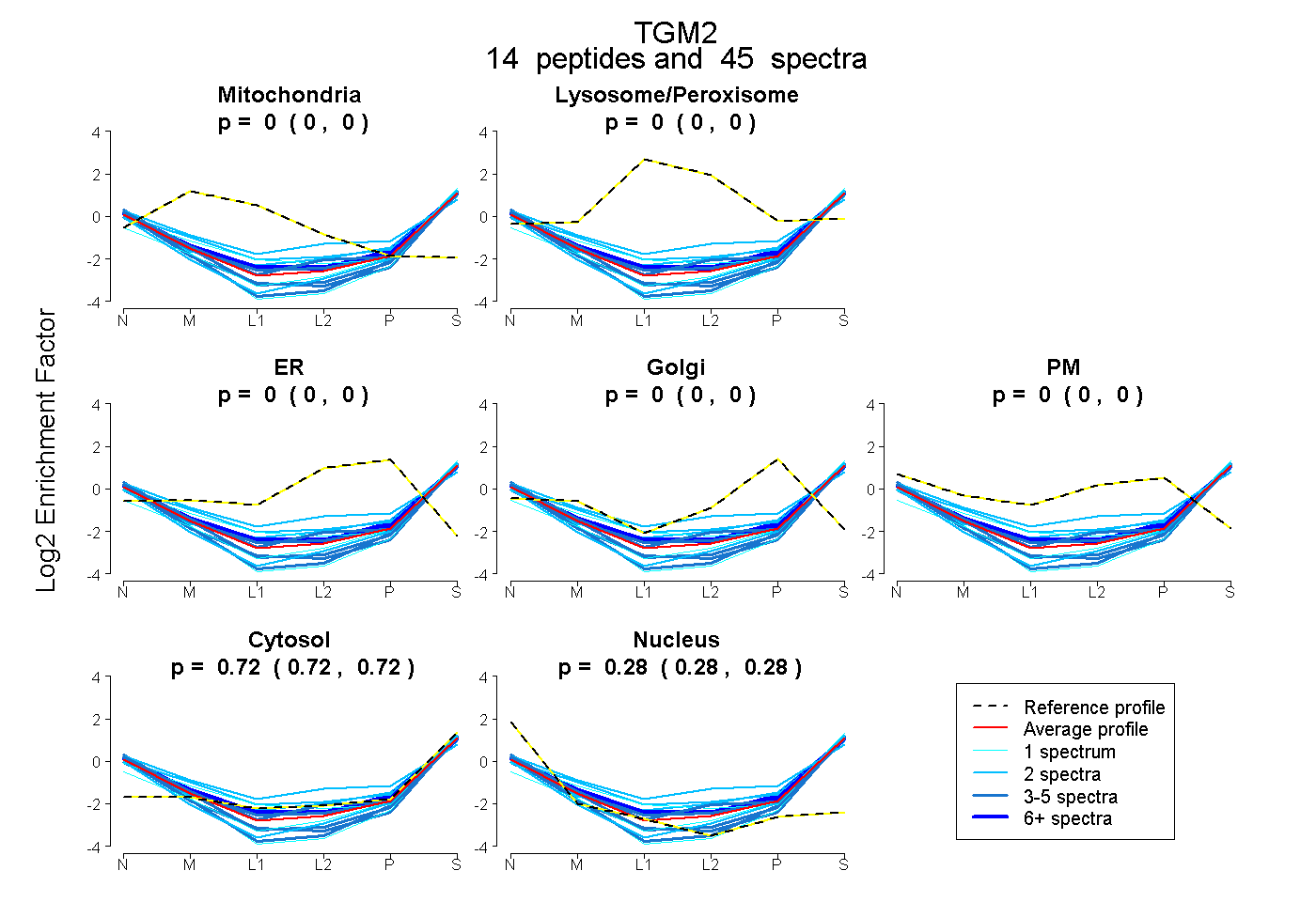 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.721 0.718 | 0.724 |
0.279 0.276 | 0.282 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
123 spectra |
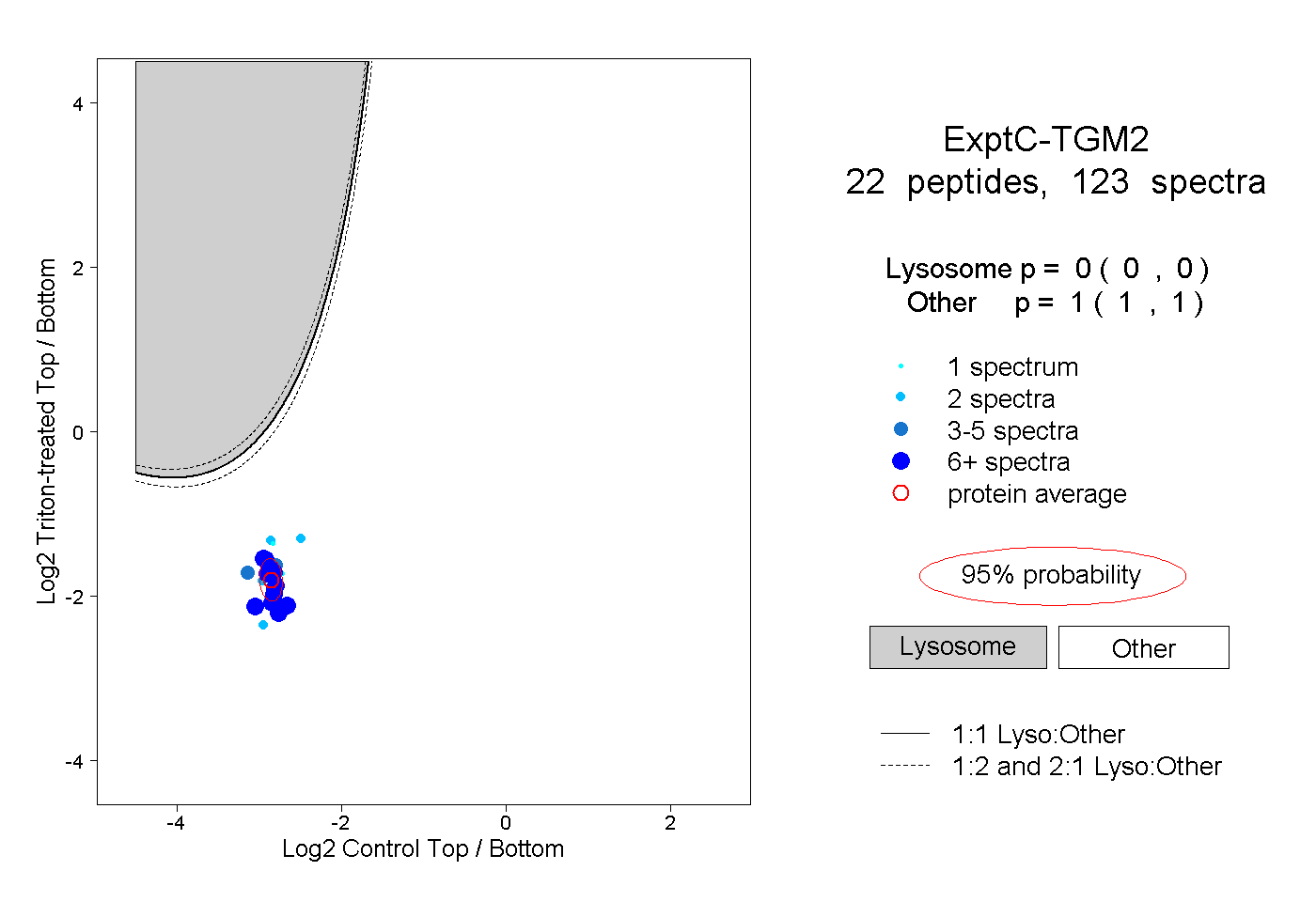 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
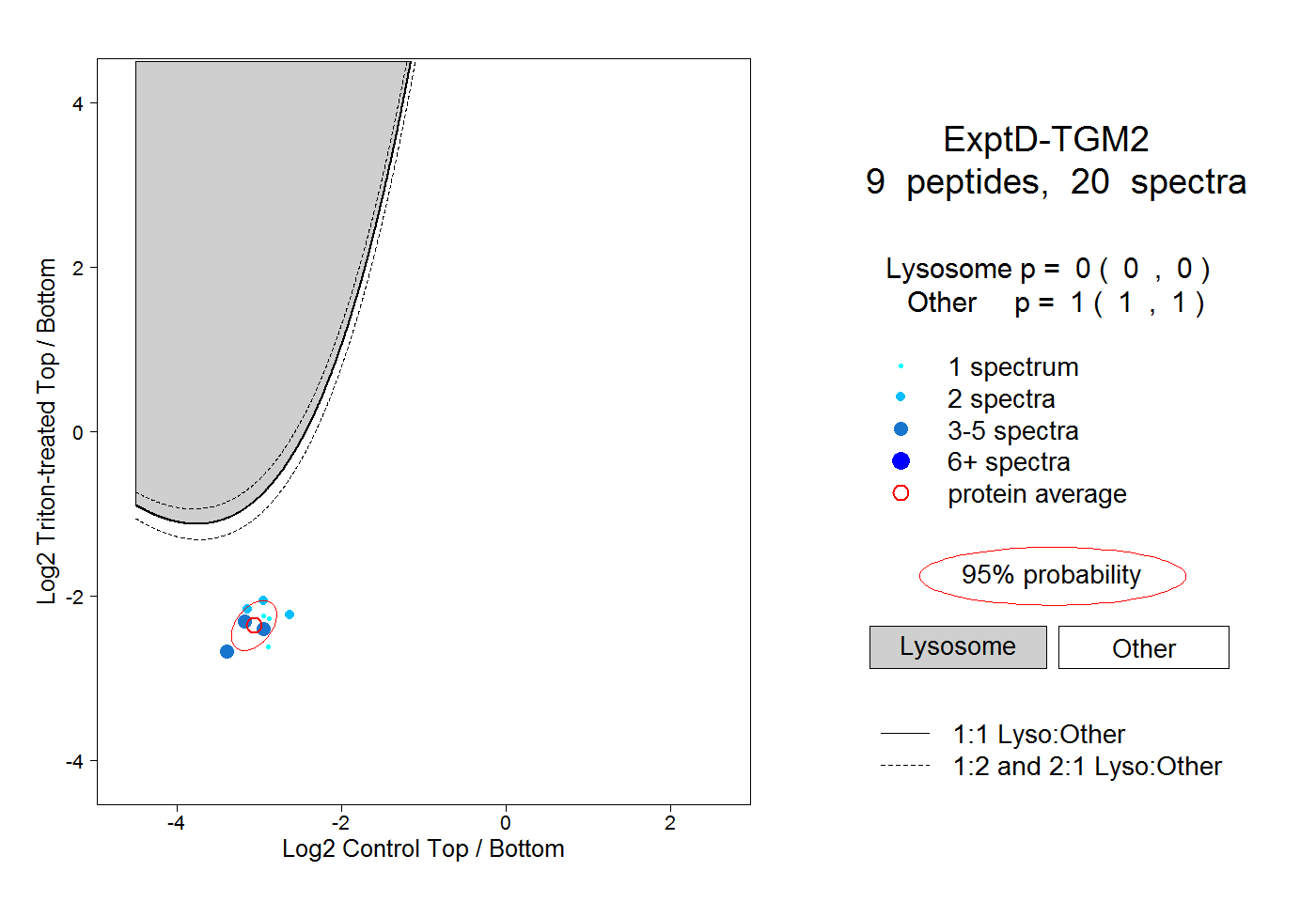 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |