peptides
spectra
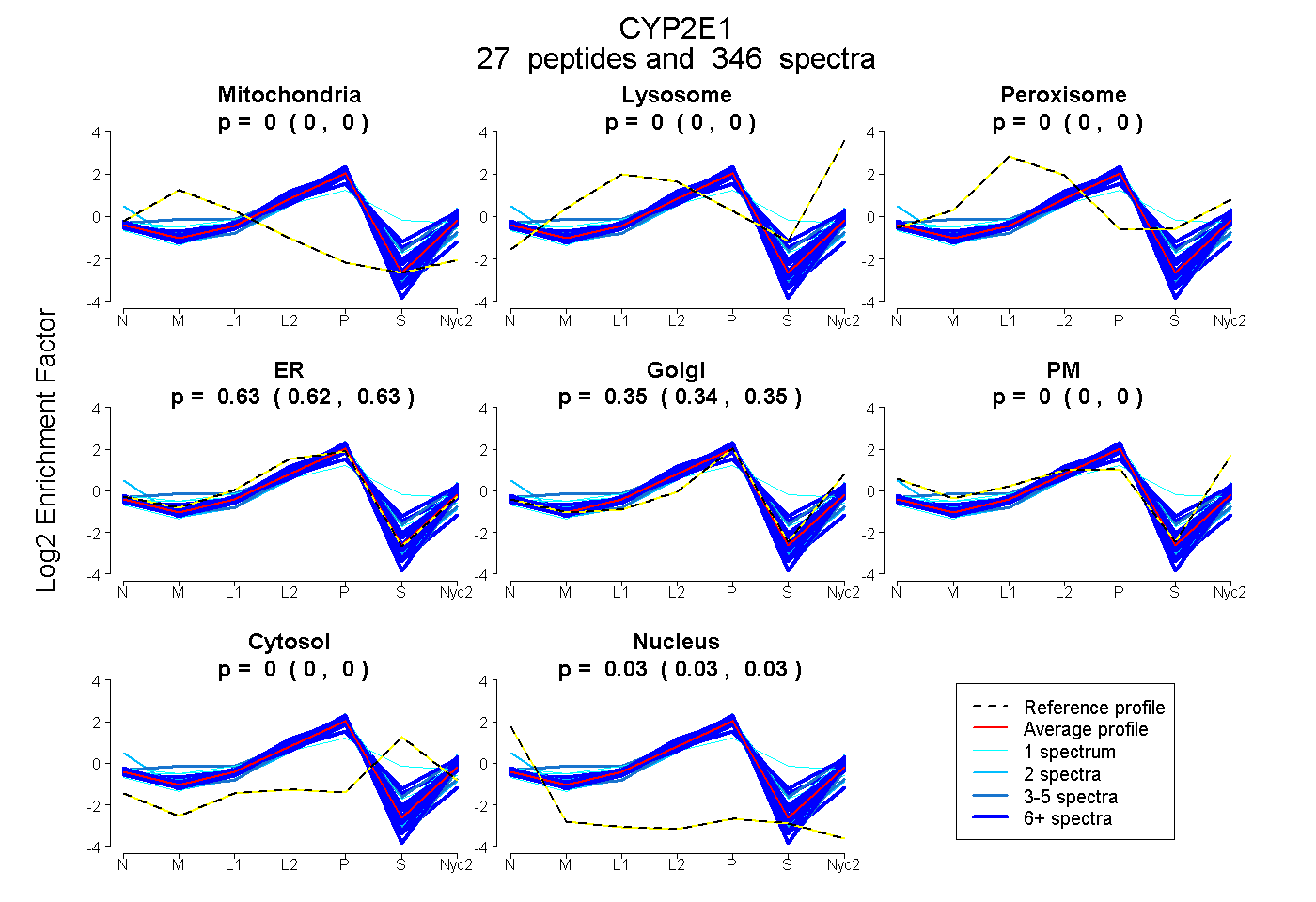
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.625 | 0.629
0.342 | 0.348
0.000 | 0.000
0.000 | 0.000
0.027 | 0.028
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
346 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.627 0.625 | 0.629 |
0.345 0.342 | 0.348 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.027 | 0.028 |
| 5 spectra, NEFSGR | 0.000 | 0.000 | 0.000 | 0.608 | 0.351 | 0.000 | 0.000 | 0.041 | ||
| 25 spectra, LCVIPR | 0.000 | 0.000 | 0.000 | 0.847 | 0.043 | 0.000 | 0.000 | 0.110 | ||
| 4 spectra, FINLVPSNLPHEATR | 0.028 | 0.000 | 0.192 | 0.320 | 0.430 | 0.000 | 0.029 | 0.000 | ||
| 18 spectra, YGLLILMK | 0.000 | 0.000 | 0.000 | 0.741 | 0.248 | 0.000 | 0.010 | 0.000 | ||
| 2 spectra, FDYNDK | 0.000 | 0.000 | 0.000 | 0.538 | 0.462 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, EHLQSLDINCAR | 0.000 | 0.000 | 0.000 | 0.839 | 0.094 | 0.000 | 0.000 | 0.067 | ||
| 12 spectra, AFSAGK | 0.000 | 0.000 | 0.000 | 0.677 | 0.323 | 0.000 | 0.000 | 0.000 | ||
| 18 spectra, DVTDCLLIEMEK | 0.000 | 0.000 | 0.000 | 0.614 | 0.305 | 0.000 | 0.067 | 0.013 | ||
| 40 spectra, VIGPSR | 0.000 | 0.000 | 0.000 | 0.648 | 0.339 | 0.000 | 0.000 | 0.013 | ||
| 1 spectrum, GIIFNNGPTWK | 0.000 | 0.000 | 0.165 | 0.380 | 0.149 | 0.000 | 0.305 | 0.000 | ||
| 11 spectra, YSDYFK | 0.000 | 0.000 | 0.000 | 0.625 | 0.306 | 0.000 | 0.049 | 0.020 | ||
| 8 spectra, VCVGEGLAR | 0.000 | 0.000 | 0.000 | 0.563 | 0.352 | 0.000 | 0.085 | 0.000 | ||
| 2 spectra, EAQFLVEELK | 0.000 | 0.000 | 0.000 | 0.697 | 0.144 | 0.000 | 0.000 | 0.159 | ||
| 13 spectra, GDIPVFQEYK | 0.000 | 0.000 | 0.000 | 0.698 | 0.288 | 0.000 | 0.000 | 0.015 | ||
| 7 spectra, LDMPYMDAVVHEIQR | 0.000 | 0.000 | 0.120 | 0.343 | 0.384 | 0.000 | 0.153 | 0.000 | ||
| 1 spectrum, GTVVIPTLDSLLYDSHEFPDPEK | 0.000 | 0.000 | 0.000 | 0.663 | 0.191 | 0.000 | 0.146 | 0.000 | ||
| 28 spectra, IVVLHGYK | 0.000 | 0.000 | 0.000 | 0.569 | 0.423 | 0.000 | 0.000 | 0.009 | ||
| 17 spectra, YLPGSHR | 0.000 | 0.000 | 0.000 | 0.560 | 0.327 | 0.000 | 0.113 | 0.000 | ||
| 8 spectra, QYTLEK | 0.000 | 0.000 | 0.000 | 0.611 | 0.363 | 0.000 | 0.000 | 0.026 | ||
| 16 spectra, YPEIEEK | 0.000 | 0.000 | 0.000 | 0.653 | 0.249 | 0.000 | 0.098 | 0.000 | ||
| 19 spectra, EVLLNHK | 0.000 | 0.000 | 0.000 | 0.567 | 0.261 | 0.000 | 0.172 | 0.000 | ||
| 12 spectra, NVSEIK | 0.000 | 0.000 | 0.000 | 0.687 | 0.313 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, FKPEHFLNENGK | 0.028 | 0.000 | 0.102 | 0.358 | 0.513 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, DWGMGK | 0.000 | 0.000 | 0.000 | 0.601 | 0.399 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, FSLSILR | 0.000 | 0.000 | 0.000 | 0.564 | 0.436 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, DTVFQGYVIPK | 0.000 | 0.000 | 0.000 | 0.657 | 0.295 | 0.000 | 0.000 | 0.048 | ||
| 42 spectra, LHEEIDR | 0.000 | 0.000 | 0.000 | 0.678 | 0.308 | 0.000 | 0.000 | 0.014 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
137 spectra |
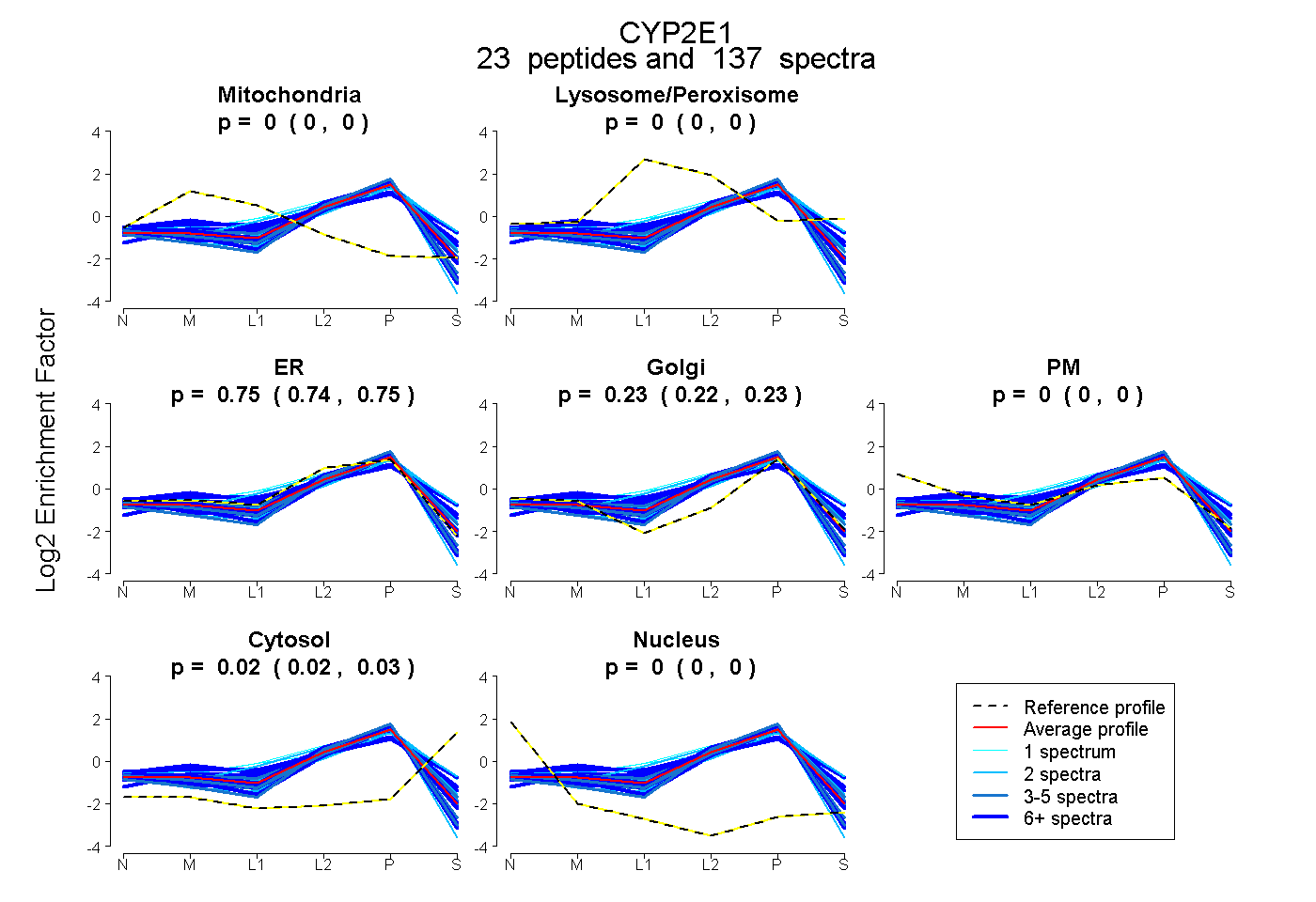 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.747 0.742 | 0.750 |
0.229 0.223 | 0.235 |
0.000 0.000 | 0.000 |
0.024 0.020 | 0.027 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
348 spectra |
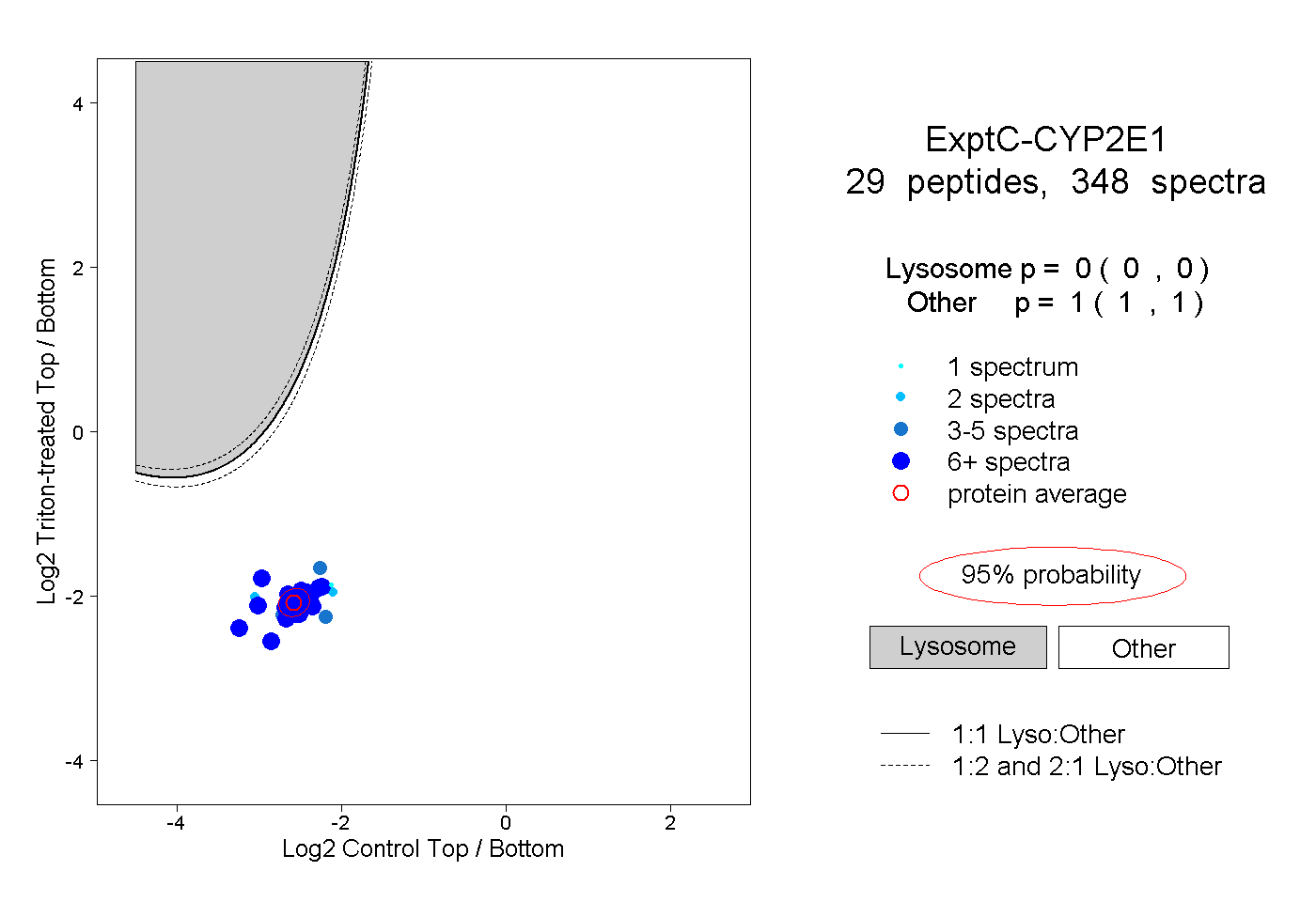 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
39 spectra |
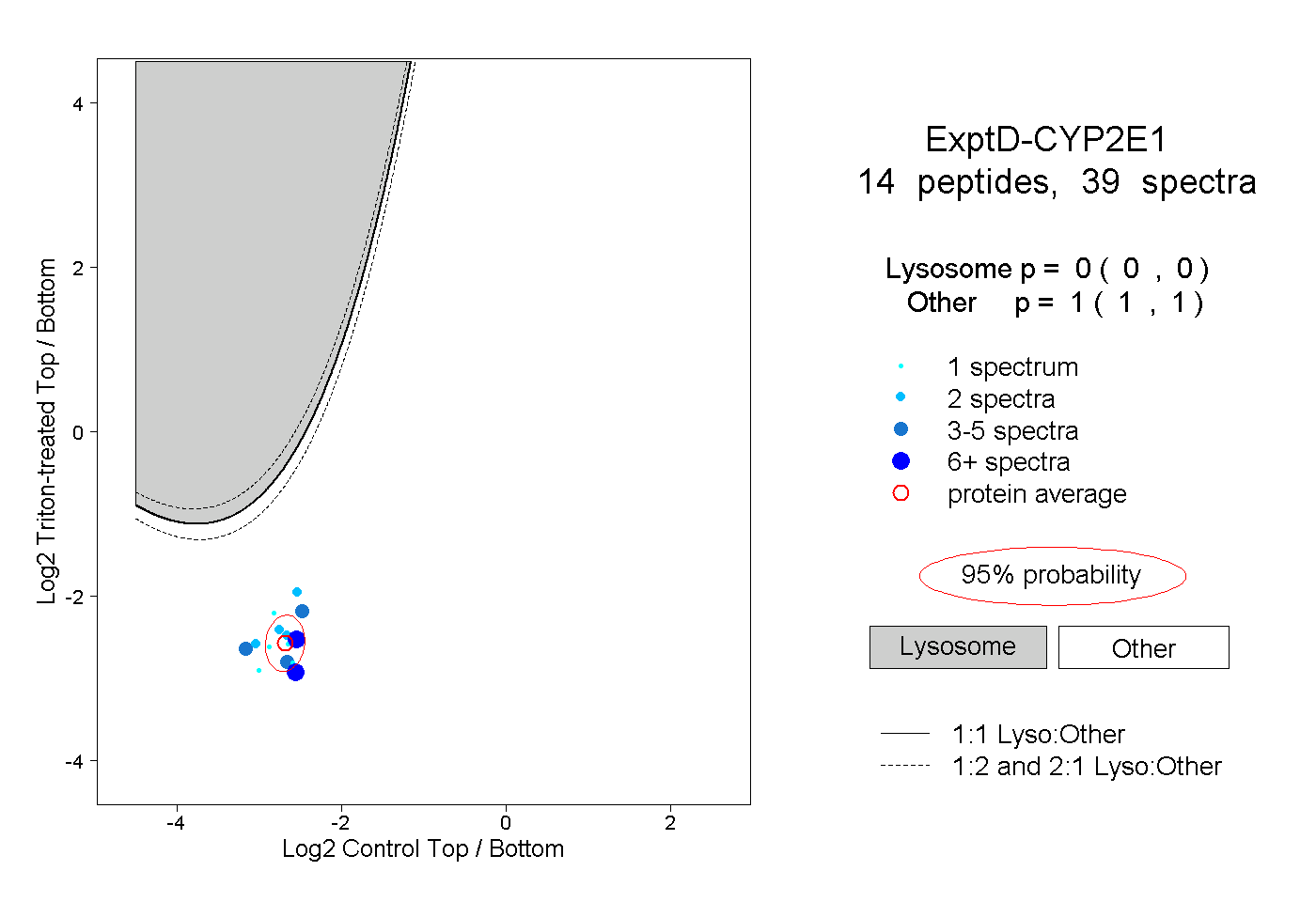 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |