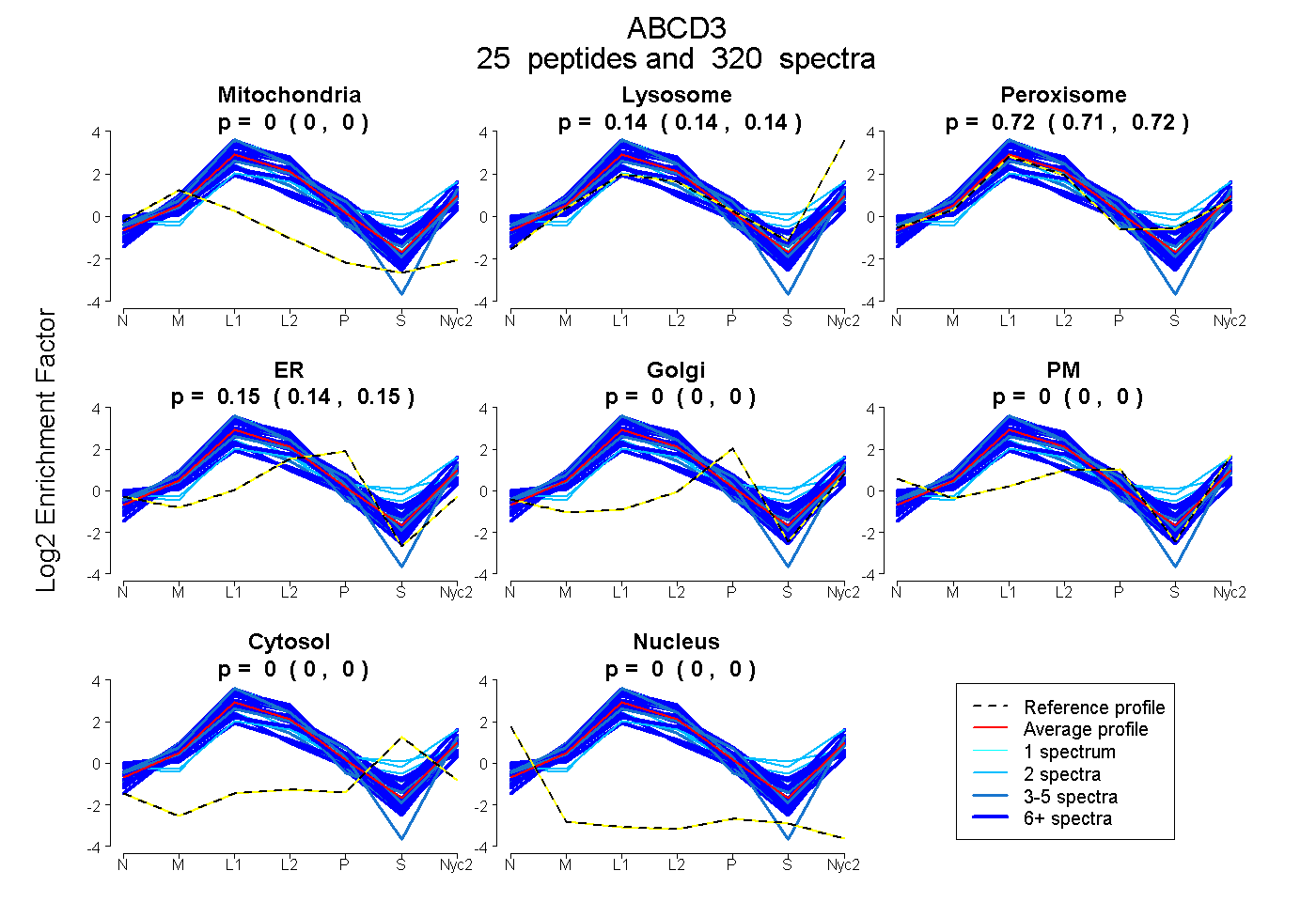
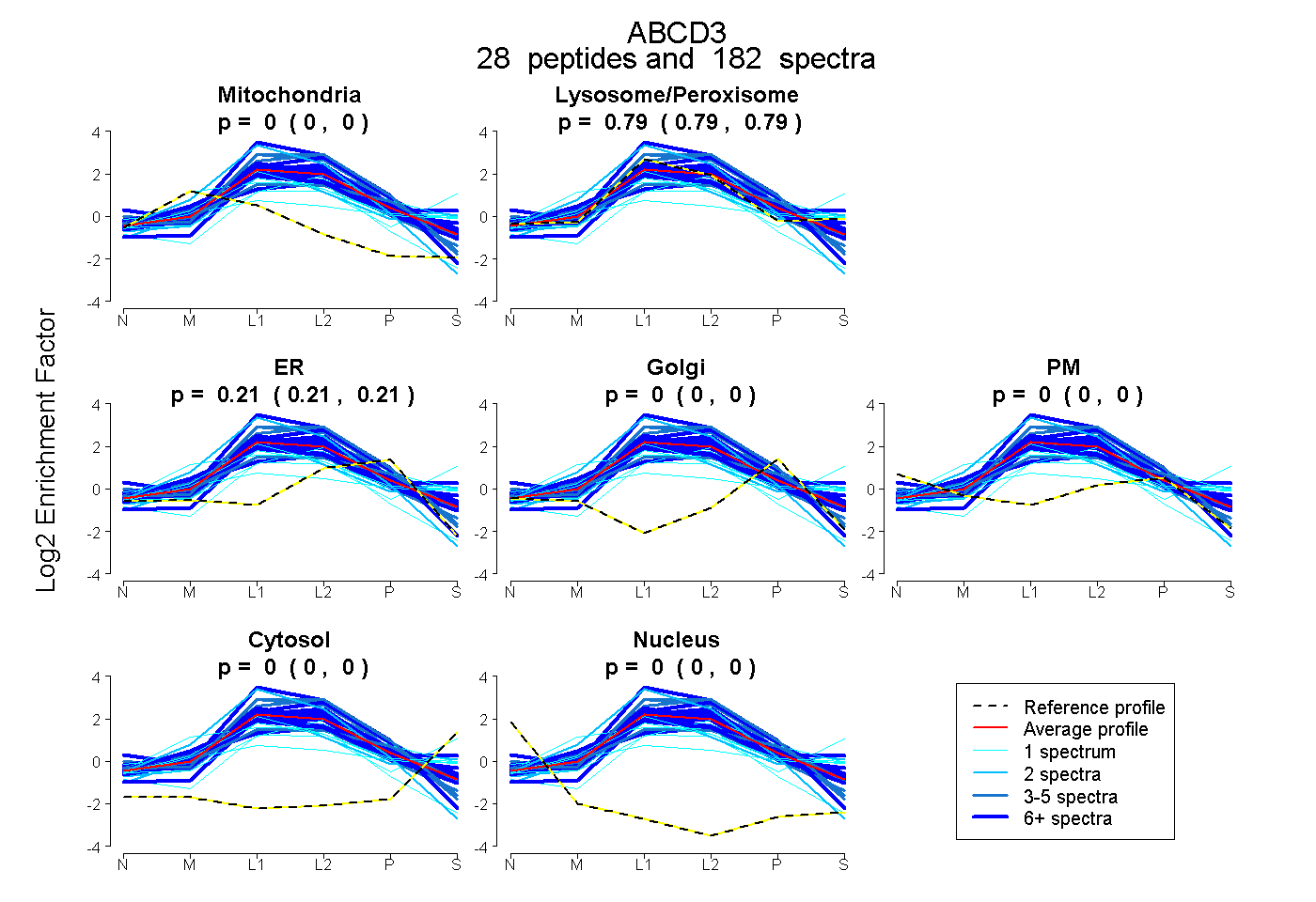
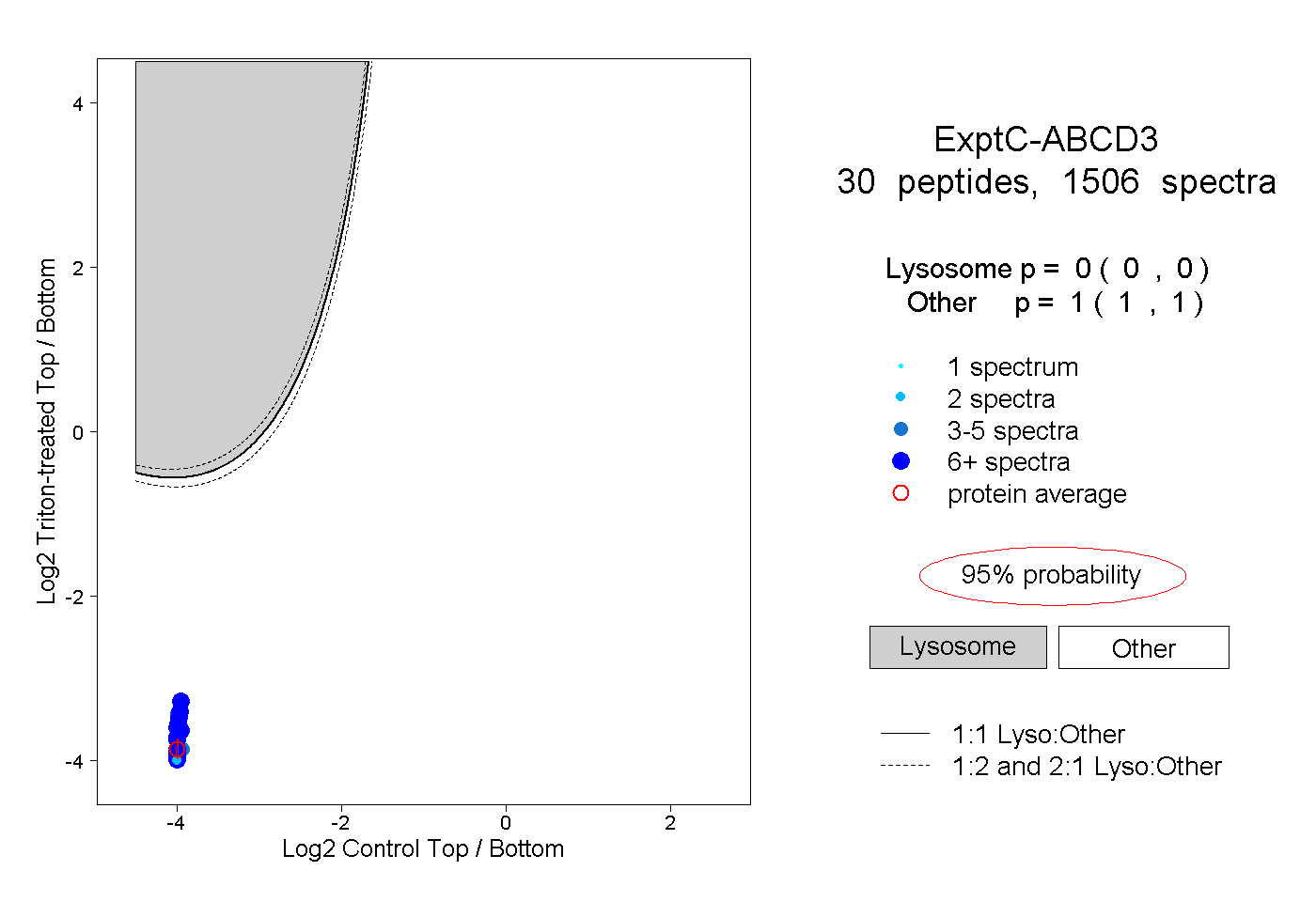
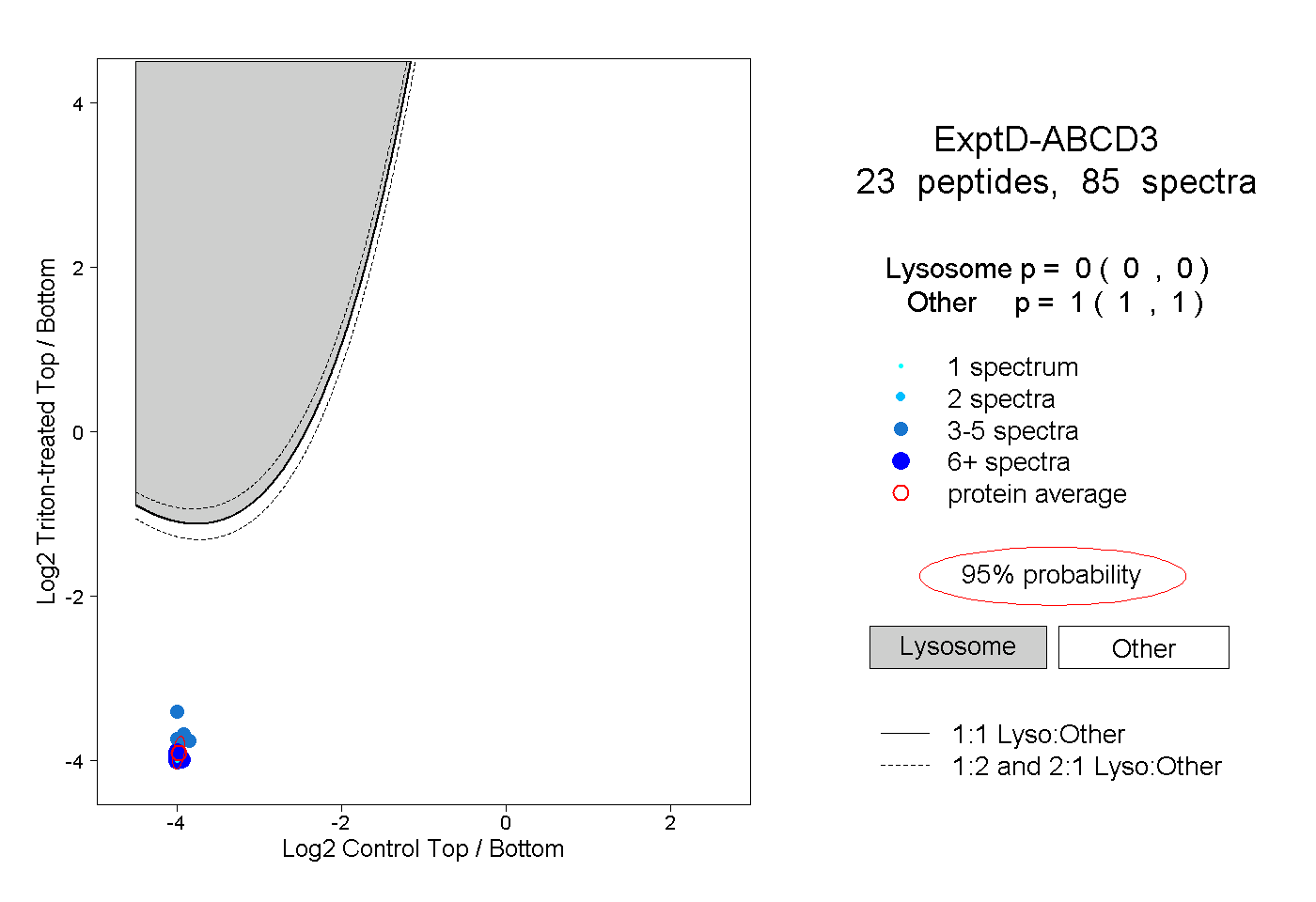
| 4 spectra, DQVIYPDGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TMVSQQDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GYLDNVQLGHILER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, YGLNELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, GISDQVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FDHVPLATPNGDILIQDLSFEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, MTIMEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DLNHGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, MSQALGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ISEIIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VLGELWPLFGGHLTKPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ISQLIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LAGFTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QTIHSVFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GNYEFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ITEDTVEFGS |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IANPDQLLTQDVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, YEGEYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SGANVLICGPNGCGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IVLAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EGGWDSVQDWMDVLSGGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ITELMQVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SGKPPLQNNEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |