peptides
spectra
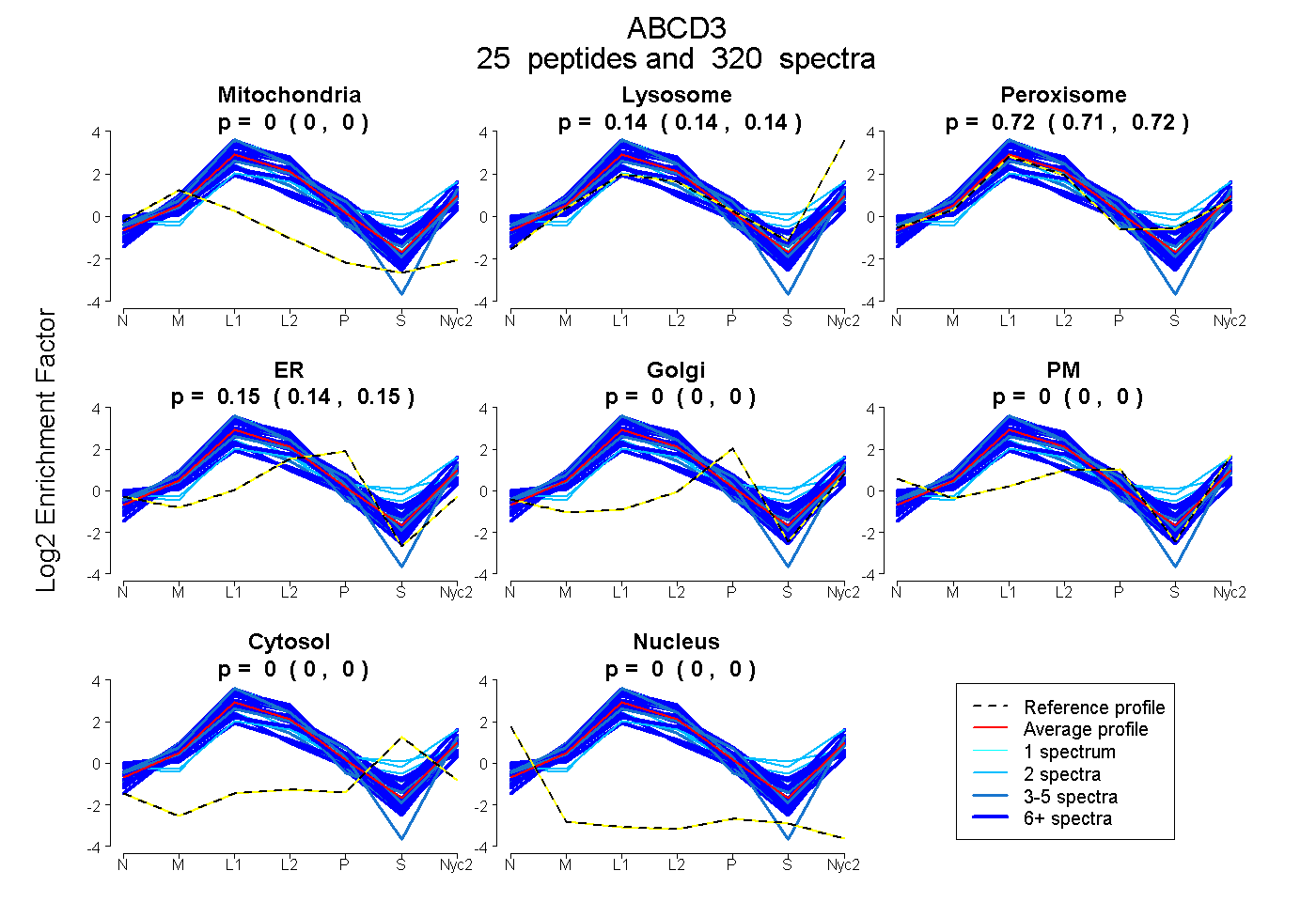
0.000 | 0.000
0.135 | 0.140
0.712 | 0.718
0.145 | 0.149
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
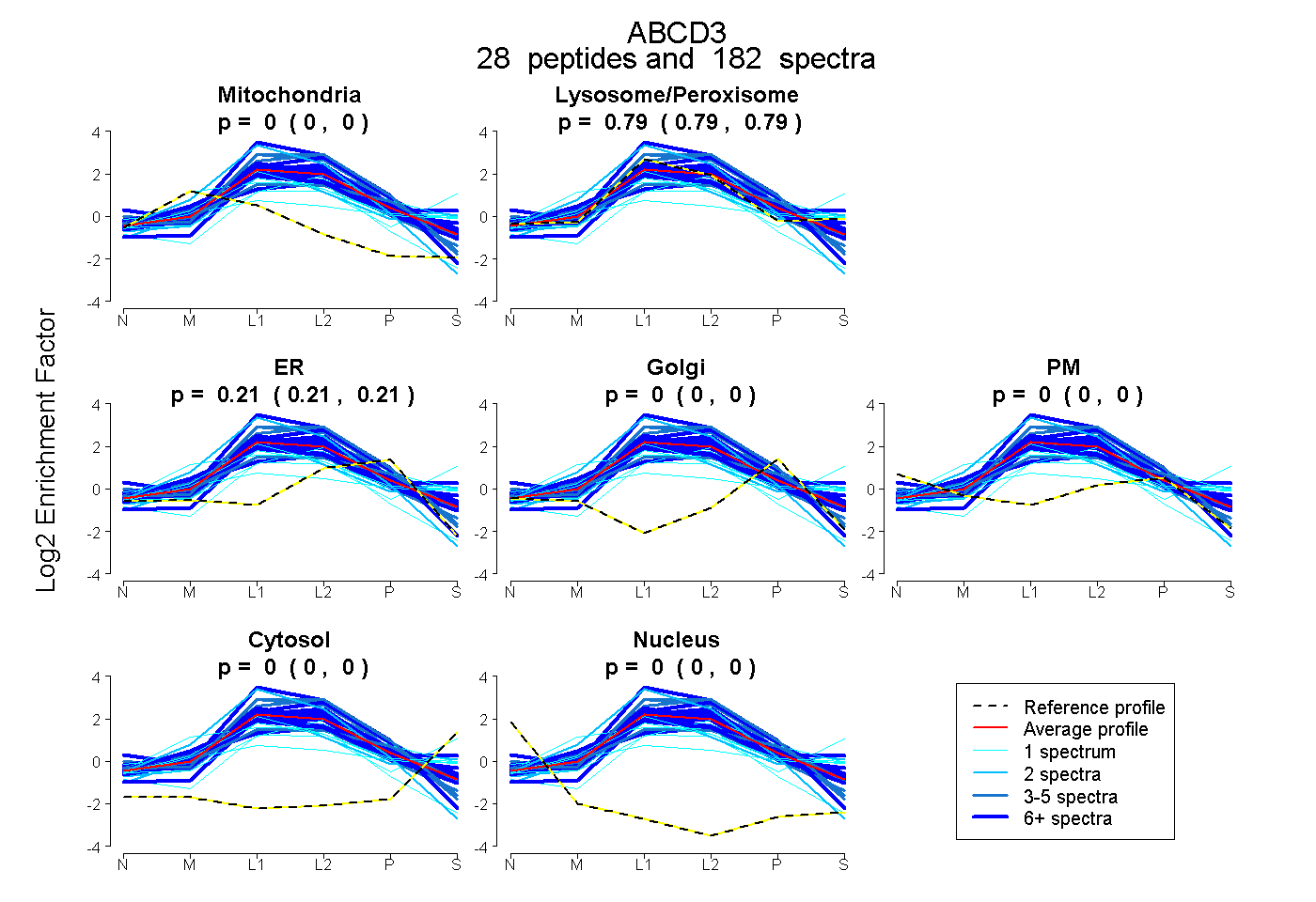
0.000 | 0.000
0.787 | 0.794
0.205 | 0.212
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
320 spectra |
 |
0.000 0.000 | 0.000 |
0.138 0.135 | 0.140 |
0.716 0.712 | 0.718 |
0.147 0.145 | 0.149 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
182 spectra |
 |
0.000 0.000 | 0.000 |
0.791 0.787 | 0.794 |
0.209 0.205 | 0.212 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, DQVIYPDGK | 0.000 | 0.787 | 0.159 | 0.000 | 0.000 | 0.054 | 0.000 | |||
| 1 spectrum, TMVSQQDK | 0.431 | 0.404 | 0.165 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 27 spectra, GYLDNVQLGHILER | 0.099 | 0.733 | 0.168 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, YGLNELK | 0.081 | 0.817 | 0.103 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, MGNLDNR | 0.000 | 0.824 | 0.024 | 0.000 | 0.151 | 0.000 | 0.000 | |||
| 9 spectra, GISDQVLK | 0.000 | 0.809 | 0.191 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FDHVPLATPNGDILIQDLSFEVR | 0.000 | 0.699 | 0.000 | 0.000 | 0.000 | 0.301 | 0.000 | |||
| 8 spectra, VGITLFTVSHR | 0.141 | 0.666 | 0.193 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MTIMEQK | 0.000 | 0.651 | 0.316 | 0.000 | 0.000 | 0.033 | 0.000 | |||
| 1 spectrum, LITNSEEIAFYNGNK | 0.059 | 0.522 | 0.000 | 0.105 | 0.177 | 0.137 | 0.000 | |||
| 3 spectra, DLNHGK | 0.000 | 0.817 | 0.183 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, YLYEEYLQAFTYYK | 0.025 | 0.805 | 0.000 | 0.128 | 0.000 | 0.042 | 0.000 | |||
| 11 spectra, MSQALGR | 0.000 | 0.804 | 0.196 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, FSMGFIDSIIAK | 0.000 | 0.880 | 0.120 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VLGELWPLFGGHLTKPER | 0.090 | 0.818 | 0.000 | 0.085 | 0.000 | 0.007 | 0.000 | |||
| 7 spectra, HHEYYLHMDGR | 0.054 | 0.568 | 0.310 | 0.000 | 0.068 | 0.000 | 0.000 | |||
| 18 spectra, LAGFTAR | 0.000 | 0.838 | 0.061 | 0.000 | 0.000 | 0.101 | 0.000 | |||
| 7 spectra, QTIHSVFR | 0.000 | 0.829 | 0.171 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, GNYEFK | 0.000 | 0.856 | 0.144 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ITEDTVEFGS | 0.024 | 0.859 | 0.000 | 0.000 | 0.000 | 0.116 | 0.000 | |||
| 3 spectra, IANPDQLLTQDVEK | 0.148 | 0.705 | 0.147 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YEGEYR | 0.000 | 0.831 | 0.169 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LSQLLK | 0.011 | 0.920 | 0.069 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, LFYVPQRPYMTLGTLR | 0.000 | 0.786 | 0.214 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, SGANVLICGPNGCGK | 0.003 | 0.604 | 0.390 | 0.004 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, IVLAGR | 0.000 | 0.869 | 0.131 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EGGWDSVQDWMDVLSGGEK | 0.000 | 0.726 | 0.274 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 18 spectra, ITELMQVLK | 0.000 | 0.763 | 0.237 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1506 spectra |
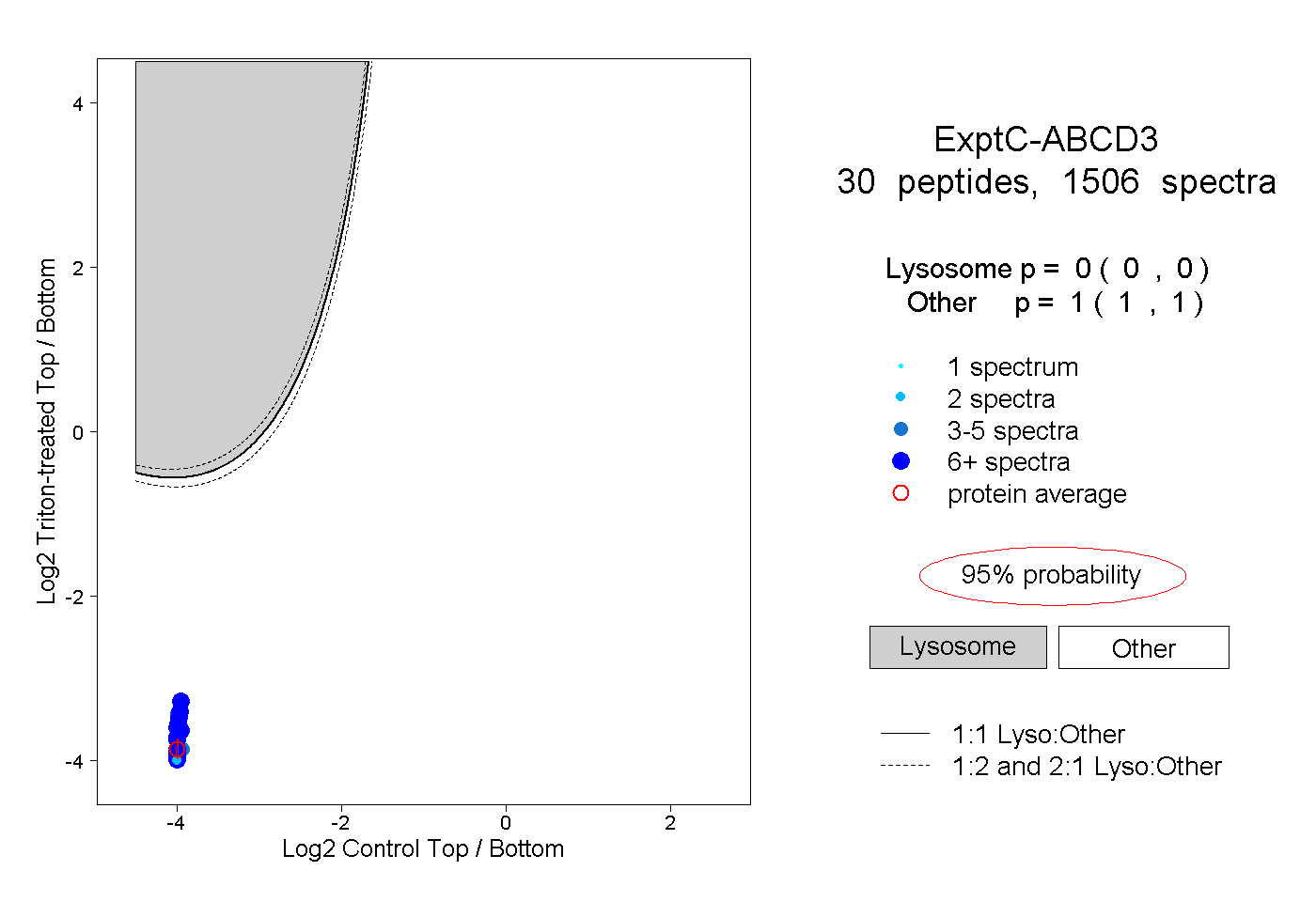 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
85 spectra |
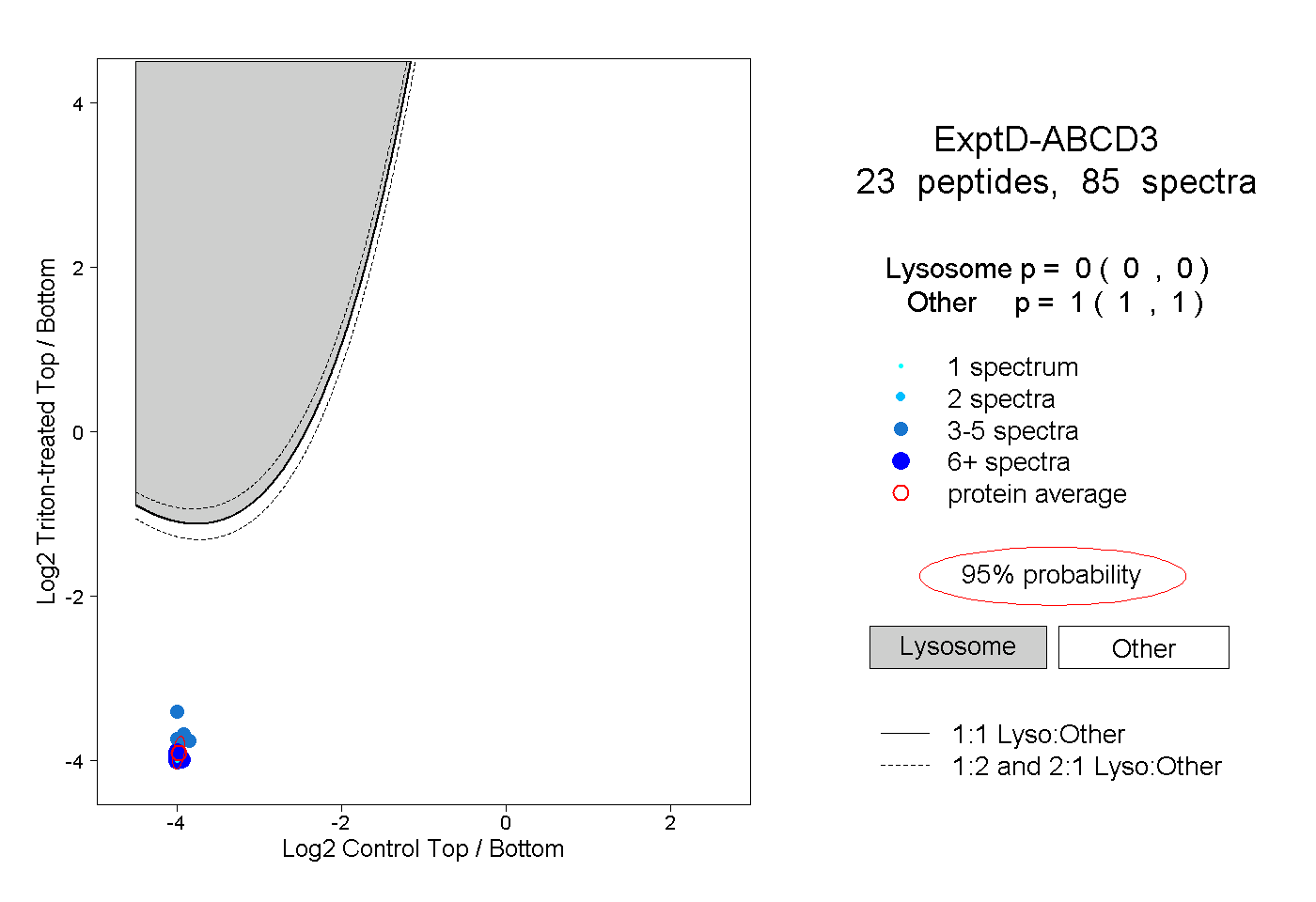 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |