peptides
spectra
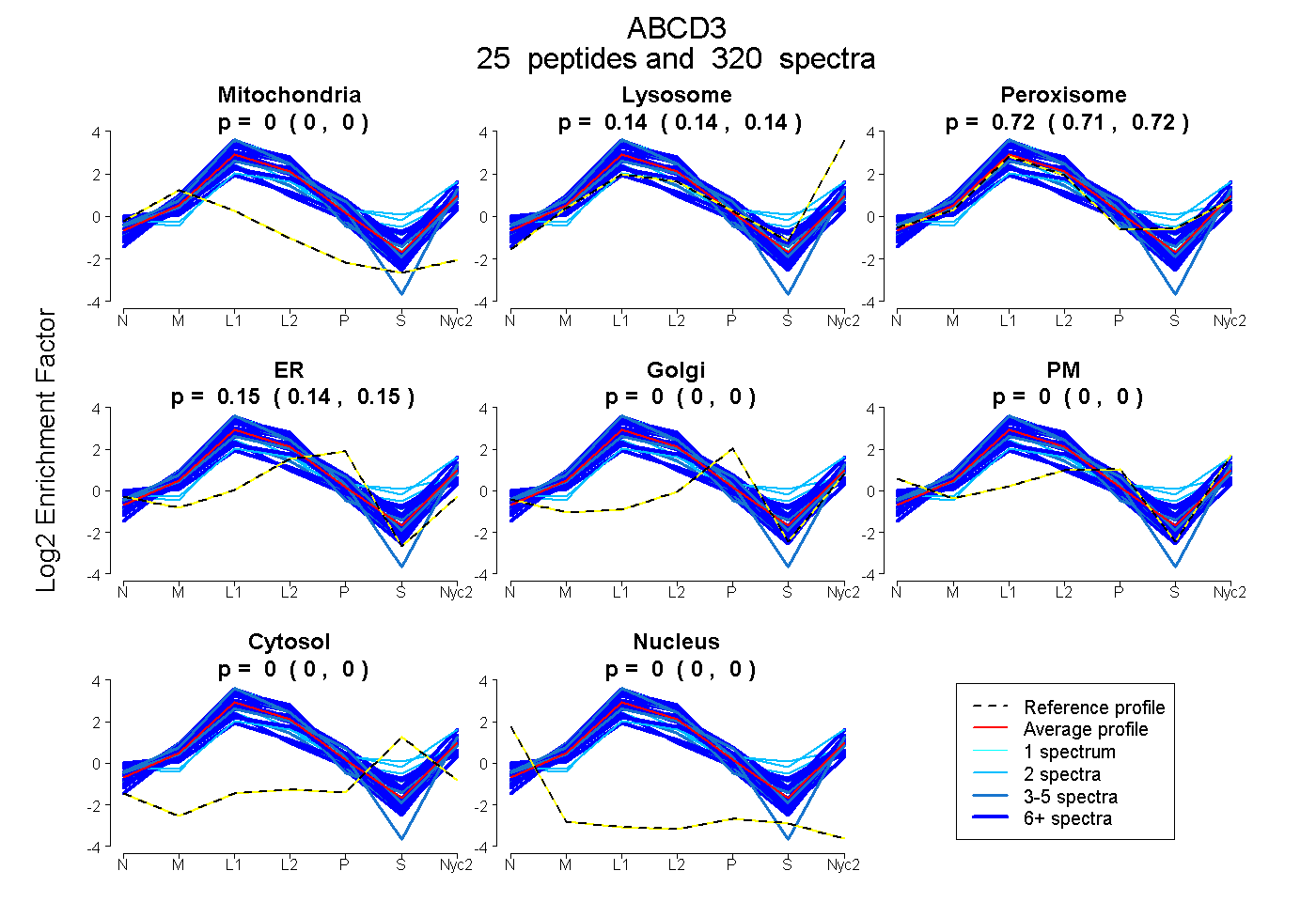
0.000 | 0.000
0.135 | 0.140
0.712 | 0.718
0.145 | 0.149
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
320 spectra |
 |
0.000 0.000 | 0.000 |
0.138 0.135 | 0.140 |
0.716 0.712 | 0.718 |
0.147 0.145 | 0.149 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 8 spectra, DQVIYPDGK | 0.000 | 0.102 | 0.841 | 0.057 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 18 spectra, TMVSQQDK | 0.000 | 0.000 | 0.694 | 0.306 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, GYLDNVQLGHILER | 0.000 | 0.000 | 0.692 | 0.188 | 0.000 | 0.120 | 0.000 | 0.000 | ||
| 4 spectra, YGLNELK | 0.000 | 0.129 | 0.583 | 0.289 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 26 spectra, MGNLDNR | 0.000 | 0.276 | 0.640 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, GISDQVLK | 0.000 | 0.185 | 0.679 | 0.136 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, FDHVPLATPNGDILIQDLSFEVR | 0.000 | 0.036 | 0.931 | 0.000 | 0.034 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, VGITLFTVSHR | 0.000 | 0.132 | 0.622 | 0.194 | 0.000 | 0.053 | 0.000 | 0.000 | ||
| 6 spectra, MTIMEQK | 0.000 | 0.183 | 0.699 | 0.118 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, DLNHGK | 0.000 | 0.068 | 0.839 | 0.093 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, YLYEEYLQAFTYYK | 0.000 | 0.225 | 0.546 | 0.229 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 69 spectra, MSQALGR | 0.000 | 0.254 | 0.678 | 0.068 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, FSMGFIDSIIAK | 0.091 | 0.088 | 0.746 | 0.045 | 0.031 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, ISQLIK | 0.000 | 0.160 | 0.739 | 0.101 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, HHEYYLHMDGR | 0.048 | 0.000 | 0.798 | 0.000 | 0.102 | 0.024 | 0.000 | 0.029 | ||
| 9 spectra, LAGFTAR | 0.000 | 0.376 | 0.467 | 0.157 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 30 spectra, QTIHSVFR | 0.000 | 0.222 | 0.626 | 0.151 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, GNYEFK | 0.000 | 0.163 | 0.773 | 0.064 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, ITEDTVEFGS | 0.016 | 0.000 | 0.746 | 0.000 | 0.209 | 0.000 | 0.002 | 0.028 | ||
| 1 spectrum, IANPDQLLTQDVEK | 0.000 | 0.082 | 0.896 | 0.023 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 31 spectra, YEGEYR | 0.000 | 0.067 | 0.846 | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SGANVLICGPNGCGK | 0.000 | 0.237 | 0.538 | 0.000 | 0.000 | 0.155 | 0.070 | 0.000 | ||
| 3 spectra, IVLAGR | 0.000 | 0.065 | 0.935 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, EGGWDSVQDWMDVLSGGEK | 0.000 | 0.000 | 0.818 | 0.000 | 0.097 | 0.000 | 0.085 | 0.000 | ||
| 26 spectra, ITELMQVLK | 0.000 | 0.242 | 0.678 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
182 spectra |
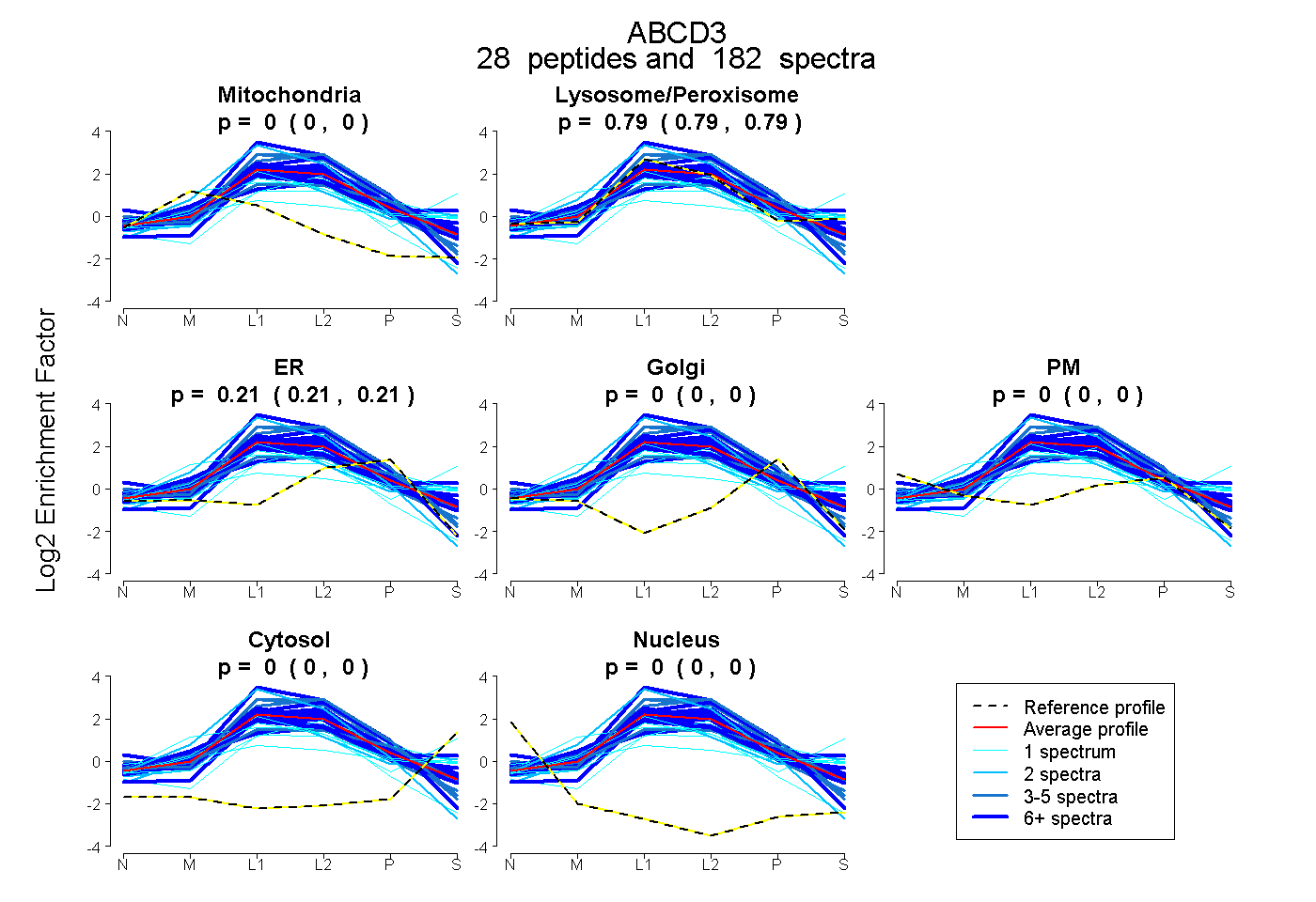 |
0.000 0.000 | 0.000 |
0.791 0.787 | 0.794 |
0.209 0.205 | 0.212 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1506 spectra |
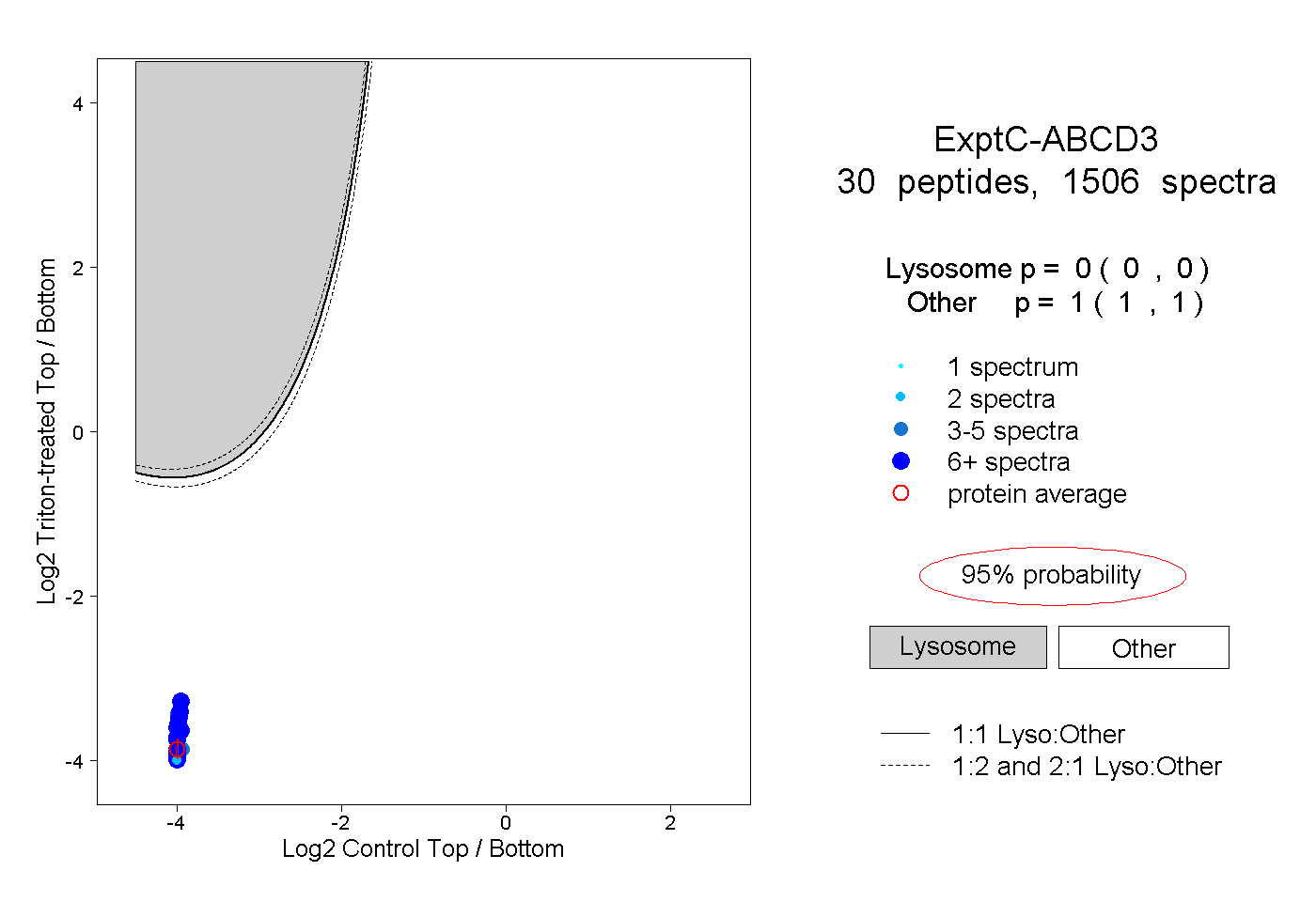 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
85 spectra |
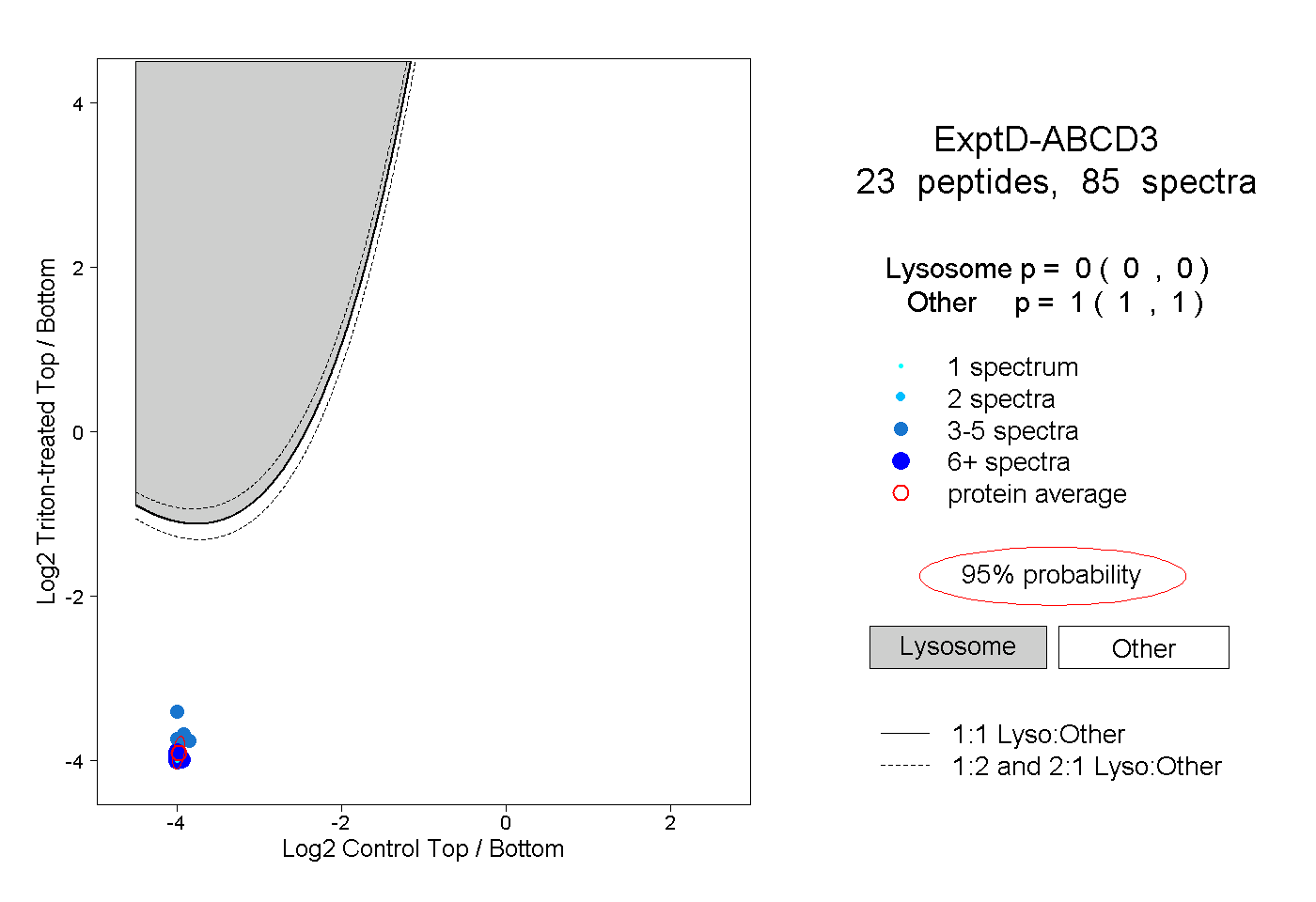 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |