peptides
spectra
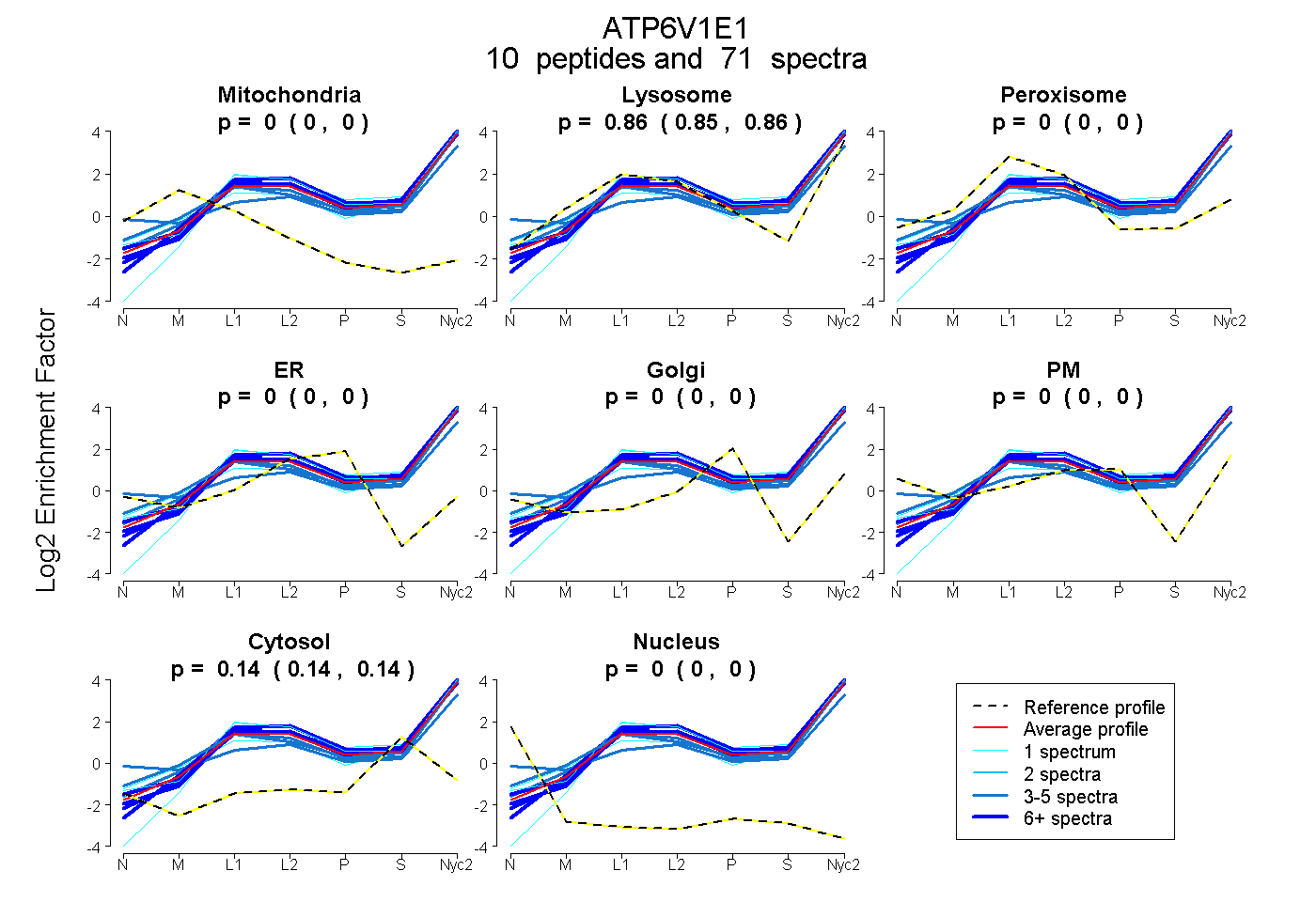
0.000 | 0.000
0.855 | 0.860
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.139 | 0.145
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
71 spectra |
 |
0.000 0.000 | 0.000 |
0.858 0.855 | 0.860 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.142 0.139 | 0.145 |
0.000 0.000 | 0.000 |
| 1 spectrum, DDLITDLLNEAK | 0.000 | 0.877 | 0.000 | 0.000 | 0.000 | 0.000 | 0.123 | 0.000 | ||
| 12 spectra, GALFGANANR | 0.000 | 0.846 | 0.000 | 0.000 | 0.000 | 0.000 | 0.154 | 0.000 | ||
| 4 spectra, IMEYYEK | 0.000 | 0.855 | 0.000 | 0.000 | 0.000 | 0.000 | 0.145 | 0.000 | ||
| 4 spectra, VSNTLESR | 0.000 | 0.881 | 0.000 | 0.000 | 0.000 | 0.000 | 0.119 | 0.000 | ||
| 3 spectra, HMMAFIEQEANEK | 0.000 | 0.658 | 0.000 | 0.000 | 0.000 | 0.136 | 0.206 | 0.000 | ||
| 1 spectrum, QDFPLVK | 0.000 | 0.906 | 0.000 | 0.000 | 0.000 | 0.000 | 0.094 | 0.000 | ||
| 15 spectra, LVQTQR | 0.000 | 0.855 | 0.000 | 0.000 | 0.000 | 0.000 | 0.145 | 0.000 | ||
| 1 spectrum, AEEEFNIEK | 0.000 | 0.821 | 0.000 | 0.000 | 0.000 | 0.000 | 0.179 | 0.000 | ||
| 23 spectra, IQMSNLMNQAR | 0.000 | 0.913 | 0.000 | 0.000 | 0.000 | 0.000 | 0.087 | 0.000 | ||
| 7 spectra, LDLIAQQMMPEVR | 0.000 | 0.858 | 0.000 | 0.000 | 0.000 | 0.000 | 0.142 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
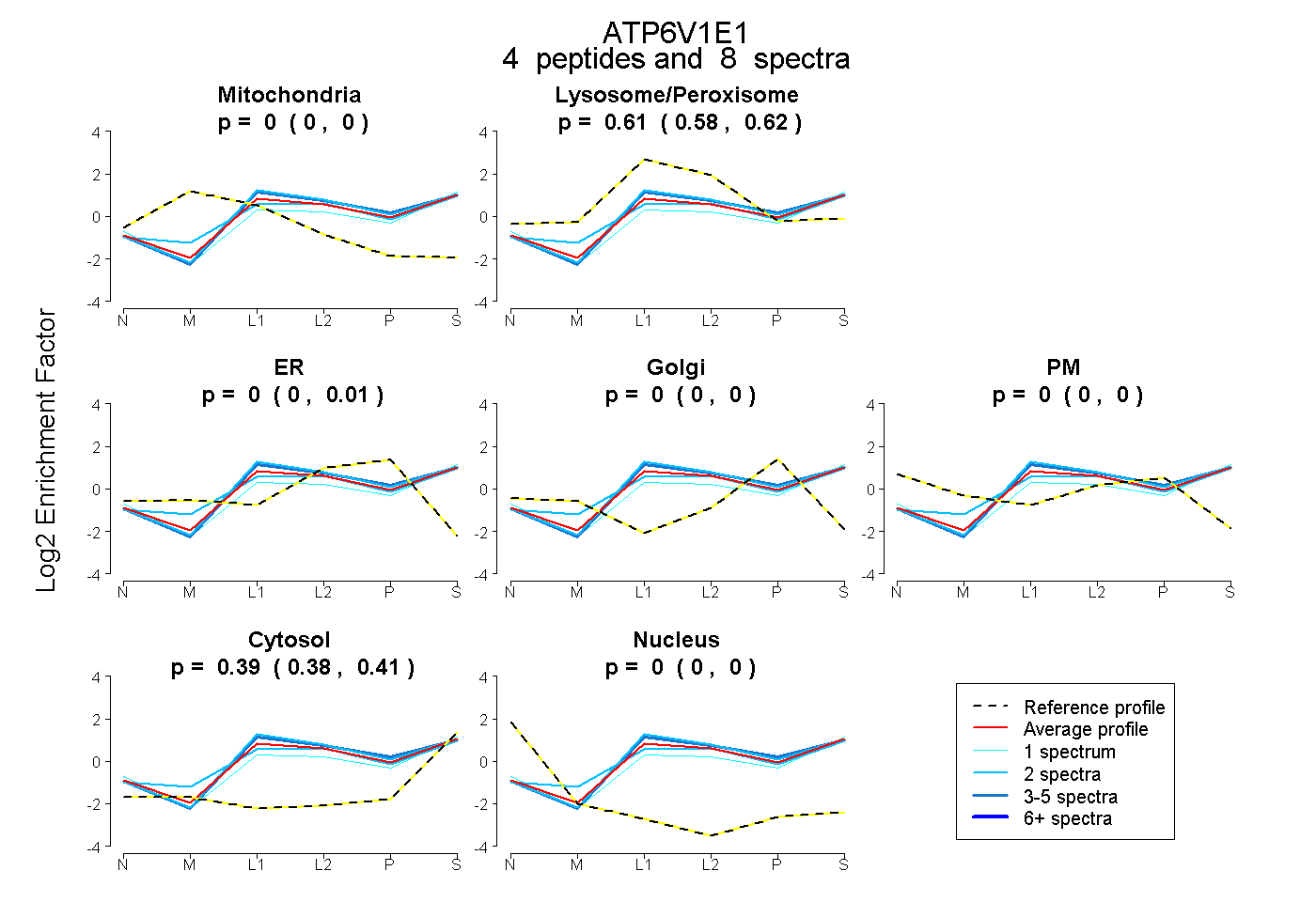 |
0.000 0.000 | 0.000 |
0.606 0.581 | 0.621 |
0.000 0.000 | 0.014 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.394 0.375 | 0.407 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
113 spectra |
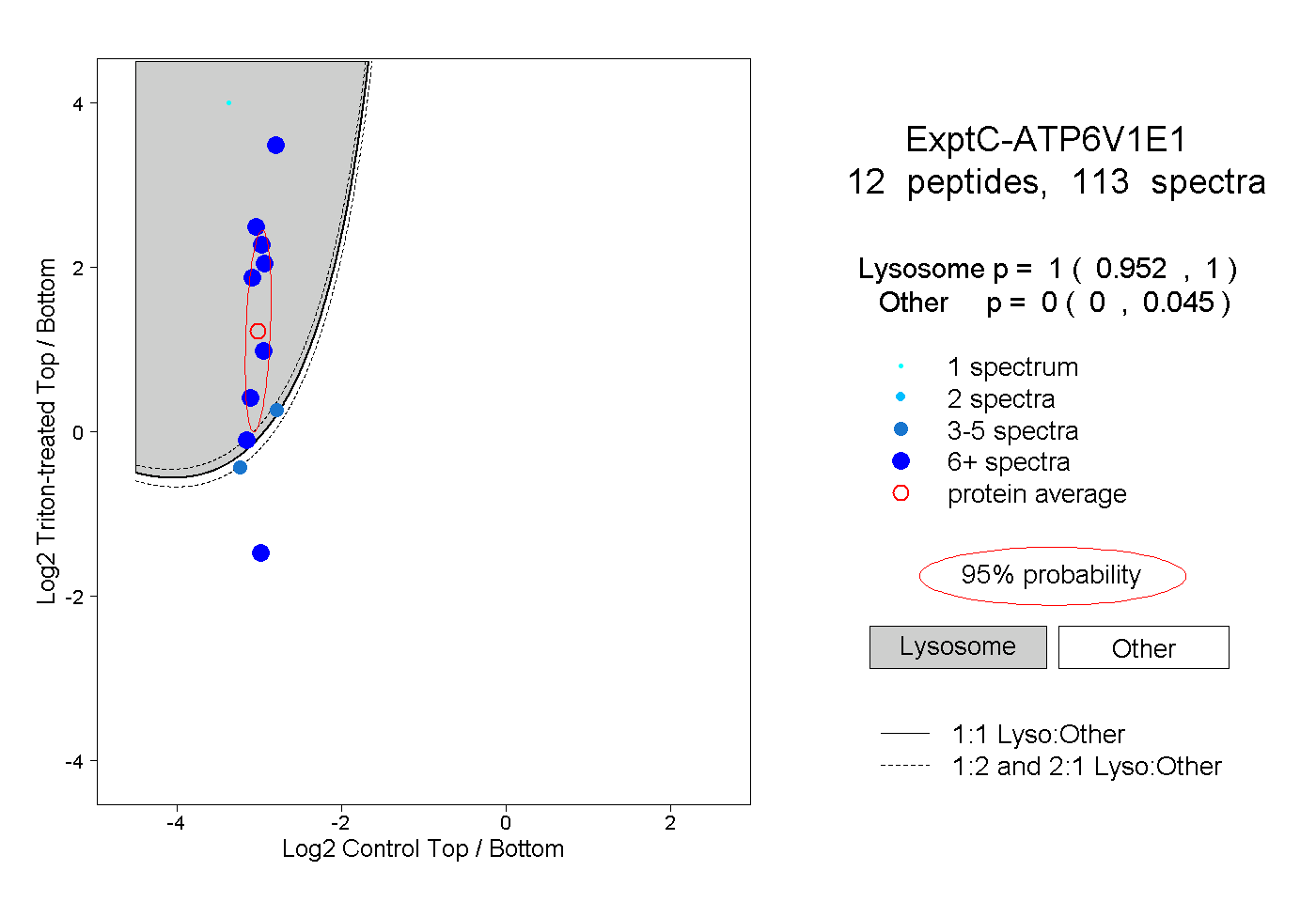 |
1.000 0.952 | 1.000 |
0.000 0.000 | 0.045 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
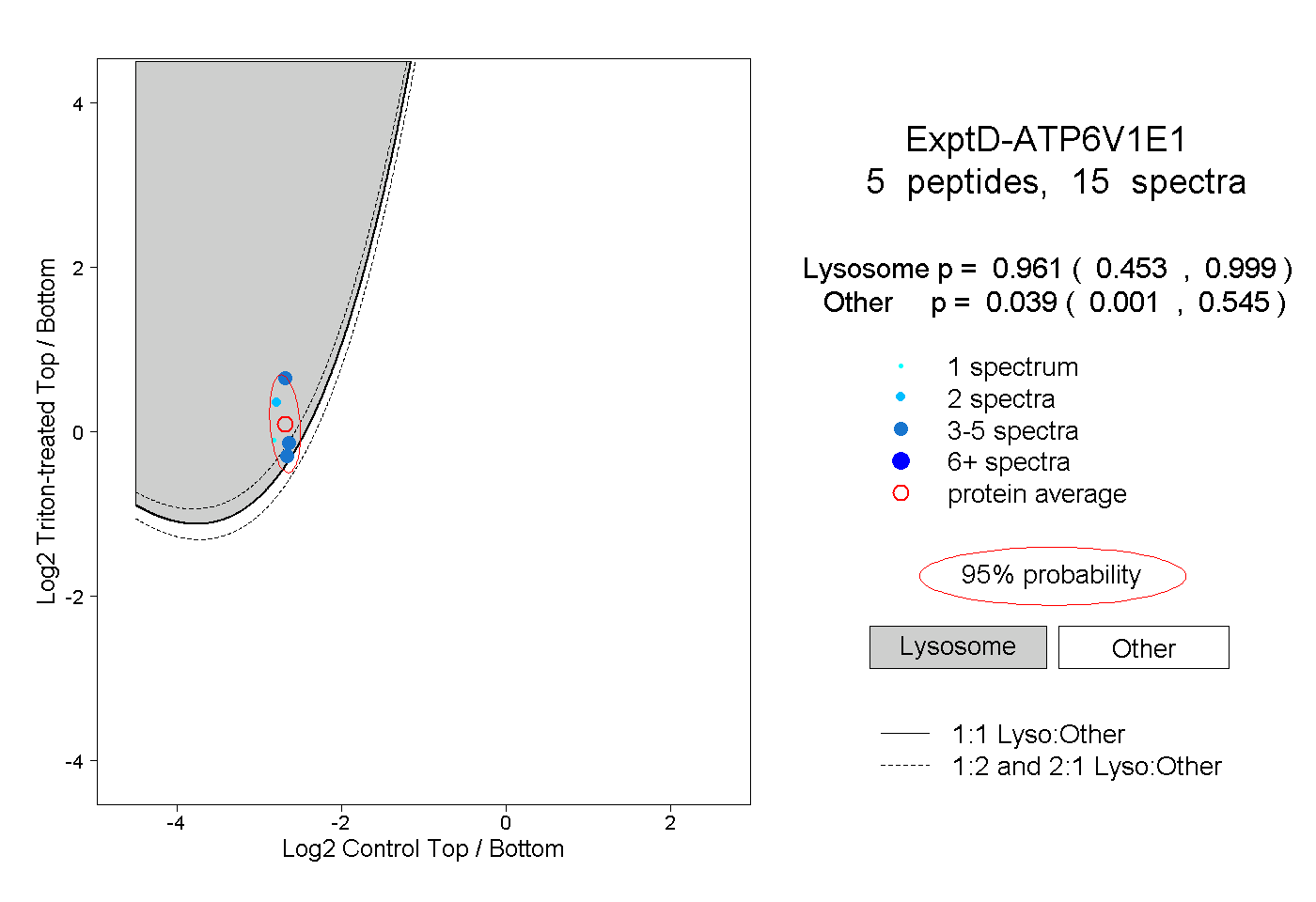 |
0.961 0.453 | 0.999 |
0.039 0.001 | 0.545 |