peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.011 | 0.015
0.000 | 0.000
0.984 | 0.989
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.066 | 0.083
0.000 | 0.000
0.915 | 0.933
0.000 | 0.000
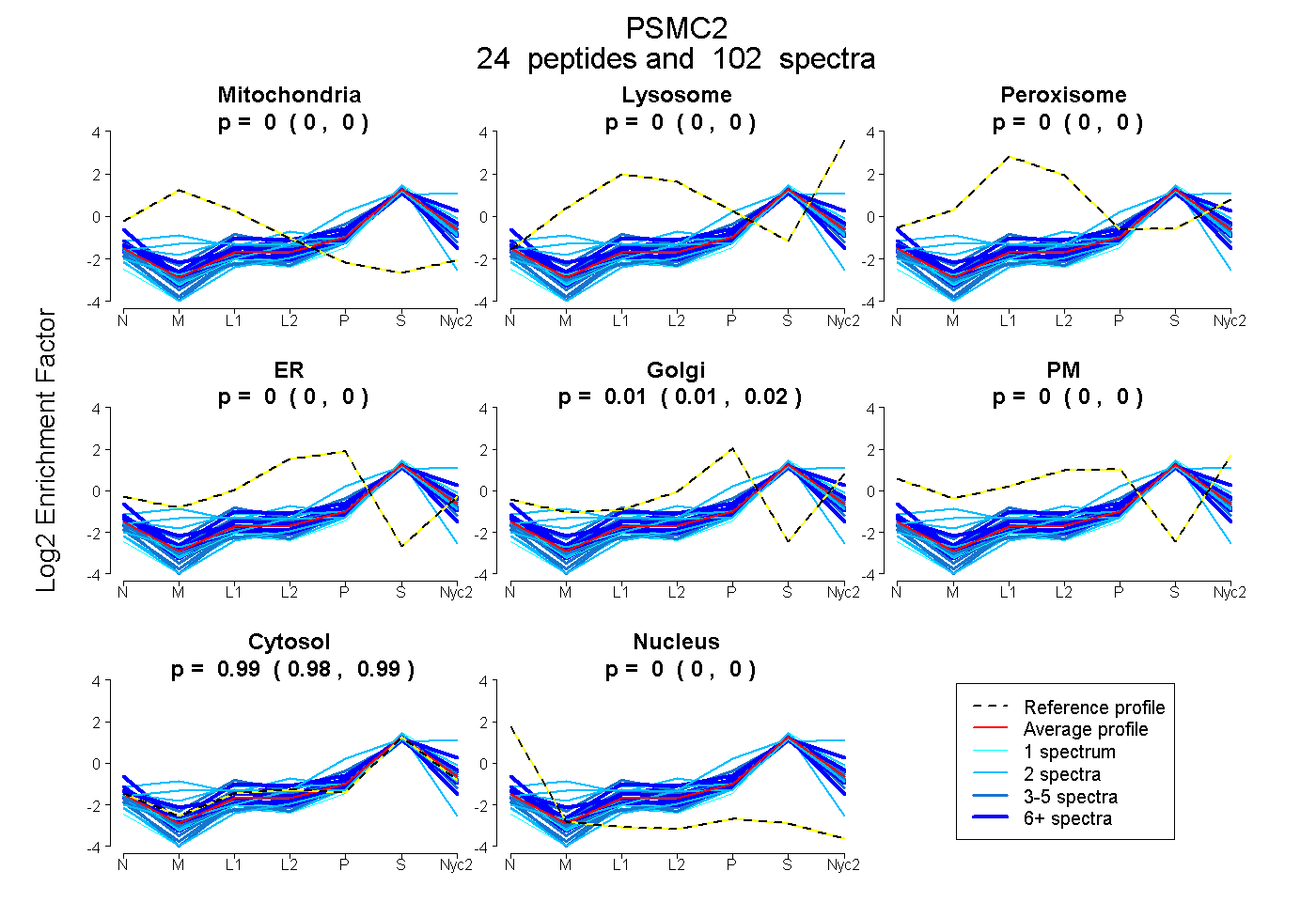
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
102 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.013 0.011 | 0.015 |
0.000 0.000 | 0.000 |
0.987 0.984 | 0.989 |
0.000 0.000 | 0.000 |
||
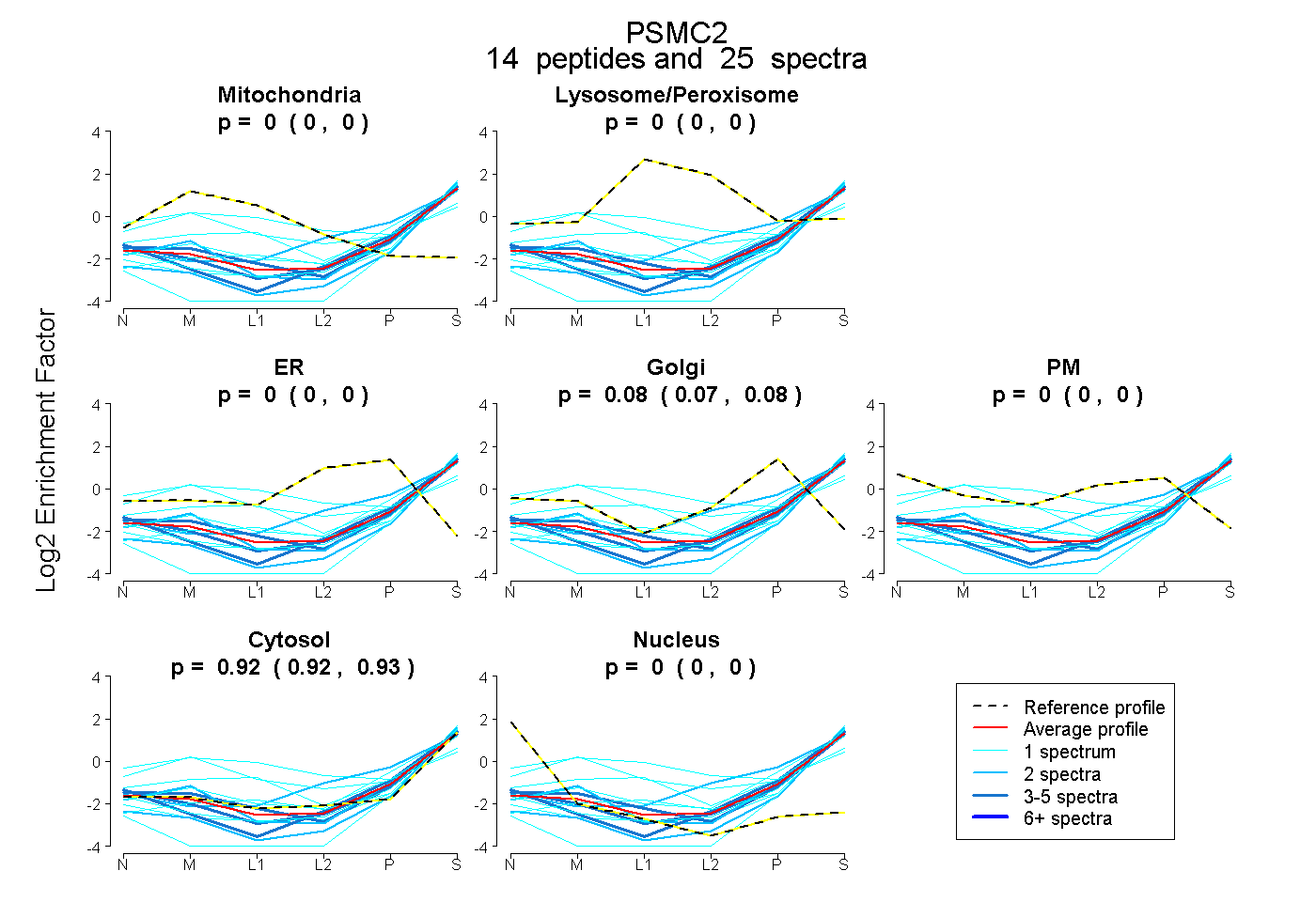
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.075 0.066 | 0.083 |
0.000 0.000 | 0.000 |
0.925 0.915 | 0.933 |
0.000 0.000 | 0.000 |
| 2 spectra, QTLQSEQPLQVAR | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 | 0.924 | 0.000 | |||
| 4 spectra, LCPNSTGAEIR | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | 0.915 | 0.039 | |||
| 1 spectrum, VLMATNRPDTLDPALMRPGR | 0.000 | 0.003 | 0.000 | 0.000 | 0.000 | 0.997 | 0.000 | |||
| 1 spectrum, ELFEMAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, SVCTEAGMFAIR | 0.233 | 0.274 | 0.000 | 0.000 | 0.115 | 0.379 | 0.000 | |||
| 2 spectra, FELLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, TDACFIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, QVEDDIQQLLK | 0.000 | 0.000 | 0.000 | 0.054 | 0.000 | 0.910 | 0.036 | |||
| 1 spectrum, YVGEGAR | 0.000 | 0.000 | 0.000 | 0.182 | 0.000 | 0.818 | 0.000 | |||
| 1 spectrum, YQIHIPLPPK | 0.078 | 0.156 | 0.000 | 0.039 | 0.000 | 0.727 | 0.000 | |||
| 1 spectrum, VIGSELVQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.978 | 0.022 | |||
| 1 spectrum, EVVETPLLHPER | 0.274 | 0.123 | 0.000 | 0.060 | 0.043 | 0.500 | 0.000 | |||
| 4 spectra, FDDGAGGDNEVQR | 0.000 | 0.000 | 0.000 | 0.032 | 0.000 | 0.926 | 0.042 | |||
| 2 spectra, ALDEGDIALLK | 0.000 | 0.000 | 0.222 | 0.000 | 0.000 | 0.778 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
69 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
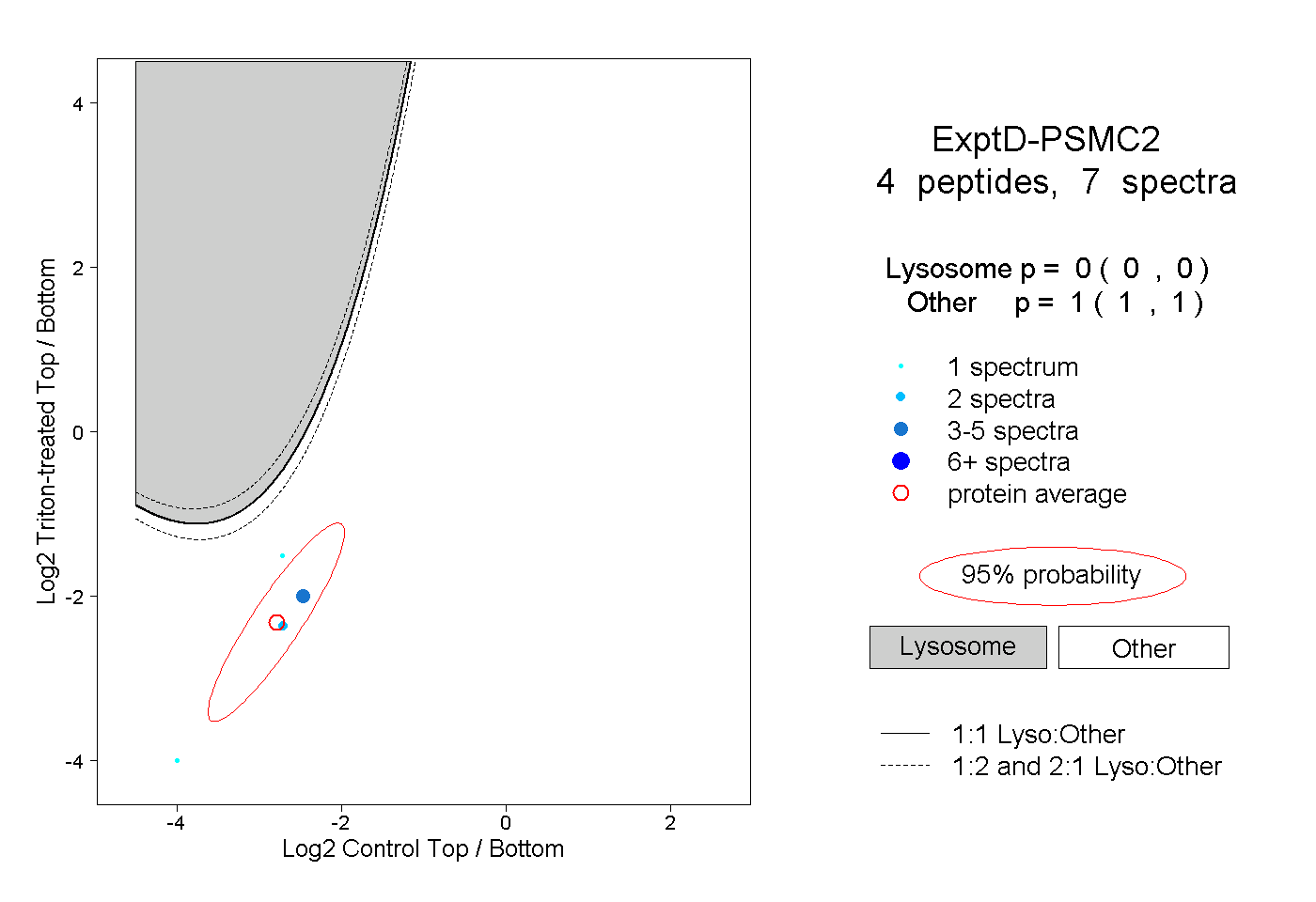 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |