peptides
spectra
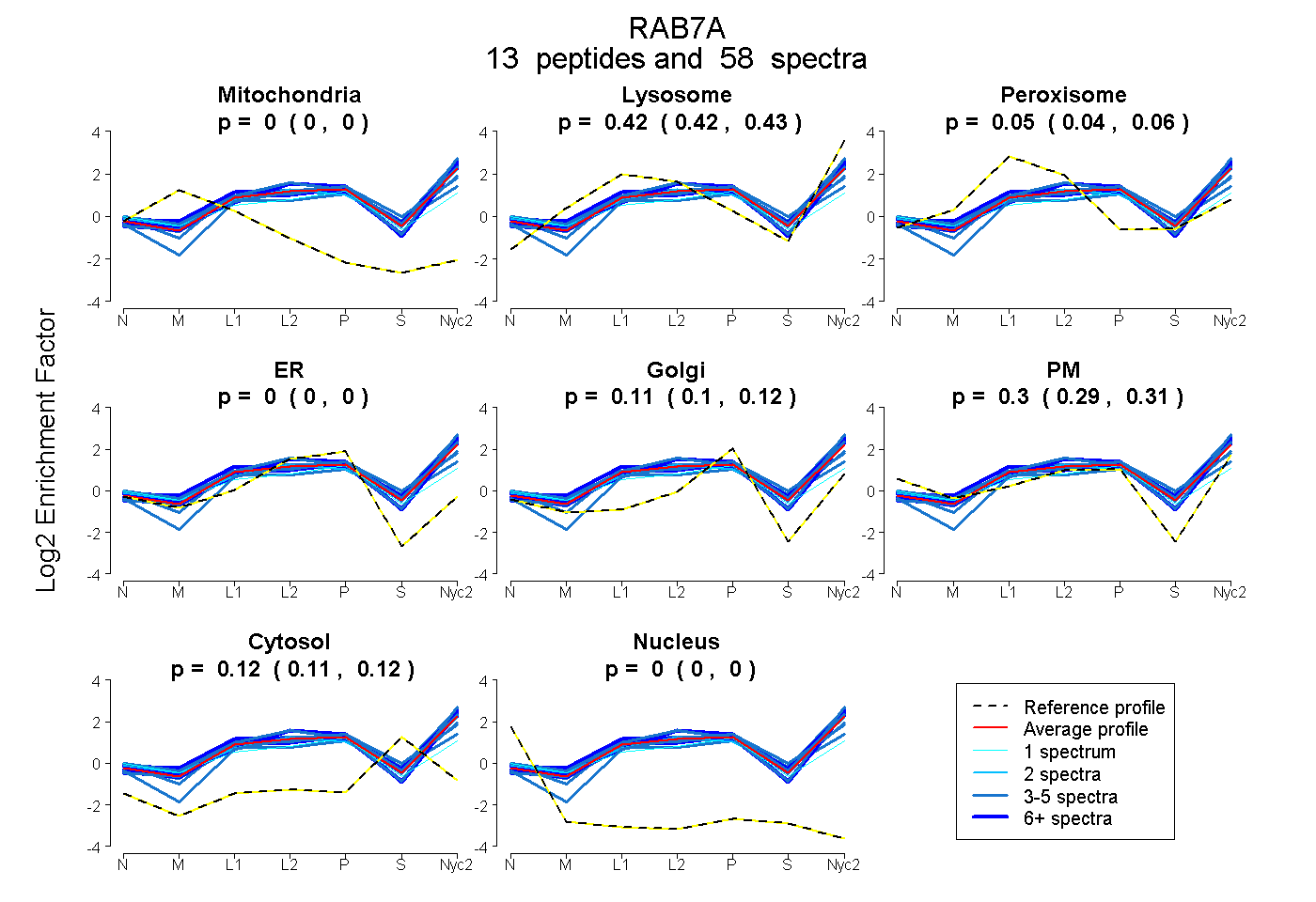
0.000 | 0.000
0.415 | 0.432
0.038 | 0.058
0.000 | 0.000
0.102 | 0.121
0.287 | 0.308
0.112 | 0.118
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.425 0.415 | 0.432 |
0.049 0.038 | 0.058 |
0.000 0.000 | 0.000 |
0.112 0.102 | 0.121 |
0.299 0.287 | 0.308 |
0.115 0.112 | 0.118 |
0.000 0.000 | 0.000 |
| 7 spectra, EVMVDDR | 0.000 | 0.537 | 0.011 | 0.000 | 0.159 | 0.170 | 0.123 | 0.000 | ||
| 6 spectra, DPENFPFVVLGNK | 0.000 | 0.473 | 0.019 | 0.000 | 0.151 | 0.233 | 0.123 | 0.000 | ||
| 6 spectra, FSNQYK | 0.000 | 0.427 | 0.000 | 0.071 | 0.061 | 0.398 | 0.044 | 0.000 | ||
| 4 spectra, EAINVEQAFQTIAR | 0.000 | 0.334 | 0.131 | 0.000 | 0.106 | 0.290 | 0.139 | 0.000 | ||
| 2 spectra, LVTMQIWDTAGQER | 0.000 | 0.394 | 0.045 | 0.000 | 0.000 | 0.414 | 0.146 | 0.000 | ||
| 3 spectra, AQAWCYSK | 0.000 | 0.242 | 0.253 | 0.000 | 0.301 | 0.050 | 0.154 | 0.000 | ||
| 4 spectra, ATIGADFLTK | 0.000 | 0.441 | 0.004 | 0.000 | 0.000 | 0.438 | 0.117 | 0.000 | ||
| 3 spectra, TSLMNQYVNK | 0.000 | 0.510 | 0.043 | 0.000 | 0.234 | 0.114 | 0.098 | 0.000 | ||
| 4 spectra, DEFLIQASPR | 0.000 | 0.532 | 0.000 | 0.000 | 0.127 | 0.203 | 0.137 | 0.000 | ||
| 1 spectrum, QETEVELYNEFPEPIK | 0.000 | 0.057 | 0.300 | 0.000 | 0.329 | 0.210 | 0.103 | 0.000 | ||
| 4 spectra, NNIPYFETSAK | 0.000 | 0.475 | 0.000 | 0.000 | 0.000 | 0.492 | 0.033 | 0.000 | ||
| 11 spectra, FQSLGVAFYR | 0.000 | 0.471 | 0.034 | 0.000 | 0.042 | 0.407 | 0.047 | 0.000 | ||
| 3 spectra, VIILGDSGVGK | 0.000 | 0.394 | 0.000 | 0.168 | 0.075 | 0.116 | 0.248 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.598 0.592 | 0.602 |
0.000 0.000 | 0.000 |
0.351 0.344 | 0.357 |
0.000 0.000 | 0.000 |
0.051 0.045 | 0.056 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
185 spectra |
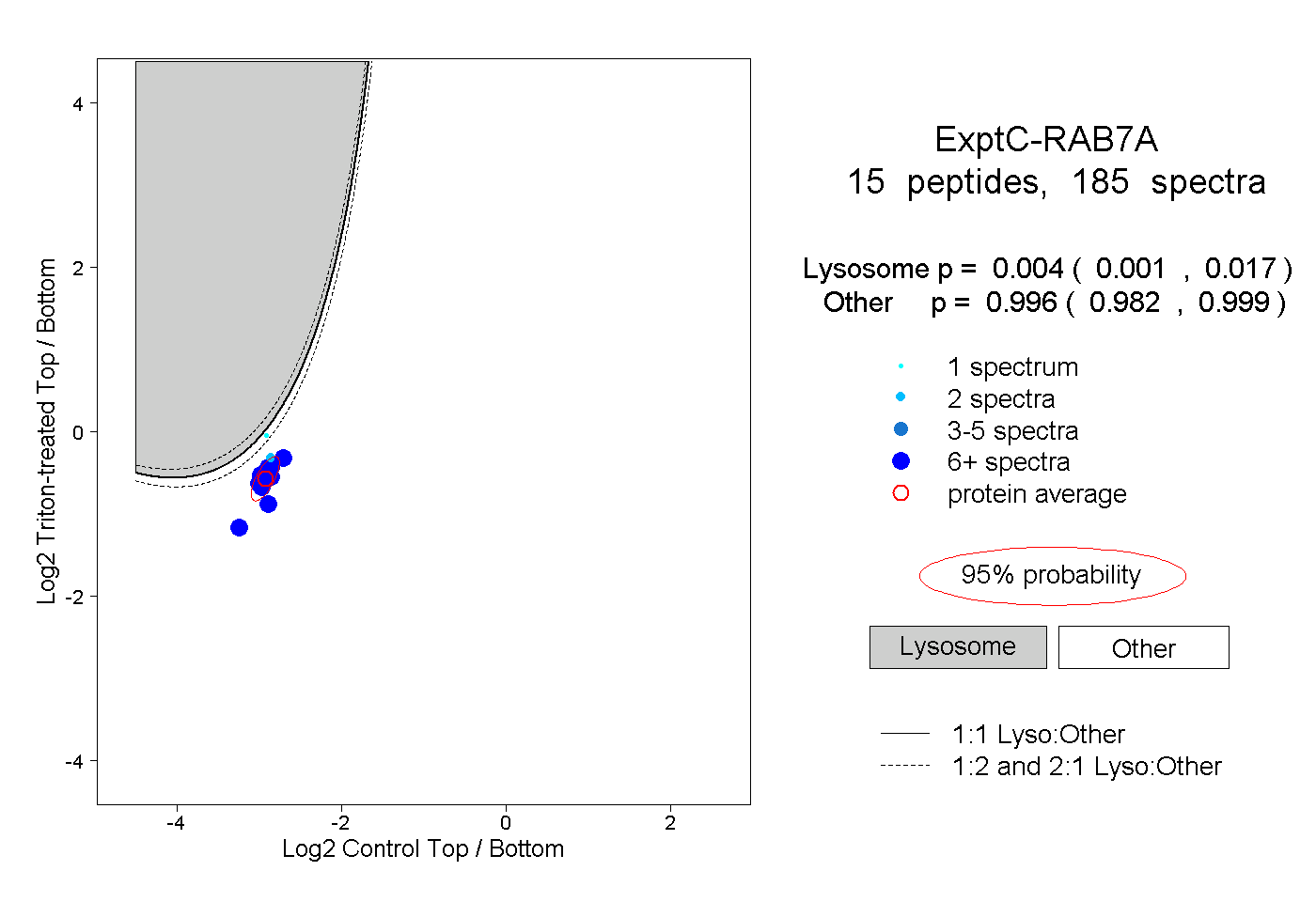 |
0.004 0.001 | 0.017 |
0.996 0.982 | 0.999 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
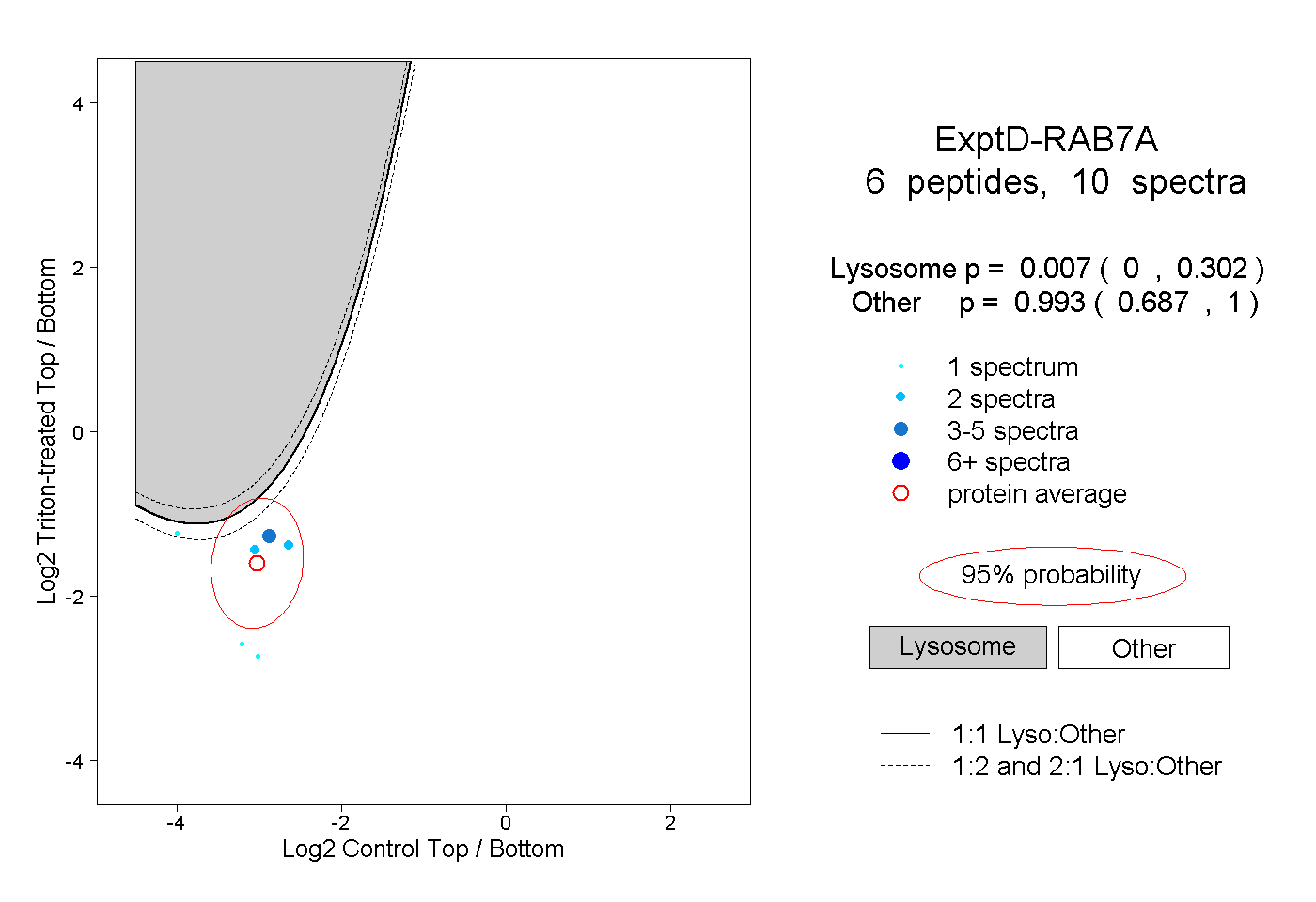 |
0.007 0.000 | 0.302 |
0.993 0.687 | 1.000 |