peptides
spectra
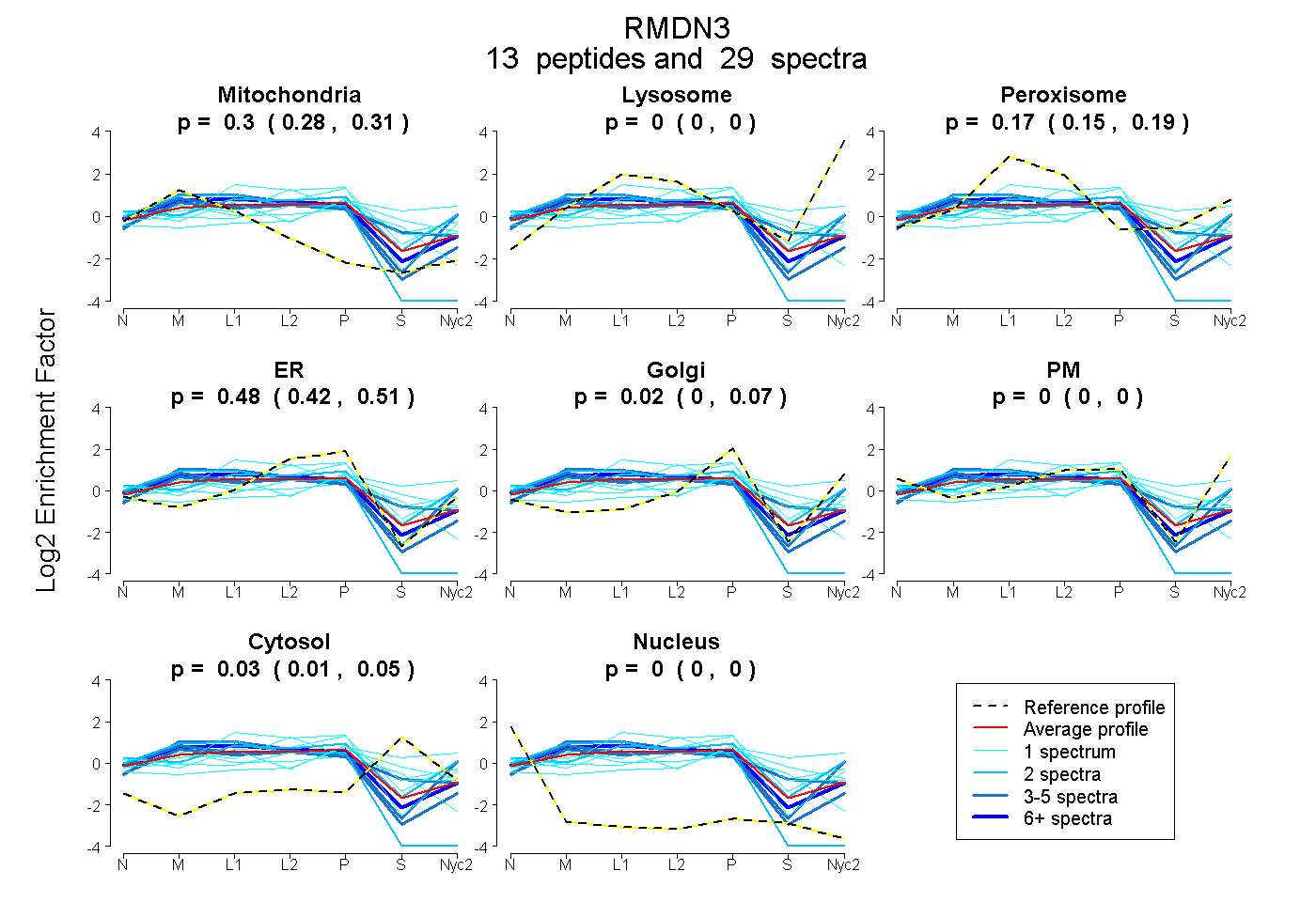
0.278 | 0.310
0.000 | 0.000
0.150 | 0.192
0.422 | 0.508
0.000 | 0.068
0.000 | 0.000
0.011 | 0.047
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
29 spectra |
 |
0.295 0.278 | 0.310 |
0.000 0.000 | 0.000 |
0.172 0.150 | 0.192 |
0.483 0.422 | 0.508 |
0.018 0.000 | 0.068 |
0.000 0.000 | 0.000 |
0.033 0.011 | 0.047 |
0.000 0.000 | 0.000 |
| 4 spectra, QDFLWR | 0.266 | 0.000 | 0.257 | 0.332 | 0.000 | 0.000 | 0.146 | 0.000 | ||
| 2 spectra, LGALGGSR | 0.121 | 0.000 | 0.291 | 0.247 | 0.185 | 0.150 | 0.000 | 0.006 | ||
| 7 spectra, GHFLLGR | 0.342 | 0.000 | 0.181 | 0.477 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EVEELQR | 0.006 | 0.000 | 0.345 | 0.295 | 0.310 | 0.000 | 0.008 | 0.036 | ||
| 1 spectrum, SHMEENQR | 0.085 | 0.000 | 0.254 | 0.661 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, QVTQLR | 0.244 | 0.000 | 0.238 | 0.122 | 0.273 | 0.000 | 0.123 | 0.000 | ||
| 1 spectrum, EEAEAALK | 0.389 | 0.000 | 0.053 | 0.331 | 0.000 | 0.000 | 0.227 | 0.000 | ||
| 3 spectra, AIELQPEDPR | 0.446 | 0.000 | 0.088 | 0.466 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, WLNLAQELPNITNEDSAFQK | 0.086 | 0.000 | 0.196 | 0.414 | 0.000 | 0.000 | 0.304 | 0.000 | ||
| 1 spectrum, SQSLPNSLDYAQTSER | 0.000 | 0.077 | 0.178 | 0.000 | 0.369 | 0.010 | 0.367 | 0.000 | ||
| 4 spectra, IQSGFSFK | 0.336 | 0.119 | 0.000 | 0.285 | 0.000 | 0.259 | 0.000 | 0.000 | ||
| 2 spectra, QEGFQLLLNNK | 0.618 | 0.000 | 0.000 | 0.382 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LAYGSR | 0.140 | 0.000 | 0.331 | 0.366 | 0.000 | 0.040 | 0.123 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
28 spectra |
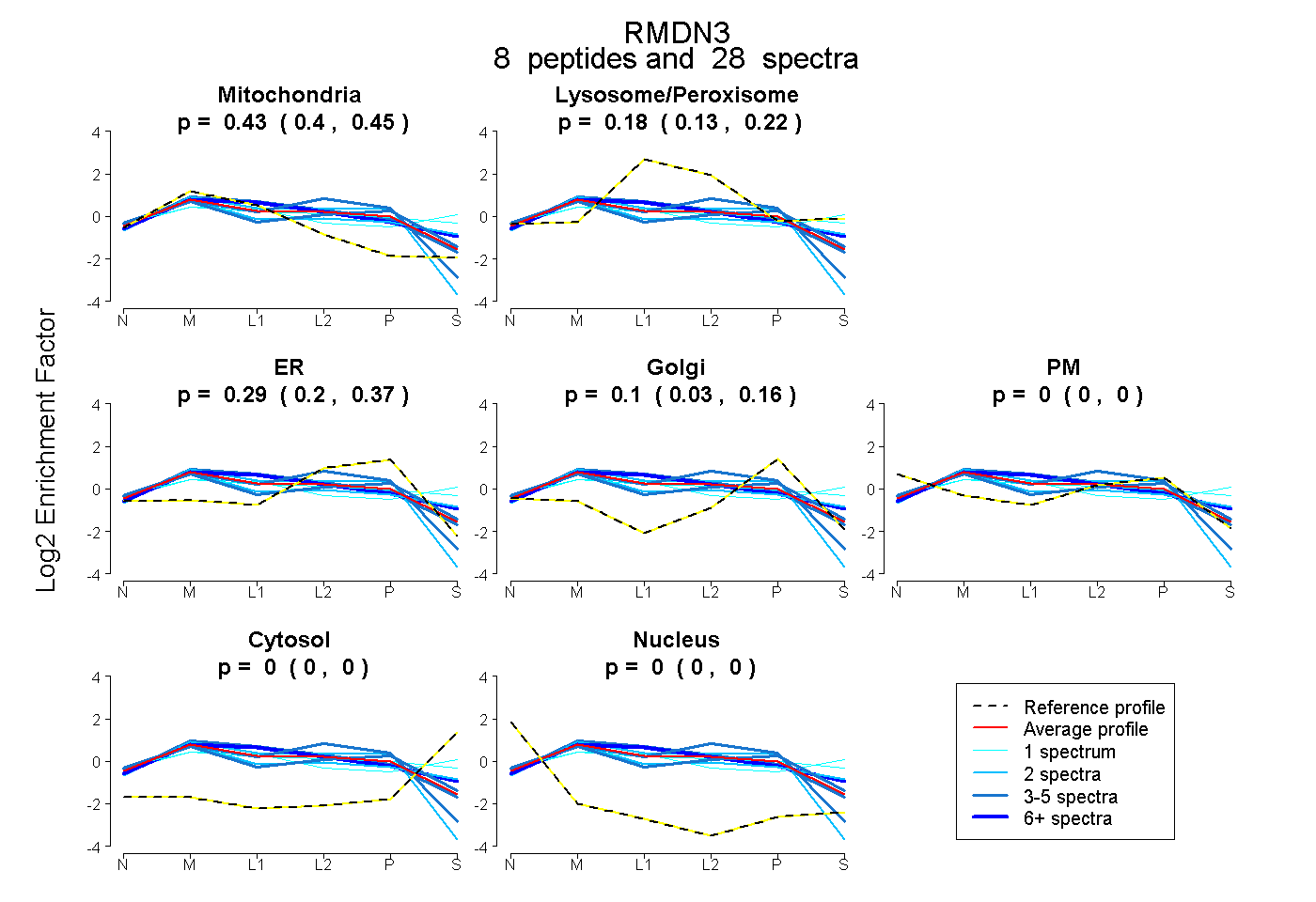 |
0.429 0.401 | 0.454 |
0.176 0.126 | 0.217 |
0.293 0.202 | 0.371 |
0.102 0.032 | 0.165 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
50 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
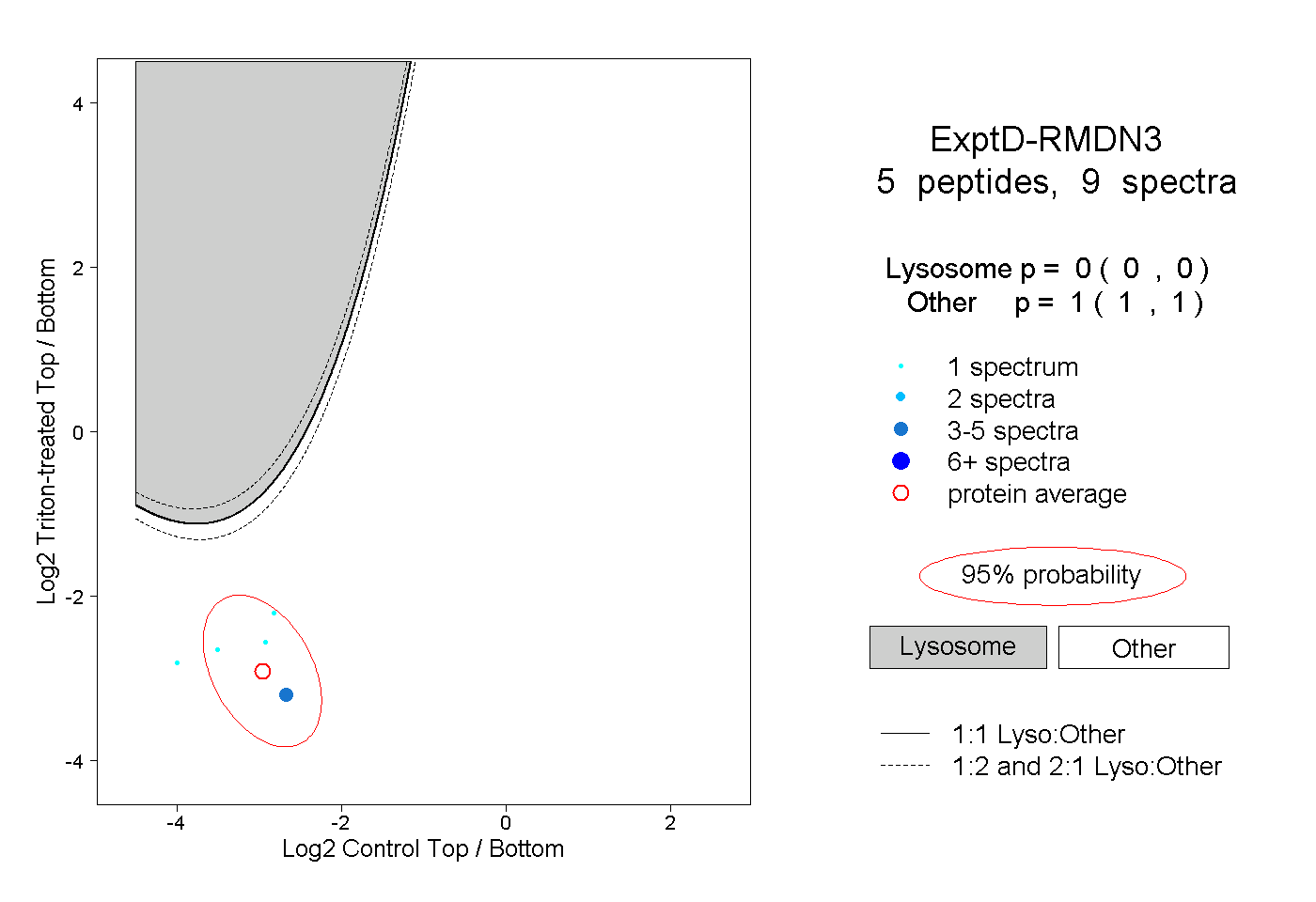 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |