peptides
spectra
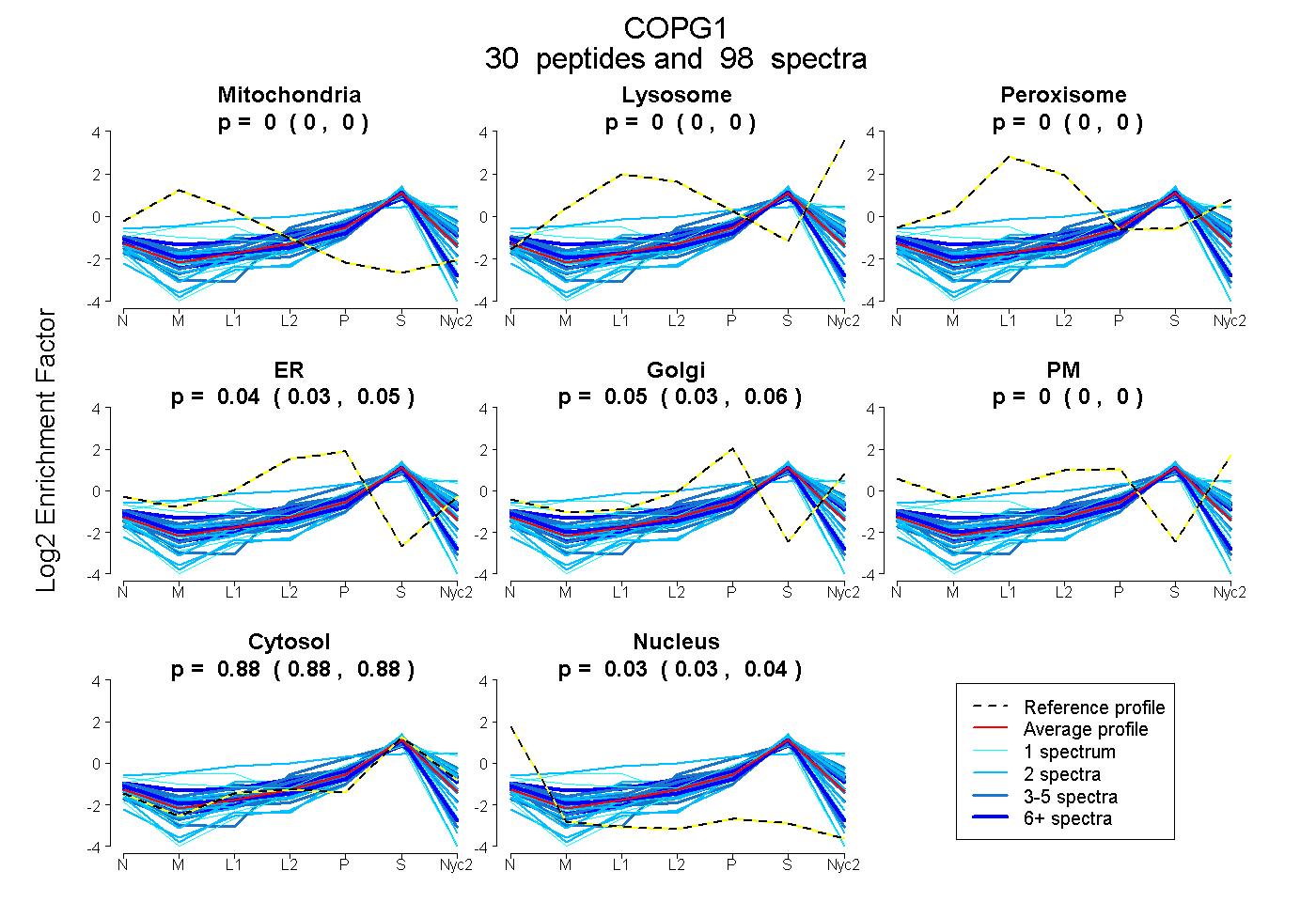
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.027 | 0.049
0.031 | 0.059
0.000 | 0.000
0.879 | 0.883
0.031 | 0.037
peptides
spectra
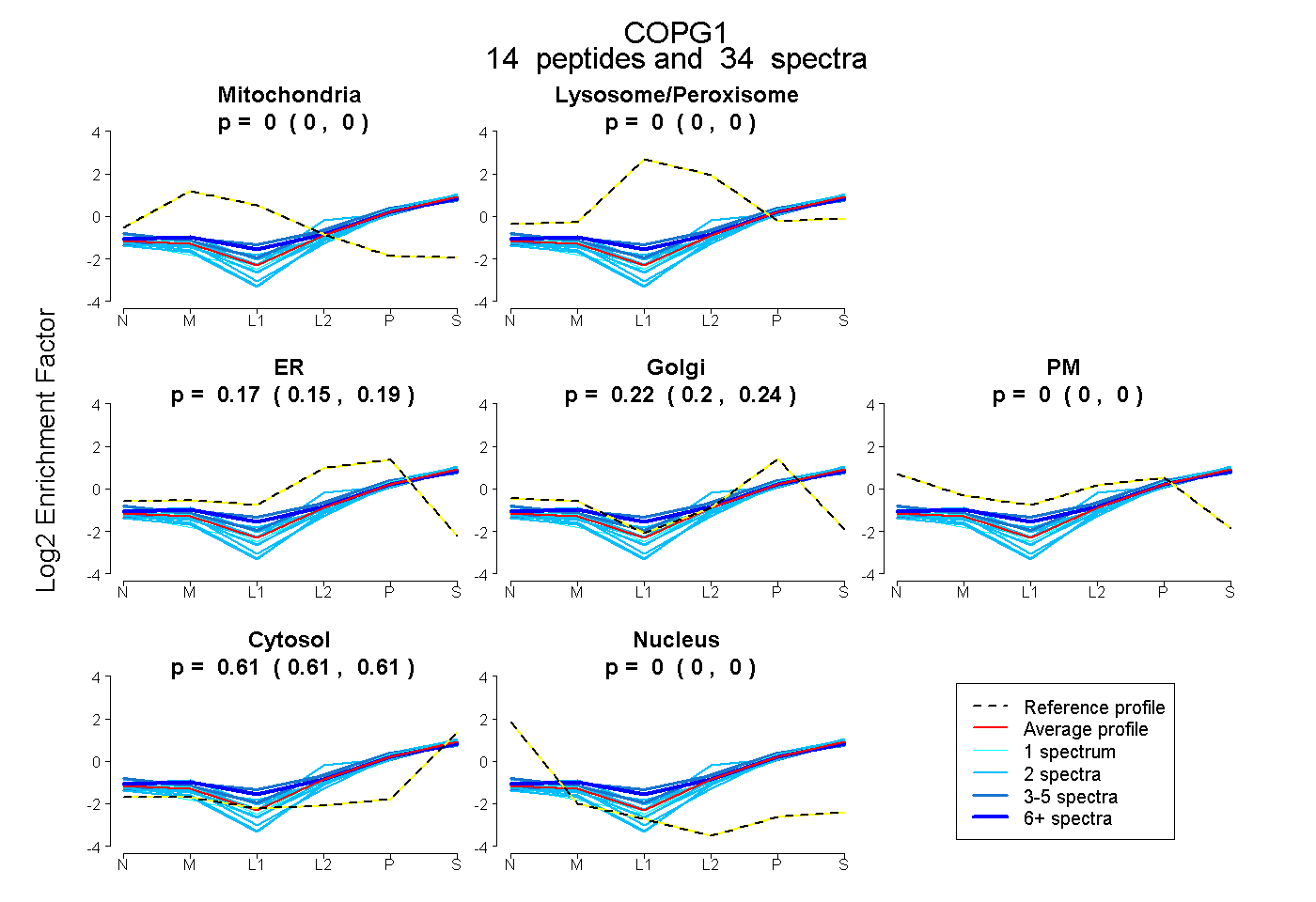
0.000 | 0.000
0.000 | 0.000
0.154 | 0.185
0.201 | 0.236
0.000 | 0.000
0.606 | 0.612
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
98 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.039 0.027 | 0.049 |
0.045 0.031 | 0.059 |
0.000 0.000 | 0.000 |
0.881 0.879 | 0.883 |
0.034 0.031 | 0.037 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.171 0.154 | 0.185 |
0.221 0.201 | 0.236 |
0.000 0.000 | 0.000 |
0.609 0.606 | 0.612 |
0.000 0.000 | 0.000 |
| 2 spectra, ILHLLGQEGPK | 0.000 | 0.000 | 0.075 | 0.307 | 0.000 | 0.618 | 0.000 | |||
| 2 spectra, VFNETPINPR | 0.000 | 0.000 | 0.042 | 0.325 | 0.000 | 0.633 | 0.000 | |||
| 2 spectra, GGHDILVR | 0.000 | 0.083 | 0.076 | 0.214 | 0.000 | 0.627 | 0.000 | |||
| 2 spectra, TGSESSIDR | 0.000 | 0.000 | 0.000 | 0.357 | 0.000 | 0.643 | 0.000 | |||
| 2 spectra, DSPLFDFIESCLR | 0.000 | 0.000 | 0.000 | 0.371 | 0.000 | 0.629 | 0.000 | |||
| 7 spectra, VVLEHEEVR | 0.000 | 0.160 | 0.000 | 0.325 | 0.000 | 0.515 | 0.000 | |||
| 3 spectra, NTHTLLLAGVFR | 0.000 | 0.191 | 0.054 | 0.208 | 0.000 | 0.547 | 0.000 | |||
| 2 spectra, LFQSNDPTLR | 0.000 | 0.000 | 0.368 | 0.000 | 0.000 | 0.632 | 0.000 | |||
| 1 spectrum, TLEEAVGNIVK | 0.000 | 0.000 | 0.136 | 0.288 | 0.000 | 0.576 | 0.000 | |||
| 2 spectra, SAVLQEAR | 0.000 | 0.085 | 0.000 | 0.417 | 0.000 | 0.498 | 0.000 | |||
| 1 spectrum, ATFYLNVLEQK | 0.000 | 0.000 | 0.113 | 0.258 | 0.000 | 0.630 | 0.000 | |||
| 2 spectra, QLEEEDGSR | 0.000 | 0.000 | 0.000 | 0.378 | 0.000 | 0.622 | 0.000 | |||
| 2 spectra, ELAPAVSVLQLFCSSPK | 0.000 | 0.040 | 0.063 | 0.343 | 0.000 | 0.554 | 0.000 | |||
| 4 spectra, SIATLAITTLLK | 0.000 | 0.094 | 0.076 | 0.339 | 0.000 | 0.490 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
54 spectra |
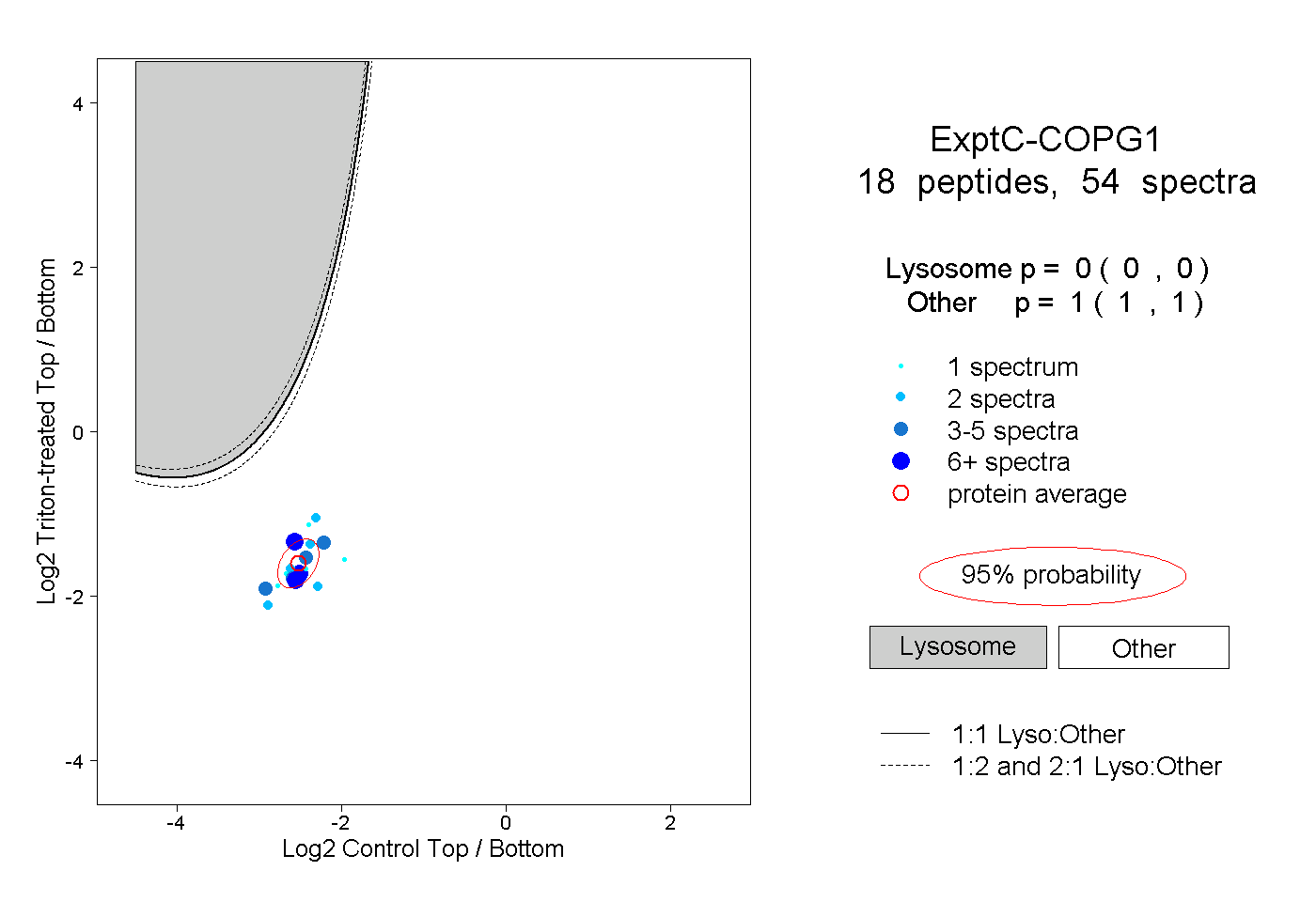 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
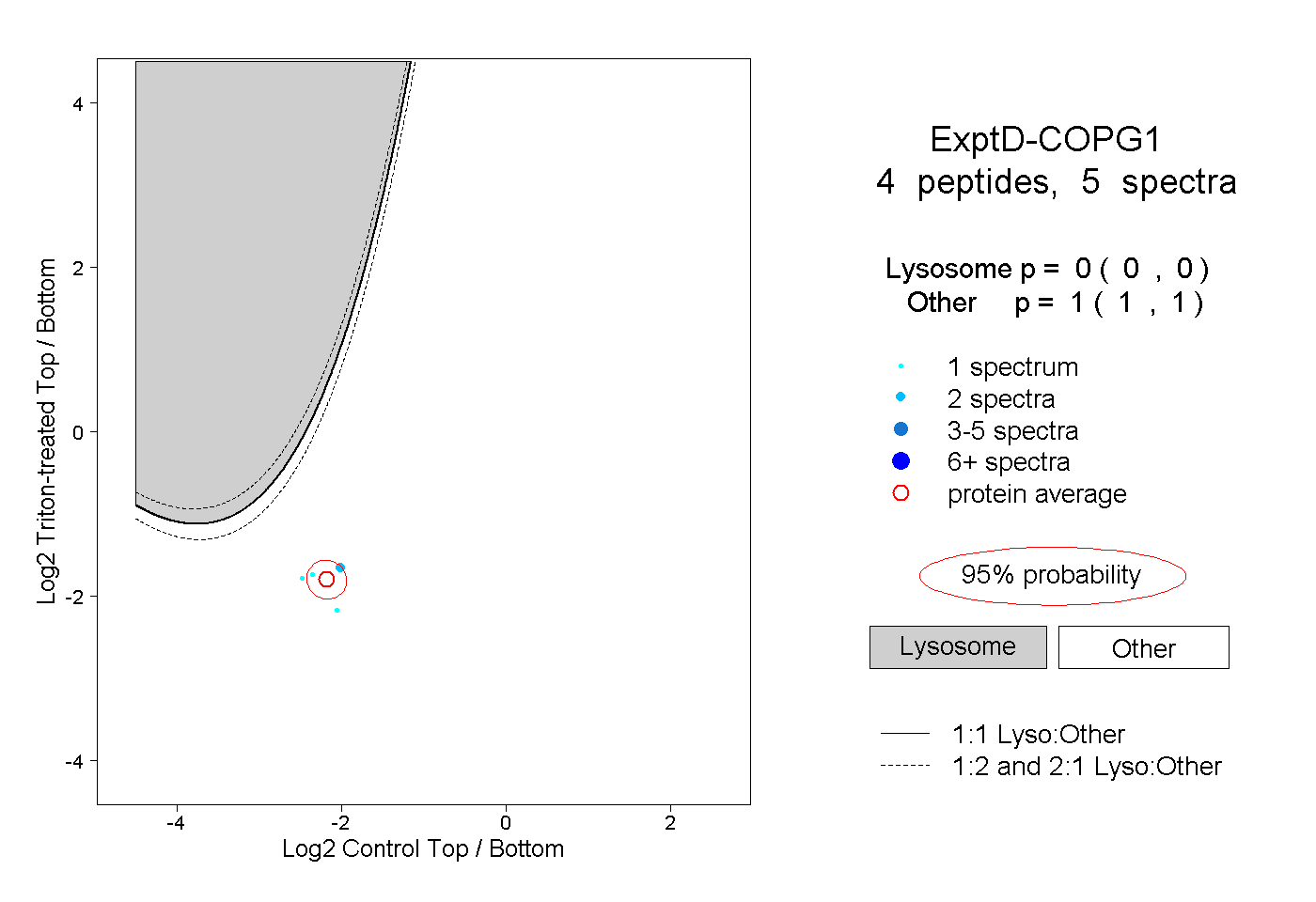 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |