peptides
spectra
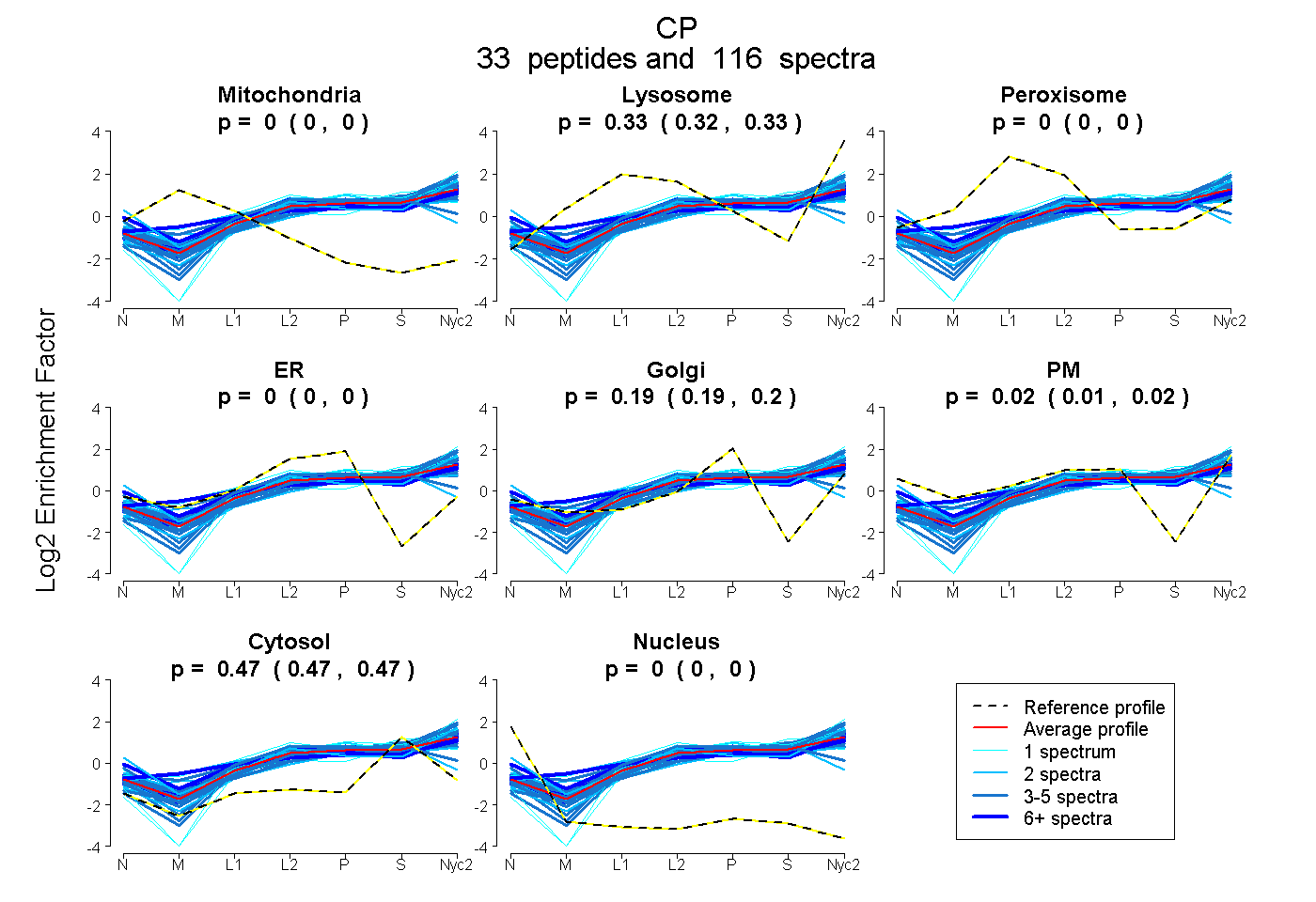
0.000 | 0.000
0.322 | 0.328
0.000 | 0.000
0.000 | 0.004
0.187 | 0.196
0.008 | 0.020
0.466 | 0.469
0.000 | 0.000
peptides
spectra

0.000 | 0.000
0.287 | 0.317
0.047 | 0.106
0.190 | 0.241
0.000 | 0.000
0.387 | 0.408
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
116 spectra |
 |
0.000 0.000 | 0.000 |
0.325 0.322 | 0.328 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.004 |
0.192 0.187 | 0.196 |
0.015 0.008 | 0.020 |
0.467 0.466 | 0.469 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.000 0.000 | 0.000 |
0.303 0.287 | 0.317 |
0.080 0.047 | 0.106 |
0.218 0.190 | 0.241 |
0.000 0.000 | 0.000 |
0.398 0.387 | 0.408 |
0.000 0.000 | 0.000 |
| 4 spectra, DIASGLIGPLILCK | 0.000 | 0.260 | 0.053 | 0.246 | 0.000 | 0.441 | 0.000 | |||
| 5 spectra, AGLQAFFQVR | 0.000 | 0.236 | 0.310 | 0.011 | 0.000 | 0.442 | 0.000 | |||
| 1 spectrum, QASHVAPK | 0.000 | 0.256 | 0.000 | 0.185 | 0.224 | 0.335 | 0.000 | |||
| 1 spectrum, EMGPTYADPVCLSK | 0.000 | 0.305 | 0.000 | 0.287 | 0.000 | 0.408 | 0.000 | |||
| 1 spectrum, EYTDDSFTNR | 0.000 | 0.159 | 0.322 | 0.000 | 0.000 | 0.519 | 0.000 | |||
| 3 spectra, IYHSHVDAPK | 0.048 | 0.338 | 0.000 | 0.245 | 0.000 | 0.369 | 0.000 | |||
| 3 spectra, EFTDSTFR | 0.000 | 0.105 | 0.380 | 0.000 | 0.000 | 0.515 | 0.000 | |||
| 5 spectra, VFFEQGATR | 0.000 | 0.169 | 0.329 | 0.000 | 0.000 | 0.501 | 0.000 | |||
| 2 spectra, ANEPSPGEGDSNCVTR | 0.000 | 0.377 | 0.000 | 0.000 | 0.365 | 0.258 | 0.000 | |||
| 2 spectra, GSLLADGR | 0.000 | 0.188 | 0.311 | 0.045 | 0.000 | 0.457 | 0.000 | |||
| 1 spectrum, ALYSEYTDGTFTK | 0.000 | 0.157 | 0.322 | 0.030 | 0.000 | 0.490 | 0.000 | |||
| 2 spectra, DTANLFPHK | 0.000 | 0.478 | 0.000 | 0.225 | 0.000 | 0.297 | 0.000 | |||
| 1 spectrum, TIDKPAWLGLLGPVIK | 0.000 | 0.479 | 0.000 | 0.211 | 0.008 | 0.302 | 0.000 | |||
| 2 spectra, ENEGTYYGPDGR | 0.000 | 0.111 | 0.369 | 0.000 | 0.000 | 0.520 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
263 spectra |
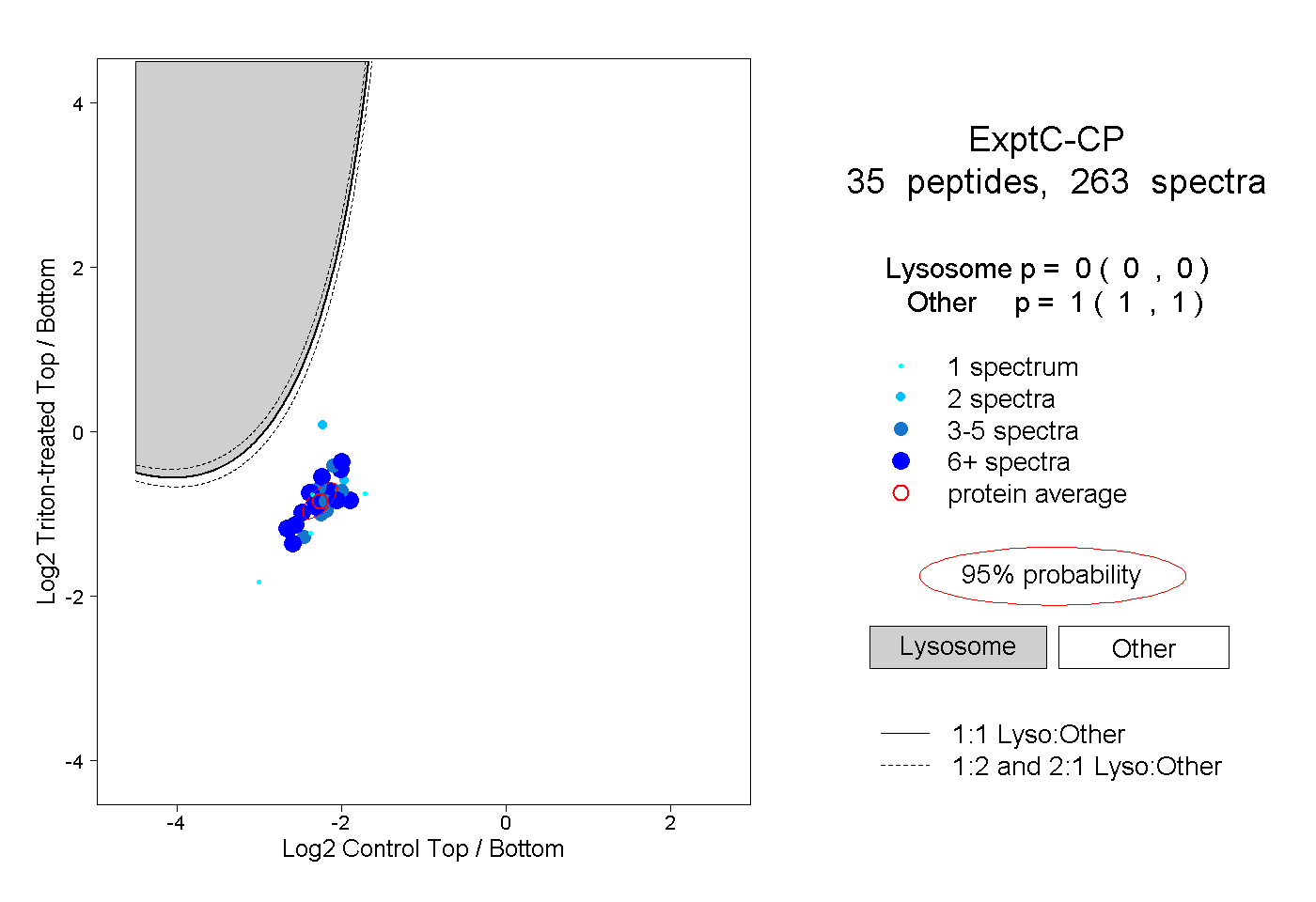 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
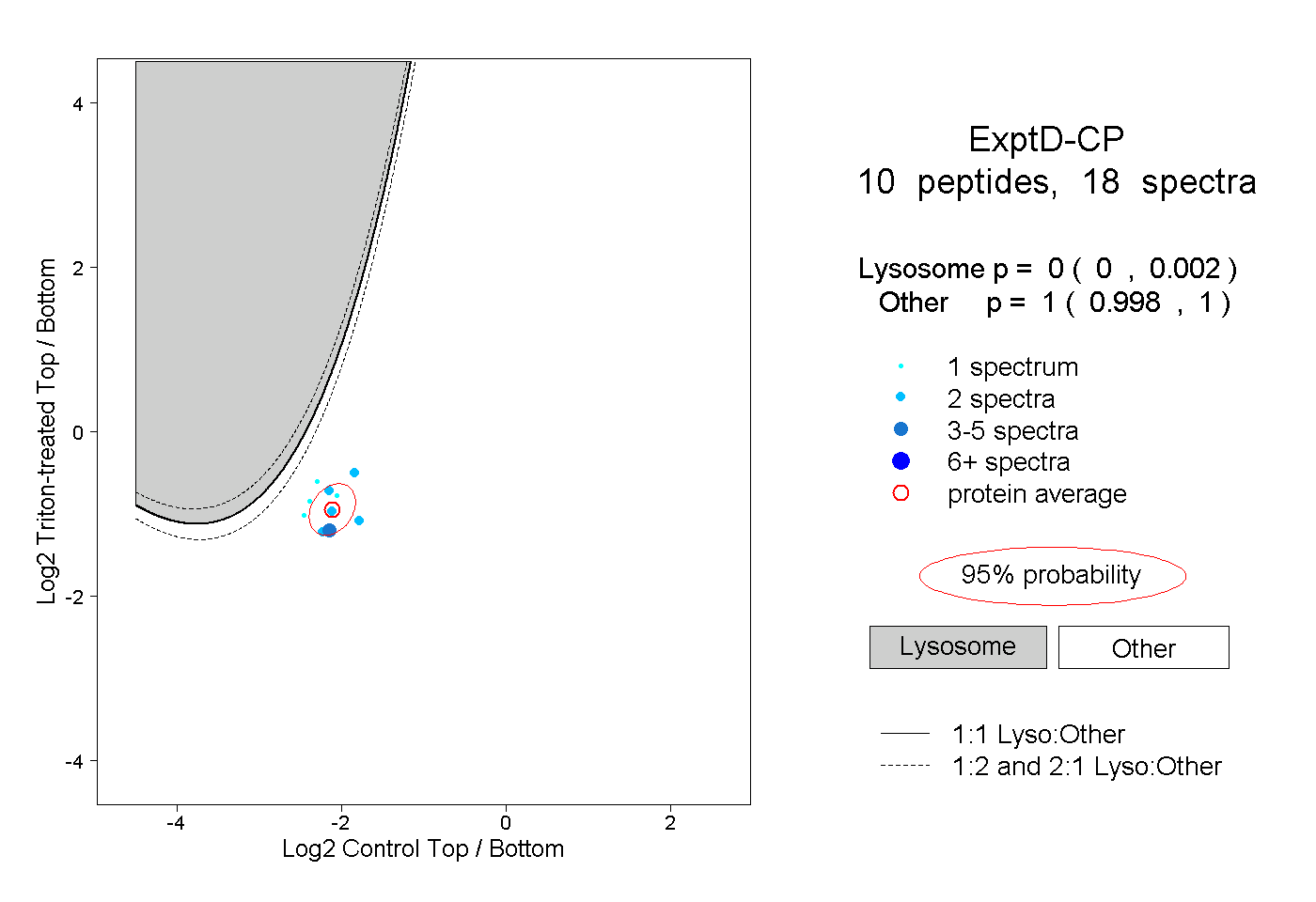 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |