peptides
spectra
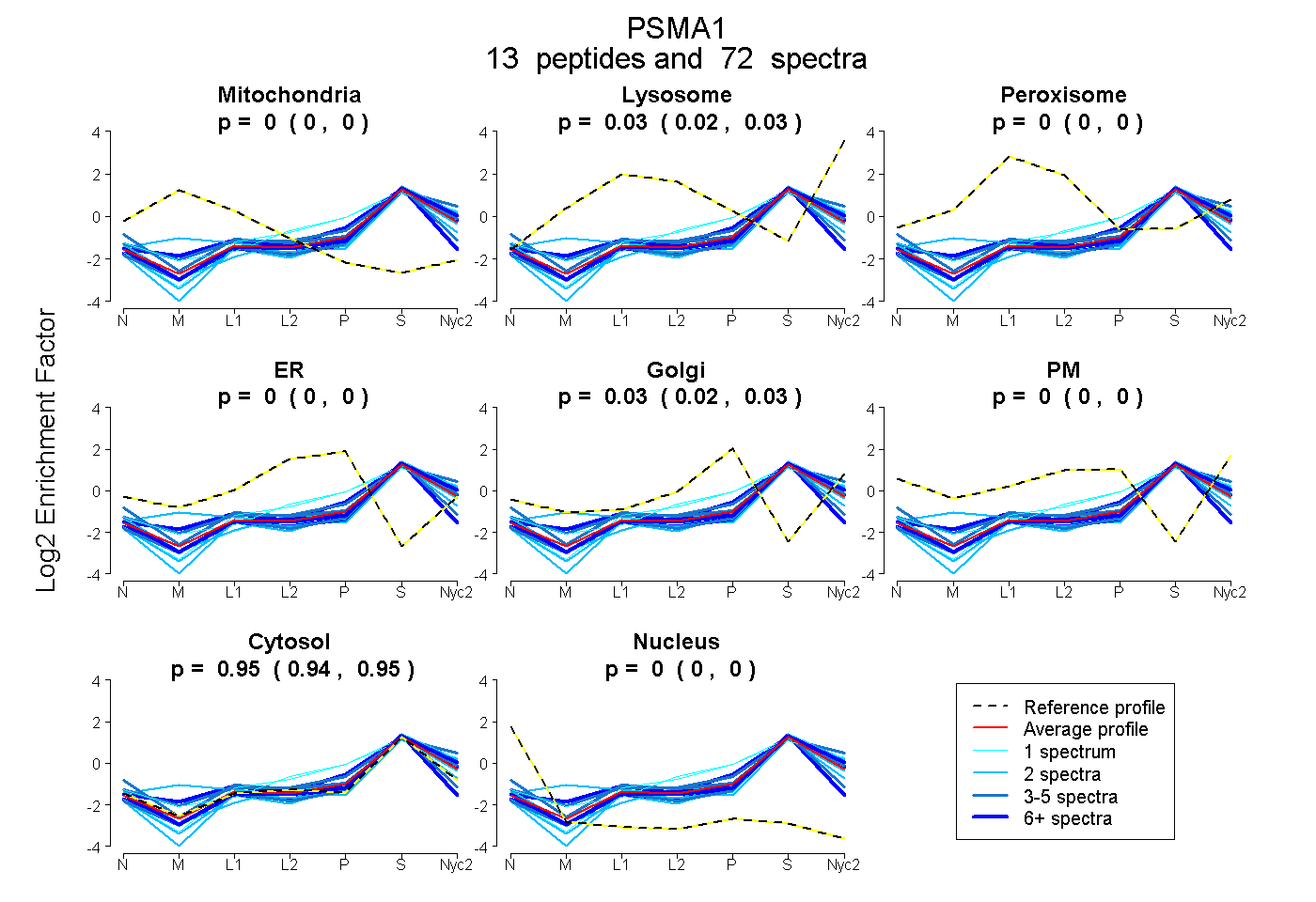
0.000 | 0.000
0.020 | 0.030
0.000 | 0.000
0.000 | 0.000
0.023 | 0.032
0.000 | 0.000
0.943 | 0.950
0.000 | 0.000
peptides
spectra
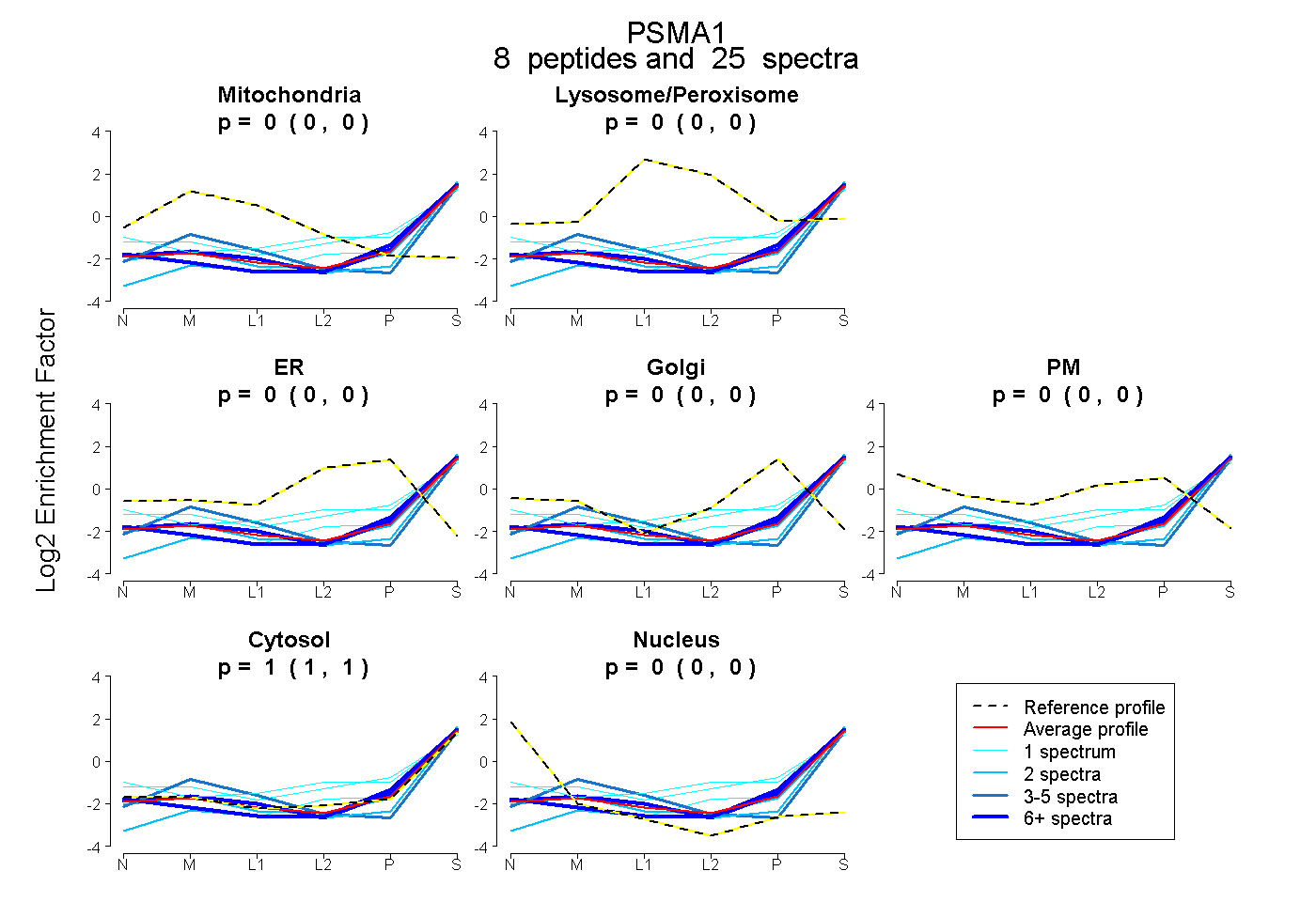
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
72 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.020 | 0.030 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.023 | 0.032 |
0.000 0.000 | 0.000 |
0.947 0.943 | 0.950 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, QGSATVGLK | 0.000 | 0.159 | 0.006 | 0.000 | 0.077 | 0.758 | 0.000 | |||
| 1 spectrum, ADEPMEH | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 9 spectra, FVFDRPLPVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, AQSELAAHQK | 0.000 | 0.114 | 0.000 | 0.146 | 0.000 | 0.740 | 0.000 | |||
| 2 spectra, THAVLVALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, LLCNFMR | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | 0.896 | 0.000 | |||
| 6 spectra, TQIPTQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, AMSIGAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
77 spectra |
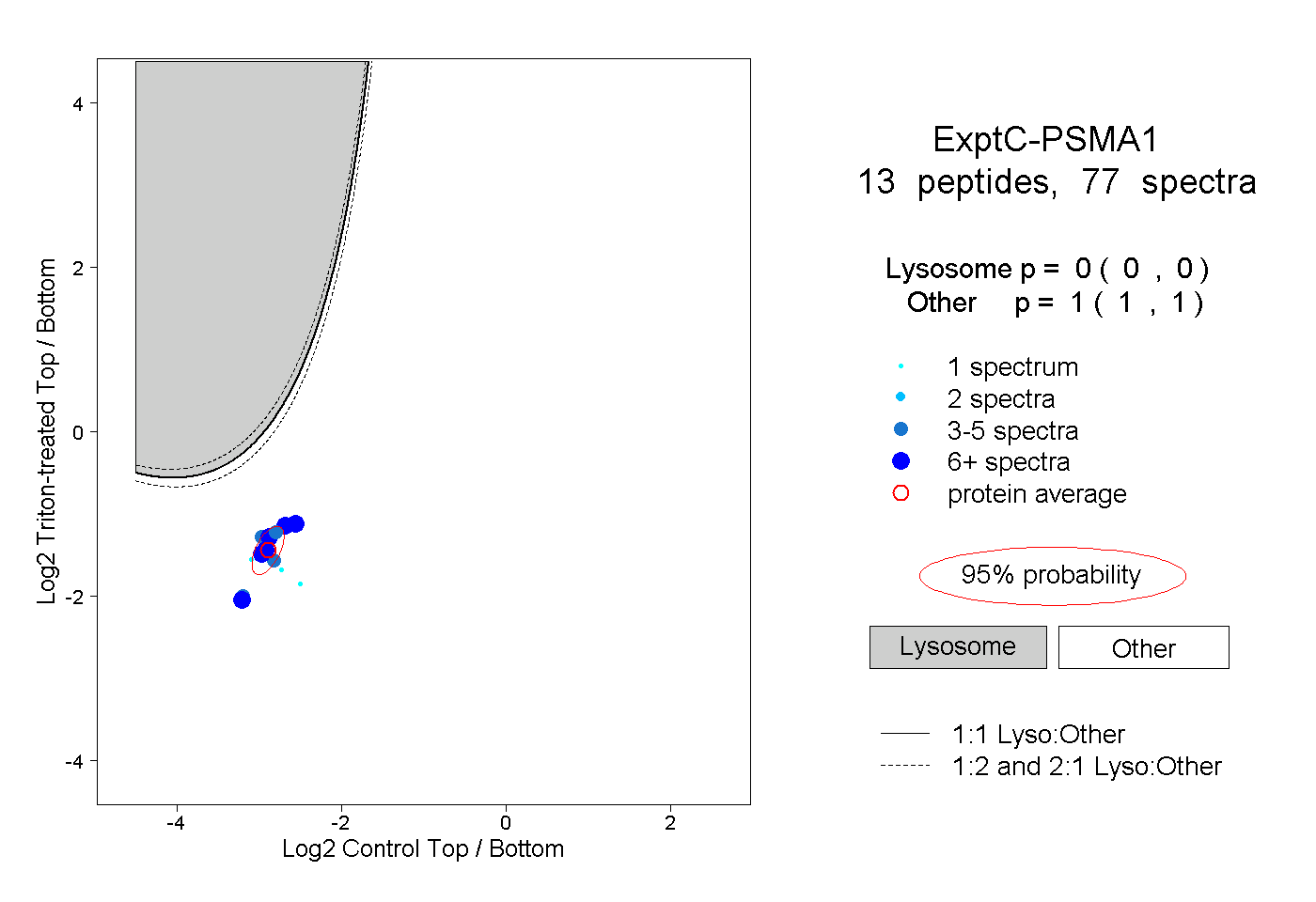 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
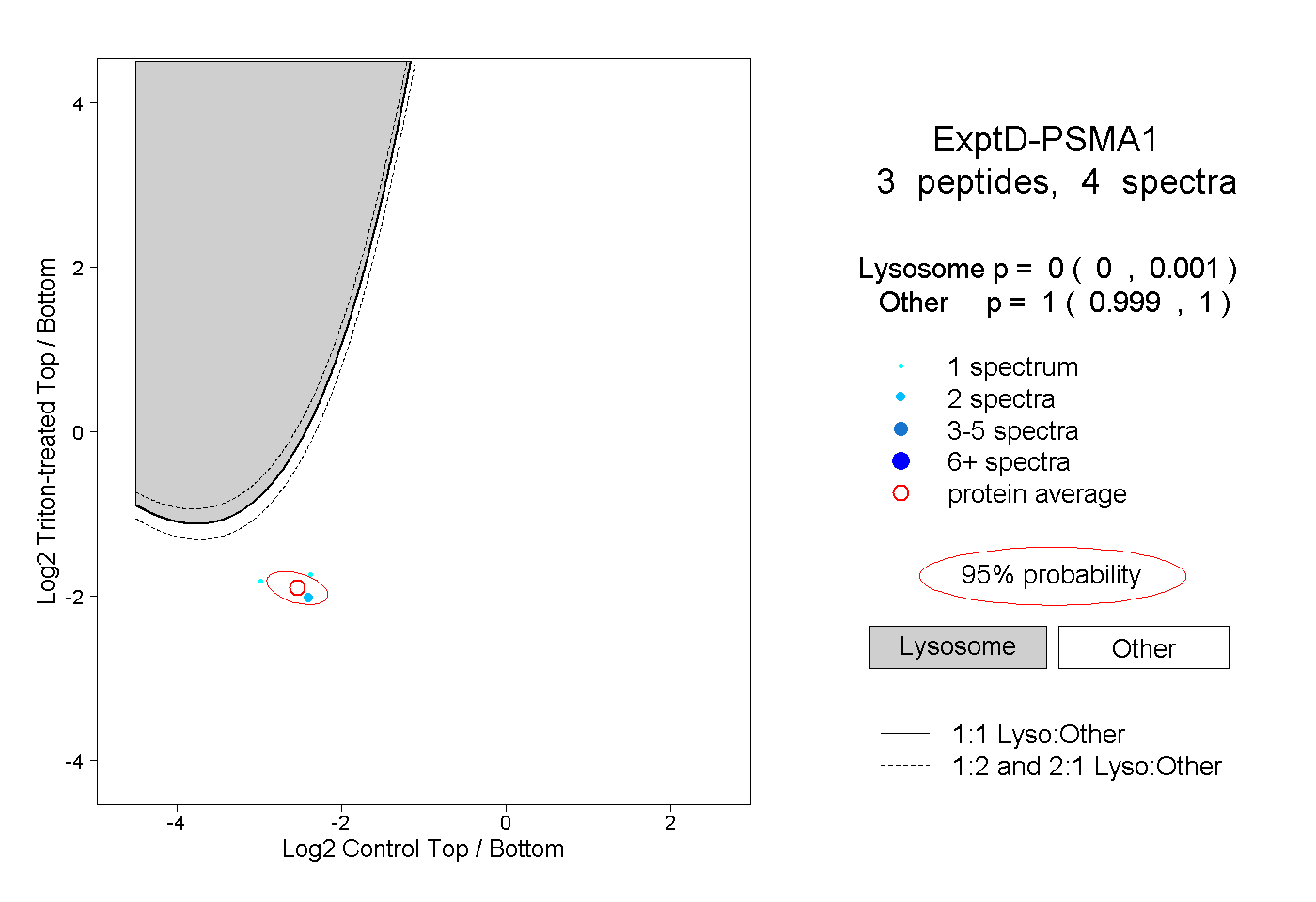 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |