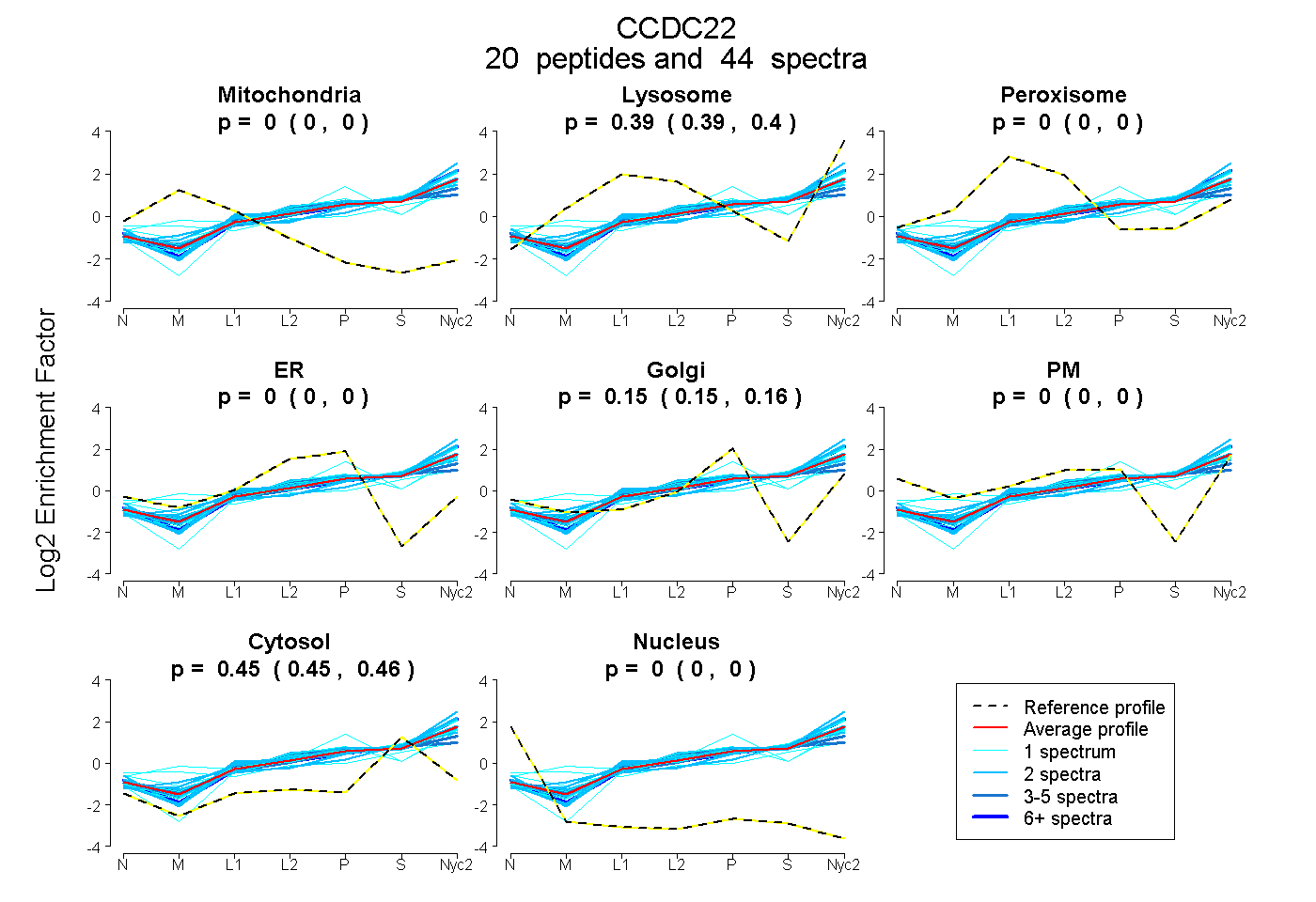
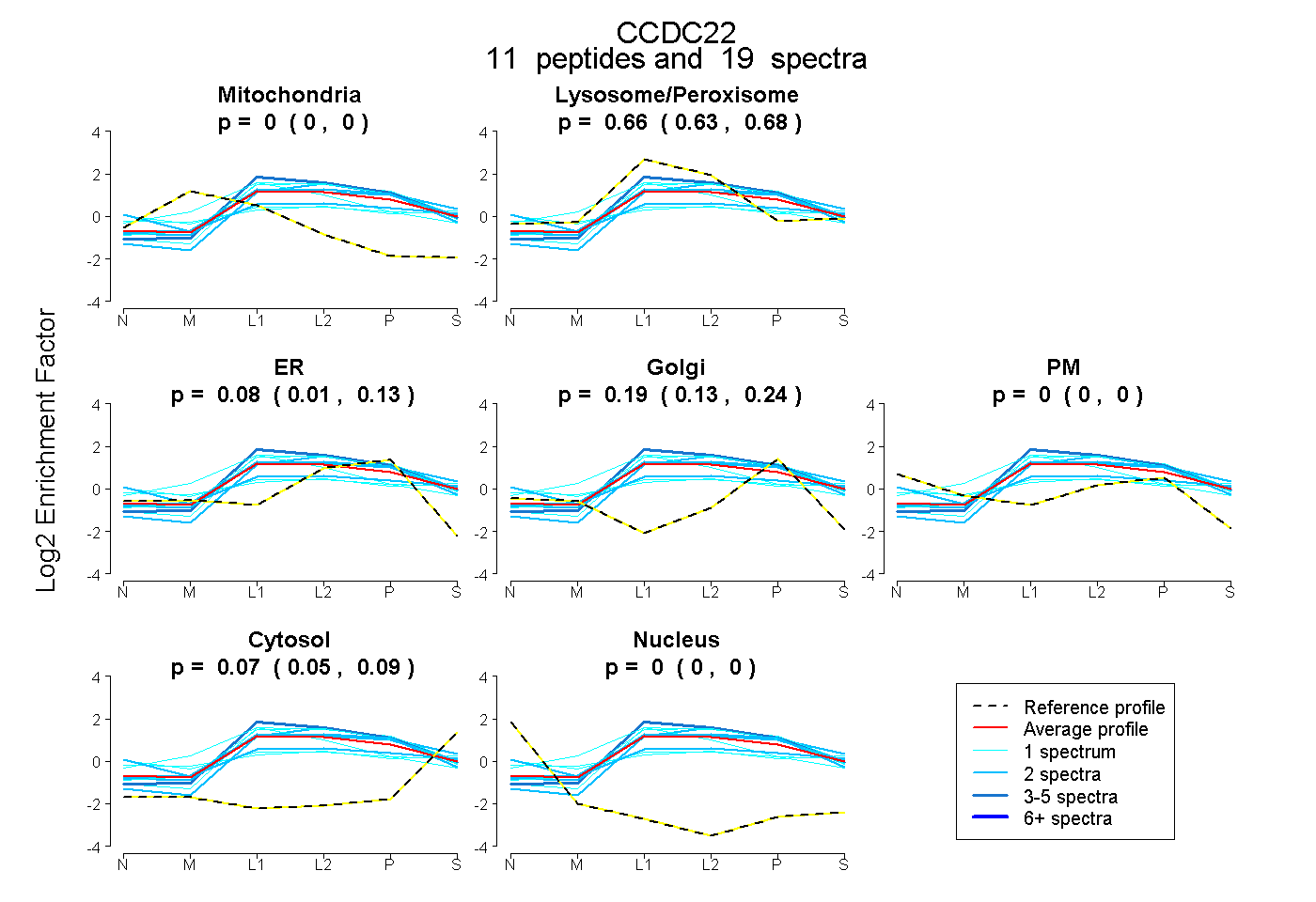
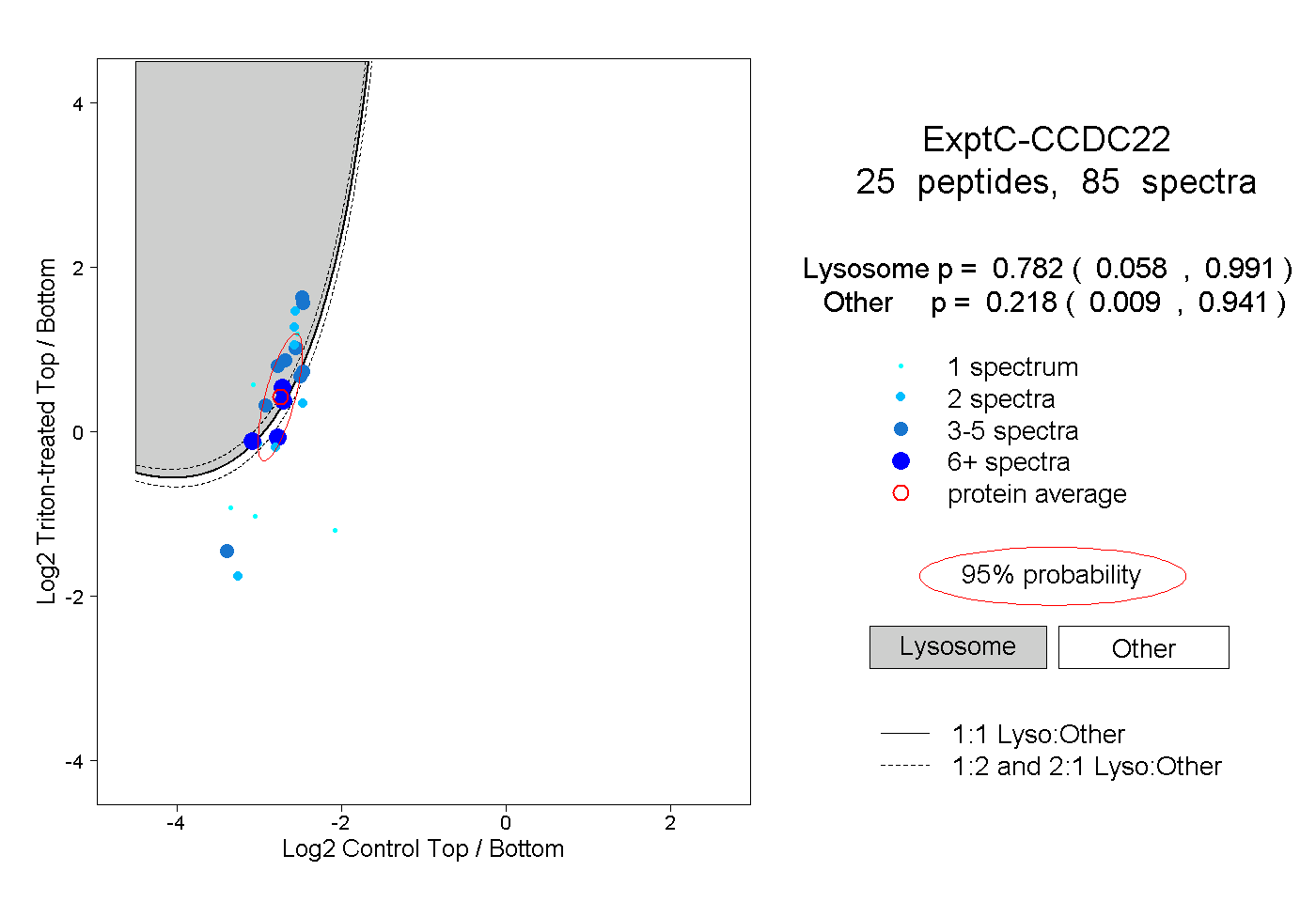
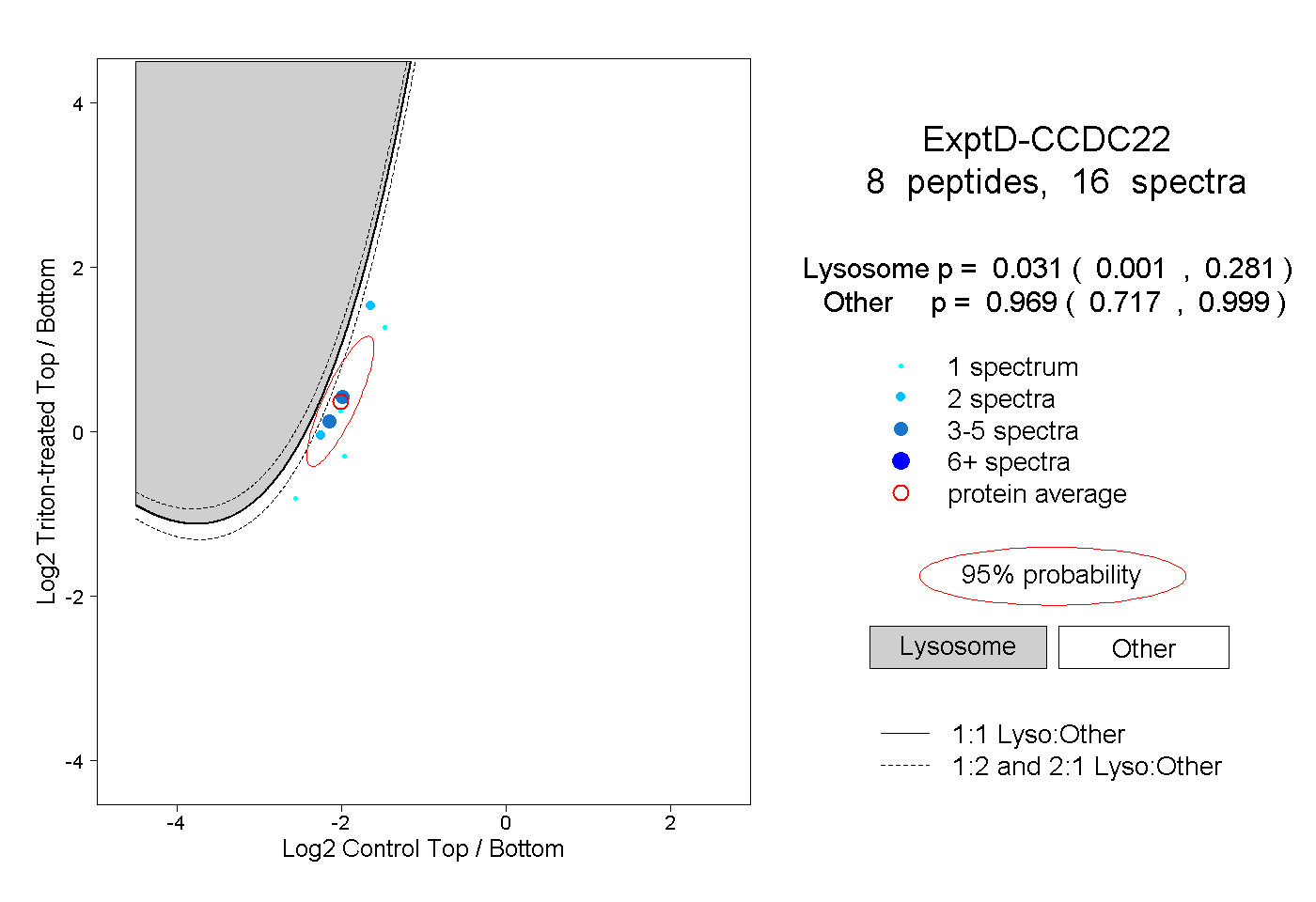
| 2 spectra, LVLPELNCR |
|
0.031 |
|
|
|
|
|
|
|
0.969 |
| 2 spectra, LQLVVESSAQR |
|
0.360 |
|
|
|
|
|
|
|
0.640 |
| 2 spectra, VINPDVGSGLSHLLPPAMSAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LPSQEDPR |
|
0.945 |
|
|
|
|
|
|
|
0.055 |
| 4 spectra, AAQEEELESLR |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 1 spectrum, DLGEMLQAWGAK |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 6 spectra, QLIEHLR |
|
0.609 |
|
|
|
|
|
|
|
0.391 |
| 1 spectrum, AFTTELVVEAVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QLVSELETLPK |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 6 spectra, LAYTQR |
|
0.076 |
|
|
|
|
|
|
|
0.924 |
| 2 spectra, ICEDYR |
|
0.996 |
|
|
|
|
|
|
|
0.004 |
| 4 spectra, EINSLSGK |
|
0.357 |
|
|
|
|
|
|
|
0.643 |
| 2 spectra, FTHSEK |
|
0.025 |
|
|
|
|
|
|
|
0.975 |
| 4 spectra, DQLALPWVPPLLR |
|
0.985 |
|
|
|
|
|
|
|
0.015 |
| 1 spectrum, SLGMNLVQVETECR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LIHLASQWEK |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 4 spectra, ILEIVGNIR |
|
0.993 |
|
|
|
|
|
|
|
0.007 |
| 8 spectra, ILIHSLR |
|
0.863 |
|
|
|
|
|
|
|
0.137 |
| 4 spectra, LVEIQELHQSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TLSNLEK |
|
0.960 |
|
|
|
|
|
|
|
0.040 |
| 1 spectrum, QAGTAVPPEVQTLR |
|
0.985 |
|
|
|
|
|
|
|
0.015 |
| 9 spectra, AMTGVPK |
|
0.607 |
|
|
|
|
|
|
|
0.393 |
| 2 spectra, VPLLAEYR |
|
0.975 |
|
|
|
|
|
|
|
0.025 |
| 4 spectra, QENAGLLGR |
|
0.393 |
|
|
|
|
|
|
|
0.607 |
| 5 spectra, DLLLFLAER |
|
0.997 |
|
|
|
|
|
|
|
0.003 |